Clear Sky Science · es
Análisis transcriptómicos de célula única y en masa revelan subtipos inmunitarios asociados con características de muerte celular programada en colangiocarcinoma intrahepático
Por qué importa este estudio sobre cáncer de hígado
El colangiocarcinoma intrahepático es un cáncer de crecimiento rápido que surge en los pequeños conductos biliares dentro del hígado y con frecuencia se detecta demasiado tarde para la cirugía. Los médicos saben que algunos pacientes viven mucho más tiempo o responden mejor a las nuevas inmunoterapias que otros, pero ha sido difícil predecir quién se beneficiará. Este estudio emplea perfiles genéticos avanzados y análisis de célula única para mostrar cómo interactúan distintas formas de muerte celular “programada” y el sistema inmune en estos tumores, y construye una puntuación práctica que podría ayudar a personalizar tratamientos y orientar decisiones clínicas.
Mirando dentro de los tumores hepáticos célula por célula
Los investigadores reunieron grandes conjuntos de datos de actividad génica procedentes de cientos de muestras tumorales, incluyendo tanto tejido a granel como células individuales, a partir de recursos públicos y una amplia cohorte clínica. Se centraron en 2.701 genes vinculados a 21 tipos de muerte celular programada —las vías internas por las que las células pueden autodestruirse cuando están dañadas o son anormales. Al comparar tejido tumoral con hígado circundante no canceroso, redujeron la lista a 87 genes que estaban desregulados en el cáncer y tenían potencial importancia para la supervivencia de los pacientes. Estos genes participaban en vías conocidas del cáncer y en formas de muerte celular como la apoptosis y la necroptosis, y también mostraron patrones característicos de mutaciones y alteraciones cromosómicas en tumores de los conductos biliares hepáticos. 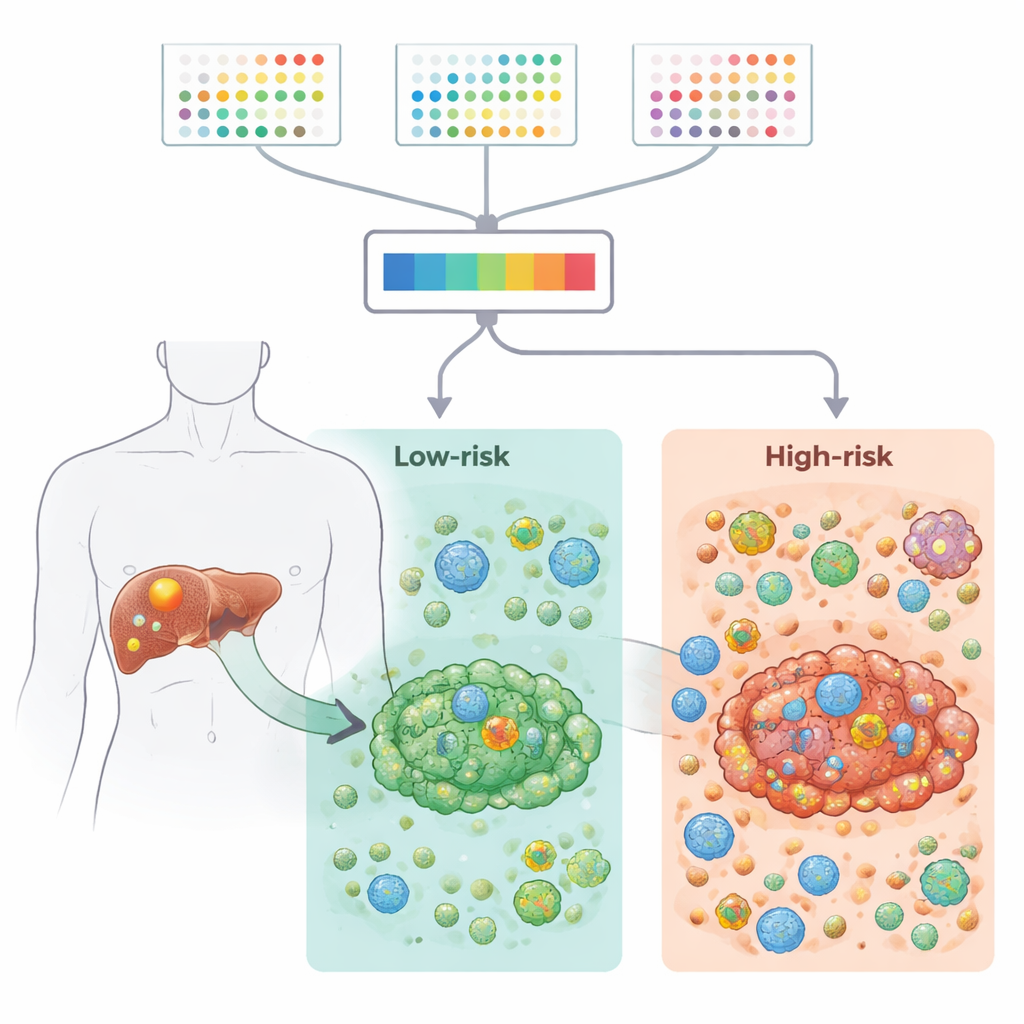
Construyendo una puntuación de riesgo a partir de nueve genes clave
Para convertir esta información compleja en algo clínicamente útil, el equipo probó 117 combinaciones de métodos de aprendizaje automático y modelos de supervivencia. El enfoque de mejor rendimiento, que combinó regresión de Cox por pasos con bosques aleatorios de supervivencia, destiló la información hasta nueve genes. Cada paciente recibió una puntuación de riesgo basada en la intensidad con la que estos genes estaban activados o silenciados en su tumor. En varios grupos independientes de pacientes, esta firma de nueve genes separó de forma fiable a las personas en grupos de alto y bajo riesgo con tiempos de supervivencia claramente distintos. Los tumores de alto riesgo se enriquecieron en vías relacionadas con estrés e inflamación, mientras que los tumores de bajo riesgo mostraron vías más activas de metabolismo y desintoxicación, lo que sugiere diferencias biológicas fundamentales entre ambos grupos.
Vecindarios inmunitarios dentro del tumor
El estudio se centró después en el microambiente tumoral —la mezcla de células inmunitarias, células de sostén y tejido conectivo que rodea e infiltra el cáncer. Usando múltiples herramientas computacionales, los autores mostraron que los tumores de alto riesgo tenían puntajes inmunes y estromales más elevados, señales inflamatorias más fuertes y más rasgos inmunosupresores, incluyendo un aumento de células T reguladoras que pueden atenuar las respuestas antitumorales. La secuenciación de ARN de célula única confirmó que estas células T reguladoras y los fibroblastos eran más abundantes en tumores de alto riesgo y participaban en redes densas de comunicación célula–célula. En contraste, los tumores de bajo riesgo tenían una señalización más fuerte relacionada con el colágeno y un entorno más equilibrado y menos supresor. En conjunto, estos hallazgos sugieren que el patrón de nueve genes está estrechamente ligado a cuán “amigable” o “hostil” es el vecindario inmune local respecto al tumor. 
Orientando la inmunoterapia y la elección de fármacos
Consciente de que la inmunoterapia está cobrando un papel central en el tratamiento del cáncer, el equipo creó una “puntuación PCD” separada a partir de los mismos nueve genes para predecir la respuesta al bloqueo de puntos de control inmunitarios. En tres cohortes independientes de pacientes tratadas con esos fármacos (procedentes de otros tipos de cáncer con datos disponibles), puntuaciones PCD más altas se asociaron de forma consistente con mejores respuestas, lo que implica que la puntuación captura rasgos del microambiente tumoral que hacen más probable el éxito de la inmunoterapia. El equipo también utilizó bases de datos de sensibilidad a fármacos y simulaciones de acoplamiento por ordenador para predecir qué medicamentos podrían ser más efectivos en diferentes grupos de riesgo. Los pacientes de alto riesgo parecían más sensibles a ciertos agentes dirigidos, incluidos los que interfieren con las vías TGF-beta y mTOR, ofreciendo posibles estrategias combinadas para superar la inmunosupresión.
De la biología compleja a herramientas prácticas
Para ayudar a trasladar estos hallazgos a la clínica, los autores construyeron un nomograma —un calculador visual de riesgo— que combina la puntuación de riesgo basada en genes con información clínica de rutina como el estadio y la invasión vascular. Esta herramienta predijo con precisión la supervivencia a uno, tres y cuatro años en su cohorte principal de pacientes. Aunque el trabajo aún requiere pruebas prospectivas en grupos más amplios y definidos por tratamiento de pacientes con colangiocarcinoma intrahepático, ofrece una hoja de ruta sobre cómo los patrones de genes relacionados con la muerte celular pueden usarse para clasificar tumores, entender sus ecosistemas inmunitarios y orientar la terapia. Para los pacientes, la promesa a largo plazo es obtener pronósticos más precisos y tratamientos mejor ajustados en función de la huella genética e inmune única de su tumor.
Cita: Zhang, T., Dou, D., Liu, Q. et al. Single-cell and bulk transcriptomic analyses uncover immune subtypes associated with programmed cell death features in intrahepatic cholangiocarcinoma. Sci Rep 16, 13678 (2026). https://doi.org/10.1038/s41598-026-44332-8
Palabras clave: colangiocarcinoma intrahepático, muerte celular programada, microambiente inmune tumoral, secuenciación de ARN de célula única, respuesta a inmunoterapia