Clear Sky Science · fr
Identification et vérification des gènes clés, CCR1 et EGR2, dans la lipophagie associée au diabète
Pourquoi les graisses et les sucres peuvent submerger nos cellules
Le diabète de type 2 est généralement présenté comme un problème de sucre, mais les graisses jouent un rôle tout aussi important et étroitement lié. Lorsque notre organisme est inondé d’un excédent calorique, des gouttelettes de graisse s’accumulent à l’intérieur d’organes comme le foie et les muscles. Les cellules saines peuvent « faire le ménage » en décomposant ces graisses stockées, mais dans le diabète ce système de nettoyage faiblit. L’étude résumée ici pose une question simple mais puissante : quels gènes se trouvent au carrefour entre la surcharge lipidique, le dysfonctionnement du nettoyage cellulaire et l’élévation de la glycémie — et pourraient-ils devenir de nouveaux signaux d’alerte ou cibles thérapeutiques ?
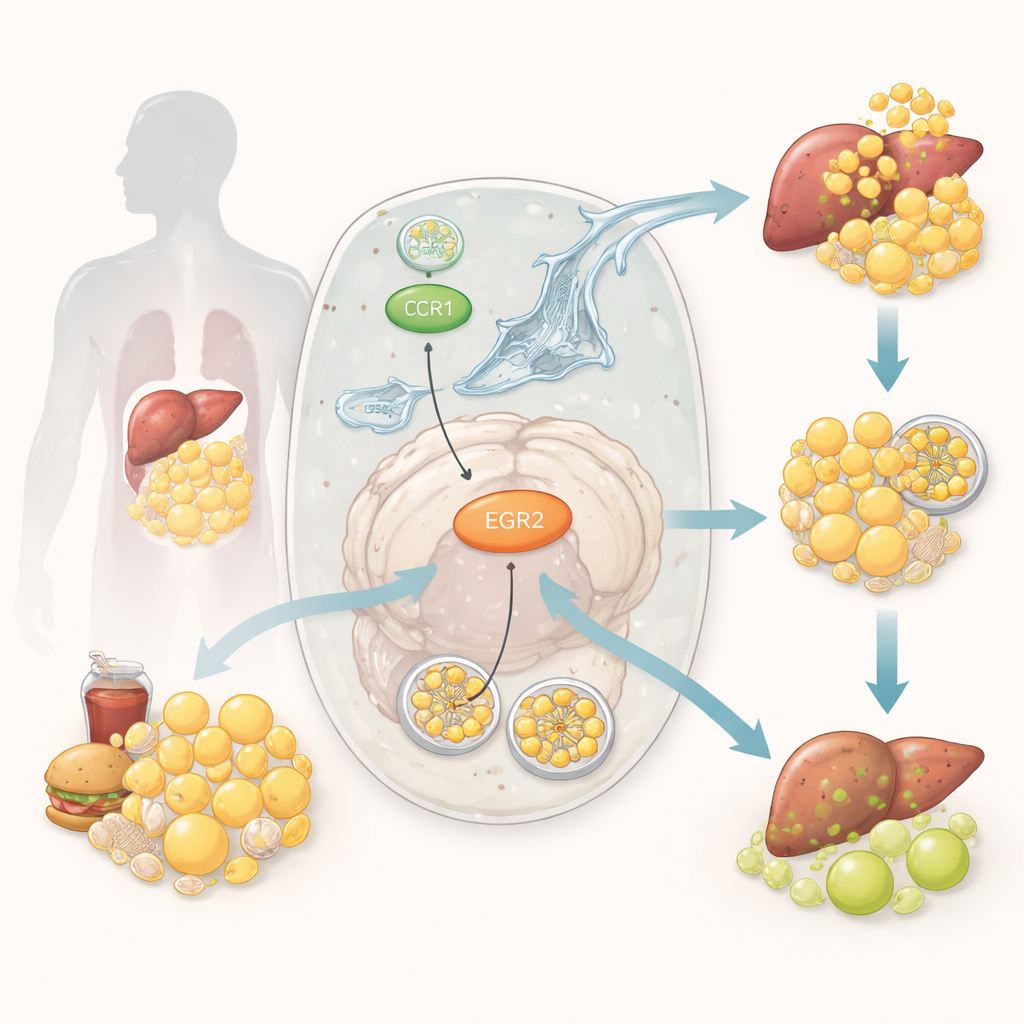
Une équipe de nettoyage cellulaire pour les graisses
À l’intérieur de nos cellules, une voie de recyclage spécialisée, appelée lipophagie, aide à regrouper et digérer les petites gouttelettes de graisse. Pensez-y comme à un camion poubelle cellulaire qui collecte l’excès de lipides et le transporte vers un centre d’élimination pour que les composants puissent être réutilisés en toute sécurité. Quand la lipophagie fonctionne bien, les réserves lipidiques restent équilibrées et les cellules répondent correctement à l’insuline. Lorsqu’elle est perturbée, les graisses s’accumulent dans des tissus tels que le foie et les muscles, alimentant l’inflammation et rendant le rôle de l’insuline plus difficile. Bien que les scientifiques sachent que la mauvaise gestion des lipides et le défaut de recyclage cellulaire participent au diabète, les interrupteurs moléculaires précis qui relient ces processus sont restés flous.
À la recherche des interrupteurs clés dans des données humaines
Les chercheurs ont commencé par exploiter de larges bases de données publiques d’activité génique issues du sang de personnes avec et sans diabète. À l’aide d’outils statistiques et d’analyses en réseau, ils ont d’abord réduit des milliers de gènes à un petit groupe dont l’activité changeait de façon cohérente dans le diabète et qui étaient déjà reliés au métabolisme lipidique ou au recyclage cellulaire. Ils ont ensuite appliqué plusieurs méthodes d’apprentissage automatique — des techniques permettant aux ordinateurs de détecter des motifs robustes dans des données complexes — pour identifier quels gènes distinguaient le mieux les échantillons diabétiques des non diabétiques. À travers ces approches indépendantes, deux gènes sont revenus en tête comme nœuds centraux : CCR1 et EGR2. Les deux étaient plus actifs dans les échantillons diabétiques, et leurs niveaux d’expression avaient tendance à varier de concert.
Confirmation des motifs dans le sang et dans le foie
Pour vérifier que ces motifs n’étaient pas de simples artefacts des jeux de données initiaux, l’équipe a testé de nouveaux échantillons sanguins provenant de personnes avec et sans diabète de type 2. À l’aide d’un test de laboratoire standard, ils ont constaté que les protéines CCR1 et EGR2 étaient effectivement plus élevées dans le sang des personnes diabétiques. Ensuite, ils se sont tournés vers un modèle murin bien établi de la maladie, qui développe obésité, foie gras et hyperglycémie. Chez ces animaux, le foie accumulait d’importants dépôts lipidiques, et les marqueurs de la voie de recyclage cellulaire montraient des signes de blocage. Dans ces mêmes foies, les niveaux de CCR1 et EGR2 étaient nettement augmentés, reflétant encore une fois les changements observés dans le sang humain. Ensemble, ces résultats suggèrent que ces deux gènes sont étroitement liés à la combinaison d’accumulation lipidique, de recyclage entravé et de mauvais contrôle glycémique.
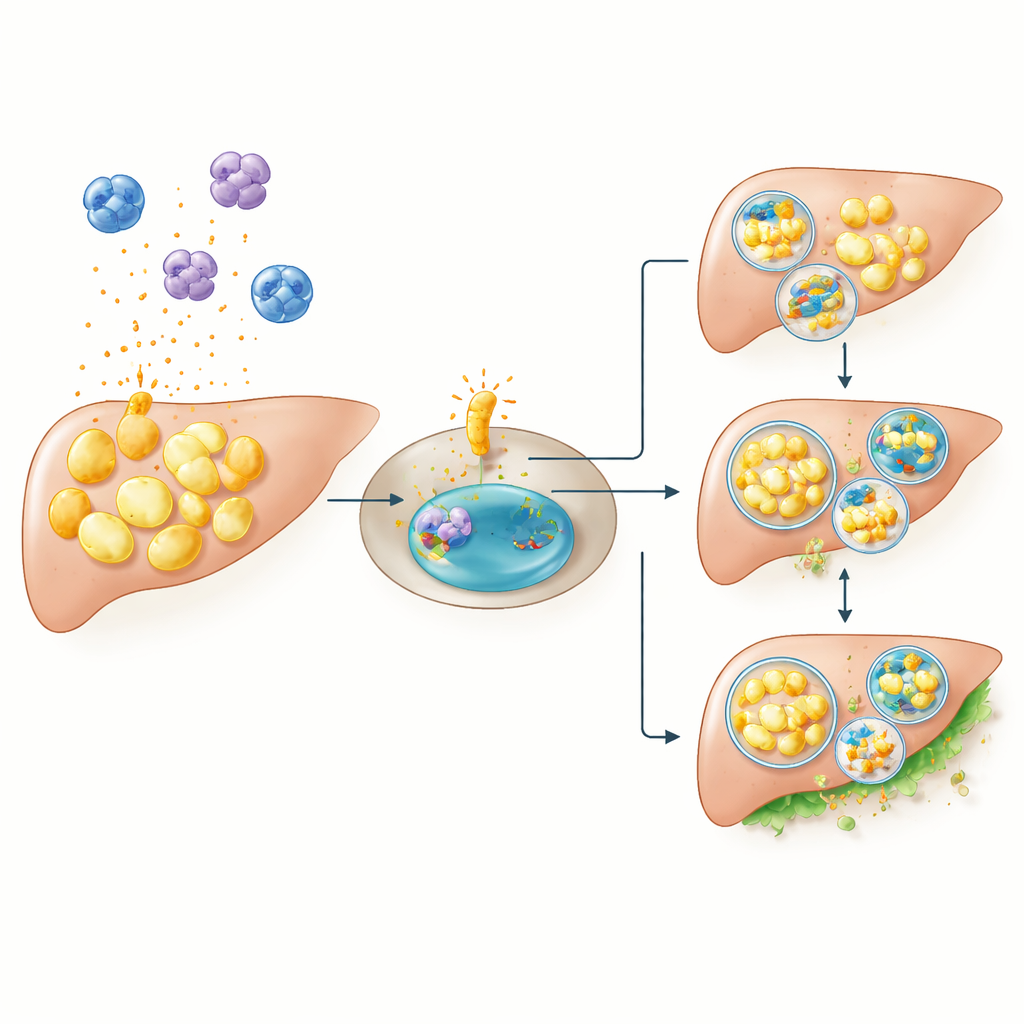
Explorer la causalité chez la souris
La corrélation seule ne peut prouver que ces gènes favorisent le diabète. Pour tester la causalité, les chercheurs ont généré des souris dépourvues de CCR1 et les ont exposées à un régime riche en graisses, un stress qui augmente normalement fortement la glycémie. Comme prévu, les souris ordinaires soumises au régime riche développaient une hyperglycémie à jeun et après les repas. En nette opposition, les souris dépourvues de CCR1 étaient en grande partie protégées : dans les mêmes conditions riches en lipides, leur glycémie restait proche de celle des animaux nourris normalement. Cela suggère que CCR1 n’est pas nécessaire pour maintenir l’équilibre glycémique au quotidien, mais devient un acteur critique lorsque l’organisme est mis au défi par un excès de graisses alimentaires, probablement en amplifiant l’inflammation et en perturbant l’élimination correcte des lipides au sein des cellules.
Ce que cela signifie pour les personnes vivant avec un diabète
En combinant l’analyse de grandes bases de données, des mesures sanguines humaines et des expériences ciblées chez la souris, cette étude met en lumière CCR1 et EGR2 comme de potentielles « manettes » moléculaires qui régulent la manière dont les cellules traitent les lipides pendant le diabète. Des niveaux plus élevés de ces gènes s’associent à un foie gras et inflammatoire et à des signes indiquant que le système de lipophagie est encombré. Fait important, la suppression de CCR1 chez la souris atténue l’élévation de la glycémie normalement déclenchée par un régime riche en graisses, ce qui suggère une nouvelle stratégie thérapeutique possible. Bien qu’il reste beaucoup à faire pour préciser comment CCR1 et EGR2 contrôlent le recyclage lipidique dans différents tissus, ils apparaissent désormais comme des biomarqueurs prometteurs pour détecter le diabète plus tôt et comme points de départ pour des médicaments visant à restaurer la capacité cellulaire de nettoyer l’excès de graisses.
Citation: Liu, J., Zhang, X., Wang, Y. et al. Identification and verification of the key genes, CCR1 and EGR2, in diabetes-associated lipophagy. Sci Rep 16, 14274 (2026). https://doi.org/10.1038/s41598-026-43737-9
Mots-clés: diabète de type 2, lipophagie, foie gras, inflammation, biomarqueurs