Clear Sky Science · es
Destilar la experiencia específica de poblaciones en un modelo unificado para la segmentación generalizable de tumores cerebrales
Por qué importa un único modelo para todos
Los tumores cerebrales no se parecen igual de una persona a otra. Niños, adultos, pacientes de distintos países y personas con distintos tipos de tumor pueden presentar patrones muy diversos en las exploraciones por RM. Sin embargo, los médicos y hospitales preferirían una única herramienta informática fiable que pueda delinear tumores automáticamente para cualquier paciente, en lugar de manejar muchos modelos separados. Este estudio presenta una nueva forma de entrenar dicho sistema unificado para que funcione bien en cinco tipos muy distintos de tumores cerebrales, lo que podría aportar una atención más consistente a pacientes de todo el mundo.
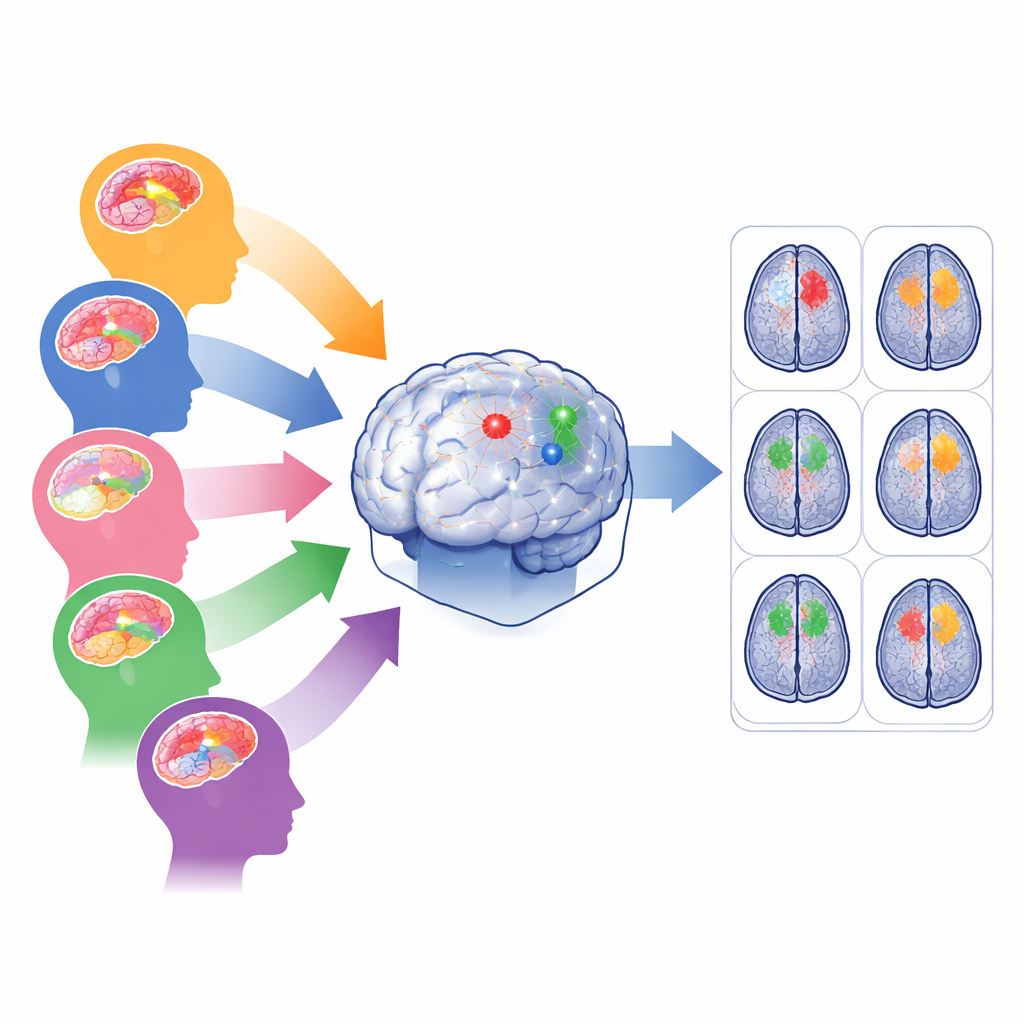
El reto de la multitud de tipos de tumores cerebrales
Las herramientas modernas de inteligencia artificial pueden trazar tumores cerebrales en exploraciones por RM con una precisión impresionante, pero por lo general solo cuando los datos se parecen a los que se usaron para entrenarlas. En hospitales reales, las exploraciones proceden de máquinas y protocolos distintos, y los tumores varían en tamaño, forma y localización. Los gliomas en adultos a menudo se hallan en profundidad dentro del cerebro; los gliomas en África subsahariana se capturan con escáneres de menor calidad; los gliomas pediátricos reorganizan regiones internas del tumor; los meningiomas se ubican en la superficie cerebral; y las metástasis pueden aparecer como numerosos puntos dispersos. Entrenar un solo modelo con todos estos casos tiende a favorecer al grupo más común y a descuidar poblaciones raras o ruidosas, lo que arriesga un rendimiento pobre precisamente donde más se necesita ayuda.
Por qué las soluciones previas se quedaron cortas
Los investigadores han intentado varias soluciones. Una opción es ajustar (fine-tune) un modelo para cada nuevo conjunto de datos u hospital, pero esto exige mantener muchas versiones y puede hacer que el sistema "olvide" conocimientos anteriores. Otra estrategia es usar ensamblajes, donde varios modelos especializados votan la respuesta final; aunque suelen ser precisos, son lentos y costosos en cómputo. El aprendizaje por currículum, que alimenta datos en un orden cuidadosamente elegido de casos más fáciles a más difíciles, puede ayudar, pero es complicado de diseñar y aún puede no captar todas las variedades tumorales. Los modelos base (foundation models) como “segment anything” prometen segmentación de propósito general, pero por lo general necesitan indicaciones humanas y no son totalmente automáticos, lo que limita su utilidad en flujos de trabajo clínicos rutinarios.
Combinar muchos expertos en un solo estudiante
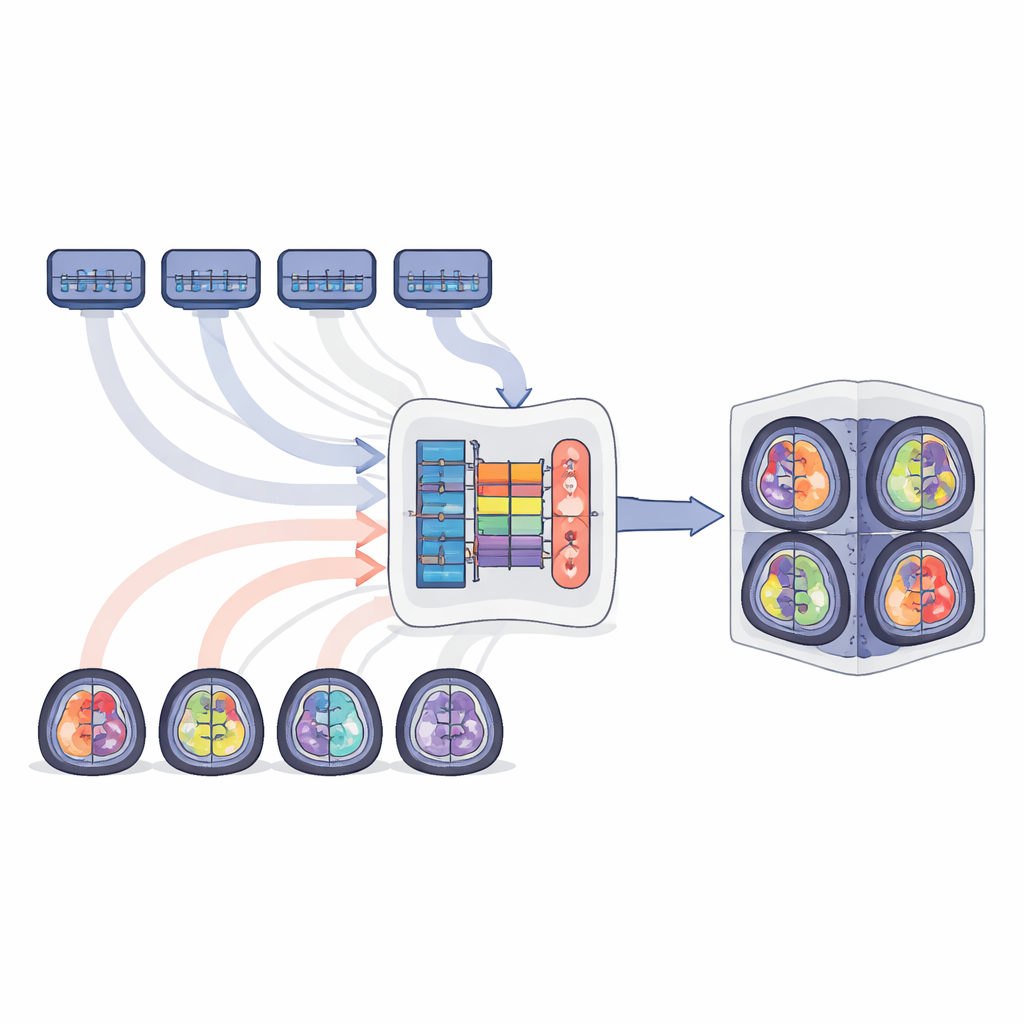
Los autores proponen MTSS-KDNet, un enfoque de "varios profesores, un solo estudiante" inspirado en cómo un médico en formación podría aprender de varios especialistas. Primero, se entrenan por separado cinco modelos expertos, cada uno centrado en una población tumoral: gliomas en adultos, gliomas en África subsahariana, gliomas pediátricos, meningiomas y metástasis. Estas redes docentes se afinan mucho en las características de su propio grupo. Luego se entrena a un único modelo estudiante para imitarlas, pero de una manera inteligente y consciente de las poblaciones. Para cada exploración de entrenamiento, el profesor correspondiente y el estudiante procesan la imagen en paralelo. Se impulsa al estudiante a igualar los patrones internos y las predicciones finales del profesor, al tiempo que se corrige con los contornos tumorales reales. Un esquema de muestreo orientado a la equidad asegura que cada lote de entrenamiento incluya siempre un caso de cada población, de modo que los grupos raros se vean con la misma frecuencia que los comunes.
Cómo funciona el modelo unificado en la práctica
Tras el entrenamiento, solo se usa el modelo estudiante para nuevos pacientes, manteniendo el despliegue simple y rápido. Los investigadores lo evaluaron en las cinco poblaciones tumorales utilizando medidas estándar de cuán estrechamente los volúmenes y bordes tumorales predichos coinciden con las etiquetas de expertos. En tumor completo, núcleo tumoral y regiones activas, el modelo unificado obtuvo puntuaciones sólidas que igualaron o superaron no solo a sus profesores individuales sino también a bases potentes como modelos ajustados, aprendizaje por currículum y ensamblajes de múltiples modelos. Las mejoras fueron especialmente llamativas en escenarios difíciles, como tumores pediátricos, exploraciones de baja calidad de África subsahariana y metástasis cerebrales dispersas, donde el estudiante superó claramente a los expertos específicos de población. Las inspecciones visuales mostraron contornos más limpios y completos, y los mapas de características internos revelaron que el modelo aprendió a separar las poblaciones en su representación interna sin necesitar etiquetas en el momento de la prueba.
Qué significa esto para la atención futura al paciente
Para un no especialista, la idea clave es que los autores han encontrado una forma de verter el saber hacer de muchos sistemas expertos estrechos en un único modelo general, sin perder lo que hace a cada experto bueno en su tarea. Su marco MTSS-KDNet conserva las ventajas prácticas de una herramienta única y automática a la vez que mantiene el rendimiento a través de pacientes, escáneres y tipos de tumor diversos. Aunque todavía exige recursos de entrenamiento sustanciales y depende de buenos modelos docentes iniciales, este enfoque apunta hacia sistemas de segmentación “fundacionales” que pueden servir a poblaciones globales con mayor equidad. A largo plazo, modelos unificados como este podrían ayudar a garantizar que pacientes con tumores raros, niños o personas en regiones con pocos recursos se beneficien del mismo nivel de precisión en imagen que aquellos en grandes centros médicos.
Cita: Elzayat, A., Hanafy, N., Magdy, M. et al. Distilling population specific expertise into a unified model for generalizable brain tumor segmentation. Sci Rep 16, 12969 (2026). https://doi.org/10.1038/s41598-026-35627-x
Palabras clave: segmentación de tumores cerebrales, IA en imagen médica, destilación de conocimiento, generalización de modelos, RM