Clear Sky Science · zh
理解支配蛋白质与DNA之间π–π非共价相互作用的底层语言代码
蛋白质如何在不永久接触的情况下读取DNA
在我们细胞中,每一秒都有无数蛋白质需要在DNA这本“说明书”中找到并读取特定的词语。它们通过瞬时的分子吸引力完成这一任务,而不与DNA发生永久性结合或切割。本文探讨了这些微妙作用力中最重要的一类:蛋白质与DNA碱基之间平面环状片段的特殊堆积相互作用。作者提出,这些接触表现得像一种简单且可重复的代码,帮助蛋白质识别DNA序列,并用量子物理学的概念来解释这套代码。
平面环的低调磁性
DNA碱基和蛋白质中的若干氨基酸都包含电子在整个环上离域的平面环结构。当两个这样的环正对并略微错位排列时,它们可以通过化学家所称的π–π(pi–pi)相互作用相互吸引。早期研究表明,这类接触强度可近似氢键,并且在蛋白质–DNA 界面中很常见。在本研究中,作者聚焦于芳香族氨基酸(如苯丙氨酸、酪氨酸和色氨酸)中的苯环样结构,以及它们如何与四种DNA碱基的环进行堆叠。他们认为,这些堆叠不仅仅把分子粘在一起:它们形成了一种有结构、具方向性的相互作用,可以传递关于碱基身份的信息。
对多种不同DNA“字母”的统一抓握
通过考察这些堆叠的几何构型,作者发现了一个反复出现的模式。对于较大的碱基(腺嘌呤和鸟嘌呤,称为嘌呤),最稳定的构型使蛋白质的苯环与碱基平行排列,使碱基上的两个特定位点(称为N3和C2)位于苯环的两个特定碳原子(C1和C2)之下。对于较小的碱基(胸腺嘧啶和胞嘧啶,称为嘧啶),相同的苯环原子则对齐于碱基上的两个碳原子C5和C6。无一例外,这些环都采用平行但水平偏移的排列,类似于两枚略微错位重叠的硬币。这种反复出现的对齐暗示了一种结构性的“字母表”:苯环保持不变,而每种碱基向这一固定框架呈现不同的富电子点模式。
像微小弹簧般振荡的电子对
为了描述这些堆叠内部发生的事,作者采用了一个模型:电子成对相关运动,在两个环之间振荡。它们并不形成新的化学键,而是一个电子暂时从一个环的占据区跳到另一个环的空位(“空穴”),随后再返回。这种成对的运动被视为共振的量子态,有点像用弹簧连接的两个质量块同步振动。在模型中,只有两个关键成分重要:电子之间的排斥和它们与分子振动的耦合。当苯环以恰当的位移放置于特定碱基上方时,这些成分结合在一起,产生一种稳定的成对振动模式,将两个环联系起来而不破坏它们原有的结构。
从量子运动到可测量的力
由于这些电子对以规律的振荡方式运动,作者可以使用来自量子力学的工具——赫尔曼–范费尔米(Hellmann–Feynman)定理——估算保持环相互吸引的力。该定理将能量变化与粒子间的力联系起来,类似于拉伸弹簧蓄能并产生恢复力。在π–π堆叠中,相关电子对的能量取决于环之间的距离以及电子在振荡时“摆动”的幅度。对该能量关于距离求导即可得到一种有效力,使环维持在偏好的位置和间距——这股力足以稳定蛋白质–DNA 复合体,但又足够弱以便在复合体需要解离时能够可逆地分开。
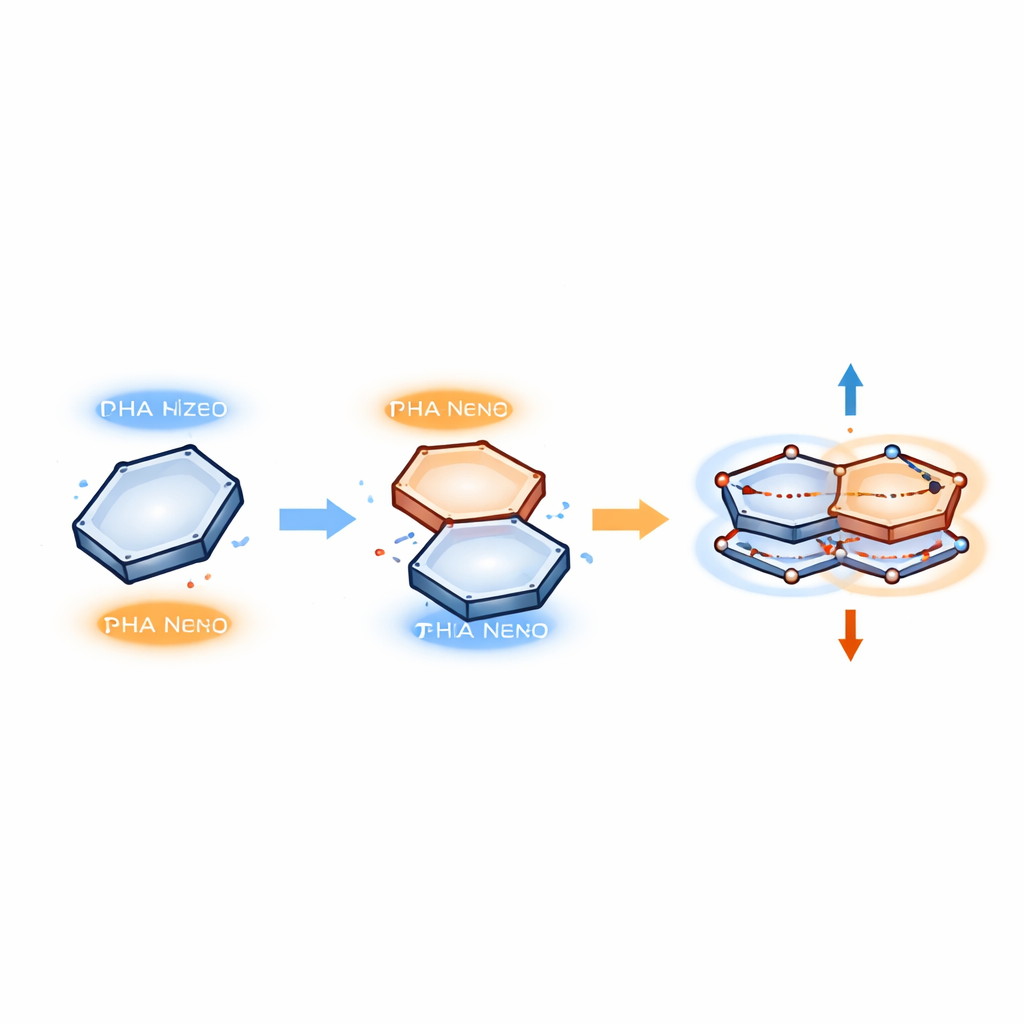
用于灵活DNA识别的简单代码
综上所述,这项工作表明蛋白质利用了一种稳健且可重复使用的设计:芳香族氨基酸中恒定的苯环与提供不同电子景观的可变DNA碱基配合。苯环提供了形成这些振荡电子对所需的稳定框架,而碱基则决定了这些电子对形成的位置和强度。这为蛋白质提供了一种非永久但特异的“触觉”方式来感知它们接触的碱基,帮助它们在浩瀚基因组中识别目标序列。通俗来说,π–π相互作用让蛋白质将一个标准形状的读头按到不同的DNA“字母”上,并通过这种微妙的、量子尺度的接触辨别其身份。
引用: Riera Aroche, R., Ortiz García, Y.M., Riera Leal, L. et al. Understanding the underlying language code that governs the π–π non-covalent interactions between proteins and DNA. Sci Rep 16, 14361 (2026). https://doi.org/10.1038/s41598-026-44532-2
关键词: 蛋白质–DNA 相互作用, 芳香族氨基酸, π–π 堆积, DNA 识别, 量子生物学