Clear Sky Science · it
Comprendere il codice sottostante che governa le interazioni non covalenti π–π tra proteine e DNA
Come le proteine leggono il DNA senza legarsene in modo permanente
Ogni secondo, innumerevoli proteine nelle nostre cellule devono trovare e leggere parole specifiche nel «libro delle istruzioni» che è il DNA. Lo fanno senza legarsi o tagliare permanentemente il DNA, sfruttando attrazioni fugaci tra le molecole. Questo articolo esplora una delle più importanti di queste forze sottili: un tipo speciale di interazione di impilamento tra parti piatte e ad anello delle proteine e le basi del DNA. Gli autori sostengono che questi contatti si comportano come un codice semplice e ripetibile che aiuta le proteine a riconoscere sequenze di DNA, e spiegano quel codice usando concetti presi dalla fisica quantistica.
Il magnetismo silenzioso degli anelli piatti
Sia le basi del DNA sia diversi amminoacidi nelle proteine contengono strutture piatte ad anello i cui elettroni sono delocalizzati sull’intero anello. Quando due di questi anelli si allineano faccia a faccia leggermente sfalsati, possono attrarsi tramite quelle che i chimici chiamano interazioni π–π (pi–pi). Lavori precedenti hanno mostrato che questi contatti possono essere quasi forti quanto i legami a idrogeno e sono comuni alle interfacce proteina–DNA. In questo studio, gli autori si concentrano sugli anelli simili al benzene presenti negli amminoacidi aromatici come fenilalanina, tirosina e triptofano, e su come essi si impilano contro gli anelli delle quattro basi del DNA. Sostengono che questi impilamenti fanno più che semplicemente incollare le molecole: formano un’interazione strutturata e direzionale che può trasmettere informazioni su quale base è presente.
Una presa coerente su molte lettere diverse del DNA
Esaminando la geometria di questi impilamenti, gli autori individuano un motivo ricorrente. Per le basi più grandi del DNA (adenina e guanina, dette purine), la configurazione più stabile pone l’anello benzene della proteina parallelo alla base in modo che due posizioni specifiche della base (chiamate N3 e C2) si trovino sopra due carboni specifici (C1 e C2) del benzene. Per le basi più piccole (timina e citosina, dette pirimidine), gli stessi atomi del benzene si allineano invece sopra due carboni chiamati C5 e C6 nella base. In ogni caso, gli anelli adottano un arrangiamento parallelo ma traslato orizzontalmente, simile a due monete sovrapposte leggermente spostate l’una rispetto all’altra. Questo allineamento ripetuto suggerisce una sorta di «alfabeto» strutturale: l’anello benzene rimane costante, mentre ciascuna base presenta il proprio schema di regioni ricche di elettroni rispetto a quel telaio fisso.
Coppie di elettroni che oscillano come piccole molle
Per descrivere ciò che avviene all’interno di questi impilamenti, gli autori impiegano un modello in cui gli elettroni si muovono in coppie correlate che oscillano tra i due anelli. Invece di formare un nuovo legame chimico, un elettrone salta temporaneamente da una regione occupata di un anello in una regione vuota (un «buco») dell’altro, e poi torna indietro. Questi moti accoppiati vengono trattati come stati quantistici risonanti, in qualche modo analoghi a due masse collegate da una molla che vibrano in sincronia. Nel modello contano solo due ingredienti chiave: la repulsione tra elettroni e il loro accoppiamento alle vibrazioni della molecola. Quando l’anello benzene è posizionato nel modo giusto sopra una base particolare, questi ingredienti si combinano per creare un pattern stabile di moti accoppiati che collega i due anelli senza rompere le loro strutture originali.
Dal moto quantistico a una forza misurabile
Poiché queste coppie di elettroni si muovono in modo regolare e oscillatorio, gli autori possono stimare la forza che tiene insieme gli anelli usando uno strumento della meccanica quantistica noto come teorema di Hellmann–Feynman. Questo teorema collega le variazioni di energia alle forze tra particelle, come accade quando allungare una molla immagazzina energia e genera una forza di richiamo. Negli impilamenti π–π, l’energia delle coppie elettroniche correlate dipende da quanto distano gli anelli l’uno dall’altro e da quanto «oscillano» gli elettroni durante la loro vibrazione. Derivando questa energia rispetto alla distanza si ottiene una forza efficace che mantiene gli anelli a uno sfasamento e a una separazione preferiti — sufficientemente forte da stabilizzare i complessi proteina–DNA, ma abbastanza debole da essere reversibile quando il complesso deve disfarsi.
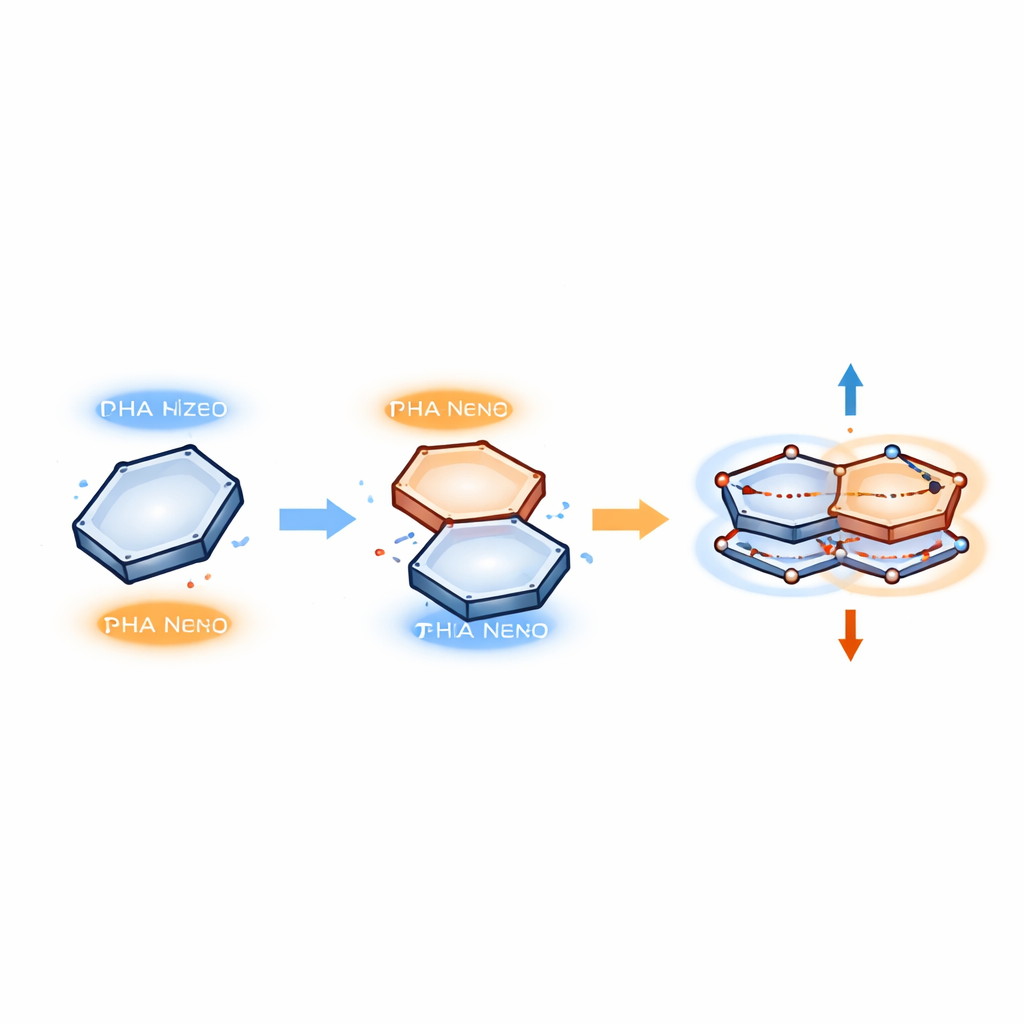
Un codice semplice per un riconoscimento del DNA flessibile
Messi insieme, i risultati suggeriscono che le proteine sfruttano un progetto robusto e riutilizzabile: un anello benzene costante nell’amminoacido aromatico e una base del DNA variabile che offre diversi paesaggi elettronici. L’anello benzene fornisce il telaio stabile necessario a formare queste coppie elettroniche oscillanti, mentre la base determina esattamente dove e con quale intensità si formano. Questo dà alle proteine un modo non permanente ma specifico per «percepire» quale base stanno toccando, aiutandole a riconoscere le sequenze target in mezzo all’enorme genoma. In termini quotidiani, le interazioni π–π permettono alle proteine di premere una testa di lettura di forma standard contro diverse «lettere» del DNA e di percepirne l’identità tramite un contatto finemente regolato a scala quantistica.
Citazione: Riera Aroche, R., Ortiz García, Y.M., Riera Leal, L. et al. Understanding the underlying language code that governs the π–π non-covalent interactions between proteins and DNA. Sci Rep 16, 14361 (2026). https://doi.org/10.1038/s41598-026-44532-2
Parole chiave: interazioni proteina–DNA, amminoacidi aromatici, impilamento pi–pi, riconoscimento del DNA, biologia quantistica