Clear Sky Science · de
Verstehen des zugrundeliegenden Sprachcodes, der die π–π nicht-kovalenten Wechselwirkungen zwischen Proteinen und DNA steuert
Wie Proteine DNA lesen, ohne sie dauerhaft zu berühren
Sekündlich müssen unzählige Proteine in unseren Zellen bestimmte „Wörter“ im DNA‑„Anleitungsbuch“ finden und ablesen. Dabei binden oder schneiden sie die DNA nicht dauerhaft, sondern nutzen flüchtige Anziehungskräfte zwischen Molekülen. Diese Arbeit untersucht eine der wichtigsten dieser subtilen Kräfte: eine spezielle Form der Stapelwechselwirkung zwischen flachen, ringförmigen Teilen von Proteinen und den Basen der DNA. Die Autoren argumentieren, dass diese Kontakte wie ein einfaches, wiederholbares Code‑System funktionieren, das Proteinen bei der Erkennung von DNA‑Sequenzen hilft, und sie erklären diesen Code mithilfe von Konzepten aus der Quantenphysik.
Der stille Magnetismus flacher Ringe
Sowohl DNA‑Basen als auch mehrere Aminosäuren in Proteinen enthalten flache, ringförmige Strukturen, deren Elektronen über den gesamten Ring delokalisiert sind. Wenn zwei solche Ringe Gesicht an Gesicht und leicht versetzt ausgerichtet sind, können sie einander durch das, was Chemiker π–π‑Wechselwirkungen nennen, anziehen. Frühere Arbeiten zeigten, dass diese Kontakte nahezu so stark wie Wasserstoffbrücken sein können und an Protein–DNA‑Schnittstellen häufig vorkommen. In dieser Studie konzentrieren sich die Autoren auf die benzolähnlichen Ringe in aromatischen Aminosäuren wie Phenylalanin, Tyrosin und Tryptophan und darauf, wie diese gegen die Ringe der vier DNA‑Basen gestapelt werden. Sie vertreten die Auffassung, dass diese Stapel mehr tun, als Moleküle zusammenzukleben: Sie bilden eine strukturierte, gerichtete Wechselwirkung, die Informationen darüber tragen kann, welche Base vorliegt.
Ein konstanter Griff an vielen verschiedenen DNA‑Buchstaben
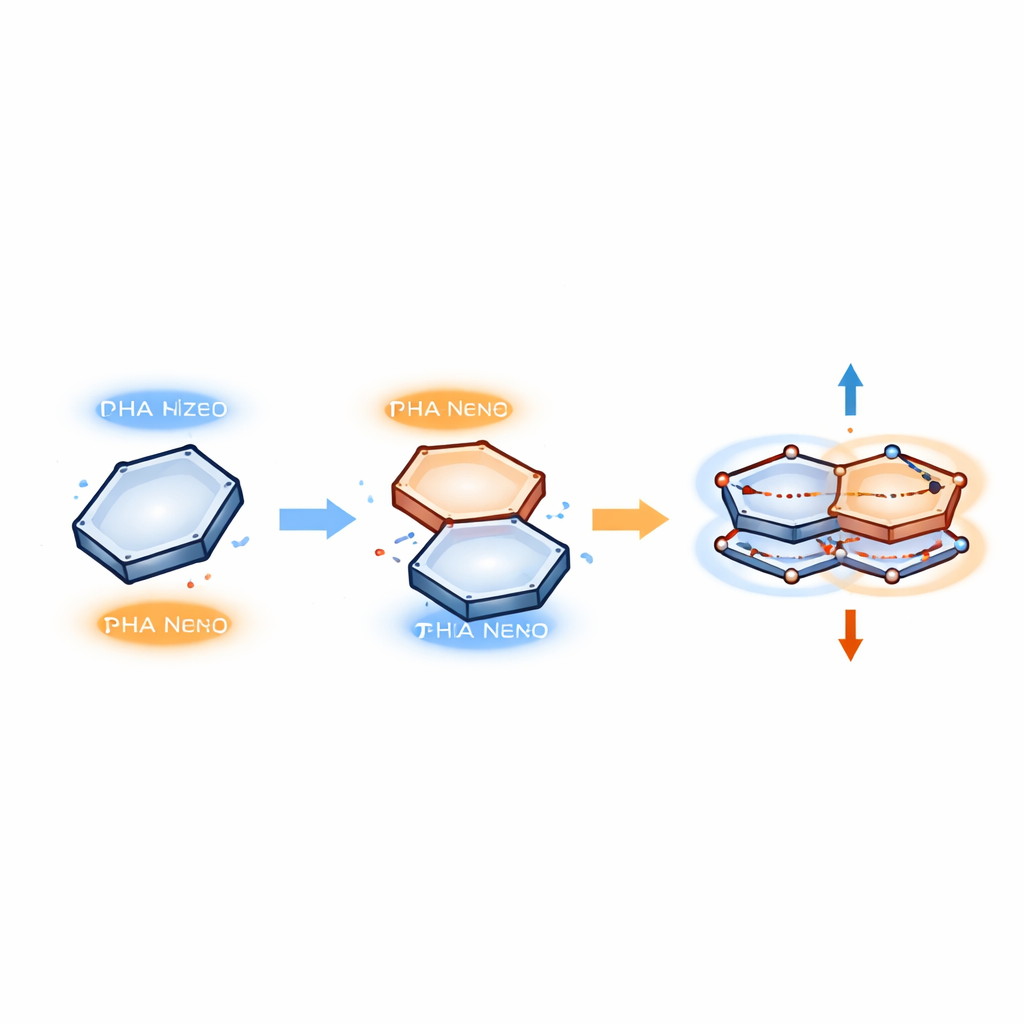
Durch die Untersuchung der Geometrie dieser Stapel finden die Autoren ein wiederkehrendes Muster. Bei den größeren DNA‑Basen (Adenin und Guanin, sogenannte Purine) führt die stabilste Konfiguration dazu, dass der Benzolring des Proteins parallel zur Base liegt, sodass zwei spezifische Positionen der Base (bezeichnet als N3 und C2) unter zwei bestimmten Kohlenstoffatomen (C1 und C2) des Benzols liegen. Bei den kleineren Basen (Thymin und Cytosin, sogenannte Pyrimidine) richten sich dieselben Benzolatome stattdessen über zwei Kohlenstoffe namens C5 und C6 der Base aus. In jedem Fall nehmen die Ringe eine parallele, aber horizontal verschobene Anordnung ein, ähnlich wie zwei sich leicht überlappende Münzen. Diese wiederholte Ausrichtung deutet auf eine Art strukturelles „Alphabet“ hin: Der Benzolring bleibt konstant, während jede Base ihr eigenes Muster elektronendichter Stellen in diesem festen Bezugsrahmen präsentiert.
Elektronenpaare, die wie winzige Federn schwingen
Um zu beschreiben, was in diesen Stapeln geschieht, verwenden die Autoren ein Modell, in dem Elektronen in korrelierten Paaren zwischen den beiden Ringen oszillieren. Anstatt eine neue chemische Bindung zu bilden, springt ein Elektron vorübergehend von einem besetzten Bereich in einem Ring in einen leeren Bereich (ein „Loch“) im anderen und dann wieder zurück. Diese gepaarten Bewegungen werden als resonante Quantenzustände behandelt, etwas ähnlich zwei Massen, die durch eine Feder verbunden sind und synchron schwingen. Im Modell sind nur zwei wesentliche Komponenten entscheidend: die gegenseitige Abstoßung der Elektronen und ihre Kopplung an Schwingungen des Moleküls. Wenn der Benzolring genau richtig über einer bestimmten Base verschoben ist, verbinden sich diese Komponenten zu einem stabilen Muster gepaarter Bewegungen, das die beiden Ringe verknüpft, ohne ihre ursprünglichen Strukturen zu zerstören.
Von quantenmechanischer Bewegung zu messbarer Kraft
Weil diese Elektronenpaare regelmäßig und oszillatorisch bewegen, können die Autoren die Kraft abschätzen, die die Ringe zusammenhält, mithilfe eines Werkzeugs aus der Quantenmechanik, bekannt als Hellmann–Feynman‑Theorem. Dieses Theorem verbindet Energieänderungen mit Kräften zwischen Teilchen, ähnlich wie das Dehnen einer Feder Energie speichert und eine rückstellende Zugkraft erzeugt. In den π–π‑Stapeln hängt die Energie der korrelierten Elektronenpaare davon ab, wie weit die Ringe voneinander entfernt sind und wie weit die Elektronen während ihrer Schwingung „ausschwingen“. Die Differentiation dieser Energie nach dem Abstand liefert eine effektive Kraft, die die Ringe in einer bevorzugten Versatz‑ und Abstandskonfiguration hält — stark genug, um Protein–DNA‑Komplexe zu stabilisieren, aber schwach genug, um reversibel zu sein, wenn der Komplex sich wieder auflösen muss.
Ein einfacher Code für flexible DNA‑Erkennung
In der Gesamtschau legen die Ergebnisse nahe, dass Proteine ein robustes, wiederverwendbares Design ausnutzen: ein konstantes Benzolringgerüst in der aromatischen Aminosäure und eine variable DNA‑Base, die unterschiedliche Elektronenlandschaften anbietet. Der Benzolring liefert das stabile Gerüst, das nötig ist, um diese oszillierenden Elektronenpaare zu bilden, während die Base bestimmt, wo und wie stark sie auftreten. Das gibt Proteinen eine nicht‑permanente, aber spezifische Möglichkeit, zu „fühlen“, welche Base sie berühren, und hilft ihnen, Zielsequenzen im riesigen Genom zu erkennen. Alltagssprachlich ermöglichen π–π‑Wechselwirkungen Proteinen, einen standardförmigen Lesekopf gegen verschiedene DNA‑„Buchstaben“ zu drücken und deren Identität durch eine fein abgestimmte, quantenskalaartige Berührung zu ertasten.
Zitation: Riera Aroche, R., Ortiz García, Y.M., Riera Leal, L. et al. Understanding the underlying language code that governs the π–π non-covalent interactions between proteins and DNA. Sci Rep 16, 14361 (2026). https://doi.org/10.1038/s41598-026-44532-2
Schlüsselwörter: Protein–DNA-Wechselwirkungen, aromatische Aminosäuren, pi–pi Stapelung, DNA-Erkennung, Quantenbiologie