Clear Sky Science · sv
Förstå den underliggande språk-koden som styr π–π icke-kovalenta interaktioner mellan proteiner och DNA
Hur proteiner läser DNA utan att fästa permanent
Varje sekund måste otaliga proteiner i våra celler hitta och läsa specifika ord i DNA:s "instruktionsbok". De gör detta utan att binda permanent eller klippa i DNA:t, genom flyktiga attraktioner mellan molekyler. Denna artikel undersöker en av de viktigaste av dessa subtila krafter: en särskild typ av staplingsinteraktion mellan platta, ringformade delar av proteiner och DNA-baser. Författarna menar att dessa kontakter beter sig som en enkel, upprepbar kod som hjälper proteiner att känna igen DNA-sekvenser, och de förklarar den koden med idéer från kvantfysiken.
De tysta magnetiska krafterna hos platta ringar
Både DNA-baser och flera aminosyror i proteiner innehåller platta, ringformade strukturer vars elektroner är delokaliserade över hela ringen. När två sådana ringar lägger sig ansikte mot ansikte och något förskjutna kan de attrahera varandra genom vad kemister kallar π–π (pi–pi) interaktioner. Tidigare arbete visade att dessa kontakter kan vara nästan lika starka som vätebindningar och är vanliga vid protein–DNA-gränssnitt. I denna studie fokuserar författarna på de bensenliknande ringarna som finns i aromatiska aminosyror såsom fenylalanin, tyrosin och tryptofan, och hur de staplas mot ringarna i de fyra DNA-baserna. De hävdar att dessa staplingar gör mer än att bara limma ihop molekyler: de bildar en strukturerad, riktad interaktion som kan bära information om vilken bas som är närvarande.
Ett konsekvent grepp om många olika DNA-bokstäver
Genom att granska geometrin hos dessa staplingar hittar författarna ett återkommande mönster. För de större DNA-baserna (adenin och guanin, kallade puriner) ger den mest stabila konfigurationen att proteinets bensenring ligger parallellt med basen så att två specifika positioner på basen (kallade N3 och C2) hamnar under två specifika kolatomer (C1 och C2) i bensen. För de mindre baserna (tymin och cytosin, kallade pyrimidiner) ligger samma bensenatomer i stället över två kolatomer som kallas C5 och C6 i basen. I varje fall antar ringarna en parallell men horisontellt förskjuten arrangemang, likt två överlappande mynt som lätt glidits förbi varandra. Denna upprepade inriktning tyder på en form av strukturellt "alfabet": bensenringen förblir densamma, medan varje bas visar sitt eget mönster av elektronrika punkter mot denna fasta ram.
Elektronpar som svänger som små fjädrar
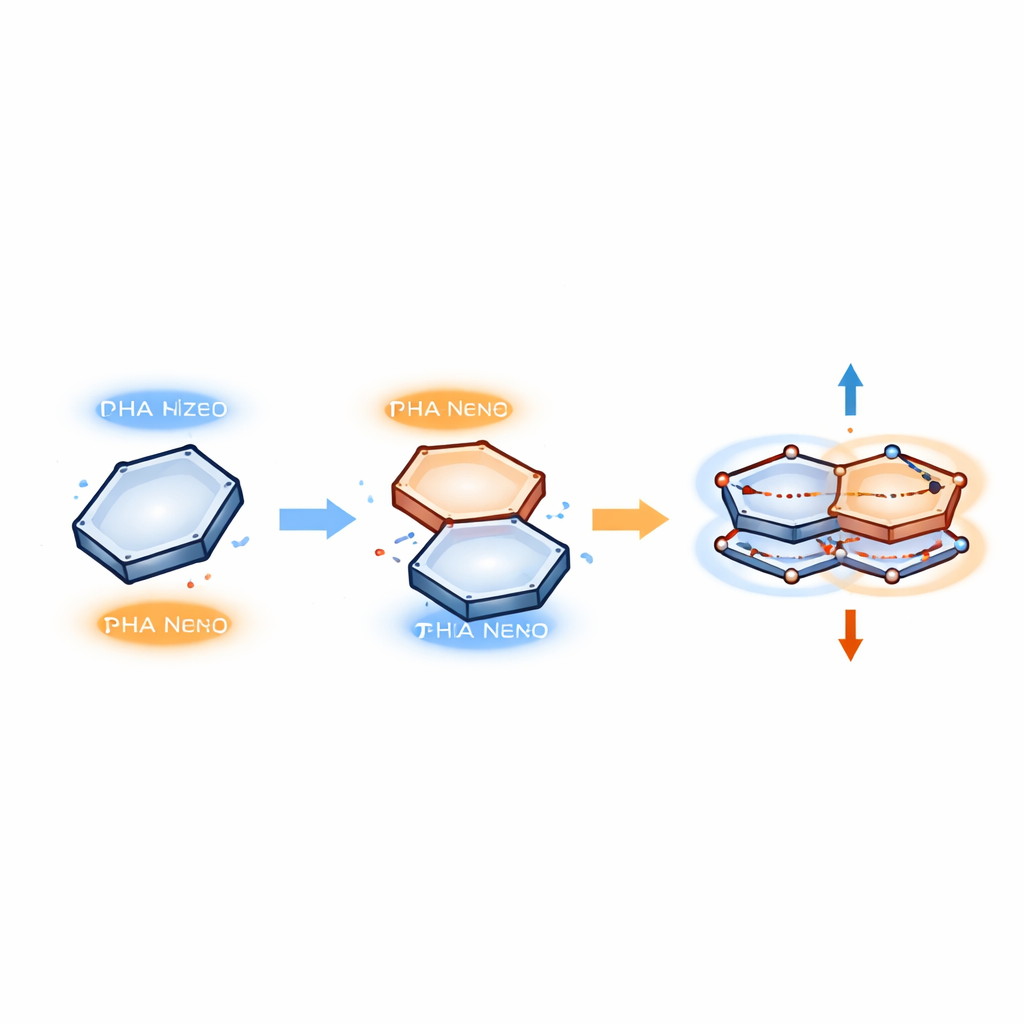
För att beskriva vad som händer inne i dessa staplingar använder författarna en modell där elektroner rör sig i korrelerade par som oscillerar mellan de två ringarna. Istället för att bilda en ny kemisk bindning hoppar en elektron tillfälligt från ett upptaget område i en ring in i ett tomt område (ett "hål") i den andra, och sedan tillbaka igen. Dessa parade rörelser behandlas som resonanta kvanttillstånd, något likt två massor kopplade med en fjäder som vibrerar i takt. I modellen spelar bara två nyckelingredienser roll: repulsionen mellan elektronerna och deras koppling till molekylens vibrationer. När bensenringen förskjuts precis rätt över en viss bas kombineras dessa faktorer för att skapa ett stabilt mönster av parade rörelser som knyter ihop de två ringarna utan att bryta deras ursprungliga strukturer.
Från kvantisk rörelse till en mätbar kraft
Eftersom dessa elektronpar rör sig på ett regelbundet, oscillerande sätt kan författarna uppskatta kraften som håller ringarna ihop med hjälp av ett verktyg från kvantmekaniken känt som Hellmann–Feynman-satsen. Denna sats kopplar förändringar i energi till krafter mellan partiklar, ungefär som att töja en fjäder lagrar energi och skapar en återställande dragning. I π–π-staplingarna beror energin hos de korrelerade elektronparen på hur långt ringarna är ifrån varandra och hur långt elektronerna "svänger" under sin oscillation. Att derivera denna energi med avseende på avstånd ger en effektiv kraft som håller ringarna på ett föredraget förskjutet läge och separation—stark nog att stabilisera protein–DNA-komplex, men svag nog att vara reversibel när komplexet behöver fallera isär.
En enkel kod för flexibel DNA-igenkänning
Sammantaget tyder arbetet på att proteiner utnyttjar en robust, återanvändbar konstruktion: en konstant bensenring i den aromatiska aminosyran och en varierande DNA-bas som erbjuder olika elektronlandskap. Bensenringen tillhandahåller den stabila ramen som behövs för att bilda dessa oscillerande elektronpar, medan basen bestämmer exakt var och hur starkt de bildas. Detta ger proteiner ett icke-permanent men ändå specifikt sätt att "känna" vilken bas de berör, och hjälper dem att känna igen målse-kvenser mitt i det vidsträckta genomet. I vardagliga termer låter π–π-interaktioner proteiner trycka ett standardformat läshuvud mot olika DNA-"bokstäver" och ana deras identitet genom en finjusterad, kvantskalig känsel.
Citering: Riera Aroche, R., Ortiz García, Y.M., Riera Leal, L. et al. Understanding the underlying language code that governs the π–π non-covalent interactions between proteins and DNA. Sci Rep 16, 14361 (2026). https://doi.org/10.1038/s41598-026-44532-2
Nyckelord: protein–DNA-interaktioner, aromatiska aminosyror, pi–pi-stapling, DNA-igenkänning, kvantbiologi