Clear Sky Science · pt
Compreendendo o código subjacente que rege as interações não covalentes π–π entre proteínas e DNA
Como as proteínas “leem” o DNA sem se ligar a ele permanentemente
A cada segundo, inúmeras proteínas em nossas células precisam localizar e ler palavras específicas no ‘‘livro de instruções’’ que é o DNA. Elas fazem isso sem se ligar ou cortar o DNA de forma permanente, valendo-se de atrações efêmeras entre moléculas. Este artigo explora uma das mais importantes dessas forças sutis: um tipo especial de interação de empilhamento entre partes planas e em forma de anel das proteínas e as bases do DNA. Os autores defendem que esses contatos se comportam como um código simples e repetível que ajuda as proteínas a reconhecer sequências de DNA, e explicam esse código usando ideias da física quântica.
O magnetismo discreto dos anéis planos
Tanto as bases do DNA quanto vários aminoácidos em proteínas contêm estruturas planas em forma de anel cujos elétrons estão delocalizados por toda a extensão do anel. Quando dois desses anéis se alinham frente a frente e ligeiramente deslocados, eles podem se atrair por meio do que os químicos chamam de interações π–π (pi–pi). Trabalhos anteriores mostraram que esses contatos podem ser quase tão fortes quanto ligações de hidrogênio e são comuns em interfaces proteína–DNA. Neste estudo, os autores concentram-se nos anéis semelhantes ao benzeno presentes em aminoácidos aromáticos como fenilalanina, tirosina e triptofano, e em como eles se empilham contra os anéis das quatro bases do DNA. Eles argumentam que essas pilhas fazem mais do que simplesmente colar moléculas: formam uma interação estruturada e direcional que pode transmitir informação sobre qual base está presente.
Uma aderência consistente para muitas letras diferentes do DNA
Examinando a geometria dessas pilhas, os autores encontram um padrão recorrente. Para as bases maiores do DNA (adenina e guanina, chamadas purinas), a configuração mais estável coloca o anel benzênico da proteína paralelo à base de modo que duas posições específicas na base (chamadas N3 e C2) fiquem sob dois carbonos específicos (C1 e C2) do benzeno. Para as bases menores (timina e citosina, chamadas pirimidinas), os mesmos átomos do benzeno alinham-se em vez disso sobre dois carbonos chamados C5 e C6 na base. Em todos os casos, os anéis adotam um arranjo paralelo, porém deslocado horizontalmente, semelhante a duas moedas sobrepostas ligeiramente deslizadas uma em relação à outra. Esse alinhamento repetido sugere uma espécie de “alfabeto” estrutural: o anel benzênico permanece constante, enquanto cada base apresenta seu próprio padrão de pontos ricos em elétrons a esse quadro fixo.
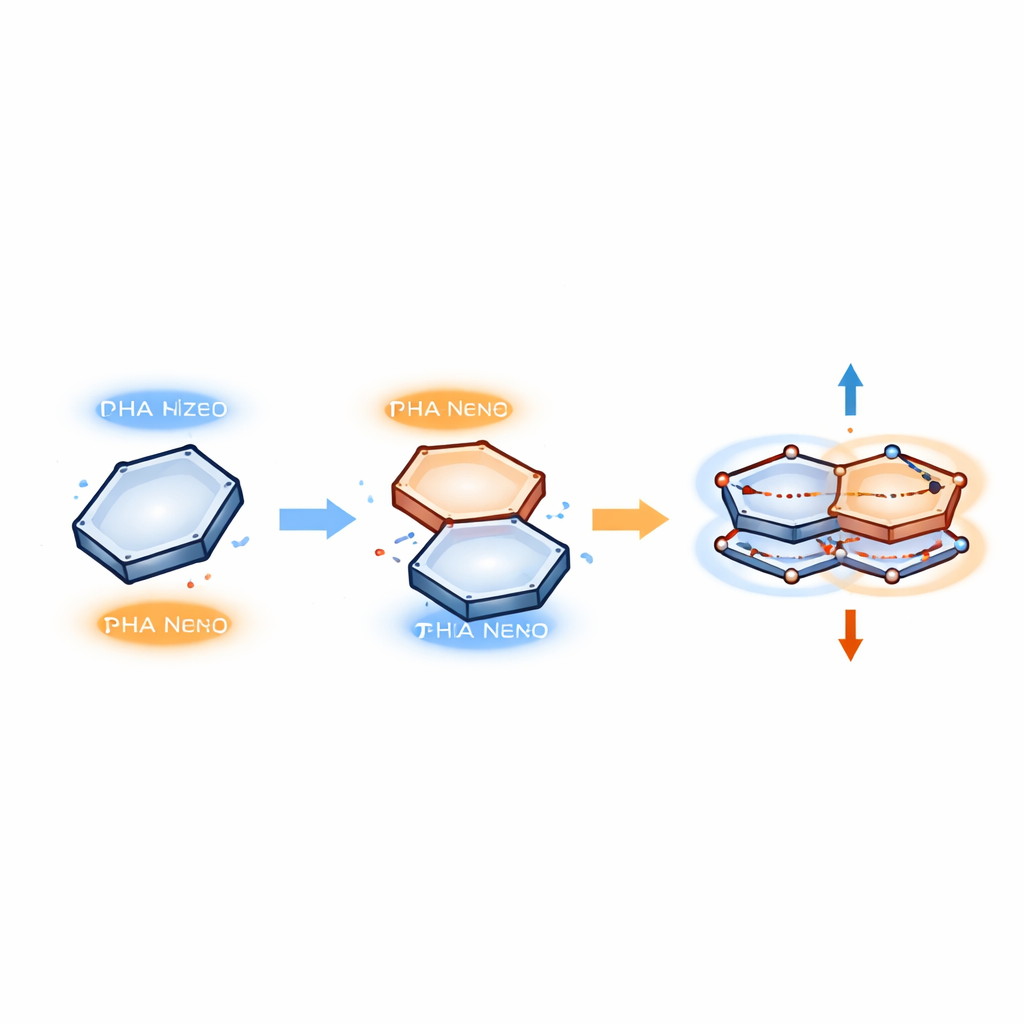
Pares de elétrons que oscilam como pequenas molas
Para descrever o que acontece dentro dessas pilhas, os autores usam um modelo em que elétrons se movem em pares correlacionados que oscilam entre os dois anéis. Em vez de formar uma nova ligação química, um elétron salta temporariamente de uma região ocupada em um anel para uma região vazia (um “buraco”) no outro, e depois volta. Esses movimentos pareados são tratados como estados quânticos ressonantes, algo como duas massas ligadas por uma mola que vibram em sincronia. No modelo, apenas dois ingredientes-chave importam: a repulsão entre elétrons e seu acoplamento às vibrações da molécula. Quando o anel de benzeno é deslocado de forma adequada sobre uma determinada base, esses ingredientes se combinam para criar um padrão estável de movimento pareado que liga os dois anéis sem romper suas estruturas originais.
Do movimento quântico a uma força mensurável
Como esses pares de elétrons se movem de maneira regular e oscilatória, os autores conseguem estimar a força que mantém os anéis juntos usando uma ferramenta da mecânica quântica conhecida como teorema de Hellmann–Feynman. Esse teorema conecta mudanças na energia às forças entre partículas, de modo semelhante a como esticar uma mola armazena energia e cria uma força restauradora. Nas pilhas π–π, a energia dos pares de elétrons correlacionados depende da distância entre os anéis e da amplitude com que os elétrons “balançam” durante a oscilação. Diferenciando essa energia em relação à distância obtém-se uma força efetiva que mantém os anéis em um deslocamento e separação preferidos — forte o suficiente para estabilizar complexos proteína–DNA, mas fraca o bastante para ser reversível quando o complexo precisa se desfazer.
Um código simples para reconhecimento flexível do DNA
Em conjunto, o trabalho sugere que as proteínas exploram um projeto robusto e reutilizável: um anel de benzeno constante no aminoácido aromático e uma base de DNA variável que oferece diferentes paisagens eletrônicas. O anel de benzeno fornece a estrutura estável necessária para formar esses pares de elétrons oscilantes, enquanto a base determina exatamente onde e com que intensidade eles se formam. Isso dá às proteínas uma maneira não permanente, porém específica, de “sentir” qual base estão tocando, ajudando-as a reconhecer sequências-alvo em meio ao vasto genoma. Em termos cotidianos, as interações π–π permitem que proteínas apoiem uma cabeça leitora de formato padrão contra diferentes “letras” do DNA e sintam sua identidade por meio de um toque afinado na escala quântica.
Citação: Riera Aroche, R., Ortiz García, Y.M., Riera Leal, L. et al. Understanding the underlying language code that governs the π–π non-covalent interactions between proteins and DNA. Sci Rep 16, 14361 (2026). https://doi.org/10.1038/s41598-026-44532-2
Palavras-chave: interações proteína–DNA, aminoácidos aromáticos, empilhamento pi–pi, reconhecimento de DNA, biologia quântica