Clear Sky Science · sv
Genomanalys av en klinisk Streptococcus suis ST1-isolat från CSF avslöjar antibiotikaresistens, virulens och en evolutionär koppling till ST7
Varför en grisbakterie spelar roll för människor
De flesta av oss ser lantbruksinfektioner som ett djurproblem, inte ett mänskligt. Men vissa mikrober kan hoppa från grisar till människor och orsaka livshotande sjukdom. Den här studien fokuserar på en sådan bakterie, Streptococcus suis, som kan ge svår meningit och bestående hörselnedsättning. Genom att läsa den fullständiga genetiska ritningen av en stam som tagits direkt från en patients cerebrospinalvätska visar forskarna hur denna mikrob motstår viktiga antibiotika, vad som gör den särskilt skadlig och hur den utvecklas i samspel med närbesläktade stammar som orsakat dödliga utbrott.

En patient, ett lumbalprov och ett dolt hot
Berättelsen börjar med en person som lagts in på intensivvård med purulent meningit, en allvarlig hjärninfektion. Läkare isolerade S. suis från patientens cerebrospinalvätska, vilket bekräftade att en grisassocierad bakterie hade invaderat centrala nervsystemet. Efter behandling förbättrades patientens tillstånd, men hen lämnades med svår hörselnedsättning, en välkänd komplikation av denna infektion. Detta verkliga fall gav forskarna en sällsynt möjlighet: att undersöka DNA från en mänskligt härledd stam, benämnd 366, och fråga vad i dess genom som kan förklara dess beteende i kroppen och dess respons på behandling.
Vilka läkemedel fungerar fortfarande — och vilka gör det inte
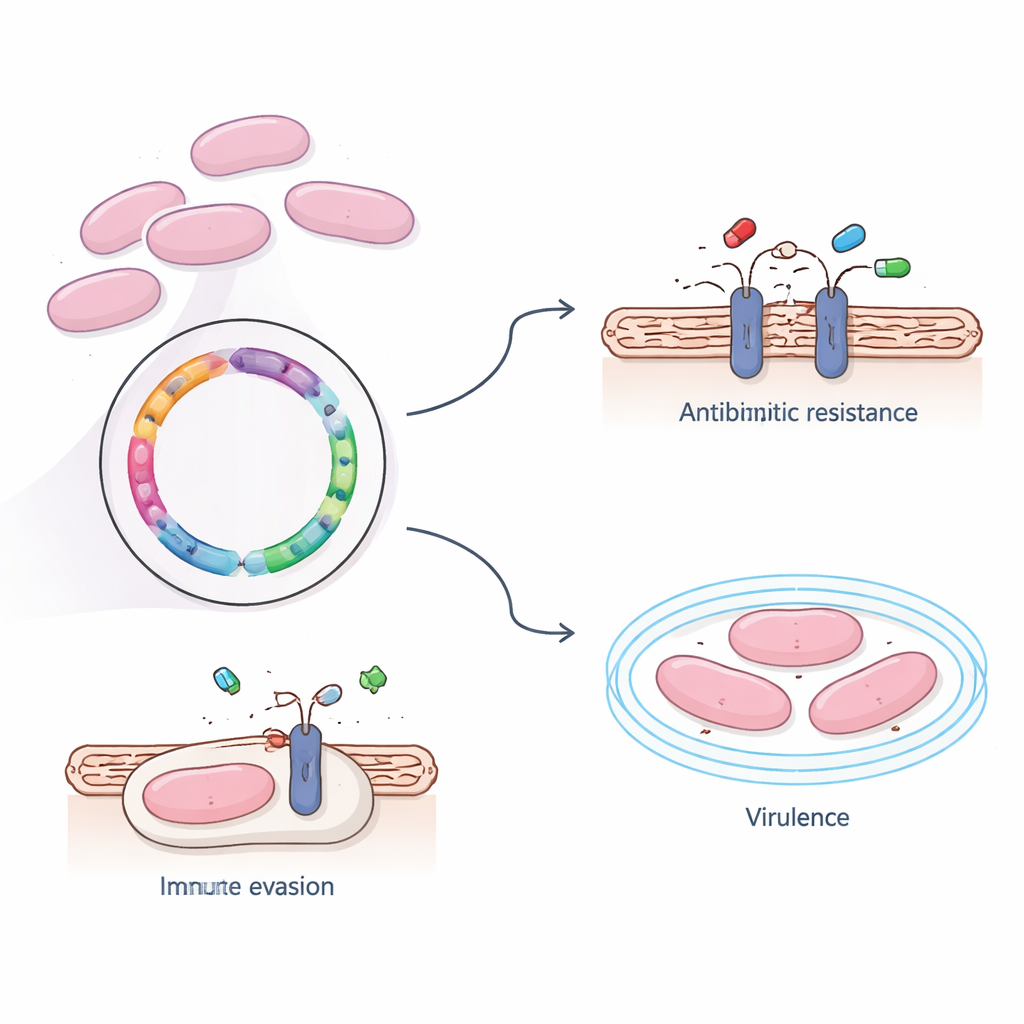
I laboratoriet testade teamet hur bakterien svarade på vanliga antibiotika. De fann att stam 366 fortfarande var känslig för flera förstahandsläkemedel, inklusive penicillin, cefalosporiner och reservläkemedel som karbapenemer och vankomycin. Däremot var den starkt resistent mot erytromycin, klindamycin och tetracyklin — läkemedel som används i stor utsträckning inom både human- och veterinärmedicin. När forskarna genomsökte genomet upptäckte de två resistensgener, ermB och tet(O), som förändrar bakteriens proteintillverkning så att dessa läkemedel inte längre kan binda effektivt. Intressant nog var dessa resistensgener inbäddade i huvudkromosomen snarare än på lättdelbara mobila DNA-element, vilket tyder på att denna stams läkemedelsresistens sprids mer genom expansion av framgångsrika bakteriestammar än genom snabb genutbyte.
Genetiska ledtrådar till hur bakterien orsakar sjukdom
Utöver läkemedelsresistens undersökte forskarna vad som gör denna stam så kapabel att överleva i blodomloppet och invadera hjärnan. Med hjälp av flera stora referensdatabaser identifierade de fyra nyckelgener kopplade till virulens — förmågan att orsaka sjukdom. Tre av dem hjälper till att bygga en sockerhaltig yttre kapsel som skyddar bakterien från att kännas igen och ätas upp av immunceller, medan den fjärde hjälper bakterien att fästa vid värdvävnader. Storskaliga analyser av alla gener visade att många stöder grundläggande livsfunktioner som ämnesomsättning och proteinsyntes, men belyste också transportsystem som förflyttar näringsämnen, toxiner och möjligen läkemedel över cellmembranet. En huvudväg, känd som ABC-transportersystemet, framträdde som en central nod för import av användbara molekyler och export av skadliga, potentiellt inklusive antibiotika.
Familjeband mellan farliga stammar
För att placera patientens stam i ett bredare sammanhang jämförde teamet dess genom med närbesläktade S. suis-stammar från grisar och människor i olika regioner. De fann att stam 366 tillhörde sekvenstyp ST1, en genetisk härkomst som redan är känd för att dominera mänskliga infektioner. När de byggde evolutions-träd med hjälp av tusentals små DNA-skillnader visade de att ST1 är nära besläktat med en annan linje kallad ST7, som kopplats till stora utbrott. Pangenomanalys — att se vilka gener som delas eller är unika över flera stammar — avslöjade en stor kärna av gemensamma gener mellan ST1 och ST7, vilket stödjer idén att epidemiska ST7-stammar utvecklats direkt från en ST1-bakgrund genom att förvärva ytterligare genetiskt material.
Vad detta betyder för folkhälsan
Tillsammans målar fynden upp bilden av en högt anpassad grisburen bakterie som korsat över till människor med en verktygslåda både för att överleva behandling och orsaka svår sjukdom. Patientens stam bär stabil, kromosombundet motstånd mot flera i dessa vitt använda antibiotika och nyckelgener som hjälper den att undvika immunsvar och fästa vid mänsklig vävnad. Samtidigt signalerar dess nära genetiska förhållande till utbrottsassocierade stammar att farliga varianter kan uppstå från samma släktträd. Genom att dissekera genomet hos ett enda, väl dokumenterat kliniskt isolat fördjupar denna studie vår förståelse av hur S. suis ST1 fungerar och utvecklas, och lägger grunden för bättre övervakning, smartare antibiotikaanvändning och mer riktade strategier för att skydda både bönder och allmänheten.
Citering: Jiang, J., Duan, W. & Liang, L. Genomic analysis of a clinical Streptococcus suis ST1 isolate from CSF reveals antimicrobial resistance, virulence, and an evolutionary link to ST7. Sci Rep 16, 11271 (2026). https://doi.org/10.1038/s41598-026-41475-6
Nyckelord: Streptococcus suis, zoonotisk meningit, antibiotikaresistens, bakteriegenomik, gris-till-människa-infektion