Clear Sky Science · de
Genomanalyse eines klinischen Streptococcus suis ST1-Isolats aus Liquor zeigt Antibiotikaresistenz, Virulenz und eine evolutionäre Verbindung zu ST7
Warum ein Schweinekeim für Menschen wichtig ist
Die meisten von uns betrachten Tierinfektionen als ein Problem der Tiere, nicht der Menschen. Manche Erreger können jedoch von Schweinen auf Menschen überspringen und lebensbedrohliche Erkrankungen auslösen. Diese Studie konzentriert sich auf einen solchen Bakterienstamm, Streptococcus suis, der schwere Meningitis und bleibenden Hörverlust verursachen kann. Durch das vollständige Ablesen des genetischen Bauplans eines Stamms, der direkt aus dem Liquor eines Patienten entnommen wurde, zeigen die Forschenden, wie dieser Keim gegen wichtige Antibiotika resistent ist, was ihn besonders schädlich macht und wie er sich in Verbindung mit verwandten Stämmen weiterentwickelt, die bereits tödliche Ausbrüche verursacht haben.

Ein Patient, eine Lumbalpunktion und eine verborgene Bedrohung
Die Geschichte beginnt mit einer Person, die mit eitriger Meningitis auf der Intensivstation aufgenommen wurde, einer schweren Hirninfektion. Ärzte isolierten S. suis aus dem Liquor des Patienten und bestätigten damit, dass ein mit Schweinen assoziierter Keim das zentrale Nervensystem befällt. Nach der Behandlung verbesserte sich die geistige Verfassung des Patienten, doch blieb ein schwerer Hörverlust zurück, eine bekannte Komplikation dieser Infektion. Dieser reale Fall bot den Wissenschaftlern eine seltene Gelegenheit: die DNA eines humanen Stamms, mit der Bezeichnung 366, zu untersuchen und zu ergründen, was im Genom sein Verhalten im Körper und seine Reaktion auf die Behandlung erklären könnte.
Welche Medikamente noch wirken — und welche nicht
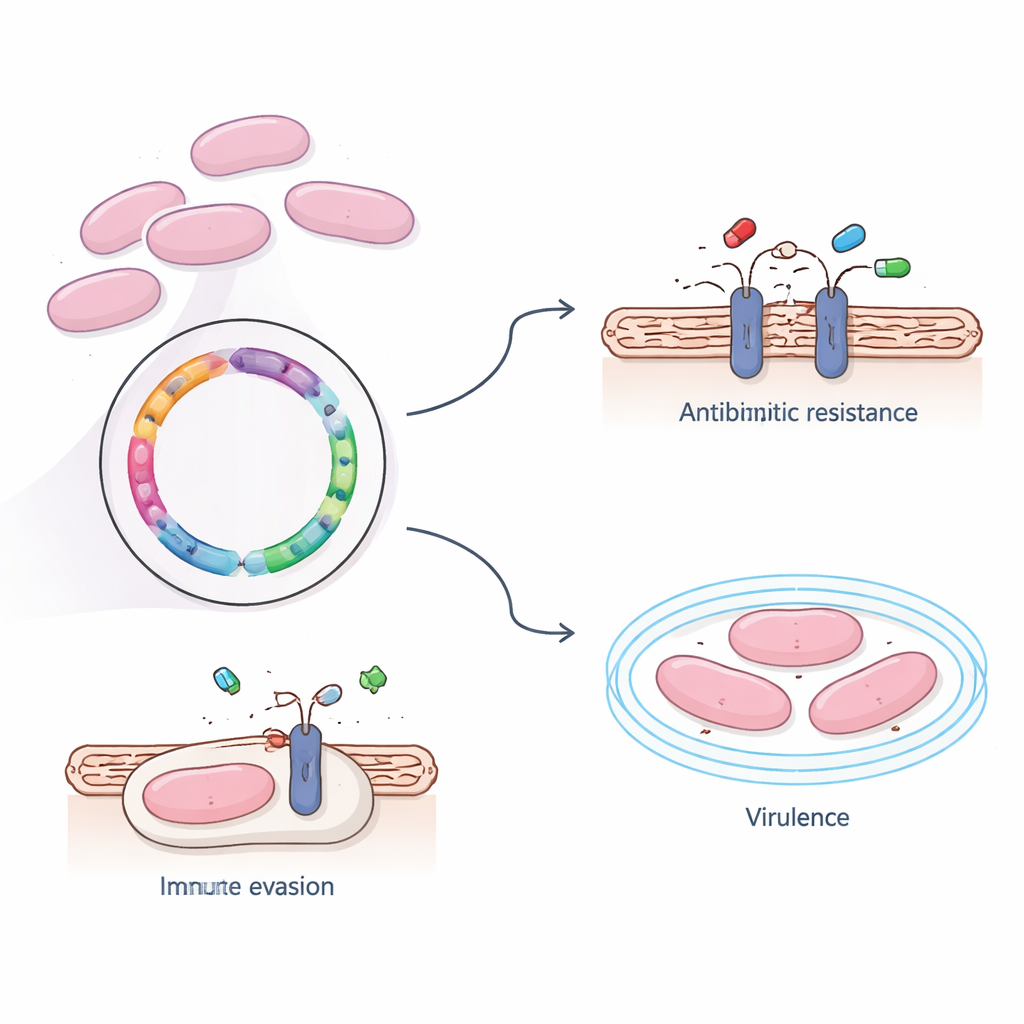
Im Labor prüfte das Team, wie das Bakterium auf gängige Antibiotika reagiert. Sie fanden heraus, dass Stamm 366 gegenüber mehreren Erstlinienmedikamenten weiterhin empfindlich war, darunter Penicillin, Cephalosporine und Reservewirkstoffe wie Carbapeneme und Vancomycin. Gleichzeitig zeigte es jedoch eine starke Resistenz gegen Erythromycin, Clindamycin und Tetracyclin — Arzneimittel, die sowohl in der Human- als auch in der Veterinärmedizin weit verbreitet sind. Beim Durchsuchen des Genoms entdeckten die Forschenden zwei Resistenzgene, ermB und tet(O), die die Proteinsynthese des Bakteriums verändern, sodass diese Medikamente nicht mehr effektiv binden können. Interessanterweise waren diese Resistenzgene in das Hauptchromosom eingebettet und nicht auf leicht übertragbaren mobilen DNA-Elementen, was nahelegt, dass sich die Antibiotikaresistenz dieses Stammes eher durch die Ausbreitung erfolgreicher bakterieller Linien als durch schnellen Genaustausch verbreitet.
Genetische Hinweise darauf, wie der Keim Krankheit verursacht
Über die Antibiotikaresistenz hinaus wollten die Forschenden wissen, was diesen Stamm befähigt, im Blut zu überleben und ins Gehirn einzudringen. Mithilfe mehrerer großer Referenzdatenbanken identifizierten sie vier Schlüsselerregergene, die mit Virulenz — der Fähigkeit, Krankheit zu verursachen — verknüpft sind. Drei davon sind am Aufbau einer zuckerhaltigen äußeren Kapsel beteiligt, die das Bakterium vor Erkennung und Aufnahme durch Immunzellen schützt, während das vierte Gen dem Keim hilft, an Wirtsgewebe zu haften. Groß angelegte Analysen aller Gene zeigten, dass viele von ihnen grundlegende Lebensfunktionen wie Stoffwechsel und Proteinproduktion unterstützen, gleichzeitig aber auch Transportsysteme hervorhoben, die Nährstoffe, Toxine und möglicherweise auch Medikamente durch die Zellmembran bewegen. Ein wichtiger Weg, das sogenannte ABC-Transportersystem, fiel als zentraler Knotenpunkt auf, der nützliche Moleküle importiert und schädliche exportiert — potenziell einschließlich Antibiotika.
Verwandtschaftsverhältnisse zwischen gefährlichen Stämmen
Um den Stamm des Patienten in einen breiteren Kontext einzuordnen, verglich das Team dessen Genom mit denen eng verwandter S.-suis-Stämme aus Schweinen und Menschen aus verschiedenen Regionen. Sie fanden heraus, dass Stamm 366 zur Sequenztyp-Gruppe ST1 gehörte, einer genetischen Linie, die bereits dafür bekannt ist, menschliche Infektionen zu dominieren. Beim Aufbau von Evolutionsbäumen anhand tausender kleiner DNA-Unterschiede zeigten sie, dass ST1 eng verwandt ist mit einer anderen Linie namens ST7, die mit größeren Ausbrüchen in Verbindung gebracht wurde. Pangenom-Analysen — bei denen untersucht wird, welche Gene zwischen mehreren Stämmen geteilt oder einzigartig sind — offenbarten einen großen Kern gemeinsamer Gene zwischen ST1 und ST7, was die Idee stützt, dass epidemische ST7-Stämme direkt aus einem ST1-Hintergrund durch Erwerb zusätzlichen genetischen Materials entstanden sind.
Was das für die öffentliche Gesundheit bedeutet
Insgesamt zeichnen die Befunde das Bild eines hochangepassten, von Schweinen stammenden Keims, der in Menschen übergegangen ist und über ein Instrumentarium verfügt, sowohl Behandlungen zu überstehen als auch schwere Erkrankungen zu verursachen. Der isolierte Patientenstamm trägt stabile, chromosomal kodierte Resistenzen gegen mehrere weit verbreitete Antibiotika sowie Schlüsselfaktoren, die ihm helfen, Immunangriffe zu umgehen und an menschlichem Gewebe haften zu bleiben. Zugleich signalisiert die enge genetische Verwandtschaft mit ausbruchassoziierten Stämmen, dass gefährliche Varianten aus derselben Stammbaumlinie entstehen können. Die Entschlüsselung des Genoms eines einzelnen, gut dokumentierten klinischen Isolats vertieft unser Verständnis darüber, wie S. suis ST1 funktioniert und sich entwickelt, und liefert eine Grundlage für bessere Überwachung, klügeren Antibiotikaeinsatz und gezieltere Strategien zum Schutz von Landwirten und der Allgemeinbevölkerung.
Zitation: Jiang, J., Duan, W. & Liang, L. Genomic analysis of a clinical Streptococcus suis ST1 isolate from CSF reveals antimicrobial resistance, virulence, and an evolutionary link to ST7. Sci Rep 16, 11271 (2026). https://doi.org/10.1038/s41598-026-41475-6
Schlüsselwörter: Streptococcus suis, zoonotische Meningitis, Antibiotikaresistenz, bakterielle Genomik, Schwein-zu-Mensch-Infektion