Clear Sky Science · pl
Analiza genomu klinicznego izolatu Streptococcus suis ST1 z płynu mózgowo-rdzeniowego ujawnia oporność na leki przeciwdrobnoustrojowe, czynniki zjadliwości i ewolucyjne powiązanie z ST7
Dlaczego zarazek od świni ma znaczenie dla ludzi
Większość z nas postrzega choroby na fermach jako problem zwierząt, a nie ludzi. Tymczasem niektóre drobnoustroje potrafią przeskoczyć ze świń na ludzi i wywołać choroby zagrażające życiu. W tym badaniu skupiono się na jednym z takich bakterii, Streptococcus suis, który może powodować ciężkie zapalenie opon mózgowo-rdzeniowych i trwałą utratę słuchu. Odczytując kompletny plan genetyczny szczepu pobranego bezpośrednio z płynu mózgowo-rdzeniowego pacjenta, badacze pokazują, jak ten zarazek opiera się kluczowym antybiotykom, co sprawia, że jest szczególnie niebezpieczny, i jak ewoluuje wraz z powiązanymi szczepami, które wywoływały śmiertelne epidemie.

Pacjent, punkcja lędźwiowa i ukryte zagrożenie
Historia zaczyna się od osoby przyjętej na oddział intensywnej terapii z ropnym zapaleniem opon — poważną infekcją mózgu. Lekarze wyizolowali S. suis z płynu mózgowo-rdzeniowego pacjenta, potwierdzając, że związany ze świnią drobnoustrój dostał się do ośrodkowego układu nerwowego. Po leczeniu stan pacjenta się poprawił, ale pozostała u niego ciężka utrata słuchu — dobrze znane powikłanie tej infekcji. Ten przypadek z praktyki klinicznej dał naukowcom rzadką okazję: zanalizować DNA szczepu pochodzącego od człowieka, oznaczonego jako 366, i sprawdzić, co w jego genomie może wyjaśniać zachowanie w organizmie oraz odpowiedź na terapię.
Które leki nadal działają — a które nie
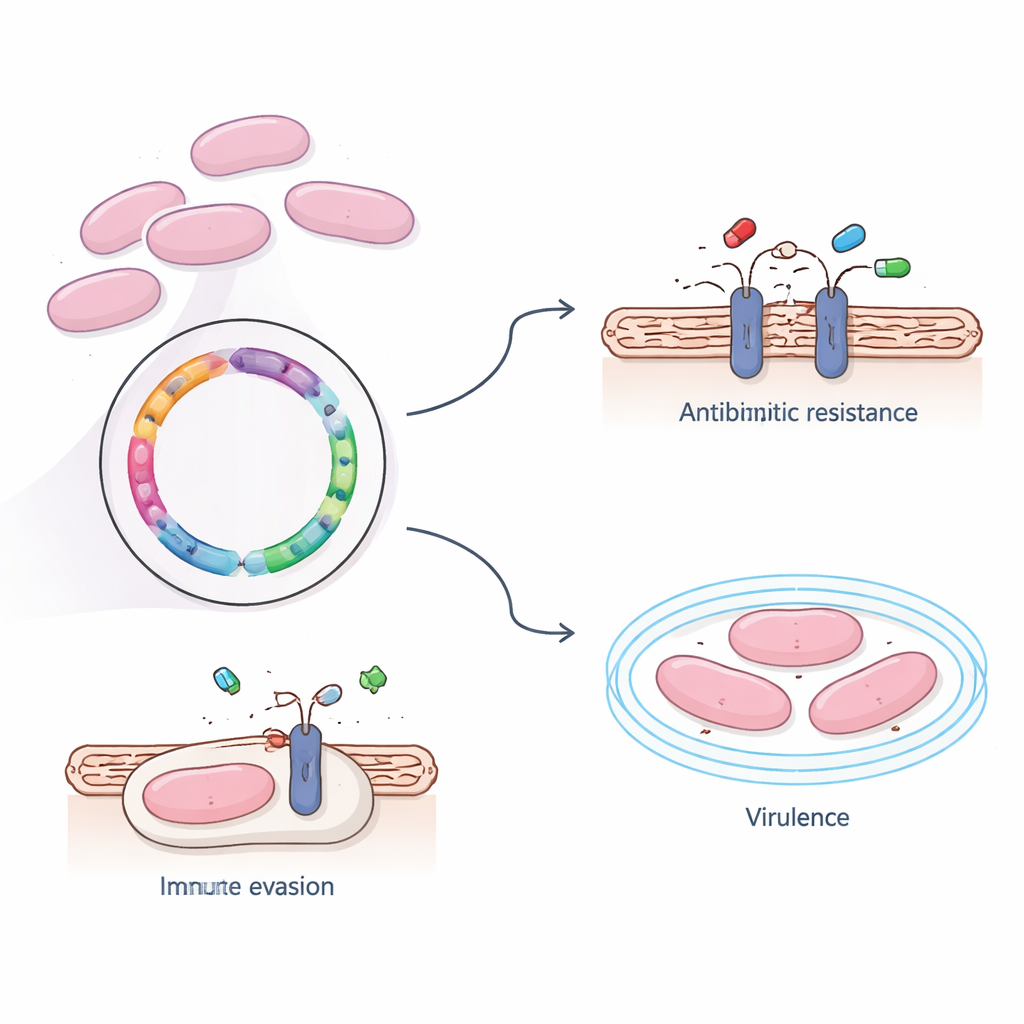
W laboratorium zespół sprawdził, jak bakteria reaguje na powszechnie stosowane antybiotyki. Stwierdzono, że szczep 366 pozostał wrażliwy na kilka leków pierwszego rzutu, w tym penicylinę, cefalosporyny oraz środki z ostatniej linii, takie jak karbapenemy i wankomycyna. Jednocześnie wykazywał silną oporność na erytromycynę, klindamycynę i tetracyklinę — leki szeroko stosowane zarówno w medycynie ludzkiej, jak i weterynaryjnej. Analiza genomu ujawniła obecność dwóch genów oporności, ermB i tet(O), które modyfikują mechanizmy syntezy białek bakterii, uniemożliwiając skuteczne wiązanie się tych leków. Co istotne, geny te znajdowały się w chromosomie głównym, a nie na łatwo przenoszonych elementach mobilnych DNA, co sugeruje, że oporność tego szczepu rozprzestrzenia się raczej poprzez ekspansję udanych linii bakteryjnych niż szybkie wymiany genów.
Genetyczne wskazówki dotyczące zdolności do wywoływania choroby
Ponad opornością na leki, badacze zastanawiali się, co sprawia, że ten szczep jest tak zdolny do przetrwania we krwi i atakowania mózgu. Korzystając z kilku dużych baz referencyjnych, zidentyfikowali cztery kluczowe geny związane ze zjadliwością — zdolnością do wywoływania choroby. Trzy z nich pomagają w budowie słodkiej otoczki zewnętrznej, która chroni bakterię przed rozpoznaniem i zjedzeniem przez komórki odpornościowe, podczas gdy czwarty ułatwia przyleganie do tkanek gospodarza. Analizy obejmujące cały zestaw genów wykazały, że wiele z nich wspiera podstawowe funkcje życiowe, takie jak metabolizm i produkcja białek, ale także uwydatniły systemy transportowe przenoszące składniki odżywcze, toksyny i potencjalnie leki przez błonę komórkową. Jedna z głównych dróg, znana jako system transportera ABC, wyróżniała się jako centralny węzeł do importu przydatnych cząsteczek i eksportu szkodliwych, być może w tym antybiotyków.
Powiązania rodzinne między niebezpiecznymi szczepami
Aby umieścić szczep pacjenta w szerszym kontekście, zespół porównał jego genom z genomami blisko spokrewnionych szczepów S. suis pochodzących od świń i ludzi z różnych regionów. Odkryli, że szczep 366 należy do typu sekwencyjnego ST1, linii genetycznej już znanej jako dominująca w zakażeniach ludzkich. Budując drzewa ewolucyjne na podstawie tysięcy drobnych różnic w DNA, pokazali, że ST1 jest blisko spokrewniony z inną linią nazwaną ST7, która była powiązana z dużymi epidemiami. Analiza pangenomu — sprawdzenie, które geny są wspólne lub unikalne dla wielu szczepów — ujawniła dużą pulę genów rdzeniowych wspólnych dla ST1 i ST7, co wspiera tezę, że epidemiczne szczepy ST7 wyewoluowały bezpośrednio z tła ST1 przez nabycie dodatkowego materiału genetycznego.
Co to oznacza dla zdrowia publicznego
W całości wyniki tworzą obraz wysoko zaadaptowanego zarazka pochodzenia świńskiego, który przeszedł na ludzi z zestawem cech umożliwiających zarówno przetrwanie terapii, jak i wywoływanie ciężkich chorób. Izolat pacjenta niesie stabilne, zakodowane w chromosomie mechanizmy oporności na kilka powszechnie stosowanych antybiotyków oraz kluczowe geny pomagające unikać ataku układu odpornościowego i przyczepiać się do tkanek ludzkich. Równocześnie jego bliskie związki genetyczne ze szczepami powiązanymi z epidemiami sygnalizują, że niebezpieczne warianty mogą wyłaniać się z tej samej linii rodowej. Rozbiór genomu pojedynczego, dobrze udokumentowanego izolatu klinicznego pogłębia nasze zrozumienie działania i ewolucji S. suis ST1, dostarczając podstaw do lepszej obserwacji, mądrzejszego stosowania antybiotyków i celniejszych strategii ochrony zarówno rolników, jak i szerszej populacji.
Cytowanie: Jiang, J., Duan, W. & Liang, L. Genomic analysis of a clinical Streptococcus suis ST1 isolate from CSF reveals antimicrobial resistance, virulence, and an evolutionary link to ST7. Sci Rep 16, 11271 (2026). https://doi.org/10.1038/s41598-026-41475-6
Słowa kluczowe: Streptococcus suis, zoonotyczne zapalenie opon mózgowo-rdzeniowych, oporność na antybiotyki, genomika bakteryjna, zakażenie od świni do człowieka