Clear Sky Science · fr
Analyse génomique d’un isolat clinique de Streptococcus suis ST1 issu du LCR révèle une résistance aux antimicrobiens, des facteurs de virulence et un lien évolutif avec ST7
Pourquoi un germe porcins importe pour les humains
La plupart d’entre nous considèrent les infections agricoles comme un problème animal, pas humain. Mais certains germes peuvent passer des porcs aux humains et provoquer des maladies potentiellement mortelles. Cette étude se concentre sur l’un de ces agents, Streptococcus suis, qui peut déclencher une méningite sévère et une perte auditive durable. En lisant l’intégralité du plan génétique d’une souche prélevée directement du liquide céphalorachidien d’un patient, les chercheurs montrent comment ce germe résiste à des antibiotiques clés, ce qui le rend particulièrement virulent et comment il évolue parallèlement à des souches apparentées responsables d’épidémies mortelles.

Un patient, une ponction lombaire et une menace cachée
L’histoire commence avec une personne admise en soins intensifs pour une méningite purulente, une grave infection cérébrale. Les médecins ont isolé S. suis dans le liquide céphalorachidien du patient, confirmant qu’un germe associé au porc avait envahi le système nerveux central. Après le traitement, l’état cognitif du patient s’est amélioré, mais il a été laissé avec une surdité sévère, une complication bien connue de cette infection. Ce cas clinique a offert aux scientifiques une opportunité rare : examiner l’ADN d’une souche d’origine humaine, nommée 366, et se demander ce que son génome peut expliquer sur son comportement dans l’organisme et sa réponse au traitement.
Quels médicaments fonctionnent encore — et lesquels non
En laboratoire, l’équipe a testé la réponse de la bactérie aux antibiotiques couramment utilisés. Ils ont constaté que la souche 366 restait sensible à plusieurs médicaments de première ligne, notamment la pénicilline, les céphalosporines et des agents de dernier recours comme les carbapénèmes et la vancomycine. En revanche, elle montrait une forte résistance à l’érythromycine, à la clindamycine et à la tétracycline — des médicaments largement employés en médecine humaine et vétérinaire. Lors de l’analyse du génome, les chercheurs ont identifié deux gènes de résistance, ermB et tet(O), qui modifient la machinerie de synthèse protéique de la bactérie de sorte que ces médicaments ne peuvent plus se fixer efficacement. Fait intéressant, ces gènes de résistance étaient intégrés au chromosome principal plutôt que sur des éléments d’ADN mobiles facilement transmissibles, ce qui suggère que la dissémination de la résistance de cette souche passe davantage par l’expansion de lignées bactériennes réussies que par un échange rapide de gènes.
Indices génétiques expliquant la capacité du germe à provoquer la maladie
Au-delà de la résistance aux médicaments, les investigateurs ont cherché ce qui permet à cette souche de survivre dans le sang et d’envahir le cerveau. En utilisant plusieurs grandes bases de référence, ils ont identifié quatre gènes clés liés à la virulence — la capacité à provoquer une maladie. Trois d’entre eux contribuent à la construction d’une capsule externe sucrée qui protège la bactérie contre la reconnaissance et la phagocytose par les cellules immunitaires, tandis que le quatrième aide le germe à s’attacher aux tissus de l’hôte. Des analyses à grande échelle de l’ensemble des gènes ont montré que beaucoup soutiennent des fonctions vitales de base telles que le métabolisme et la production de protéines, mais ont également mis en évidence des systèmes de transport qui déplacent nutriments, toxines et possiblement des médicaments à travers la membrane cellulaire. Une voie majeure, connue sous le nom de système de transporteurs ABC, s’est démarquée comme un point central pour l’importation de molécules utiles et l’exportation de substances nocives, potentiellement y compris des antibiotiques.
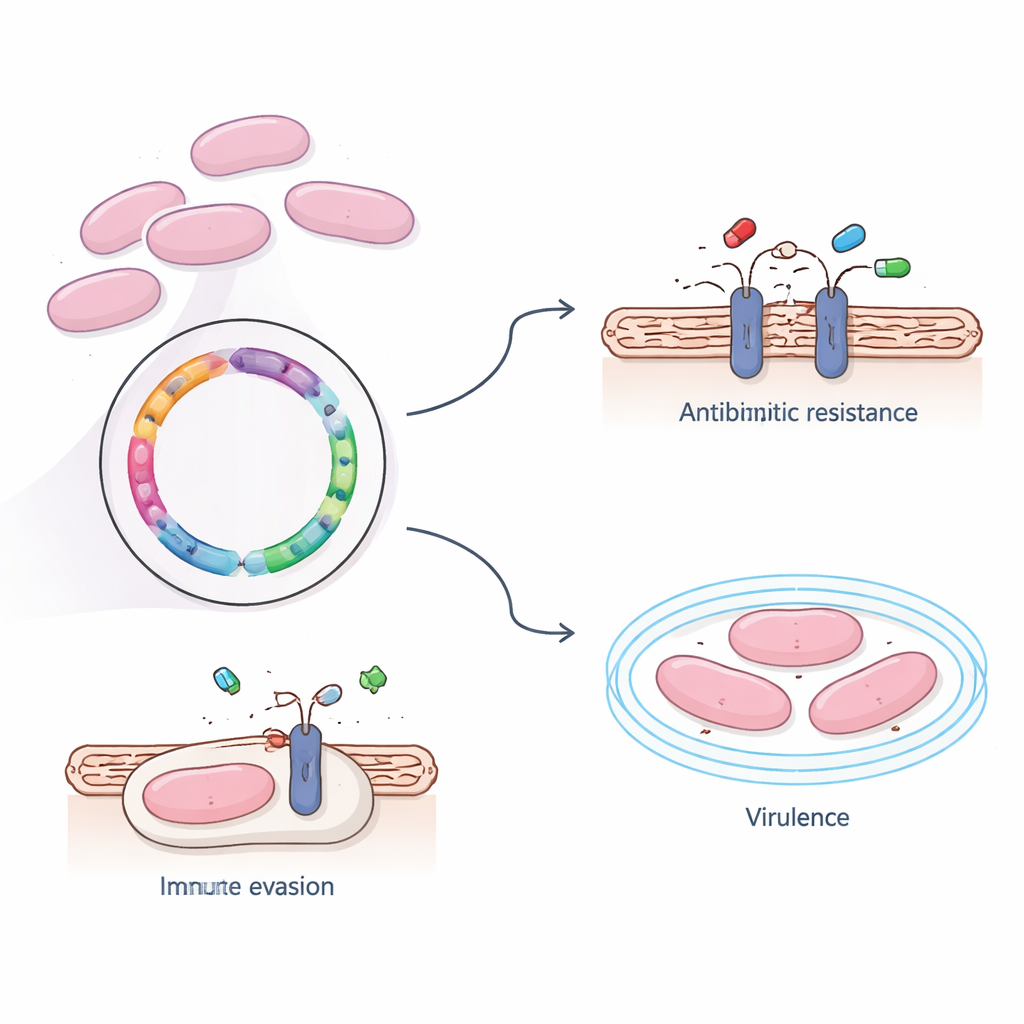
Liens de parenté entre souches dangereuses
Pour replacer la souche du patient dans un contexte plus large, l’équipe a comparé son génome à ceux de souches étroitement apparentées de S. suis provenant de porcs et d’humains dans différentes régions. Ils ont constaté que la souche 366 appartenait au type de séquence ST1, une lignée génétique déjà connue pour dominer les infections humaines. En construisant des arbres évolutifs à partir de milliers de petites différences d’ADN, ils ont montré que ST1 est étroitement lié à une autre lignée appelée ST7, qui a été associée à de grandes épidémies. L’analyse du pangenome — l’examen des gènes partagés ou uniques entre plusieurs souches — a révélé un large noyau de gènes communs entre ST1 et ST7, soutenant l’idée que les souches épidémiques ST7 ont évolué directement à partir d’un fond ST1 en acquérant du matériel génétique additionnel.
Ce que cela signifie pour la santé publique
En somme, les résultats dressent le portrait d’un germe porcino-adapté qui a franchi la barrière vers l’humain avec un dispositif lui permettant à la fois de survivre au traitement et de provoquer des maladies graves. La souche du patient porte une résistance stable, codée sur le chromosome, à plusieurs antibiotiques largement utilisés, ainsi que des gènes clés qui l’aident à échapper à l’attaque immunitaire et à adhérer aux tissus humains. Parallèlement, sa proche parenté génétique avec des souches associées à des épidémies indique que des variantes dangereuses peuvent émerger au sein d’un même arbre généalogique. En disséquant le génome d’un isolat clinique unique et bien documenté, cette étude approfondit notre compréhension du fonctionnement et de l’évolution de S. suis ST1, fournissant une base pour une meilleure surveillance, un usage plus judicieux des antibiotiques et des stratégies ciblées pour protéger tant les éleveurs que le grand public.
Citation: Jiang, J., Duan, W. & Liang, L. Genomic analysis of a clinical Streptococcus suis ST1 isolate from CSF reveals antimicrobial resistance, virulence, and an evolutionary link to ST7. Sci Rep 16, 11271 (2026). https://doi.org/10.1038/s41598-026-41475-6
Mots-clés: Streptococcus suis, méningite zoonotique, résistance aux antibiotiques, génomique bactérienne, transmission du porc à l’humain