Clear Sky Science · es
Análisis genómico de un aislamiento clínico de Streptococcus suis ST1 procedente del LCR revela resistencia antimicrobiana, virulencia y un vínculo evolutivo con ST7
Por qué un germen porcino importa a las personas
La mayoría de nosotros concebimos las infecciones en las granjas como un problema de los animales y no de los humanos. Pero algunos gérmenes pueden saltar de los cerdos a las personas y provocar enfermedades potencialmente mortales. Este estudio se centra en uno de esos bacterias, Streptococcus suis, que puede desencadenar meningitis grave y pérdida auditiva duradera. Al leer el plano genético completo de una cepa tomada directamente del líquido cefalorraquídeo de un paciente, los investigadores muestran cómo este germen resiste antibióticos clave, qué lo hace especialmente dañino y cómo está evolucionando junto a cepas relacionadas que han causado brotes mortales.

Un paciente, una punción lumbar y una amenaza oculta
La historia comienza con una persona ingresada en cuidados intensivos con meningitis purulenta, una infección cerebral grave. Los médicos aislaron S. suis del líquido cefalorraquídeo del paciente, confirmando que un germen asociado a cerdos había invadido el sistema nervioso central. Tras el tratamiento, la función cognitiva del paciente mejoró, pero quedó con una pérdida auditiva severa, una complicación bien conocida de esta infección. Este caso clínico real ofreció a los científicos una oportunidad poco frecuente: examinar el ADN de una cepa de origen humano, denominada 366, y preguntarse qué en su genoma podría explicar su comportamiento en el organismo y su respuesta al tratamiento.
Qué fármacos aún funcionan—y cuáles no
En el laboratorio, el equipo probó cómo respondía la bacteria a antibióticos de uso habitual. Encontraron que la cepa 366 seguía siendo vulnerable a varios fármacos de primera línea, incluidos la penicilina, las cefalosporinas y agentes de último recurso como los carbapenémicos y la vancomicina. Sin embargo, mostró una fuerte resistencia a la eritromicina, la clindamicina y la tetraciclina—medicamentos ampliamente usados tanto en medicina humana como veterinaria. Al escanear el genoma, los investigadores descubrieron dos genes de resistencia, ermB y tet(O), que alteran la maquinaria de síntesis proteica de la bacteria para que estos fármacos ya no se unan eficazmente. De forma interesante, estos genes de resistencia estaban integrados en el cromosoma principal en lugar de en elementos móviles de ADN fácilmente transferibles, lo que sugiere que la propagación de la resistencia en esta cepa ocurre más por la expansión de linajes bacterianos exitosos que por un intercambio rápido de genes.
Pistas genéticas sobre cómo el germen causa enfermedad
Más allá de la resistencia a fármacos, los investigadores indagaron qué hace que esta cepa sea tan capaz de sobrevivir en la sangre e invadir el cerebro. Usando varias grandes bases de referencia, identificaron cuatro genes clave vinculados con la virulencia—la capacidad de causar enfermedad. Tres de ellos contribuyen a formar una cápsula externa azucarada que protege a la bacteria de ser reconocida y fagocitada por las células inmunitarias, mientras que el cuarto ayuda al germen a adherirse a los tejidos del huésped. Los análisis a gran escala de todos los genes mostraron que muchos apoyan funciones vitales básicas como el metabolismo y la producción de proteínas, pero también destacaron sistemas de transporte que mueven nutrientes, toxinas y posiblemente fármacos a través de la membrana celular. Una vía principal, conocida como el sistema transportador ABC, destacó como un núcleo central para importar moléculas útiles y exportar las nocivas, potencialmente incluidos antibióticos.
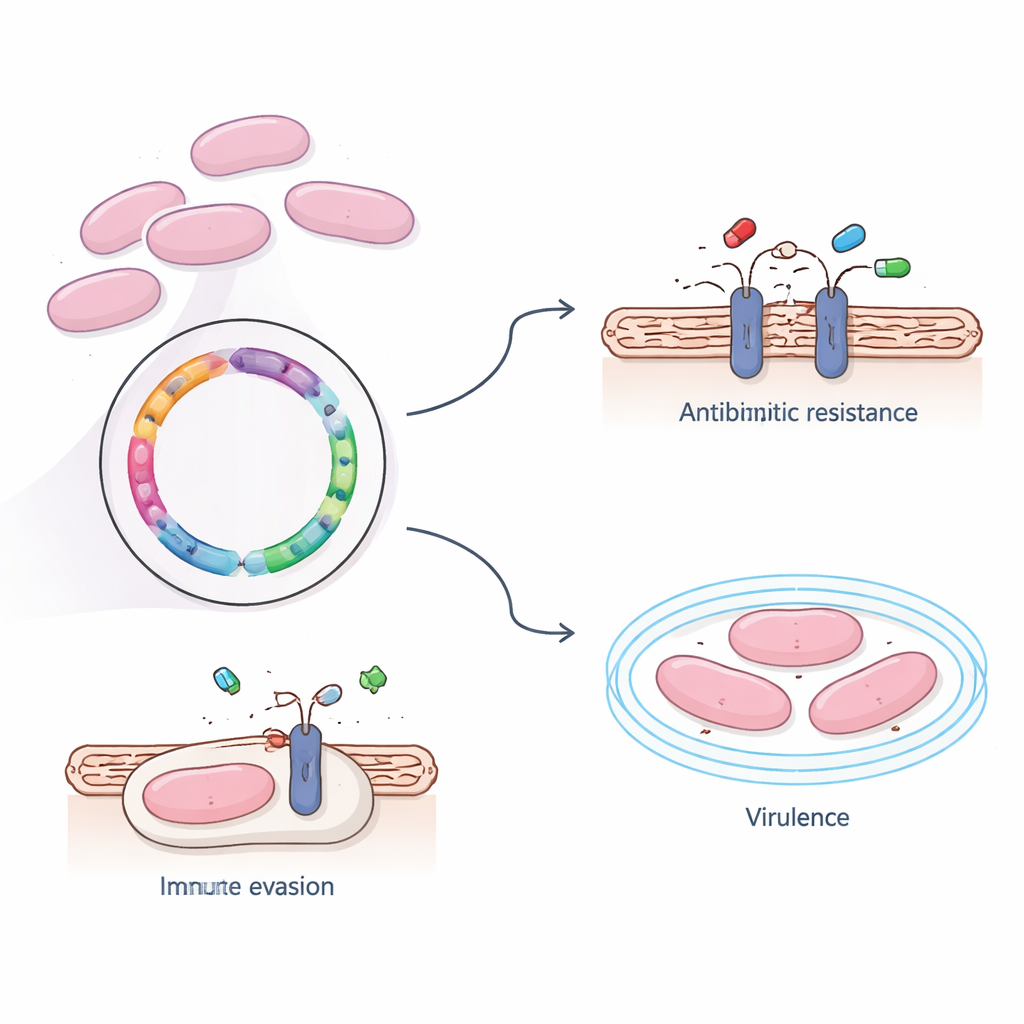
Lazos familiares entre cepas peligrosas
Para situar la cepa del paciente en un contexto más amplio, el equipo comparó su genoma con los de cepas de S. suis estrechamente relacionadas procedentes de cerdos y personas de distintas regiones. Encontraron que la cepa 366 pertenecía al tipo de secuencia ST1, un linaje genético ya conocido por dominar las infecciones humanas. Al construir árboles evolutivos usando miles de pequeñas diferencias en el ADN, demostraron que ST1 está estrechamente relacionado con otro linaje llamado ST7, que se ha asociado con grandes brotes. El análisis del pangenoma—que examina qué genes se comparten o son únicos entre múltiples cepas—reveló un gran núcleo de genes comunes entre ST1 y ST7, lo que respalda la idea de que las cepas epidémicas ST7 evolucionaron directamente a partir de un fondo ST1 mediante la adquisición de material genético adicional.
Qué significa esto para la salud pública
En conjunto, los hallazgos pintan el cuadro de un germen porcino altamente adaptado que ha saltado a humanos con un conjunto de herramientas tanto para sobrevivir al tratamiento como para causar enfermedad grave. La cepa del paciente porta resistencia estable, codificada en el cromosoma, a varios antibióticos de uso generalizado y genes clave que le permiten evadir el ataque inmune y adherirse a los tejidos humanos. Al mismo tiempo, su estrecha relación genética con cepas asociadas a brotes señala que variantes peligrosas pueden emerger dentro del mismo árbol familiar. Al diseccionar el genoma de un aislamiento clínico único y bien documentado, este estudio profundiza nuestra comprensión de cómo opera y evoluciona S. suis ST1, proporcionando una base para una mejor vigilancia, un uso más racional de antibióticos y estrategias más dirigidas para proteger tanto a agricultores como al público en general.
Cita: Jiang, J., Duan, W. & Liang, L. Genomic analysis of a clinical Streptococcus suis ST1 isolate from CSF reveals antimicrobial resistance, virulence, and an evolutionary link to ST7. Sci Rep 16, 11271 (2026). https://doi.org/10.1038/s41598-026-41475-6
Palabras clave: Streptococcus suis, meningitis zoonótica, resistencia a antibióticos, genómica bacteriana, infección de cerdo a humano