Clear Sky Science · sv
MIrROR release 02: Utökat och förfinat dataset för 16S-ITS-23S rRNA-operonet
Varför små mikrober spelar roll för oss
Mikrober påverkar vår hälsa, vår miljö och till och med klimatet, men att exakt identifiera vilka mikroskopiska arter som finns i ett jordprov, en flod eller människans tarm är överraskande svårt. Denna artikel introducerar en uppgraderad referensdatabas kallad MIrROR release 02, som hjälper forskare att läsa långa sträckor av mikrobiellt DNA mer precist så att de kan skilja åt nära besläktade arter och bättre förstå hur mikrobiella samhällen fungerar.
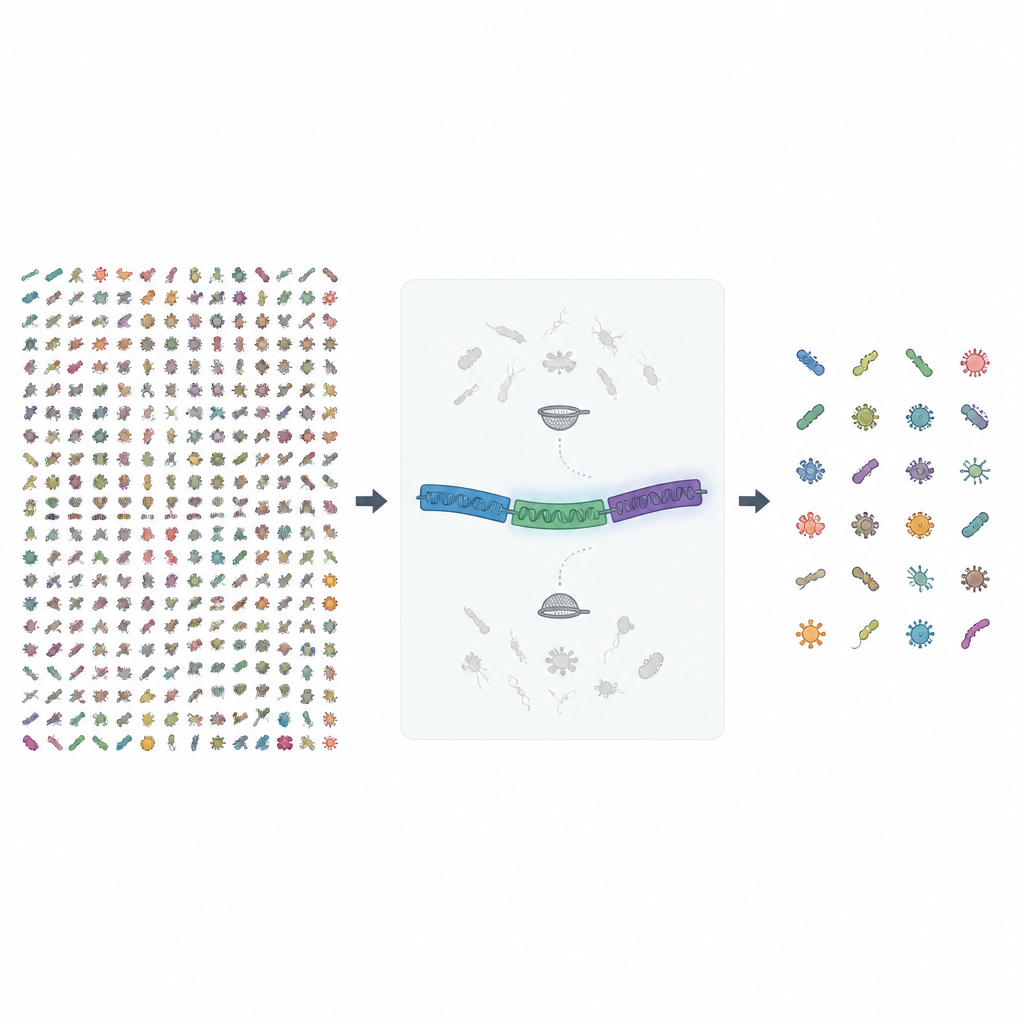
Att se bortom en enda genetisk ledstjärna
I årtionden har mikrobiologer förlitat sig på korta utdrag av en enda gen, känd som 16S rRNA, för att upptäcka och räkna bakterier och arkeéer i ett prov. Den metoden är snabb och billig, men den suddar ofta bilden och behandlar olika arter som om de vore samma. Även med nyare långläsningsmaskiner som kan läsa hela 16S-genen förblir vissa arter omöjliga att skilja åt eftersom denna gen är för lik mellan nära släktingar. MIrROR-projektet tar sig an detta genom att använda en längre DNA-sträcka som täcker hela rRNA-operonet, inklusive 16S, en spacer-region och en annan rRNA-gen kallad 23S, vilket ger många fler sekvensdetaljer för att skilja snarlika mikrober åt.
Att bygga en större och renare referenskarta
I denna nya release samlade författarna nästan 1,7 miljoner bakteriella och arkeala genom från ett offentligt arkiv och sökte igenom dem efter kompletta rRNA-operonsekvenser av rimlig längd. De körde sedan dessa råa sekvenser genom flera rundor av kvalitetskontroller. Genom utan tydliga artsnamn slängdes, exakta dubletter över arter togs bort och sekvenser med för många osäkra DNA-bokstäver filtrerades bort. Slutligen klustrades mycket lika sekvenser, och grupper som blandade arter granskades noggrant och rengjordes, inklusive manuella kontroller med jämförelse av sekvenser och byggande av fylogenetiska träd för att rensa ut kontamination.
Lägga till försummade grenar i livets träd
Ett stort framsteg i MIrROR release 02 är inkluderingen av arkeéer, en omfattande grupp mikrober som trivs i miljöer från heta källor till människans tarm. Datasetet täcker nu över tusen arkeala arter, bland dem medicinskt och industriellt viktiga organismer. Samtidigt uppdaterade författarna namnen och grupperingarna av många mikrober med hjälp av en modern genom-baserad taxonomi. Denna omklassificering påverkade ungefär hälften av alla genom i datasetet och förde in nästan nitton tusen ytterligare bakteriella arter, inklusive sällsynta miljömikrober, kliniskt relevanta patogener och arter viktiga inom bioteknik och livsmedelsproduktion.
Göra långläsningsundersökningar användbara i verkliga och testade samhällen
För att visa att det utökade datasetet inte bara är större utan också mer användbart testade teamet det på både laboratorieframställda och datorgenererade mikrobblandningar. De jämförde MIrROR release 02 med tidigare MIrROR-data och med andra vanliga referenssamlingar. I kontrollerade tester var det nya datasetet bättre på att peka ut arter, inklusive sådana som äldre dataset helt missade, som en viss Prevotella-art i en tarmstandard. När arkeala arter lades till i en simulerad tarmgemenskap kunde den nya MIrROR-versionen upptäcka och klassificera dem både på släkte- och artnivå, medan en ofta använd 16S-endast-referens ofta gav vaga etiketter som oförklarade bakterier och hade svårt att tilldela läsningar till rätt art.
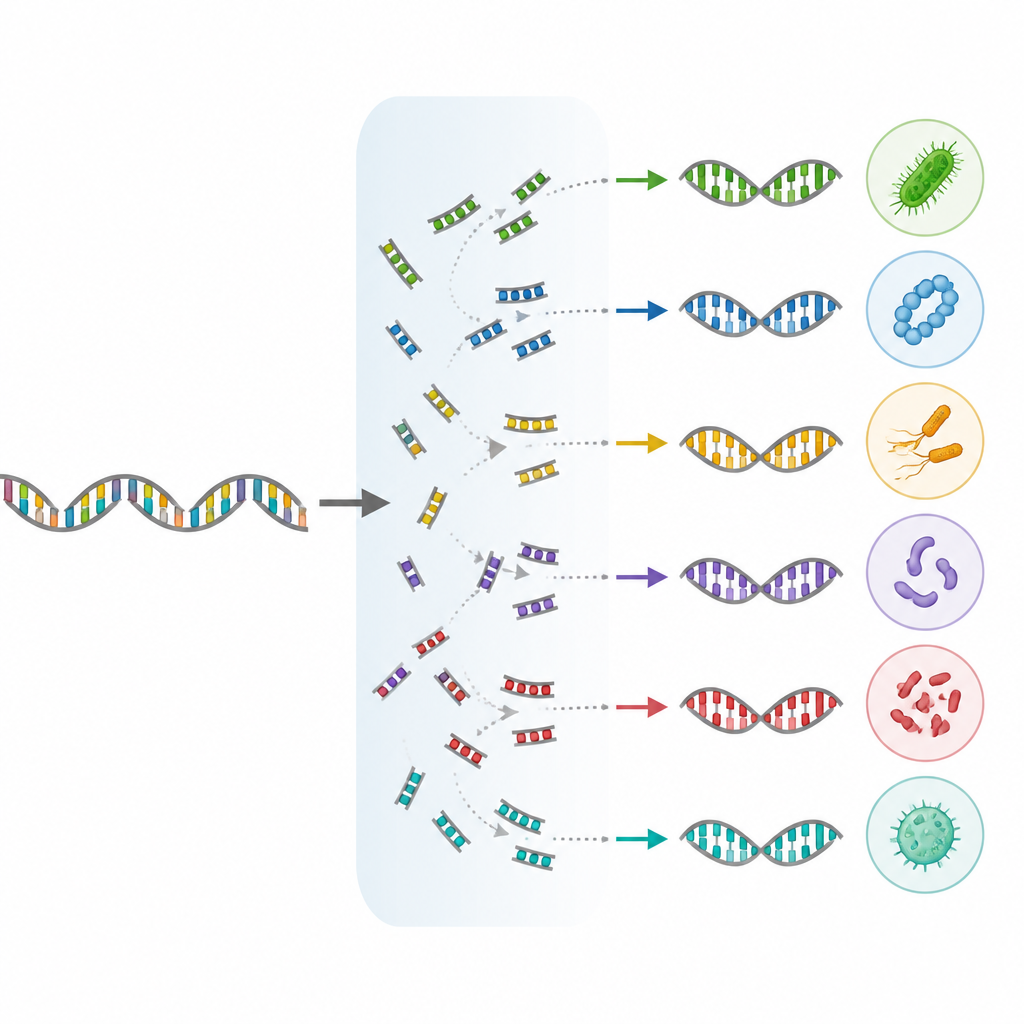
Hjälpa forskare att välja rätt verktyg
Eftersom långläsningssekvensering förlitar sig på specifika DNA-startpunkter kallade primrar, testade författarna också olika primerpar i datorsimuleringar för att se vilka som bäst kunde fånga både bakterier och arkeéer över hela operonet. De rekommenderar två primerset som hittar en balans mellan bred täckning och kompatibilitet med långläsningsplattformar. Samtidigt pekar de på kända biologiska egenheter, såsom mikrober som har orelaterade rRNA-gener eller flera något olika kopior, vilket kan snedvrida räkningar och måste beaktas vid tolkning av samhällsdata.
Vad detta betyder för vardagliga frågor
Enkelt uttryckt är MIrROR release 02 en mycket större, bättre organiserad adressbok för mikrober, byggd för att fungera med modern långläsande DNA-sekvensering. Den låter forskare skilja likartade arter mer pålitligt, inkludera arkeéer i sina undersökningar och jämföra resultat över olika studier med större förtroende. Även om den inte tar bort alla utmaningar i att läsa mikrobiella samhällen ger den forskare en skarpare lins för att utforska hur mikrober påverkar människors hälsa, ekosystem och industriella processer.
Citering: Lee, J., Hong, J., Seol, D. et al. MIrROR release 02: Expanded and refined 16S-ITS-23S rRNA operon dataset. Sci Data 13, 714 (2026). https://doi.org/10.1038/s41597-026-06729-y
Nyckelord: mikrobiom, rRNA-operon, långläsningssekvensering, mikrobiell taxonomi, arkeéer