Clear Sky Science · es
MIrROR versión 02: Conjunto de datos ampliado y refinado del operón rRNA 16S-ITS-23S
Por qué nos importan los microbios diminutos
Los microbios moldean nuestra salud, nuestro entorno e incluso el clima, pero identificar con precisión qué especies microscópicas están presentes en una muestra de suelo, un río o el intestino humano resulta sorprendentemente difícil. Este artículo presenta un conjunto de referencia mejorado llamado MIrROR versión 02, que ayuda a los científicos a leer tramos largos de ADN microbiano con más precisión para distinguir especies estrechamente relacionadas y comprender mejor cómo funcionan las comunidades microbianas.
Mirar más allá de un único punto genético
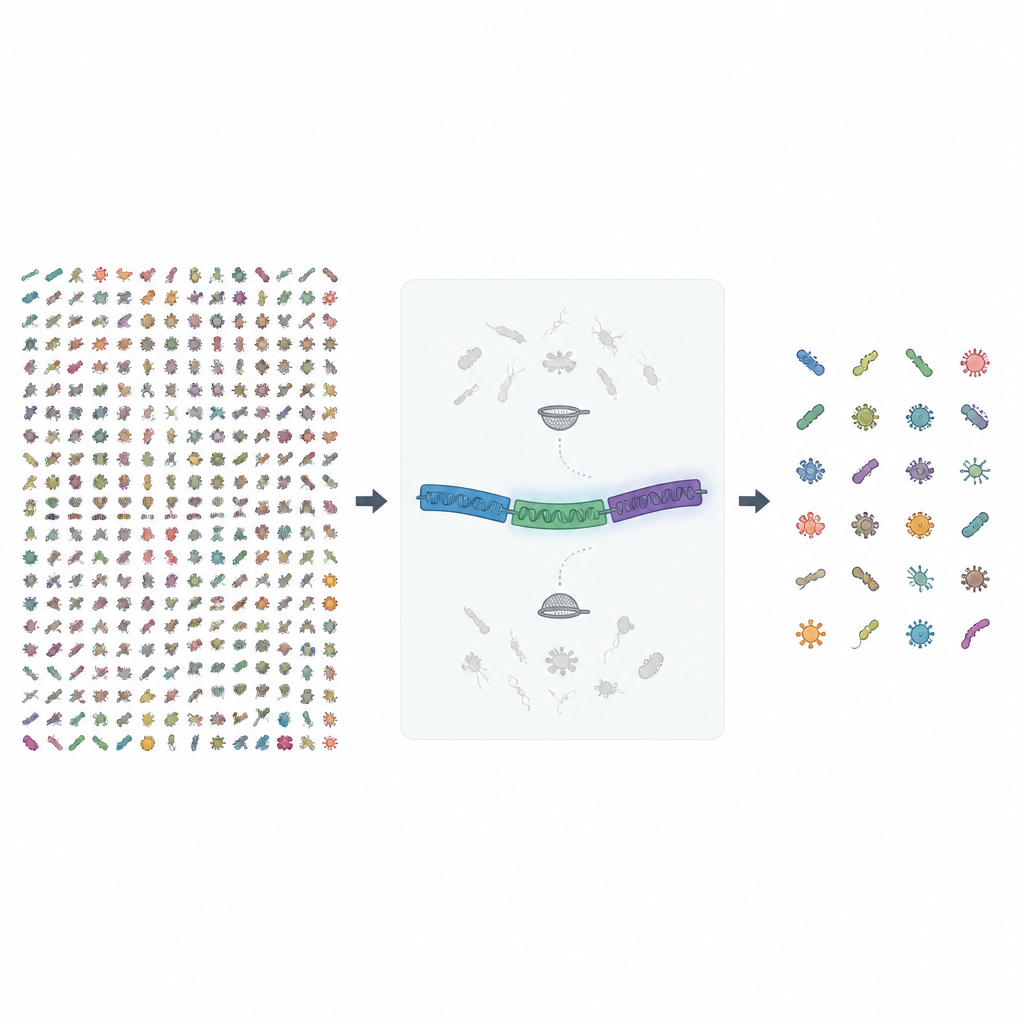
Durante años, los microbiólogos han confiado en fragmentos cortos de un solo gen, conocido como 16S rRNA, para detectar y cuantificar bacterias y arqueas en una muestra. Ese método es rápido y barato, pero a menudo empapa la imagen, tratando especies distintas como si fueran la misma. Incluso con las nuevas máquinas de secuenciación de lecturas largas que pueden leer el 16S completo, algunas especies siguen siendo indistinguibles porque este gen es demasiado similar entre parientes cercanos. El proyecto MIrROR aborda esto usando un tramo más largo de ADN que cubre el operón rRNA completo, incluyendo 16S, una región espaciadora y otro gen rRNA llamado 23S, proporcionando muchos más detalles de secuencia para separar microbios semejantes.
Construir un mapa de referencia mayor y más limpio
En esta nueva versión, los autores recopilaron casi 1,7 millones de genomas bacterianos y arqueales de un archivo público y los buscaron para encontrar secuencias completas del operón rRNA de longitud razonable. Luego sometieron estas secuencias crudas a varias rondas de controles de calidad. Se descartaron genomas sin nombres de especie claros, se eliminaron duplicados exactos entre especies y se filtraron secuencias con demasiadas letras de ADN inciertas. Finalmente, se agruparon secuencias altamente similares y se inspeccionaron y limpiaron cuidadosamente los grupos que mezclaban especies, incluyendo comprobaciones manuales con herramientas de comparación de secuencias y construcción de árboles evolutivos para eliminar contaminación.
Añadir ramas descuidadas del árbol de la vida
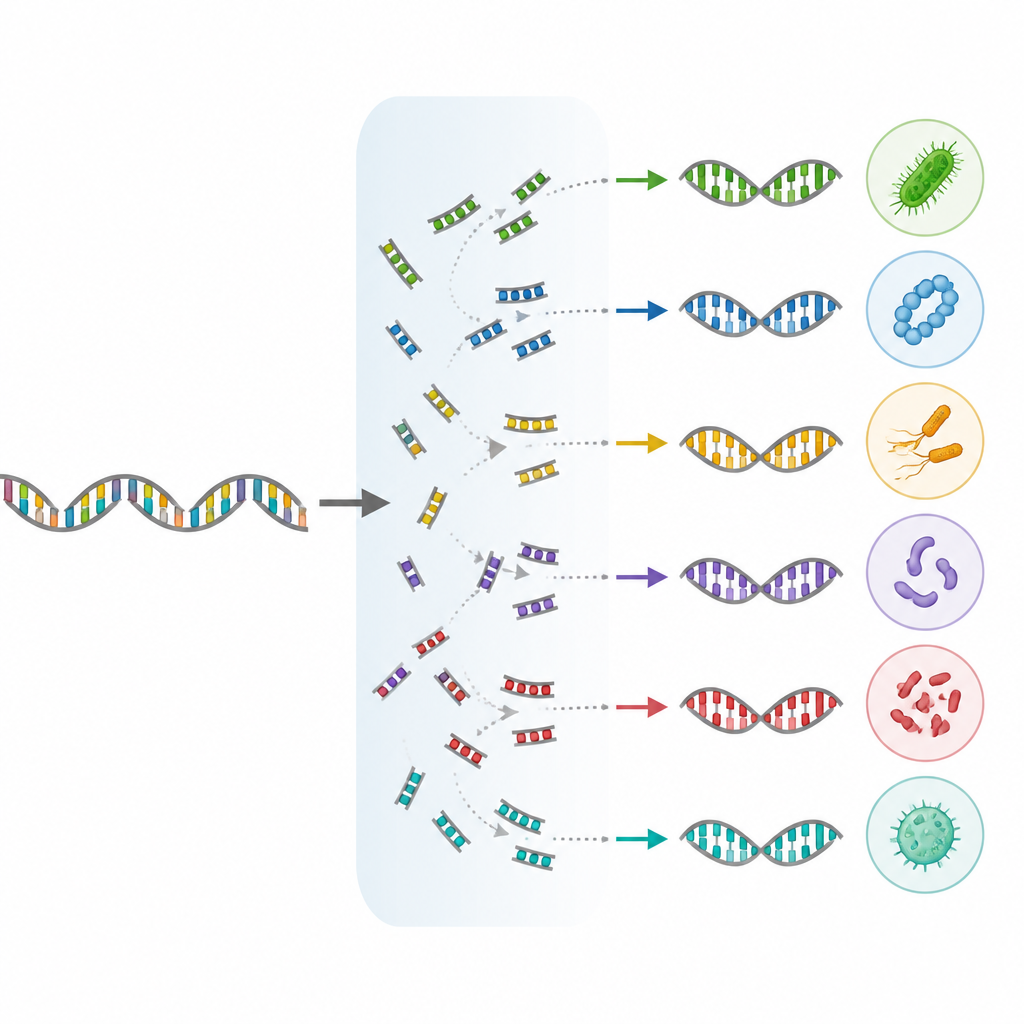
Un avance importante en MIrROR versión 02 es la inclusión de las arqueas, un amplio grupo de microbios que prosperan en entornos que van desde manantiales termales hasta el intestino humano. El conjunto de datos ahora cubre más de mil especies arqueales, entre ellas organismos de importancia médica e industrial. Al mismo tiempo, los autores actualizaron los nombres y agrupamientos de muchos microbios utilizando una taxonomía moderna basada en genomas. Esta reclasificación afectó aproximadamente a la mitad de todos los genomas del conjunto y añadió casi diecinueve mil especies bacterianas adicionales, incluidas microbianas ambientales raras, patógenos clínicamente relevantes y especies importantes en biotecnología y producción alimentaria.
Hacer que los estudios con lecturas largas funcionen en comunidades reales y de prueba
Para demostrar que el conjunto ampliado no es solo más grande sino más útil, el equipo lo evaluó en mezclas microbianas hechas en laboratorio y simuladas por ordenador. Compararon MIrROR versión 02 con datos de MIrROR anteriores y con otras colecciones de referencia comunes. En pruebas controladas, el nuevo conjunto fue mejor identificando especies, incluidas algunas que los conjuntos antiguos no detectaron en absoluto, como una especie particular de Prevotella en un estándar de comunidad intestinal. Cuando se añadieron especies arqueales a una comunidad intestinal simulada, la nueva versión de MIrROR pudo detectarlas y clasificarlas a niveles de género y especie, mientras que una referencia ampliamente usada basada solo en 16S a menudo producía etiquetas vagas como bacterias sin identificar y tenía dificultades para asignar lecturas a la especie correcta.
Ayudar a los científicos a elegir las herramientas adecuadas
Dado que la secuenciación de lecturas largas depende de puntos de inicio de ADN específicos llamados cebadores, los autores también comprobaron distintos pares de cebadores en simulaciones informáticas para ver cuáles podían capturar mejor tanto bacterias como arqueas a lo largo del operón completo. Recomiendan dos conjuntos de cebadores que equilibran amplia cobertura y compatibilidad con plataformas de lecturas largas. Al mismo tiempo, señalan peculiaridades biológicas conocidas, como microbios que mantienen sus genes rRNA no enlazados o en varias copias ligeramente diferentes, lo que puede sesgar los recuentos y debe tenerse en cuenta al interpretar datos comunitarios.
Qué significa esto para preguntas cotidianas
En términos simples, MIrROR versión 02 es una agenda mucho más grande y mejor organizada de microbios, diseñada para funcionar con la secuenciación de ADN de lecturas largas moderna. Permite a los científicos separar especies parecidas con más fiabilidad, incluir arqueas en sus estudios y comparar resultados entre diferentes trabajos con mayor confianza. Aunque no elimina todos los desafíos en la interpretación de comunidades microbianas, ofrece a los investigadores una lente más nítida para explorar cómo los microbios influyen en la salud humana, los ecosistemas y los procesos industriales.
Cita: Lee, J., Hong, J., Seol, D. et al. MIrROR release 02: Expanded and refined 16S-ITS-23S rRNA operon dataset. Sci Data 13, 714 (2026). https://doi.org/10.1038/s41597-026-06729-y
Palabras clave: microbioma, operón rRNA, secuenciación de lecturas largas, taxonomía microbiana, arqueas