Clear Sky Science · pl
Wydanie MIrROR 02: Rozszerzony i dopracowany zestaw danych operonu rRNA 16S-ITS-23S
Dlaczego drobne mikroby mają dla nas znaczenie
Mikroby kształtują nasze zdrowie, środowisko, a nawet klimat, jednak dokładne rozpoznanie, które mikroskopijne gatunki występują w próbce gleby, rzece czy jelicie ludzkim, bywa zaskakująco trudne. Niniejszy tekst przedstawia zaktualizowany zestaw referencyjny o nazwie MIrROR wydanie 02, który pomaga naukowcom dokładniej odczytywać długie fragmenty DNA mikroorganizmów, by rozróżniać blisko spokrewnione gatunki i lepiej rozumieć funkcjonowanie społeczności mikrobiologicznych.
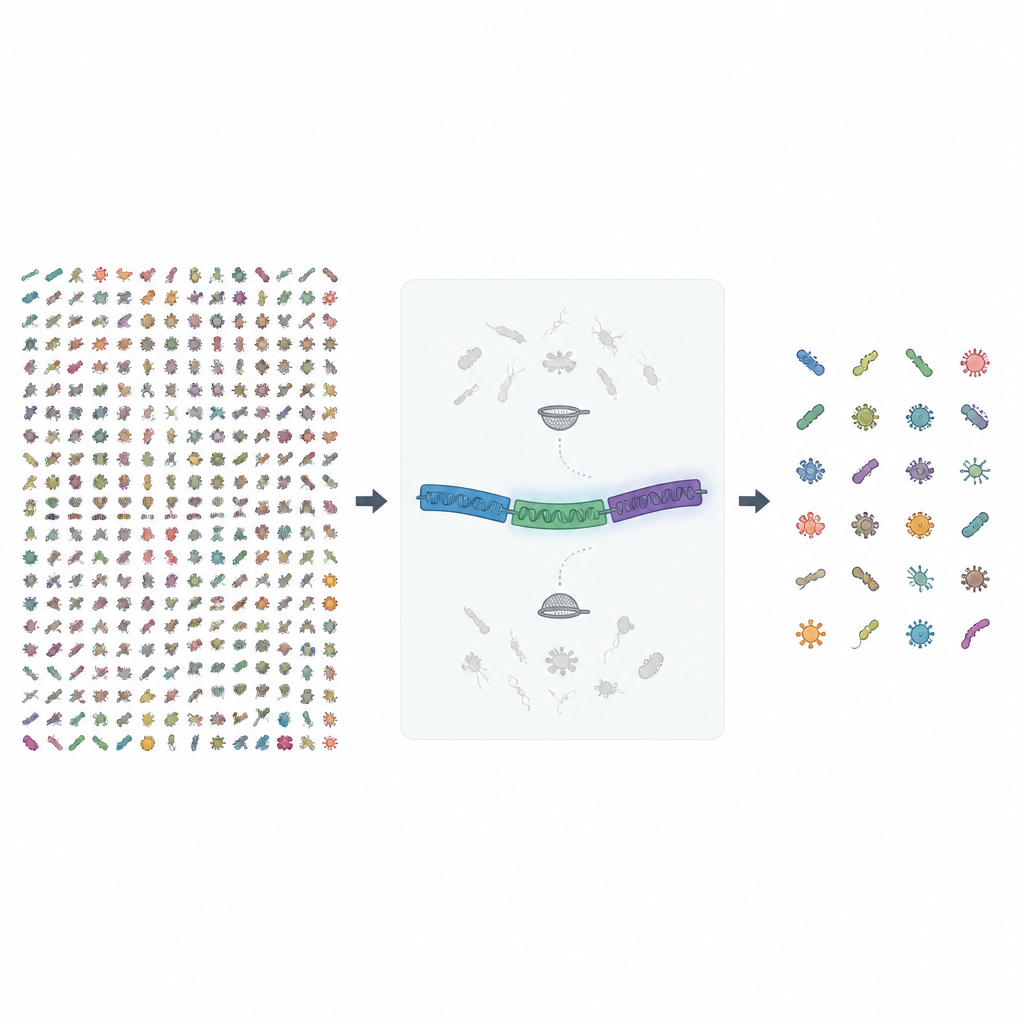
Patrząc poza jedną genetyczną latarnię
Przez lata mikrobiolodzy polegali na krótkich fragmentach pojedynczego genu, znanego jako 16S rRNA, by wykrywać i zliczać bakterie oraz archeony w próbce. Ta metoda jest szybka i tania, ale często zaciera obraz, traktując różne gatunki jak ten sam. Nawet przy nowszych urządzeniach do sekwencjonowania długich odczytów, które mogą czytać pełen gen 16S, niektóre gatunki pozostają nierozróżnialne, ponieważ ten gen jest zbyt podobny u bliskich krewniaków. Projekt MIrROR rozwiązuje to, korzystając z dłuższego fragmentu DNA obejmującego cały operon rRNA — włącznie z 16S, regionem spacera oraz drugim genem rRNA zwanym 23S — co dostarcza znacznie więcej szczegółów sekwencyjnych umożliwiających rozdzielenie podobnych mikroorganizmów.
Budowanie większej i czystszej mapy referencyjnej
W tym wydaniu autorzy zgromadzili prawie 1,7 miliona genomów bakterii i archeonów z publicznego archiwum i przeszukali je w poszukiwaniu kompletnych sekwencji operonu rRNA o odpowiedniej długości. Następnie surowe sekwencje poddali kilku turam kontroli jakości. Genomy bez wyraźnych nazw gatunkowych zostały odrzucone, dokładne duplikaty między gatunkami usunięto, a sekwencje zbyt dużą liczbą niepewnych znaków DNA przefiltrowano. W końcu bardzo podobne sekwencje zgrupowano, a zbiory mieszane gatunkowo starannie przejrzano i oczyszczono, w tym ręcznie sprawdzono porównania sekwencji oraz budowę drzew filogenetycznych, aby wyeliminować zanieczyszczenia.
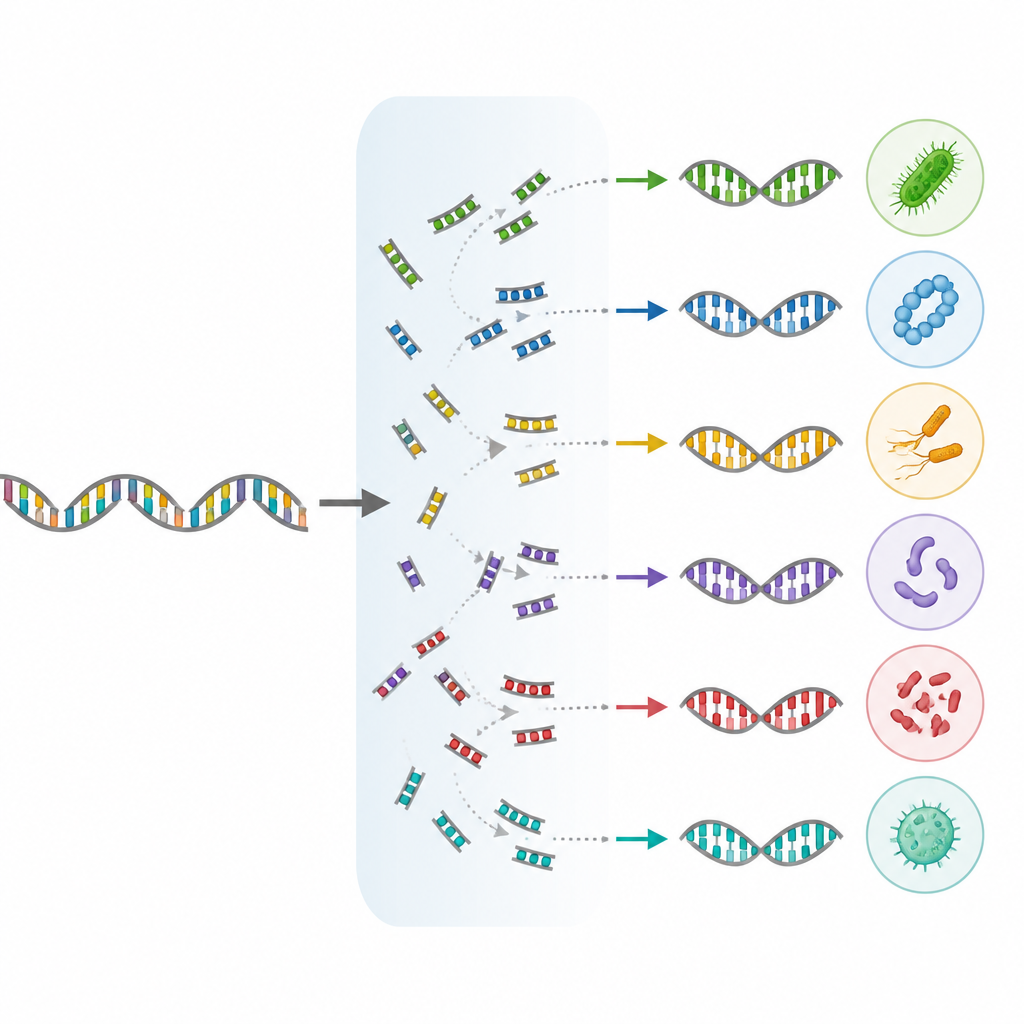
Dodawanie zaniedbanych gałęzi drzewa życia
Głównym postępem w wydaniu MIrROR 02 jest włączenie archeonów — szerokiej grupy drobnoustrojów, które prosperują w środowiskach od gorących źródeł po jelito ludzkie. Zestaw danych obejmuje teraz ponad tysiąc gatunków archeonów, w tym organizmy o znaczeniu medycznym i przemysłowym. Jednocześnie autorzy zaktualizowali nazewnictwo i grupowania wielu mikrobów, korzystając z nowoczesnej taksonomii opartej na genomach. Reklasyfikacja objęła około połowy genomów w zbiorze i dodała prawie dziewiętnaście tysięcy dodatkowych gatunków bakterii, w tym rzadkie mikroby środowiskowe, patogeny istotne klinicznie oraz gatunki ważne w biotechnologii i produkcji żywności.
Sprawianie, by badania długich odczytów działały w rzeczywistych i testowych społecznościach
Aby pokazać, że rozszerzony zestaw nie jest jedynie większy, ale i bardziej użyteczny, zespół przetestował go na mieszankach mikrobiologicznych przygotowanych w laboratorium oraz symulacjach komputerowych. Porównali wydanie MIrROR 02 z wcześniejszymi danymi MIrROR oraz z innymi powszechnymi kolekcjami referencyjnymi. W kontrolowanych testach nowy zestaw lepiej wskazywał gatunki, w tym takie, które wcześniejsze zbiory zupełnie pomijały, jak pewien gatunek Prevotella w standardzie społeczności jelitowej. Po dodaniu gatunków archeonów do symulowanej społeczności jelitowej nowa wersja MIrROR potrafiła wykrywać i klasyfikować je zarówno na poziomie rodzaju, jak i gatunku, podczas gdy powszechnie używana referencja ograniczona do 16S często dawała nieprecyzyjne określenia typu "nieokreślone bakterie" i miała trudności z przypisaniem odczytów do właściwych gatunków.
Pomoc naukowcom w wyborze właściwych narzędzi
Ponieważ sekwencjonowanie długich odczytów zależy od specyficznych punktów startowych DNA zwanych primerami, autorzy przetestowali różne pary primerów w symulacjach komputerowych, aby sprawdzić, które najlepiej uchwycą bakterie i archeony na całym operonie. Zalecają dwa zestawy primerów, które równoważą szerokie pokrycie i zgodność z platformami długich odczytów. Jednocześnie wskazują znane biologiczne osobliwości, takie jak mikroby mające niezwiązane ze sobą geny rRNA lub występujące w wielu lekko różnych kopiach, co może zniekształcać liczby i należy mieć to na uwadze przy interpretacji danych o społecznościach.
Co to oznacza dla codziennych pytań
Mówiąc prostymi słowami, MIrROR wydanie 02 to znacznie większa, lepiej zorganizowana książka adresowa mikroorganizmów, stworzona do pracy z nowoczesnym sekwencjonowaniem długich odczytów DNA. Umożliwia naukowcom niezawodniejsze rozdzielanie podobnych gatunków, włączanie archeonów do badań oraz porównywanie wyników między różnymi badaniami z większą pewnością. Choć nie usuwa wszystkich wyzwań związanych z odczytywaniem społeczności mikrobiologicznych, daje badaczom ostrzejsze narzędzie do badania, jak mikroby wpływają na zdrowie człowieka, ekosystemy i procesy przemysłowe.
Cytowanie: Lee, J., Hong, J., Seol, D. et al. MIrROR release 02: Expanded and refined 16S-ITS-23S rRNA operon dataset. Sci Data 13, 714 (2026). https://doi.org/10.1038/s41597-026-06729-y
Słowa kluczowe: mikrobiom, operon rRNA, długie sekwencjonowanie odczytów, taksonomia mikrobiologiczna, archeony