Clear Sky Science · ja
MIrROR リリース02:拡張・精緻化された16S-ITS-23S rRNAオペロンデータセット
なぜ微小な微生物が私たちに重要なのか
微生物は私たちの健康や環境、さらには気候にも影響を与えますが、土壌、河川、あるいはヒト腸内のサンプルにどの微細な種が存在するかを正確に特定するのは意外と難しい作業です。本稿では、長鎖の微生物DNAをより精確に読み取れるようにして近縁種を見分け、微生物群集の機能をよりよく理解するための参照データセット、MIrROR リリース02を紹介します。
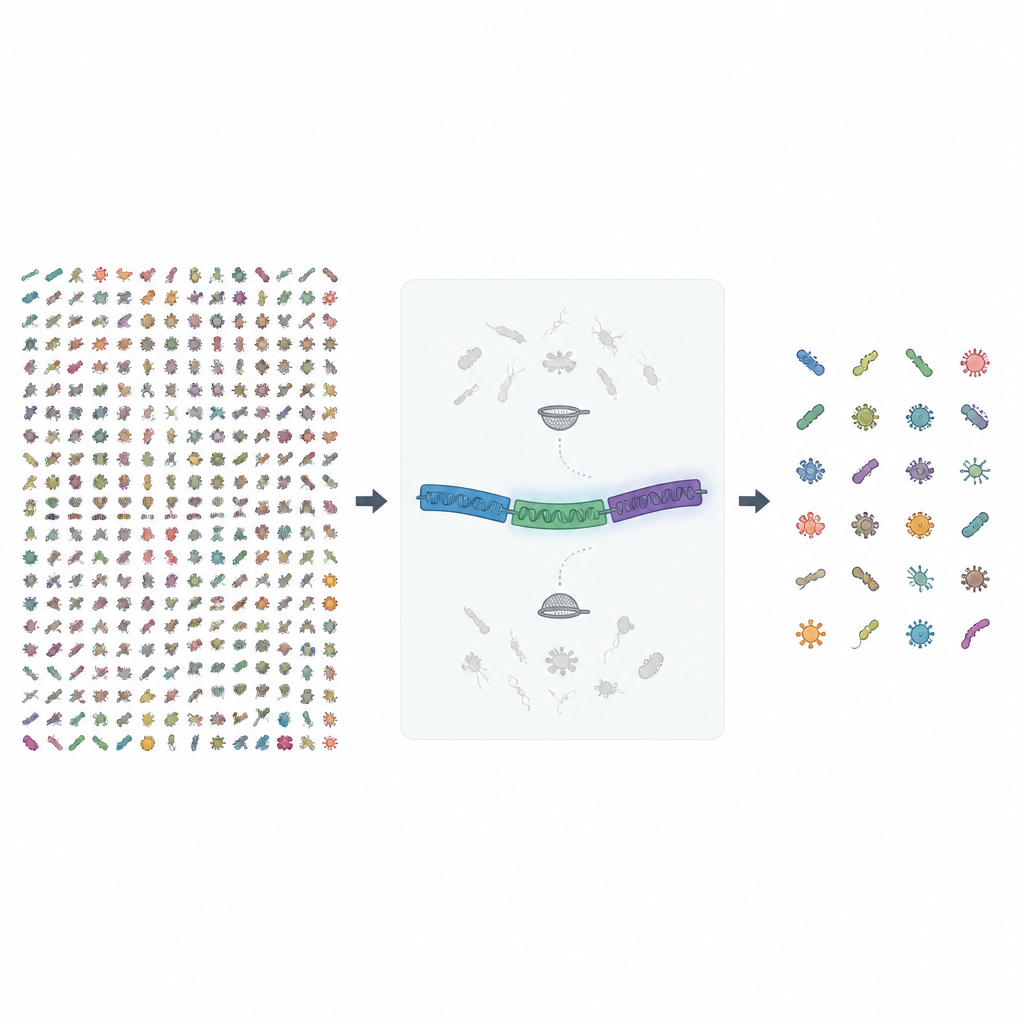
単一の遺伝的目印を超えて見る
これまで微生物学者は、16S rRNAとして知られる単一遺伝子の短い断片に頼って、サンプル中の細菌や古細菌を検出・計数してきました。この方法は速く安価ですが、異なる種を同一視してしまうなど、しばしば画像をぼやけさせます。完全な16S遺伝子を読めるようになった新しいロングリードシーケンサでも、近縁種間ではこの遺伝子だけでは判別できない場合があります。MIrRORプロジェクトは、16Sに加えスペーサー領域やもう一つのrRNA遺伝子である23Sを含む完全なrRNAオペロンという、より長いDNA領域を用いることで、似た微生物を見分けるためのはるかに多くの配列情報を提供します。
より大きく、より精錬された参照地図の構築
この新しいリリースでは、著者らは公共アーカイブから約170万件の細菌・古細菌ゲノムを収集し、適切な長さの完全なrRNAオペロン配列を検索しました。得られた生の配列は複数段階の品質チェックにかけられました。明確な種名のないゲノムは除外され、種間で重複する完全一致配列は削除され、不確かな塩基(不明文字)が多い配列はフィルタリングされました。最後に高い類似性を持つ配列はクラスタ化され、種が混在するグループは配列比較や系統樹作成ツールによる手動検査を含めて慎重に精査・除去され、汚染を排除しました。
生命の木の見落とされていた枝を加える
MIrROR リリース02の大きな進歩は、古細菌(アーキア)の包含です。古細菌は温泉からヒト腸内まで多様な環境で生息する広範な微生物群であり、本データセットは現在1000種を超える古細菌をカバーしています。その中には医療や産業で重要な種も含まれます。同時に、著者らは最新のゲノムベースの分類法を用いて多くの微生物の名前とグルーピングを更新しました。この再分類はデータセット中のゲノムのおよそ半数に影響を与え、希少な環境微生物、臨床的に重要な病原体、バイオテクノロジーや食品生産に重要な種を含む約1万9千種の細菌種を新たに組み込みました。
実試料とテスト群でロングリード調査を実用化する
拡張データセットが単に大きくなっただけでなく有用であることを示すため、チームは実験室で作成した混合コミュニティとコンピュータでシミュレートした混合物の両方でテストを行いました。MIrROR リリース02を従来のMIrRORデータや他の一般的な参照コレクションと比較したところ、管理されたテストでは新しいデータセットが種の同定に優れており、従来のデータが完全に見逃していた種(例えば腸内群集の標準に含まれる特定のPrevotella種など)も特定できました。古細菌種を模擬腸内群集に加えた場合、新しいMIrRORは属および種レベルでそれらを検出・分類できましたが、16Sのみの広く使われる参照は『不明な細菌』のような曖昧なラベルをしばしば返し、リードを正しい種に割り当てるのに苦労しました。
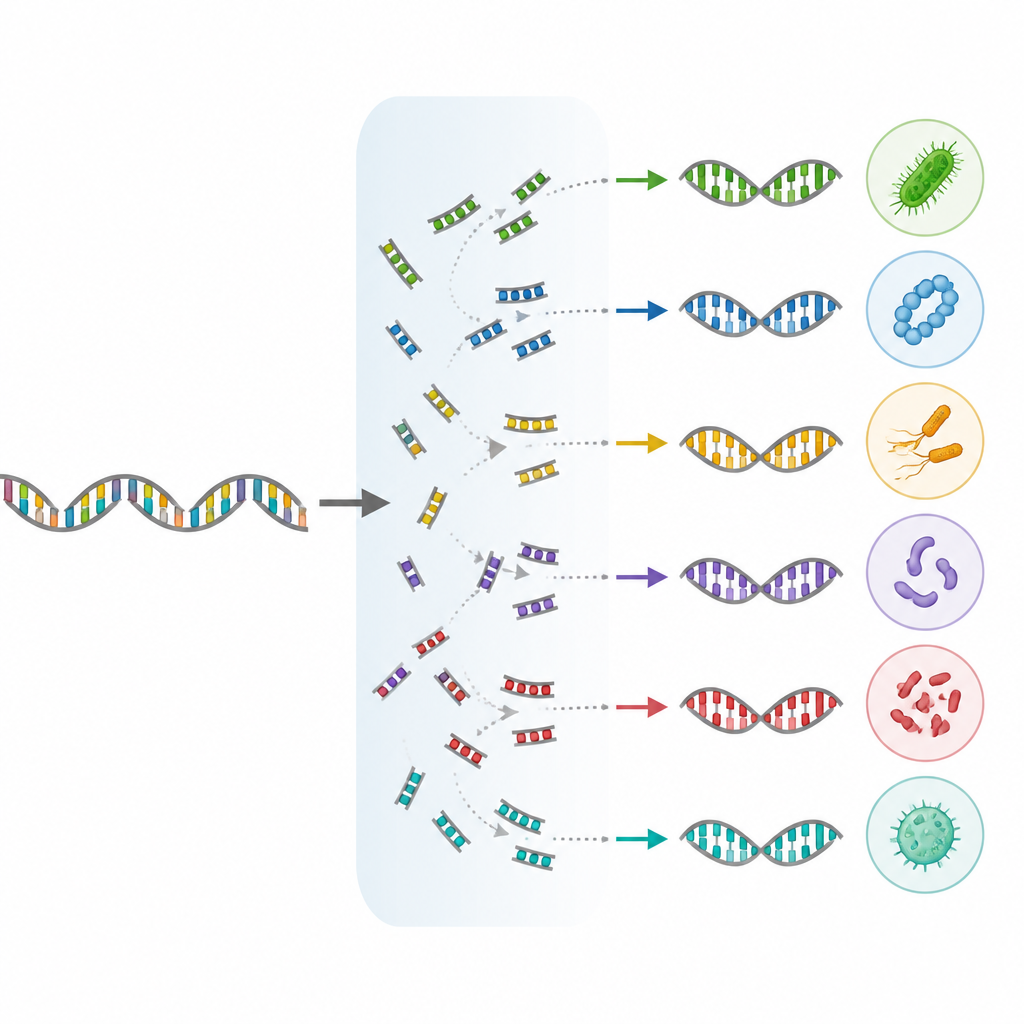
研究者が適切なツールを選ぶ手助け
ロングリードシーケンシングはプライマーと呼ばれる特定のDNA開始点に依存するため、著者らはコンピュータシミュレーションで異なるプライマー対を検証し、オペロン全体で細菌と古細菌の両方を最も広く捉えられるものを調べました。彼らは広いカバレッジとロングリードプラットフォームとの互換性のバランスが取れた2つのプライマーセットを推奨しています。同時に、rRNA遺伝子が連結されていなかったり、わずかに異なるコピーを複数持つ微生物のような既知の生物学的特性が、カウントに偏りをもたらす可能性があり、群集データを解釈する際には留意が必要であることも指摘しています。
日常的な問いへの意味
簡単に言えば、MIrROR リリース02はモダンなロングリードDNAシーケンシングと連携するために作られた、はるかに大きく整理された微生物の住所録です。これにより研究者は類似した種をより確実に分離でき、古細菌を調査に含められ、異なる研究間で結果をより自信を持って比較できるようになります。微生物群集を読み解く上でのすべての課題がなくなるわけではありませんが、ヒトの健康、エコシステム、産業プロセスにおける微生物の影響を探るためのより鋭いレンズを研究者に提供します。
引用: Lee, J., Hong, J., Seol, D. et al. MIrROR release 02: Expanded and refined 16S-ITS-23S rRNA operon dataset. Sci Data 13, 714 (2026). https://doi.org/10.1038/s41597-026-06729-y
キーワード: マイクロバイオーム, rRNAオペロン, ロングリードシーケンシング, 微生物分類学, 古細菌