Clear Sky Science · it
MIrROR release 02: Dataset espanso e perfezionato dell’operone rRNA 16S-ITS-23S
Perché i microbe minuscoli contano per noi
I microbi influenzano la nostra salute, il nostro ambiente e persino il clima, ma identificare esattamente quali specie microscopiche sono presenti in un campione di suolo, in un fiume o nell’intestino umano è sorprendentemente difficile. Questo articolo presenta un dataset di riferimento aggiornato chiamato MIrROR release 02, che aiuta gli scienziati a leggere tratti lunghi di DNA microbico con maggiore precisione, permettendo di distinguere specie strettamente correlate e comprendere meglio il funzionamento delle comunità microbiche.
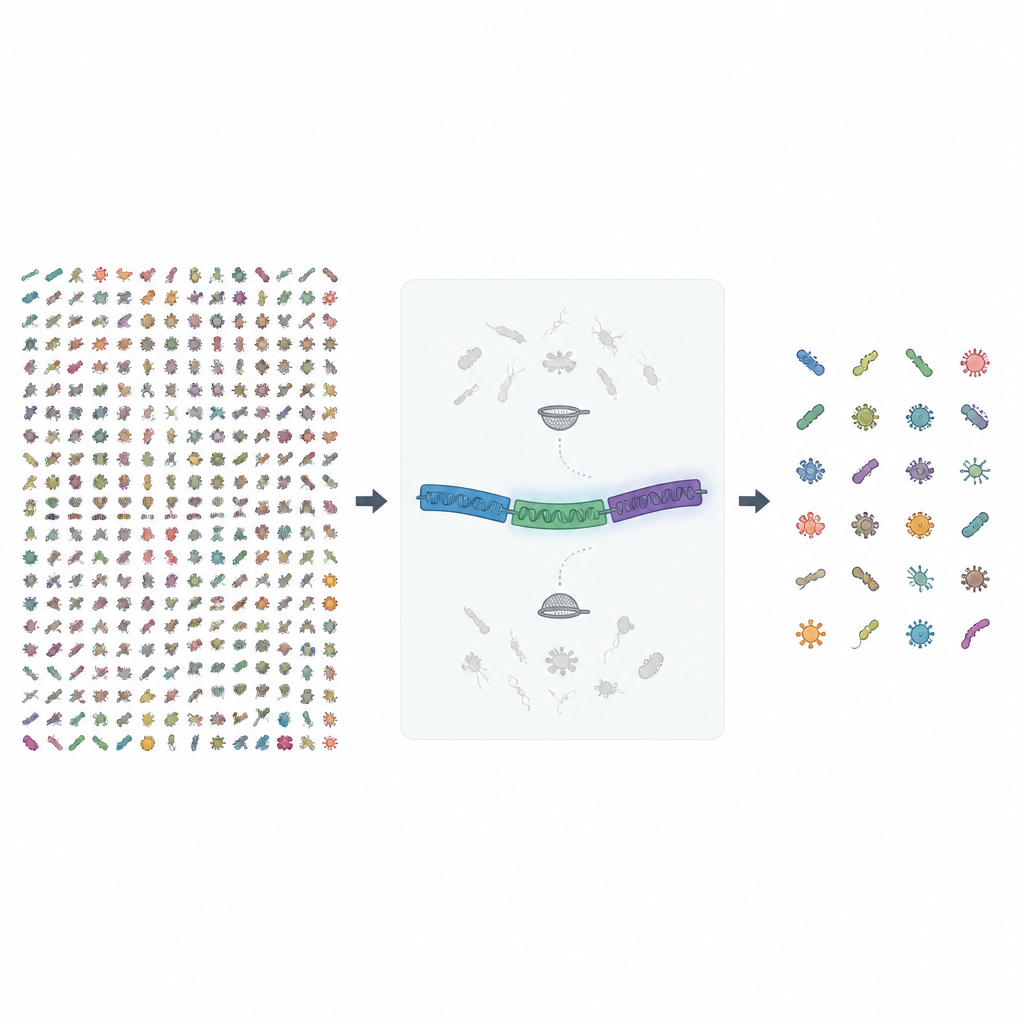
Guardare oltre un singolo punto di riferimento genetico
Costruire una mappa di riferimento più grande e più pulita
Nella nuova release, gli autori hanno raccolto quasi 1,7 milioni di genomi batterici e archaeali da un archivio pubblico e li hanno cercati per sequenze complete dell’operone rRNA di lunghezza ragionevole. Hanno quindi sottoposto queste sequenze grezze a diversi passaggi di controllo qualità. I genomi privi di nomi di specie chiari sono stati esclusi, i duplicati esatti tra specie rimossi e le sequenze con troppe basi incerte filtrate. Infine, le sequenze molto simili sono state raggruppate in cluster e i gruppi che mescolavano specie sono stati ispezionati e ripuliti con attenzione, inclusi controlli manuali con strumenti di confronto di sequenze e costruzione di alberi evolutivi per rimuovere contaminazioni.
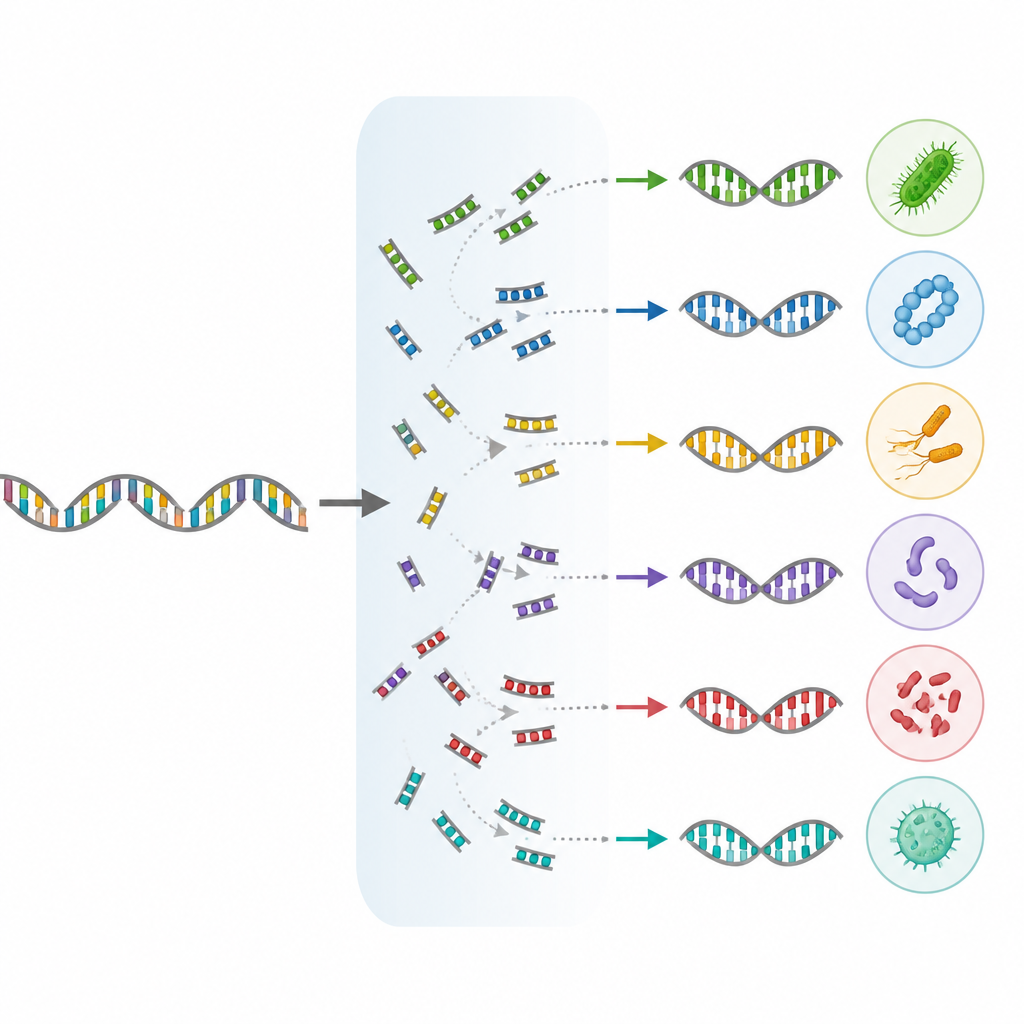
Aggiungere rami del tutto della vita finora trascurati
Un importante avanzamento di MIrROR release 02 è l’inclusione degli archaea, un ampio gruppo di microbi che prosperano in ambienti che vanno dalle sorgenti termali all’intestino umano. Il dataset ora copre oltre mille specie archaeali, tra cui organismi di rilevanza medica e industriale. Allo stesso tempo, gli autori hanno aggiornato nomi e raggruppamenti di molti microbi usando una tassonomia moderna basata sui genomi. Questa riclassificazione ha interessato circa la metà di tutti i genomi nel dataset e ha aggiunto quasi diciannovemila specie batteriche supplementari, incluse specie ambientali rare, patogeni clinicamente rilevanti e specie importanti in biotecnologia e produzione alimentare.
Far funzionare i survey long read su comunità reali e di test
Per dimostrare che il dataset ampliato non è solo più grande ma anche più utile, il team lo ha testato sia su miscele microbiche create in laboratorio sia su simulazioni al computer. Hanno confrontato MIrROR release 02 con dati MIrROR precedenti e con altre collezioni di riferimento comuni. Nei test controllati, il nuovo dataset si è dimostrato migliore nel riconoscere le specie, incluse quelle che i dataset più vecchi non rilevavano affatto, come una specifica specie di Prevotella in uno standard di comunità intestinale. Quando sono state aggiunte specie archaeali a una comunità intestinale simulata, la nuova versione di MIrROR è stata in grado di rilevarle e classificarle sia a livello di genere che di specie, mentre un riferimento basato solo sul 16S largamente usato spesso produceva etichette vaghe come batteri non spiegati e faticava ad assegnare le letture alla specie corretta.
Aiutare gli scienziati a scegliere gli strumenti giusti
Poiché il sequenziamento long read dipende da specifici punti di partenza del DNA chiamati primer, gli autori hanno anche verificato diversi coppie di primer in simulazioni al computer per vedere quali potessero catturare meglio sia batteri che archaea sull’intero operone. Raccomandano due set di primer che bilanciano ampia copertura e compatibilità con le piattaforme long read. Allo stesso tempo, segnalano notevoli caratteristiche biologiche, come microbi che mantengono i loro geni rRNA non collegati o in copie multiple leggermente diverse, che possono introdurre bias nei conteggi e devono essere considerati nell’interpretazione dei dati di comunità.
Cosa significa per le domande di tutti i giorni
In termini semplici, MIrROR release 02 è una rubrica per i microbi molto più ampia e meglio organizzata, progettata per funzionare con il sequenziamento del DNA long read moderno. Permette agli scienziati di separare specie simili in modo più attendibile, di includere gli archaea nelle loro indagini e di confrontare i risultati tra diversi studi con maggiore fiducia. Pur non eliminando tutte le sfide nell’analisi delle comunità microbiche, fornisce ai ricercatori una lente più nitida per esplorare come i microbi influenzano la salute umana, gli ecosistemi e i processi industriali.
Citazione: Lee, J., Hong, J., Seol, D. et al. MIrROR release 02: Expanded and refined 16S-ITS-23S rRNA operon dataset. Sci Data 13, 714 (2026). https://doi.org/10.1038/s41597-026-06729-y
Parole chiave: microbioma, operone rRNA, sequenziamento long read, tassonomia microbica, archaea