Clear Sky Science · sv
Identifiering av Obelisk-liknande RNA-replikoner i heta källor och utvidgad mångfald i Obelisk-superfamiljen
Gömda cirklar i extrema heta källor
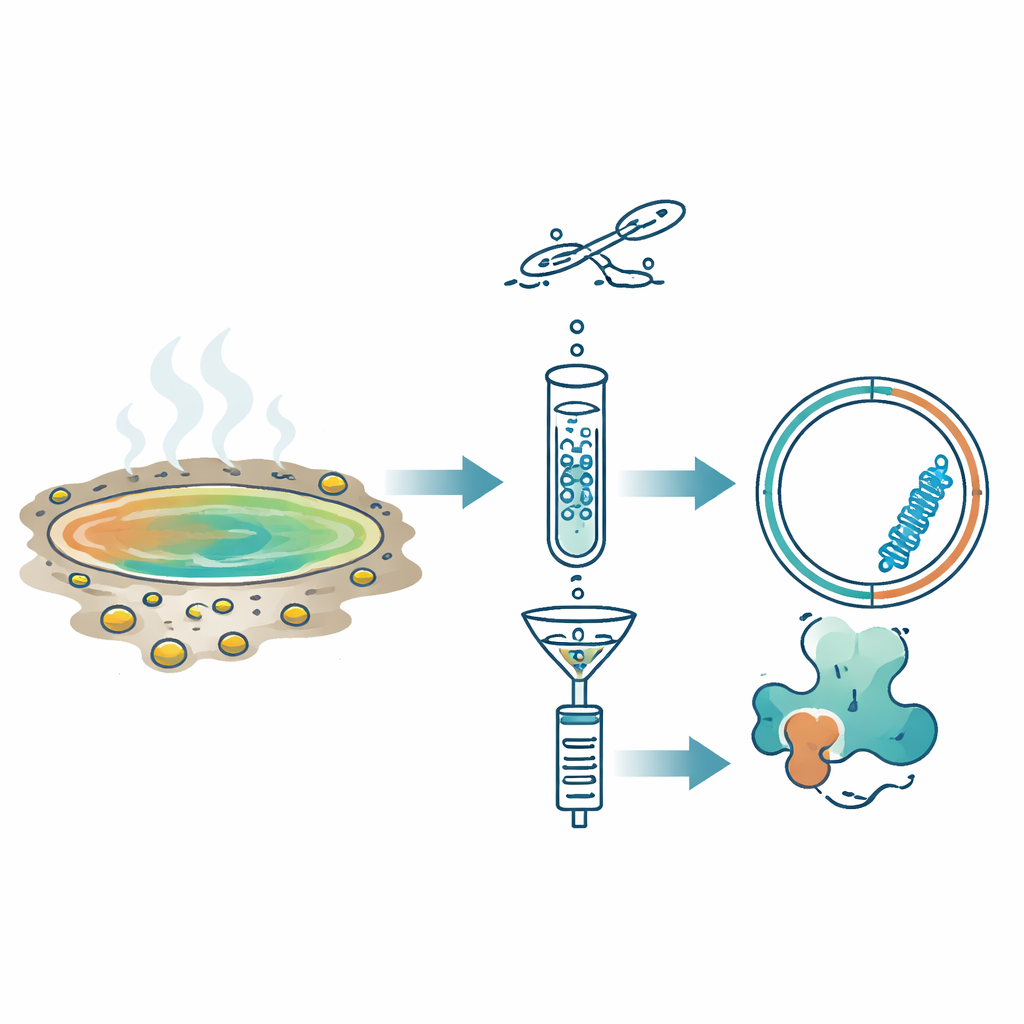
Nästan kokande, surt brunnsvatten låter som platser där liv borde falla sönder. Ändå sjuder dessa hårda pooler av mikrober – och, som denna studie visar, av små ringformade RNA-molekyler som tyst kopierar sig själva. Forskarlaget ville ta reda på om en mystisk klass av RNA-cirklar, kända som Obelisks, också lever i sådana extrema miljöer. I processen upptäckte de nya medlemmar i denna märkliga familj och visade att dessa mikroskopiska ”kodcirklar” är mycket vanligare och mer varierade i jordens ekosystem än man tidigare trott.
Hur små RNA-ringarna skiljer sig från välkända virus
De flesta känner igen virus som partiklar som bär DNA eller RNA som kodar för flera proteiner. Viroider och besläktade agenter är annorlunda. De är korta RNA-loopar som ofta viker sig till ståliknande former och kanske inte kodar för något protein alls. De kapar värdcellens maskineri för att skapa kopior, ibland skadar de grödor men förblir i övrigt relativt okända. Under de senaste åren har storskalig sekvensering av miljö-RNA avslöjat ett zoo av sådana cirkulära molekyler på platser med få växter eller djur, vilket antyder att mikrober också kan hysa dessa minimala genetiska element. Bland dem finns Obelisks, cirkulära RNA på ungefär tusen byggstenar som faktiskt kodar för ett enda protein med en tidigare okänd tredimensionell form.
Hitta nya RNA-cirklar genom att läsa dubbelsträngade mellanformer
I stället för att söka direkt efter kända sekvenser använde teamet ett annat kännetecken hos RNA-replikoner: under kopiering bildar de tillfälligt dubbelsträngat RNA. De tillämpade en metod kallad Fragmented and primer-Ligated DsRNA Sequencing (FLDS), som berikar dessa dubbelsträngade former från miljöprover. Efter att ha renat dubbelsträngat RNA från elva sura heta källor i Japan sekvenserade de det och använde ett stegvis filtreringsflöde. Endast molekyler som verkade cirkulära, var väl täckta av sekvenseringsläsningar och veckade sig till stabila, ståliknande strukturer behölls. För att validera metoden bekräftade de först att den kunde återupptäcka en känd växtviroide i infekterade krysantemumblad. Därefter, med samma logik på källproverna, isolerade de en framstående kandidat som de kallade Hot spring Obelisk (HsOb).
Nya Obelisks som frodas i nästan kokande sura pooler
Det viktigaste RNA:t som upptäcktes i en källa kallad Oi var cirka 870 nukleotider långt och bildade en utsträckt ståliknande struktur även när det modellerades vid 80 °C, vattentemperaturen på platsen. Det innehöll ett enda långt öppet läsram som skulle ge ett protein på 213 aminosyror, döpt till HsOblin-1. Även om aminosyrasekvensen visade nästan ingen likhet med kända proteiner avslöjade strukturberekningsverktyg att HsOblin-1 viker sig till samma grundläggande arkitektur som det ursprungliga Obelisk-proteinet, Oblin-1: en kompakt, α-helixrik kärna följd av en flexibel, positivt laddad svans troligen lämpad för att gripa RNA. Ett besläktat RNA från en annan källa, H5, kodade för ett liknande protein. De mikrobiella samhällena i dessa prover dominerades av termoacidofila bakterier i familjen Hydrogenobaculaceae, vilket gör dessa bakterier till ledande kandidater som värdar för de heta källornas Obelisks, även om direkt värdtillhörighet ännu inte är bevisad.
En global undersökning visar en stor och varierad familj
Beväpnade med känsliga strukturmedvetna sökverktyg genomsökte forskarna därefter miljontals presumtiva cirkulära RNA från över 7 000 miljömetatranskriptom, tillsammans med ytterligare dataset från publika arkiv. Med utgångspunkt i de heta källornas HsOblin-1-proteiner och det ursprungligen beskrevna Oblin-1 byggde de iterativt profiler som fångar avlägsna släktingar även när sekvenslikheten är svag. Denna insats avslöjade 6 443 distinkta proteiner med en Oblin-liknande veckning, kodade av mer än 8 000 Obelisk-RNA-genom. Genom att gruppera dessa proteiner efter likhet och efter förutsagd tredimensionell struktur framkom 21 huvudsubfamiljer. Alla delar samma kärnveckning men skiljer sig i ytegenskaper och i delar av en lång, flexibel loop, vilket tyder på att de har differentierat för att interagera med olika värdar eller partner samtidigt som det grundläggande replikationsverktyget bevarats. Vissa subfamiljer tycks också bära extra små proteiner med enkla helixformade strukturer, vilket antyder tilläggsfunktioner som utvecklats oberoende.
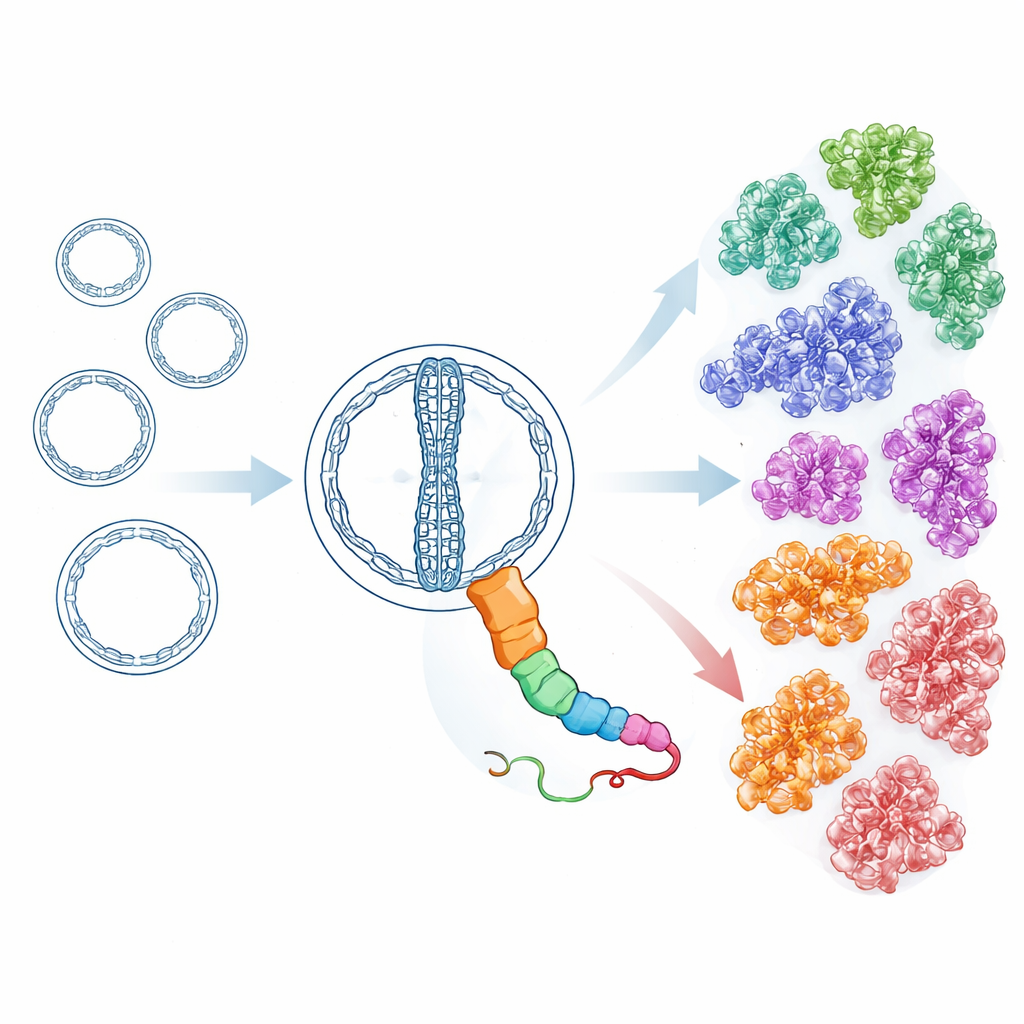
Spåra värdar och livsstilar över livets träd
För att förstå vilka dessa RNA-cirklar lever med sökte teamet efter träffar mellan Obelisk-sekvenser och CRISPR-spacers – korta genetiska register som bakterier och arkéer håller av tidigare infektioner. De fann dussintals övertygande träffar, särskilt i bakterier som lever i tarmarna hos människor och idisslare, vilket stärker idén att Obelisks ofta infekterar eller samexisterar med bakterier. Tillsammans med tidigare arbete som hittat Obelisks i människomunnen och i havsvatten tyder dessa resultat på att Obelisks inte är sällsynta kuriositeter, utan utbredda medlemmar av mikrobiella samhällen från oceanen till heta källor till djurs mikrobiom. Många gåtor återstår dock: det är fortfarande oklart om Obelisks beter sig mer som plasmider (extra genetiska element som stannar inom en cellinje) eller som infektiösa agenter som sprids mellan värdar, och detaljerna i hur de kopierar sig själva är fortfarande okända.
Vad detta betyder för vår bild av livets mångfald
För en icke-specialist visar dessa fynd att även på platser lika ogästvänliga som nästan kokande sura pooler har evolutionen fyllt den mikroskopiska världen med okonventionella genetiska enheter. Heta källors Obelisks bevisar att cirkulära RNA-replikoner med en delad proteinveckning kan frodas vid höga temperaturer och i mycket olika habitat. Genom att nästan fördubbla den kända mångfalden av Obelisks och kartlägga deras sannolika bakteriepartners avslöjar denna studie ett stort, tidigare osett lager av genetiskt liv. Det antyder att enkla RNA-baserade replikoner inte bara är historiska reliker, utan aktiva, anpassningsbara aktörer i dagens biosfär som tyst formar mikrobiella ekosystem över hela planeten.
Citering: Urayama, Si., Fukudome, A., Mutz, P. et al. Identification of hot spring Obelisk-like RNA replicons and expanded diversity of the Obelisk superfamily. Nat Commun 17, 3041 (2026). https://doi.org/10.1038/s41467-026-71096-6
Nyckelord: cirkulärt RNA, varma källor, mikrobiella ekosystem, RNA-replikoner, Obelisk-element