Clear Sky Science · fr
Identification d’Obélisques ARN réplicons semblables à des obélisques dans des sources chaudes et diversité élargie de la superfamille Obelisk
Cercles cachés dans des sources chaudes extrêmes
Des sources chaudes acides proches du point d’ébullition semblent des lieux où la vie devrait se décomposer. Pourtant, ces bassins hostiles regorgent de microbes — et, comme le montre cette étude, de minuscules molécules d’ARN en forme d’anneau qui se copient silencieusement. Les chercheurs ont cherché à savoir si une classe mystérieuse de cercles d’ARN, connue sous le nom d’Obelisks, vivait aussi dans de tels milieux extrêmes. Ce faisant, ils ont mis au jour de nouveaux membres de cette étrange famille et montré que ces « cercles de code » microscopiques sont beaucoup plus répandus et variés dans les écosystèmes terrestres qu’on ne le pensait.
En quoi de minuscules anneaux d’ARN diffèrent des virus familiers
La plupart des gens connaissent les virus comme des particules contenant de l’ADN ou de l’ARN codant plusieurs protéines. Les viroïdes et agents apparentés sont différents. Ce sont de courtes boucles d’ARN qui se replient souvent en formes en tige et peuvent ne coder aucune protéine. Ils détournent la machinerie de leur cellule hôte pour se répliquer, endommageant parfois les cultures mais restant par ailleurs peu connus. Ces dernières années, le séquençage à haut débit de l’ARN environnemental a révélé une faune de telles molécules circulaires dans des lieux dépourvus de plantes ou d’animaux, laissant entendre que les microbes peuvent aussi héberger ces éléments génétiques minimaux. Parmi eux se trouvent les Obelisks, des ARN circulaires d’environ mille nucléotides qui codent pour une unique protéine présentant une architecture tridimensionnelle jusque-là inconnue.
Trouver de nouveaux cercles d’ARN en lisant des intermédiaires double brin
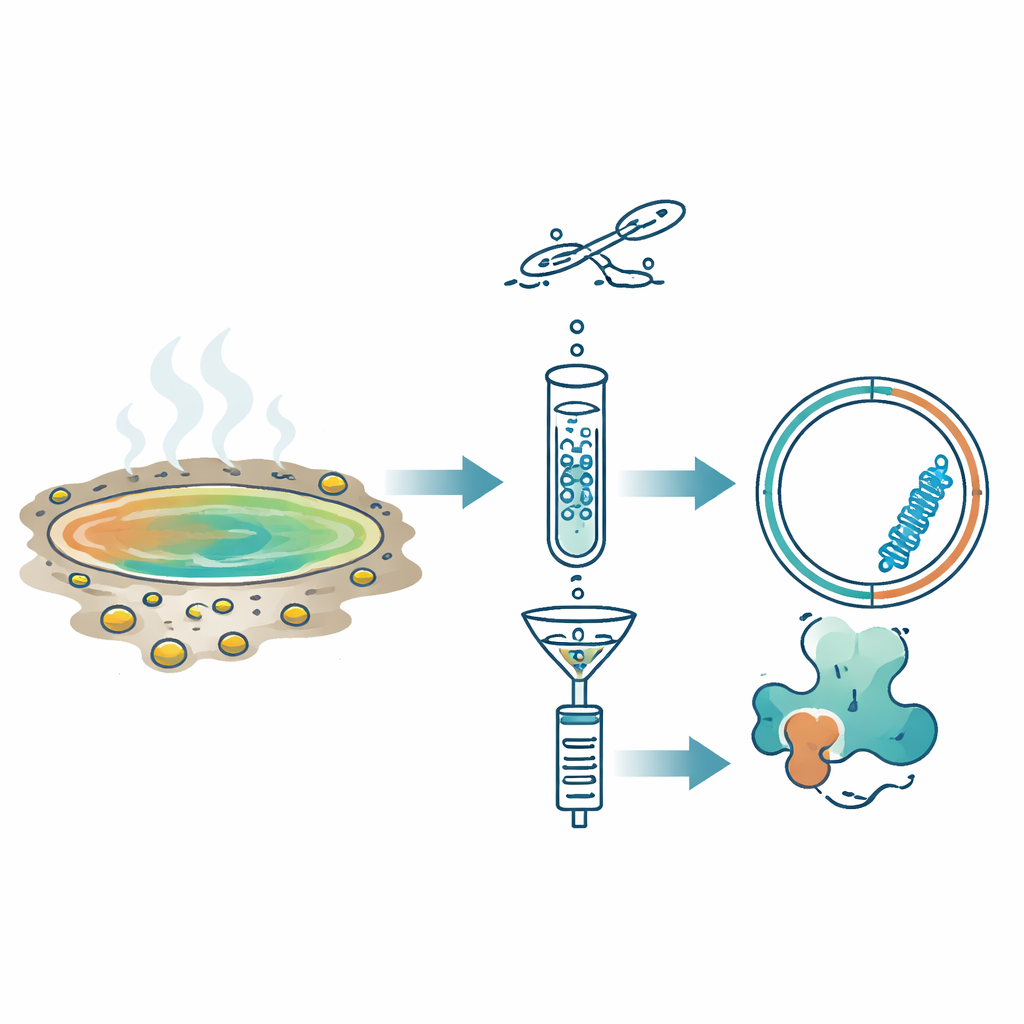
Plutôt que de rechercher directement des séquences connues, l’équipe a utilisé un autre signe distinctif des réplicons ARN : lors de la copie, ils forment brièvement de l’ARN double brin. Ils ont appliqué une méthode appelée Fragmented and primer-Ligated DsRNA Sequencing (FLDS), qui enrichit ces formes double brin à partir d’échantillons environnementaux. Après avoir purifié l’ARN double brin de onze sources chaudes acides au Japon, ils l’ont séquencé et ont utilisé un pipeline de filtrage en plusieurs étapes. Seules les molécules apparaissant circulaires, correctement couvertes par les lectures de séquençage et se repliant en structures stables et en tige ont été conservées. Pour valider l’approche, ils ont d’abord confirmé qu’elle pouvait redécouvrir un viroïde végétal connu dans des feuilles de chrysanthème infectées. Ensuite, en appliquant la même logique aux échantillons des sources chaudes, ils ont isolé un candidat remarquable qu’ils ont nommé Obelisk de source chaude (HsOb).
Nouveaux Obelisks prospérant dans des bassins acides presque bouillants
L’ARN clé découvert dans une source appelée Oi mesurait environ 870 nucléotides et formait une structure étendue en tige même lorsqu’on la modélisait à 80 °C, la température de l’eau sur site. Il contenait un unique long cadre de lecture ouvert qui produirait une protéine de 213 acides aminés, baptisée HsOblin-1. Bien que sa séquence en acides aminés montrait presque aucune similarité avec des protéines connues, des outils de prédiction structurale ont révélé que HsOblin-1 se replie selon la même architecture de base que la protéine Obelisk originale, Oblin-1 : un cœur compact riche en hélices α suivi d’une queue flexible, chargée positivement, vraisemblablement adaptée à la liaison de l’ARN. Un ARN apparenté provenant d’une autre source, H5, codait une protéine similaire. Les communautés microbiennes dans ces échantillons étaient dominées par des bactéries thermoacidophiles de la famille des Hydrogenobaculaceae, faisant de ces bactéries les principaux candidats comme hôtes des Obelisks de source chaude, même si l’attribution directe des hôtes reste à démontrer.
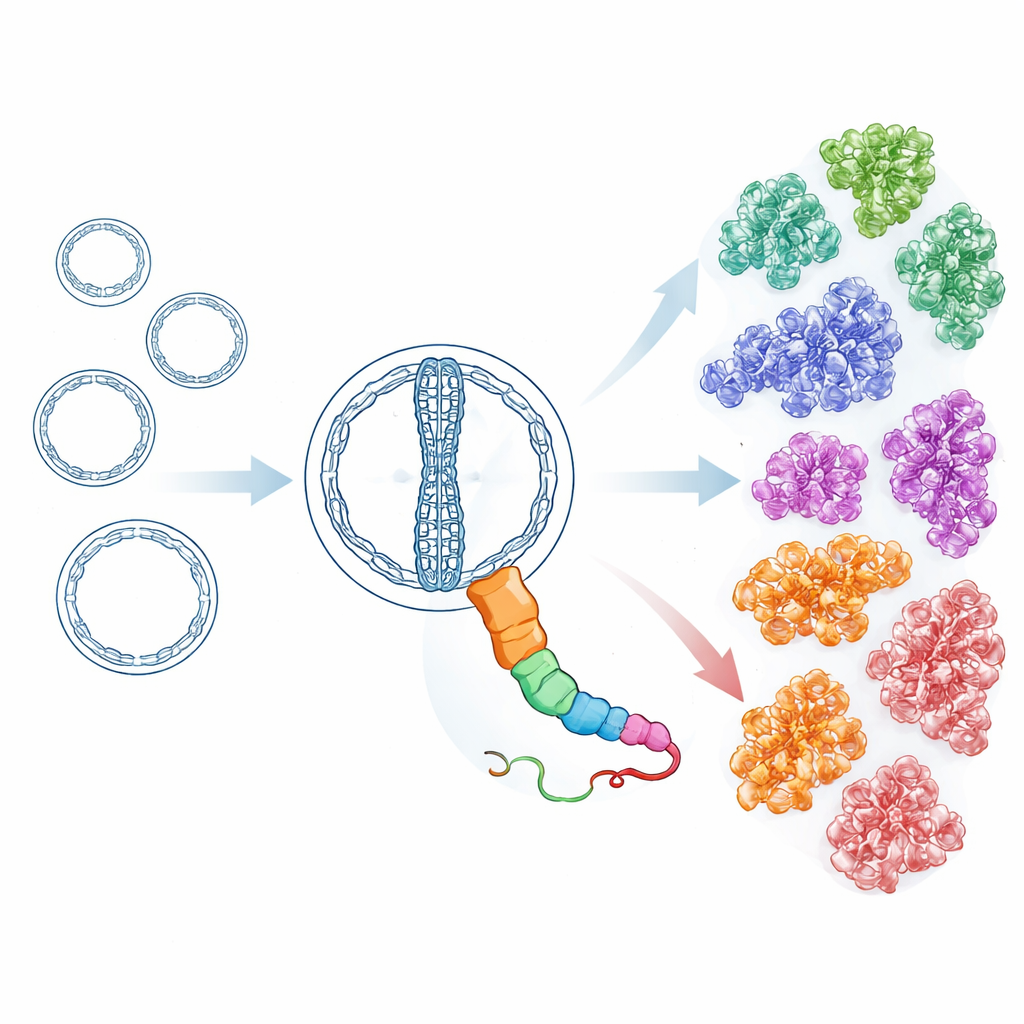
Une enquête mondiale révèle une famille vaste et variée
Équipés d’outils de recherche sensibles et tenant compte de la structure, les chercheurs ont ensuite analysé des millions d’ARN circulaires putatifs provenant de plus de 7 000 métatranscriptomes environnementaux, ainsi que d’ensembles de données supplémentaires issus de dépôts publics. À partir des protéines HsOblin-1 des sources chaudes et d’Oblin-1 décrit à l’origine, ils ont construit itérativement des profils capturant des parents lointains même lorsque la similarité de séquence est faible. Cet effort a mis au jour 6 443 protéines distinctes présentant un repliement de type Oblin, encodées par plus de 8 000 génomes ARN Obelisk. Le regroupement de ces protéines par similarité et par structure tridimensionnelle prédite a révélé 21 sous-familles principales. Toutes partagent le même repliement de base mais diffèrent par leurs caractéristiques de surface et par des parties d’une longue boucle flexible, suggérant qu’elles se sont diversifiées pour interagir avec différents hôtes ou partenaires tout en conservant l’outillage fondamental de réplication. Certaines sous-familles semblent aussi porter de petites protéines additionnelles à formes hélicoïdales simples, évoquant des fonctions annexes apparues indépendamment.
Retrouver hôtes et modes de vie à travers l’arbre du vivant
Pour comprendre avec qui vivent ces cercles d’ARN, l’équipe a cherché des correspondances entre les séquences Obelisk et des éponges CRISPR — de courts enregistrements génétiques que les bactéries et archées conservent de précédentes infections. Ils ont trouvé des dizaines de correspondances convaincantes, notamment chez des bactéries peuplant les intestins humains et de ruminants, renforçant l’idée que les Obelisks infectent ou coexistent couramment avec des bactéries. Combinés à des travaux antérieurs ayant détecté des Obelisks dans la bouche humaine et en milieu marin, ces résultats suggèrent que les Obelisks ne sont pas de rares curiosités, mais des membres répandus des communautés microbiennes, de l’océan aux sources chaudes en passant par les microbiotes animaux. De nombreuses questions demeurent toutefois : on ne sait pas encore si les Obelisks se comportent davantage comme des plasmides (éléments génétiques accessoires restant dans une lignée cellulaire) ou comme des agents infectieux se propageant entre hôtes, et les détails de leur mécanisme de réplication restent inconnus.
Ce que cela change pour notre vision de la diversité du vivant
Pour un non-spécialiste, ces découvertes montrent que même dans des lieux aussi inhospitaliers que des bassins acides proches de l’ébullition, l’évolution a rempli le monde microscopique d’entités génétiques non conventionnelles. Les Obelisks des sources chaudes prouvent que des réplicons ARN circulaires partageant un même repliement protéique peuvent prospérer à haute température et dans des habitats très différents. En doublant presque la diversité connue des Obelisks et en cartographiant leurs partenaires bactériens probables, cette étude révèle une vaste couche de vie génétique jusque-là invisible. Elle suggère que des réplicons simples à base d’ARN ne sont pas de simples reliques historiques, mais des acteurs actifs et adaptables du biosphère contemporaine, façonnant discrètement les écosystèmes microbiens à travers la planète.
Citation: Urayama, Si., Fukudome, A., Mutz, P. et al. Identification of hot spring Obelisk-like RNA replicons and expanded diversity of the Obelisk superfamily. Nat Commun 17, 3041 (2026). https://doi.org/10.1038/s41467-026-71096-6
Mots-clés: ARN circulaire, sources chaudes, écosystèmes microbiens, réplicons ARN, éléments Obelisk