Clear Sky Science · pt
Identificação de replicões de RNA em forma de obelisco em fontes termais e diversidade ampliada da superfamília Obelisk
Círculos ocultos em fontes termais extremas
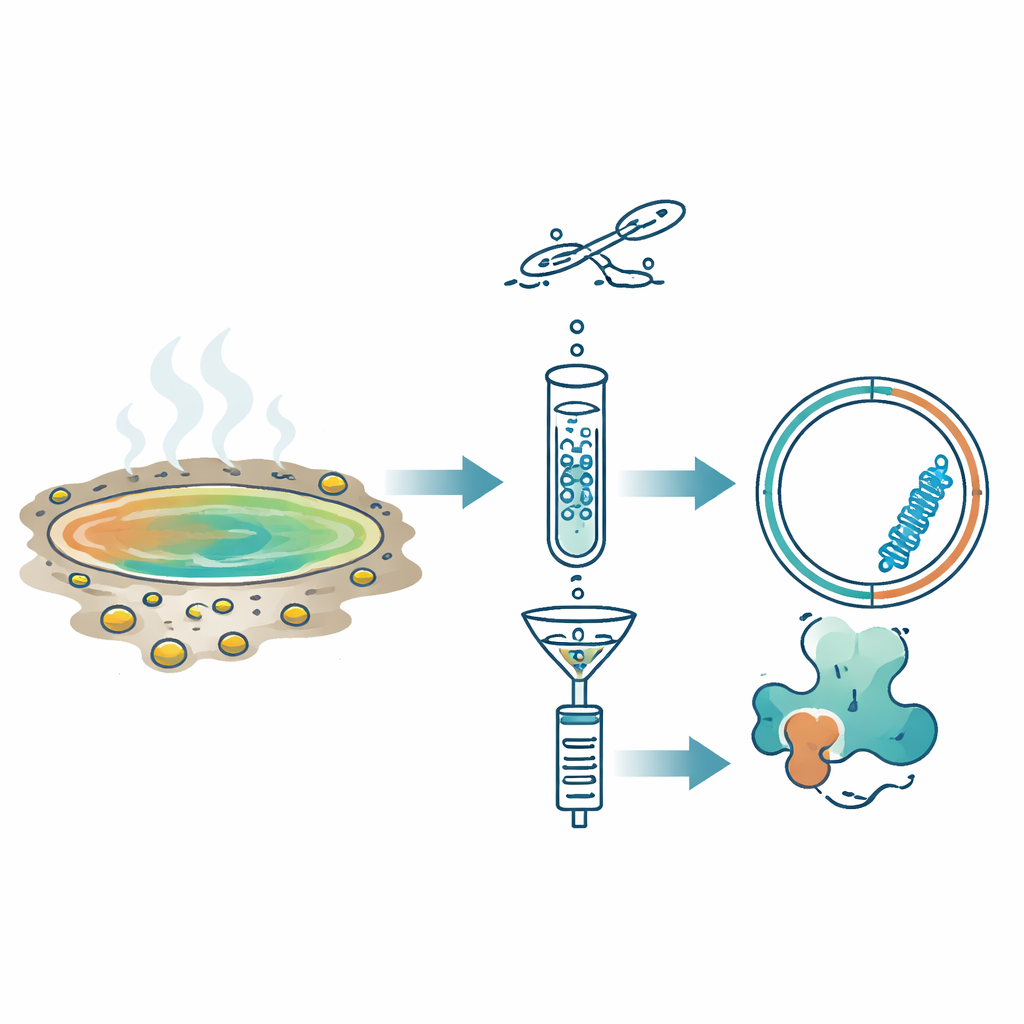
Fontes termais ácidas próximas do ponto de ebulição parecem lugares em que a vida deveria se desfazer. Ainda assim, essas piscinas hostis fervilham de micróbios — e, como mostra este estudo, de minúsculas moléculas de RNA em forma de anel que silenciosamente se replicam. Os pesquisadores buscaram determinar se uma classe misteriosa de círculos de RNA, conhecida como Obelisks, também habita esses ambientes extremos. Ao fazê-lo, descobriram novos membros dessa família estranha e mostraram que esses microscópicos “círculos de código” são muito mais comuns e variados nos ecossistemas da Terra do que se imaginava.
Como pequenos anéis de RNA diferem de vírus familiares
A maioria das pessoas conhece vírus como partículas que carregam DNA ou RNA que codificam várias proteínas. Viroides e agentes relacionados são diferentes. Eles são loops curtos de RNA que frequentemente se dobram em formas parecidas com hastes e podem não codificar nenhuma proteína. Eles sequestram a maquinaria da célula hospedeira para se copiar, às vezes prejudicando plantações, mas na maior parte permanecem obscuros. Nos últimos anos, o sequenciamento de alto rendimento de RNA ambiental revelou um verdadeiro zoológico desses moléculas circulares em locais com poucas plantas ou animais, sugerindo que micróbios também podem hospedar esses elementos genéticos mínimos. Entre eles estão os Obelisks, RNAs circulares de cerca de mil nucleotídeos que codificam uma única proteína com uma forma tridimensional previamente desconhecida.
Encontrando novos círculos de RNA lendo intermediários de fita dupla
Em vez de procurar diretamente por sequências conhecidas, a equipe usou uma marca diferente dos replicões de RNA: durante a cópia, eles formam brevemente RNA de fita dupla. Aplicaram um método chamado Fragmented and primer-Ligated DsRNA Sequencing (FLDS), que enriquece essas formas de fita dupla a partir de amostras ambientais. Após purificar RNA de fita dupla de onze fontes termais ácidas no Japão, sequenciaram o material e usaram um pipeline de filtragem em etapas. Foram mantidas apenas moléculas que aparentavam ser circulares, bem cobertas por leituras de sequenciamento e que se dobravam em estruturas estáveis e alongadas parecidas com hastes. Para validar a abordagem, confirmaram primeiro que ela poderia redescobrir um viroide vegetal conhecido em folhas de crisântemo infectadas. Em seguida, aplicando a mesma lógica às amostras das fontes termais, isolaram um candidato de destaque que nomearam Obelisk de Fonte Termal (HsOb).
Novos Obelisks prosperando em piscinas ácidas quase em ebulição
O RNA-chave descoberto em uma fonte chamada Oi tinha cerca de 870 nucleotídeos e formava uma estrutura alongada em forma de haste mesmo quando modelado a 80 °C, a temperatura da água no local. Continha um único longo quadro de leitura aberto que produziria uma proteína de 213 aminoácidos, denominada HsOblin-1. Embora sua sequência de aminoácidos mostrasse quase nenhuma semelhança com proteínas conhecidas, ferramentas de predição estrutural revelaram que HsOblin-1 se dobra na mesma arquitetura básica que a proteína Obelisk original, Oblin-1: um núcleo compacto rico em α-hélices seguido de uma cauda flexível e carregada positivamente, provavelmente adequada para agarrar RNA. Um RNA relacionado de outra fonte, H5, codificava uma proteína similar. As comunidades microbianas nessas amostras eram dominadas por bactérias termoacidofílicas da família Hydrogenobaculaceae, tornando essas bactérias as candidatas principais como hospedeiras dos Obelisks das fontes termais, embora a atribuição direta de hospedeiro ainda precise ser comprovada.
Uma pesquisa global revela uma família vasta e variada
Munidos de ferramentas de busca sensíveis e conscientes da estrutura, os pesquisadores então vasculharam milhões de putativos RNAs circulares a partir de mais de 7.000 metatranscritomas ambientais, junto com conjuntos de dados adicionais de repositórios públicos. Partindo das proteínas HsOblin-1 das fontes termais e da Oblin-1 descrita originalmente, construíram iterativamente perfis que capturam parentes distantes mesmo quando a similaridade de sequência é fraca. Esse esforço revelou 6.443 proteínas distintas com um dobramento do tipo Oblin, codificadas por mais de 8.000 genomas de RNA Obelisk. Agrupar essas proteínas por similaridade e por predição de estrutura tridimensional revelou 21 subfamílias principais. Todas compartilham o mesmo núcleo estrutural, mas diferem em características de superfície e em partes de uma longa alça flexível, sugerindo que se diversificaram para interagir com diferentes hospedeiros ou parceiros enquanto mantêm a maquinaria básica de replicação intacta. Algumas subfamílias também parecem carregar proteínas pequenas extras com formas helicoidais simples, indicando funções complementares que evoluíram de forma independente.
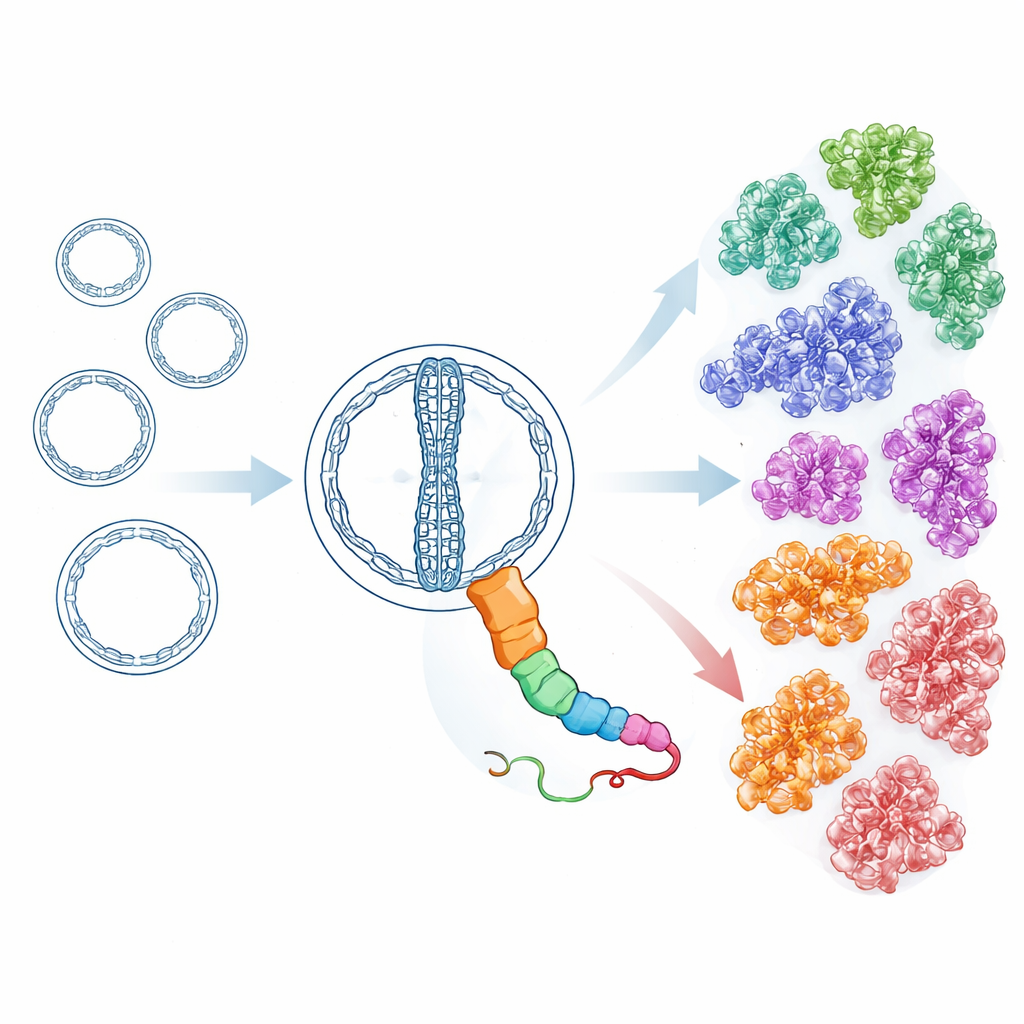
Rastreando hospedeiros e estilos de vida através da árvore da vida
Para entender com quem esses círculos de RNA convivem, a equipe procurou correspondências entre sequências de Obelisk e espaçadores CRISPR — registros genéticos curtos que bactérias e arqueias mantêm de infecções passadas. Encontraram dezenas de correspondências convincentes, especialmente em bactérias que habitam os intestinos de humanos e ruminantes, reforçando a ideia de que Obelisks comumente infectam ou coexistem com bactérias. Combinado com trabalhos anteriores que encontraram Obelisks na boca humana e em águas marinhas, esses resultados sugerem que Obelisks não são curiosidades raras, mas membros disseminados de comunidades microbianas, do oceano às fontes termais e aos microbiomas animais. Ainda assim, muitos enigmas permanecem: não está claro se os Obelisks se comportam mais como plasmídeos (elementos genéticos extras que ficam dentro de uma linhagem celular) ou como agentes infecciosos que se espalham entre hospedeiros, e os detalhes de como eles se replicam ainda são desconhecidos.
O que isso significa para nossa visão da diversidade da vida
Para um não especialista, essas descobertas mostram que mesmo em locais tão inóspitos quanto piscinas ácidas quase em ebulição, a evolução preencheu o mundo microscópico com entidades genéticas não convencionais. Os Obelisks das fontes termais provam que replicões de RNA circulares com um mesmo dobramento proteico podem prosperar em altas temperaturas e em habitats muito diferentes. Ao quase dobrar a diversidade conhecida de Obelisks e mapear seus prováveis parceiros bacterianos, este estudo revela uma vasta camada de vida genética até então invisível. Sugere que replicões simples baseados em RNA não são apenas relíquias históricas, mas atores ativos e adaptáveis no biosfera atual, moldando silenciosamente ecossistemas microbianos em todo o planeta.
Citação: Urayama, Si., Fukudome, A., Mutz, P. et al. Identification of hot spring Obelisk-like RNA replicons and expanded diversity of the Obelisk superfamily. Nat Commun 17, 3041 (2026). https://doi.org/10.1038/s41467-026-71096-6
Palavras-chave: RNA circular, fontes termais, ecossistemas microbianos, replicões de RNA, elementos Obelisk