Clear Sky Science · es
Identificación de replicones de ARN en forma de obelisco en fuentes termales y diversidad ampliada de la superfamilia Obelisk
Círculos ocultos en fuentes termales extremas
Las fuentes termales ácidas y casi hirvientes parecen lugares donde la vida debería desintegrarse. Sin embargo, estas piscinas extremas están llenas de microbios y, como muestra este estudio, de pequeñas moléculas de ARN en forma de anillo que se copian silenciosamente. Los investigadores se propusieron comprobar si una clase misteriosa de círculos de ARN, conocida como Obelisks, también habita en estos entornos extremos. Al hacerlo, descubrieron nuevos miembros de esta extraña familia y demostraron que estos microscópicos “círculos de código” son mucho más comunes y variados en los ecosistemas de la Tierra de lo que se pensaba.
En qué se diferencian los pequeños anillos de ARN de los virus conocidos
La mayoría de la gente conoce los virus como partículas que transportan ADN o ARN que codifican varias proteínas. Los viroides y agentes relacionados son distintos. Son bucles cortos de ARN que a menudo se pliegan en formas similares a varillas y pueden no codificar ninguna proteína. Secuestran la maquinaria de la célula huésped para copiarse, a veces dañando cosechas, pero por lo demás pasan desapercibidos. En años recientes, la secuenciación masiva del ARN ambiental ha revelado un zoológico de tales moléculas circulares en lugares con pocas plantas o animales, lo que sugiere que los microbios también pueden alojar estos elementos genéticos mínimos. Entre ellos están los Obelisks, ARN circulares de aproximadamente mil bloques de construcción que sí codifican una única proteína con una forma tridimensional previamente desconocida.
Encontrar nuevos círculos de ARN leyendo intermedios de doble cadena
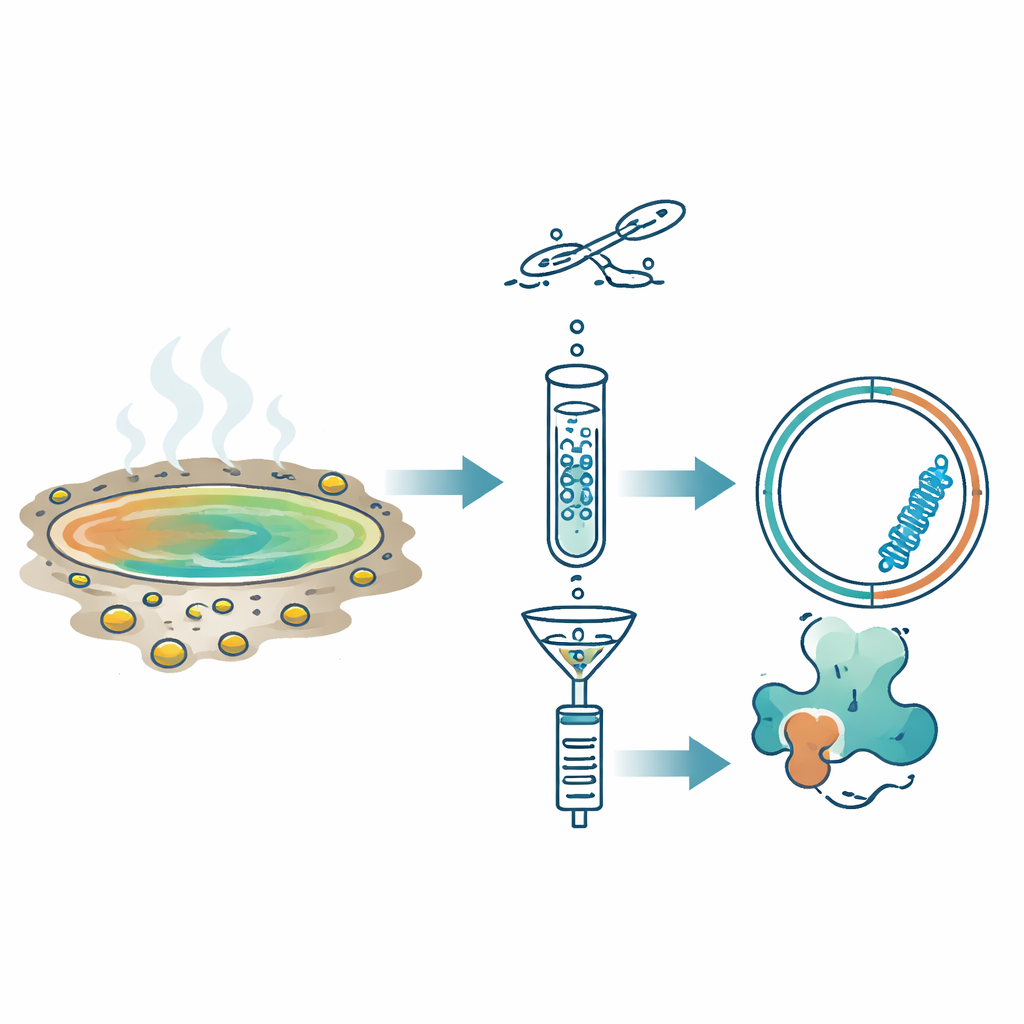
En lugar de buscar directamente secuencias conocidas, el equipo usó otra característica distintiva de los replicones de ARN: durante la copia, forman brevemente ARN de doble hebra. Aplicaron un método llamado Fragmented and primer-Ligated DsRNA Sequencing (FLDS), que enriquece estas formas de doble hebra a partir de muestras ambientales. Tras purificar ARN de doble hebra de once fuentes termales ácidas en Japón, lo secuenciaron y emplearon una canalización de filtrado por etapas. Solo se conservaron las moléculas que parecían circulares, que estaban bien cubiertas por las lecturas de secuenciación y que se plegaban en estructuras estables y similares a varillas. Para validar el enfoque, primero confirmaron que podía redescubrir un viroide de planta conocido en hojas de crisantemo infectadas. Luego, aplicando la misma lógica a las muestras de las fuentes termales, aislaron un candidato destacado que denominaron Obelisk de Fuente Termal (HsOb).
Nuevos Obelisks que prosperan en piscinas ácidas casi hirvientes
El ARN clave descubierto en una fuente llamada Oi tenía aproximadamente 870 nucleótidos y formaba una estructura alargada similar a una varilla incluso cuando se modeló a 80 °C, la temperatura del agua en el sitio. Contenía un único marco de lectura abierto largo que produciría una proteína de 213 aminoácidos, denominada HsOblin-1. Aunque su secuencia de aminoácidos mostraba casi ninguna similitud con proteínas conocidas, las herramientas de predicción estructural revelaron que HsOblin-1 se pliega en la misma arquitectura básica que la proteína Obelisk original, Oblin-1: un núcleo compacto rico en hélices α seguido de una cola flexible y cargada positivamente, probablemente apta para sujetar ARN. Un ARN relacionado de otra fuente, H5, codificaba una proteína similar. Las comunidades microbianas en estas muestras estaban dominadas por bacterias termoacidófilas de la familia Hydrogenobaculaceae, lo que convierte a estas bacterias en las principales candidatas a hospedadores de los Obelisks de las fuentes termales, aunque la asignación directa del hospedador aún está por demostrar.
Una encuesta global muestra una familia vasta y variada
Con herramientas de búsqueda sensibles y conscientes de la estructura, los investigadores examinaron millones de ARN circulares putativos procedentes de más de 7.000 metatranscriptomas ambientales, junto con conjuntos de datos adicionales de repositorios públicos. Partiendo de las proteínas HsOblin-1 de la fuente termal y de la Oblin-1 descrita originalmente, fueron construyendo perfiles de forma iterativa que capturan parientes distantes incluso cuando la similitud de secuencia es baja. Este esfuerzo descubrió 6.443 proteínas distintas con un pliegue similar al de Oblin, codificadas por más de 8.000 genomas de ARN Obelisk. Agrupar estas proteínas por similitud y por la estructura tridimensional predicha reveló 21 subfamilias principales. Todas comparten el mismo pliegue central pero difieren en características superficiales y en partes de un largo bucle flexible, lo que sugiere que se han diversificado para interactuar con distintos hospedadores o socios mientras mantienen intacto el equipo básico de replicación. Algunas subfamilias también parecen portar proteínas pequeñas adicionales con formas helicoidales simples, lo que insinúa funciones complementarias que han evolucionado de forma independiente.
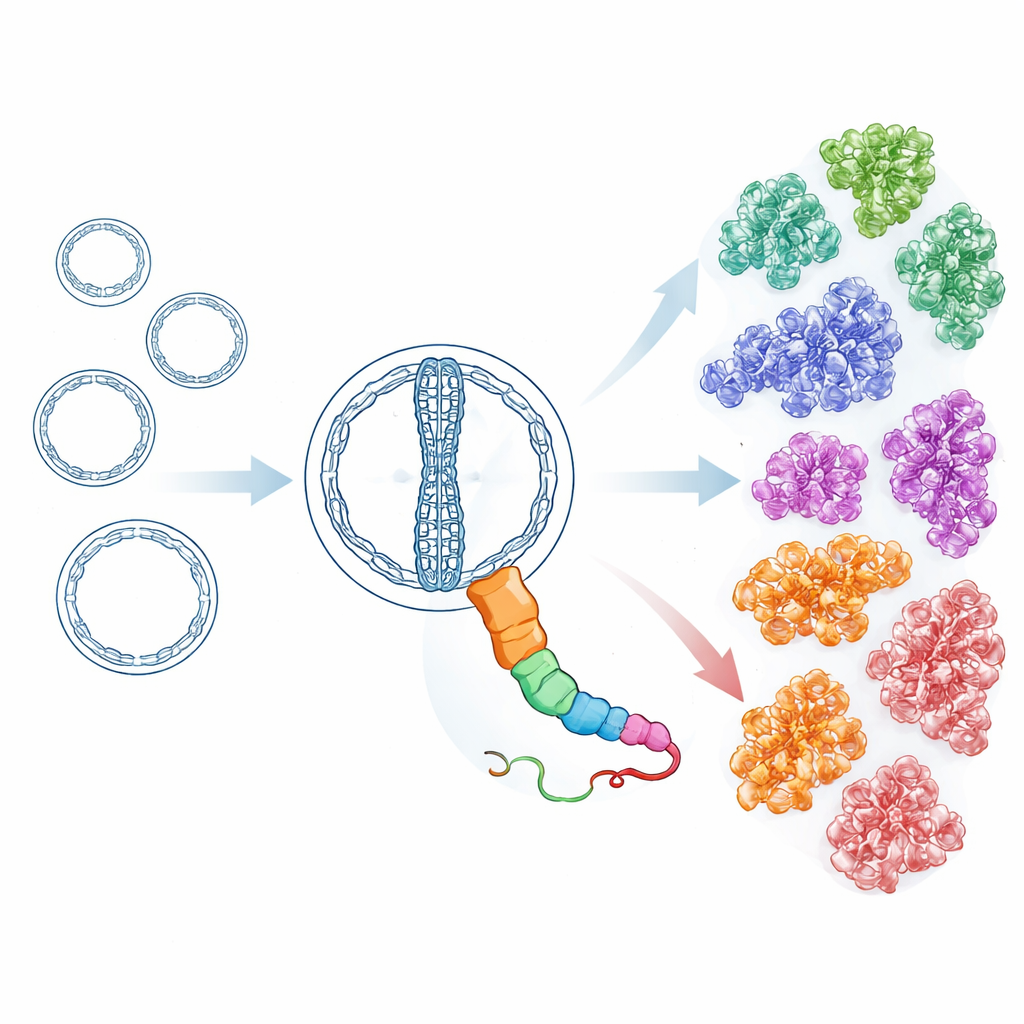
Rastreando hospedadores y estilos de vida a través del árbol de la vida
Para entender con quién conviven estos círculos de ARN, el equipo buscó coincidencias entre secuencias Obelisk y espaciadores CRISPR, registros genéticos cortos que bacterias y arqueas conservan de infecciones pasadas. Encontraron docenas de coincidencias convincentes, especialmente en bacterias que habitan el tracto intestinal de humanos y rumiantes, lo que refuerza la idea de que los Obelisks infectan o coexisten comúnmente con bacterias. Junto con trabajos previos que encontraron Obelisks en la boca humana y en aguas marinas, estos resultados sugieren que los Obelisks no son rarezas curiosas, sino miembros ampliamente distribuidos de las comunidades microbianas, desde océanos y fuentes termales hasta microbiomas animales. No obstante, quedan muchos interrogantes: no está claro si los Obelisks se comportan más como plásmidos (elementos genéticos extra que se mantienen dentro de una línea celular) o como agentes infecciosos que se propagan entre hospedadores, y los detalles de cómo se copian aún se desconocen.
Qué significa esto para nuestra visión de la diversidad de la vida
Para un público no especialista, estos hallazgos muestran que incluso en lugares tan inhóspitos como piscinas ácidas casi hirvientes, la evolución ha llenado el mundo microscópico con entidades genéticas poco convencionales. Los Obelisks de fuentes termales demuestran que los replicones de ARN circulares con un pliegue proteico compartido pueden prosperar a altas temperaturas y en hábitats muy distintos. Al casi duplicar la diversidad conocida de Obelisks y mapear a sus probables socios bacterianos, este estudio revela una vasta capa de vida genética previamente invisible. Sugiere que los replicones simples basados en ARN no son solo reliquias históricas, sino actores activos y adaptables en el biosfera actual, moldeando silenciosamente los ecosistemas microbianos en todo el planeta.
Cita: Urayama, Si., Fukudome, A., Mutz, P. et al. Identification of hot spring Obelisk-like RNA replicons and expanded diversity of the Obelisk superfamily. Nat Commun 17, 3041 (2026). https://doi.org/10.1038/s41467-026-71096-6
Palabras clave: ARN circular, fuentes termales, ecosistemas microbianos, replicones de ARN, elementos Obelisk