Clear Sky Science · de
Identifizierung von obeliskähnlichen RNA-Repliconen in heißen Quellen und erweiterte Vielfalt der Obelisk-Superfamilie
Verborgene Kreise in extremen heißen Quellen
Beinahe kochendheiße, saure Quellen wirken wie Orte, an denen Leben auseinanderfallen sollte. Doch diese rauen Becken wimmeln von Mikroben – und, wie diese Studie zeigt, von winzigen ringförmigen RNA-Molekülen, die still und leise sich selbst kopieren. Die Forschenden wollten herausfinden, ob eine rätselhafte Klasse von RNA-Kreisen, bekannt als Obelisken, auch in solchen extremen Umgebungen vorkommt. Dabei entdeckten sie neue Mitglieder dieser eigenartigen Familie und zeigten, dass diese mikroskopischen „Coderingskreise“ in den Ökosystemen der Erde viel häufiger und vielfältiger sind, als bisher angenommen.
Worin sich winzige RNA-Ringe von vertrauten Viren unterscheiden
Die meisten Menschen kennen Viren als Partikel, die DNA oder RNA tragen und mehrere Proteine kodieren. Viroide und verwandte Agenzien sind anders. Es sind kurze RNA-Schleifen, die sich oft zu stabförmigen Gestalten falten und möglicherweise keine Proteine kodieren. Sie kapern die Maschinerie ihrer Wirtszellen zur Replikation, schädigen manchmal Nutzpflanzen, bleiben ansonsten jedoch meist unauffällig. In den letzten Jahren hat Hochdurchsatz-Sequenzierung von Umwelt-RNA einen Zoo solcher zirkulärer Moleküle in Lebensräumen mit wenigen Pflanzen oder Tieren offenbart, was darauf hindeutet, dass auch Mikroben diese minimalen genetischen Elemente beherbergen können. Zu ihnen gehören Obelisken, zirkuläre RNAs von etwa tausend Bausteinen Länge, die ein einzelnes Protein mit zuvor unbekannter dreidimensionaler Gestalt kodieren.
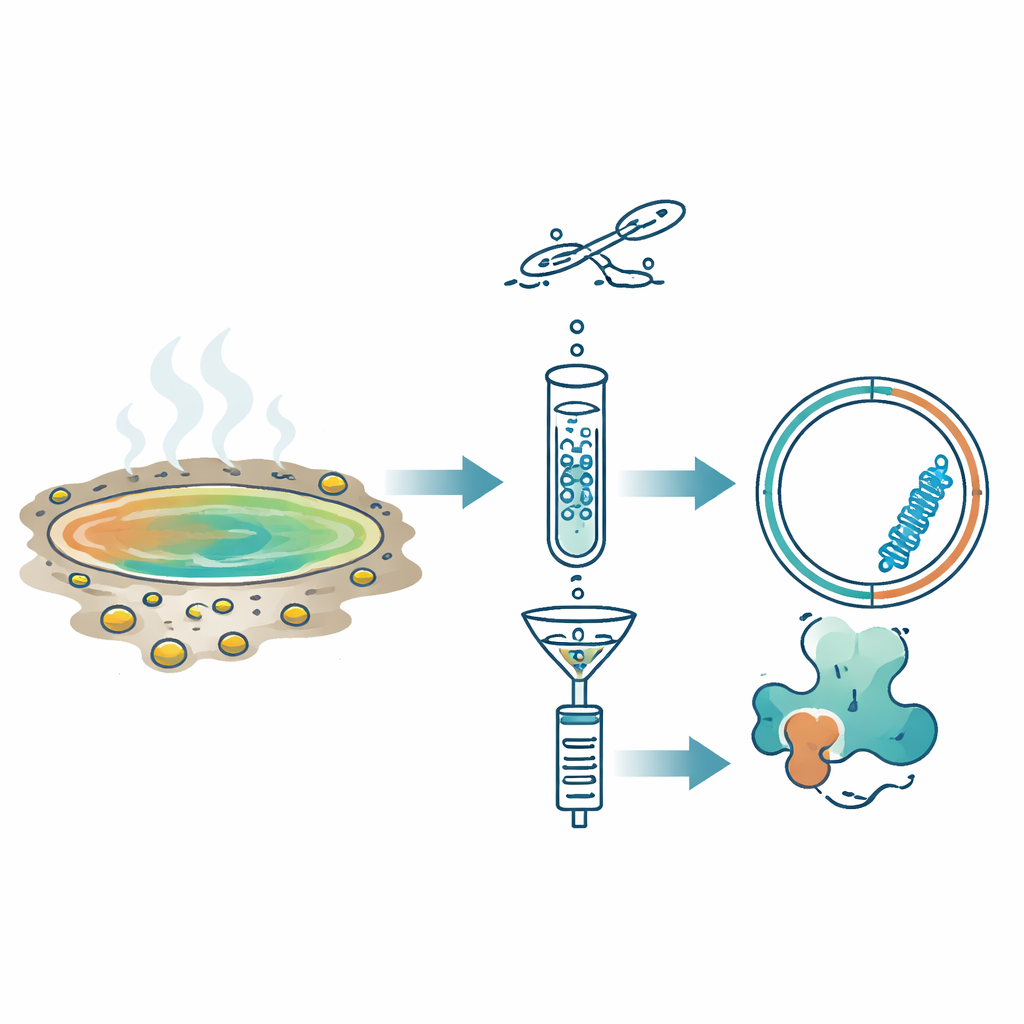
Neue RNA-Kreise finden durch Lesen doppelsträngiger Zwischenformen
Anstatt direkt nach bekannten Sequenzen zu suchen, nutzte das Team ein anderes Kennzeichen von RNA-Replicons: Während der Kopie bilden sie kurzzeitig doppelsträngige RNA. Sie wandten eine Methode namens Fragmented and primer-Ligated DsRNA Sequencing (FLDS) an, die diese doppelsträngigen Formen aus Umweltproben anreichert. Nachdem sie doppelsträngige RNA aus elf sauren Quellen in Japan gereinigt hatten, sequenzierten sie diese und wendeten eine schrittweise Filterpipeline an. Behalten wurden nur Moleküle, die kreisförmig erschienen, gut durch Sequenzierungsreads abgedeckt waren und sich zu stabilen, stabförmigen Strukturen falten ließen. Zur Validierung bestätigten sie zunächst, dass die Methode ein bekanntes Pflanzenviroid in infizierten Chrysanthemenblättern wiederfinden konnte. Anschließend isolierten sie mit derselben Logik aus den heißen Quellproben einen auffälligen Kandidaten, den sie Hot spring Obelisk (HsOb) nannten.
Neue Obelisken gedeihen in beinahe kochendheißen sauren Becken
Die Schlüssel-RNA, entdeckt in einer Quelle namens Oi, war etwa 870 Nukleotide lang und bildete selbst bei Modellen für 80 °C – der Wassertemperatur vor Ort – eine ausgedehnte stabförmige Struktur. Sie enthielt ein einzelnes langes offenes Lesegerüst, das ein Protein von 213 Aminosäuren ergeben würde, bezeichnet als HsOblin-1. Obwohl die Aminosäuresequenz kaum Ähnlichkeit mit bekannten Proteinen zeigte, offenbarten Strukturvorhersage-Tools, dass HsOblin-1 dieselbe Grundarchitektur wie das ursprüngliche Obelisk-Protein Oblin-1 aufweist: einen kompakten, α-Helix-reichen Kern gefolgt von einem flexiblen, positiv geladenen Schwanz, der vermutlich zum Greifen von RNA geeignet ist. Eine verwandte RNA aus einer anderen Quelle, H5, kodierte ein ähnliches Protein. Die mikrobiellen Gemeinschaften in diesen Proben wurden von thermoacidophilen Bakterien der Familie Hydrogenobaculaceae dominiert, was diese Bakterien zu führenden Wirtskandidaten für die heißen Quellen-Obelisken macht, auch wenn eine direkte Zuweisung der Wirte noch nachgewiesen werden muss.
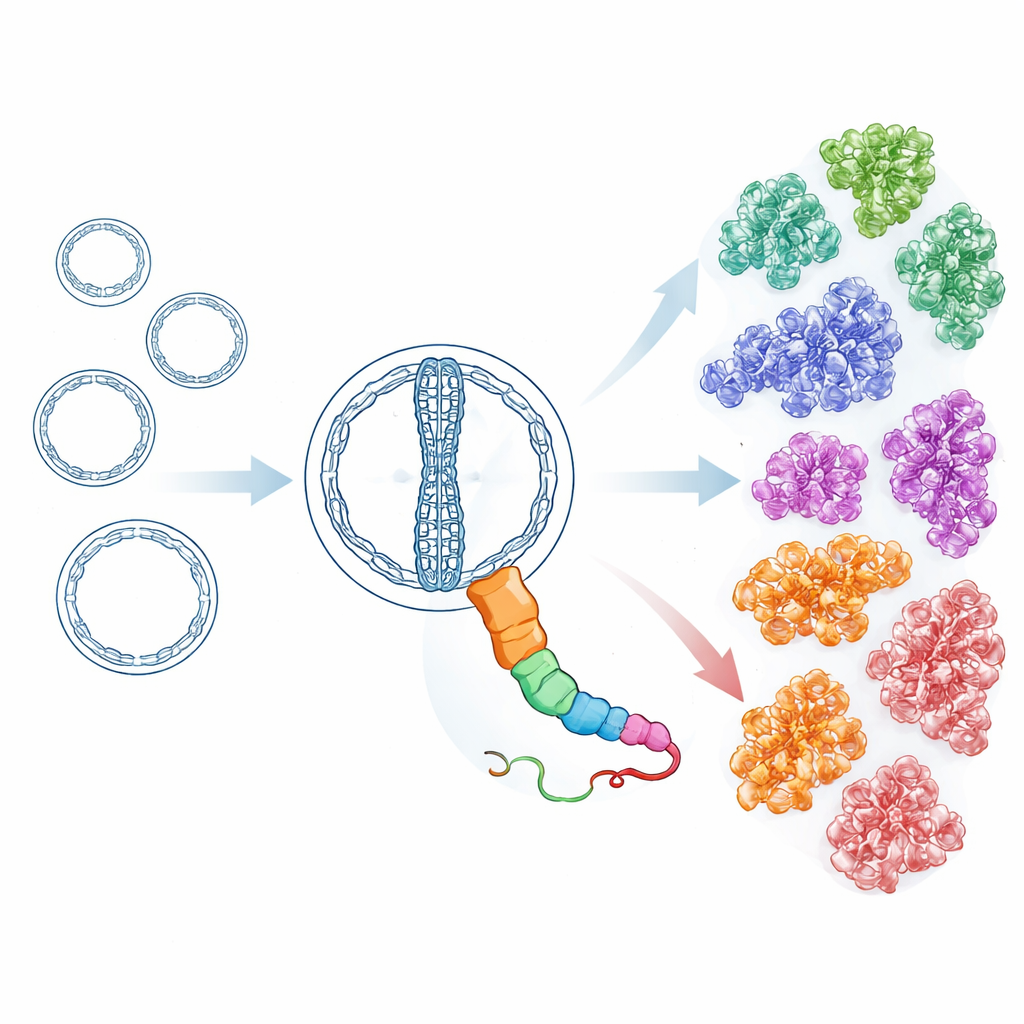
Eine globale Untersuchung zeigt eine große und vielfältige Familie
Mit empfindlichen, struktur-sensitiven Suchwerkzeugen durchkämmten die Forschenden anschließend Millionen potenzieller zirkulärer RNAs aus mehr als 7.000 Umwelt-Metatranskriptomen sowie weitere Datensätze aus öffentlichen Repositorien. Ausgehend von den HsOblin-1-Proteinen aus der heißen Quelle und dem ursprünglich beschriebenen Oblin-1 bauten sie iterativ Profile auf, die auch entfernte Verwandte erfassen, selbst wenn die Sequenzähnlichkeit gering ist. Dieser Aufwand förderte 6.443 verschiedene Proteine mit einem Oblin-ähnlichen Faltmuster zutage, kodiert von mehr als 8.000 Obelisk-RNA-Genomen. Die Gruppierung dieser Proteine nach Ähnlichkeit und nach vorhergestrukturten dreidimensionalen Formen ergab 21 Hauptunterfamilien. Alle teilen denselben Kernfalt, unterscheiden sich jedoch in Oberflächenmerkmalen und in Teilen einer langen, flexiblen Schleife, was nahelegt, dass sie sich diversifiziert haben, um mit unterschiedlichen Wirten oder Partnern zu interagieren, während das grundlegende Replikationswerkzeug intakt blieb. Einige Unterfamilien scheinen zudem zusätzliche kleine Proteine mit einfachen helikalen Formen zu tragen, was auf unabhängig entwickelte Zusatzfunktionen hindeutet.
Wirte und Lebensweisen über den Stammbaum des Lebens zurückverfolgen
Um zu verstehen, mit wem diese RNA-Kreise zusammenleben, suchte das Team nach Übereinstimmungen zwischen Obelisk-Sequenzen und CRISPR-Spacern – kurzen genetischen Aufzeichnungen, die Bakterien und Archaeen über vergangene Infektionen aufbewahren. Sie fanden dutzende überzeugende Treffer, insbesondere in Bakterien, die den Darm von Menschen und Wiederkäuern besiedeln, was die Vorstellung stärkt, dass Obelisken häufig Bakterien infizieren oder mit ihnen koexistieren. In Kombination mit früheren Arbeiten, die Obelisken im menschlichen Mund und im Meerwasser fanden, deuten diese Ergebnisse darauf hin, dass Obelisken keine seltenen Kuriositäten sind, sondern weit verbreitete Mitglieder mikrobieller Gemeinschaften von den Ozeanen über heiße Quellen bis hin zu Tier-Mikrobiomen. Viele Rätsel bleiben jedoch: Es ist unklar, ob Obelisken sich eher wie Plasmide verhalten (zusätzliche genetische Elemente, die innerhalb einer Zelllinie verbleiben) oder wie infektiöse Agenzien, die zwischen Wirten übertragen werden, und die Details ihrer Replikation sind weiterhin unbekannt.
Was das für unser Bild der Vielfalt des Lebens bedeutet
Für Nichtfachleute zeigen diese Ergebnisse, dass selbst an Orten, die so unwirtlich sind wie beinahe kochendheiße Säurebecken, die Evolution die mikroskopische Welt mit unkonventionellen genetischen Einheiten gefüllt hat. Heiße-Quellen-Obelisken beweisen, dass zirkuläre RNA-Replicons mit einem gemeinsamen Proteinfaltmuster bei hohen Temperaturen und in sehr unterschiedlichen Lebensräumen gedeihen können. Indem die Studie die bekannte Vielfalt der Obelisken nahezu verdoppelt und ihre wahrscheinlichen bakteriellen Partner kartiert, offenbart sie eine große, bislang ungesehene Schicht genetischen Lebens. Sie legt nahe, dass einfache RNA-basierte Replicons nicht nur historische Relikte sind, sondern aktive, anpassungsfähige Akteure in der heutigen Biosphäre, die still und leise mikrobielle Ökosysteme auf dem Planeten mitgestalten.
Zitation: Urayama, Si., Fukudome, A., Mutz, P. et al. Identification of hot spring Obelisk-like RNA replicons and expanded diversity of the Obelisk superfamily. Nat Commun 17, 3041 (2026). https://doi.org/10.1038/s41467-026-71096-6
Schlüsselwörter: zirkuläre RNA, heiße Quellen, mikrobielle Ökosysteme, RNA-Replicons, Obelisk-Elemente