Clear Sky Science · it
Identificazione di repliconi di RNA a forma di obelisco nelle sorgenti termali e diversità ampliata della superfamiglia Obelisk
Cerchi nascosti nelle sorgenti termali estreme
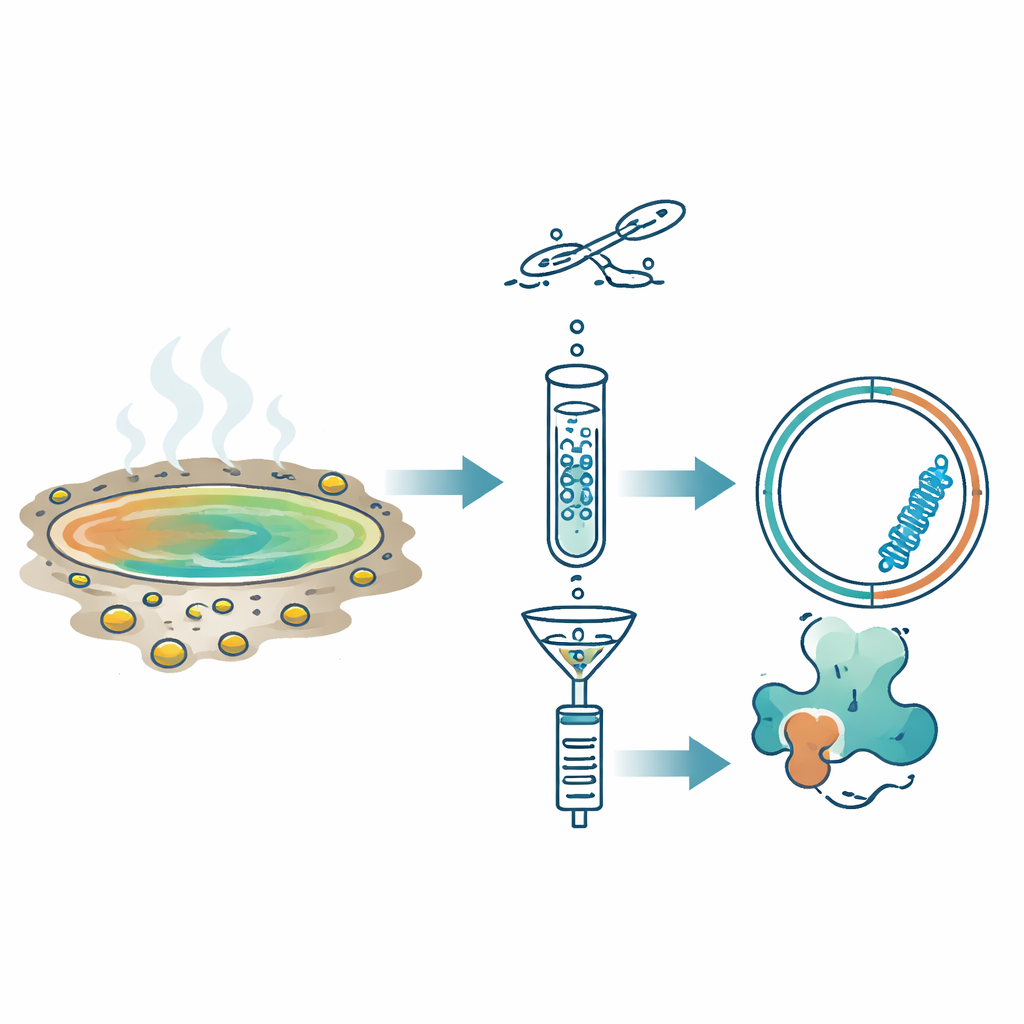
Sorgenti termali acide quasi bollenti sembrano luoghi in cui la vita dovrebbe disgregarsi. Eppure queste vasche aspre sono brulicanti di microbi e, come mostra questo studio, di minuscole molecole di RNA ad anello che si copiano silenziosamente. I ricercatori hanno cercato di capire se una classe misteriosa di cerchi di RNA, nota come Obelisk, vivesse anche in questi ambienti estremi. Nel farlo hanno scoperto nuovi membri di questa famiglia insolita e dimostrato che questi microscopici “cerchi di codice” sono molto più comuni e vari nella biosfera terrestre di quanto si pensasse.
In che modo i piccoli anelli di RNA differiscono dai virus noti
La maggior parte delle persone conosce i virus come particelle che trasportano DNA o RNA che codificano diversi proteine. I viroidi e agenti simili sono diversi. Si tratta di brevi anelli di RNA che spesso si ripiegano in strutture a forma di barra e possono non codificare alcuna proteina. Sfruttano la macchina molecolare della cellula ospite per replicarsi, talvolta danneggiando colture, ma per il resto restano poco noti. Negli ultimi anni, il sequenziamento ad alto rendimento di RNA ambientale ha rivelato uno zoo di tali molecole circolari in luoghi con poche piante o animali, suggerendo che anche i microbi possano ospitare questi elementi genetici minimali. Tra questi ci sono gli Obelisk, RNA circolari di circa mille unità costitutive che codificano una singola proteina con una forma tridimensionale precedentemente sconosciuta.
Trovare nuovi cerchi di RNA leggendo gli intermedi a doppio filamento
Invece di cercare direttamente sequenze note, il team ha usato un altro segnale caratteristico dei repliconi di RNA: durante la copia formano brevemente RNA a doppio filamento. Hanno applicato un metodo chiamato Fragmented and primer-Ligated DsRNA Sequencing (FLDS), che arricchisce queste forme a doppio filamento dai campioni ambientali. Dopo aver purificato l’RNA a doppio filamento da undici sorgenti termali acide in Giappone, lo hanno sequenziato e analizzato con una pipeline di filtraggio passo-passo. Sono stati conservati solo i molecole che apparivano circolari, erano ben coperte dalle letture di sequenziamento e si ripiegavano in strutture stabili a forma di barra. Per convalidare l’approccio hanno prima confermato che fosse in grado di riscoprire un viroide vegetale noto in foglie di crisantemo infette. Poi, applicando la stessa logica ai campioni delle sorgenti termali, hanno isolato un candidato di spicco che hanno chiamato Hot spring Obelisk (HsOb).
Nuovi Obelisk che prosperano in pozze acide quasi bollenti
L’RNA chiave scoperto in una sorgente chiamata Oi era lungo circa 870 nucleotidi e formava una struttura allungata a barra anche quando modellato a 80 °C, la temperatura dell’acqua sul sito. Conteneva un unico lungo frame di lettura aperto che produrrebbe una proteina di 213 amminoacidi, denominata HsOblin-1. Sebbene la sua sequenza amminoacidica mostrasse quasi nessuna somiglianza con proteine note, gli strumenti di predizione strutturale hanno rivelato che HsOblin-1 si ripiega nella stessa architettura di base della proteina Obelisk originale, Oblin-1: un nucleo compatto ricco di eliche α seguito da una coda flessibile e carica positivamente probabilmente adatta a legare l’RNA. Un RNA correlato proveniente da un’altra sorgente, H5, codificava una proteina simile. Le comunità microbiche in questi campioni erano dominate da batteri termoacidofili della famiglia Hydrogenobaculaceae, rendendo questi batteri i candidati principali come ospiti per gli Obelisk delle sorgenti termali, anche se l’assegnazione diretta dell’ospite deve ancora essere dimostrata.
Un’indagine globale mostra una famiglia vasta e variegata
Muniti di strumenti di ricerca sensibili e consapevoli della struttura, i ricercatori hanno quindi scandagliato milioni di presunti RNA circolari provenienti da oltre 7.000 metatranscrittomi ambientali, insieme ad altri dataset di repository pubblici. Partendo dalle proteine HsOblin-1 delle sorgenti termali e dalla Oblin-1 descritta inizialmente, hanno costruito iterativamente profili capaci di catturare parenti distanti anche quando la similarità di sequenza è debole. Questo sforzo ha portato alla scoperta di 6.443 proteine distinte con un ripiegamento simile a Oblin, codificate da più di 8.000 genomi di RNA Obelisk. Raggruppando queste proteine per similarità e per struttura tridimensionale predetta sono emerse 21 sottogruppi principali. Tutti condividono lo stesso nucleo di ripiegamento ma differiscono nelle caratteristiche superficiali e in parti di una lunga ansa flessibile, suggerendo che si siano diversificati per interagire con ospiti o partner diversi mantenendo intatto l’insieme di base per la replicazione. Alcuni sottogruppi sembrano anche portare piccole proteine aggiuntive con forme elicoidali semplici, suggerendo funzioni accessorie evolutesi indipendentemente.
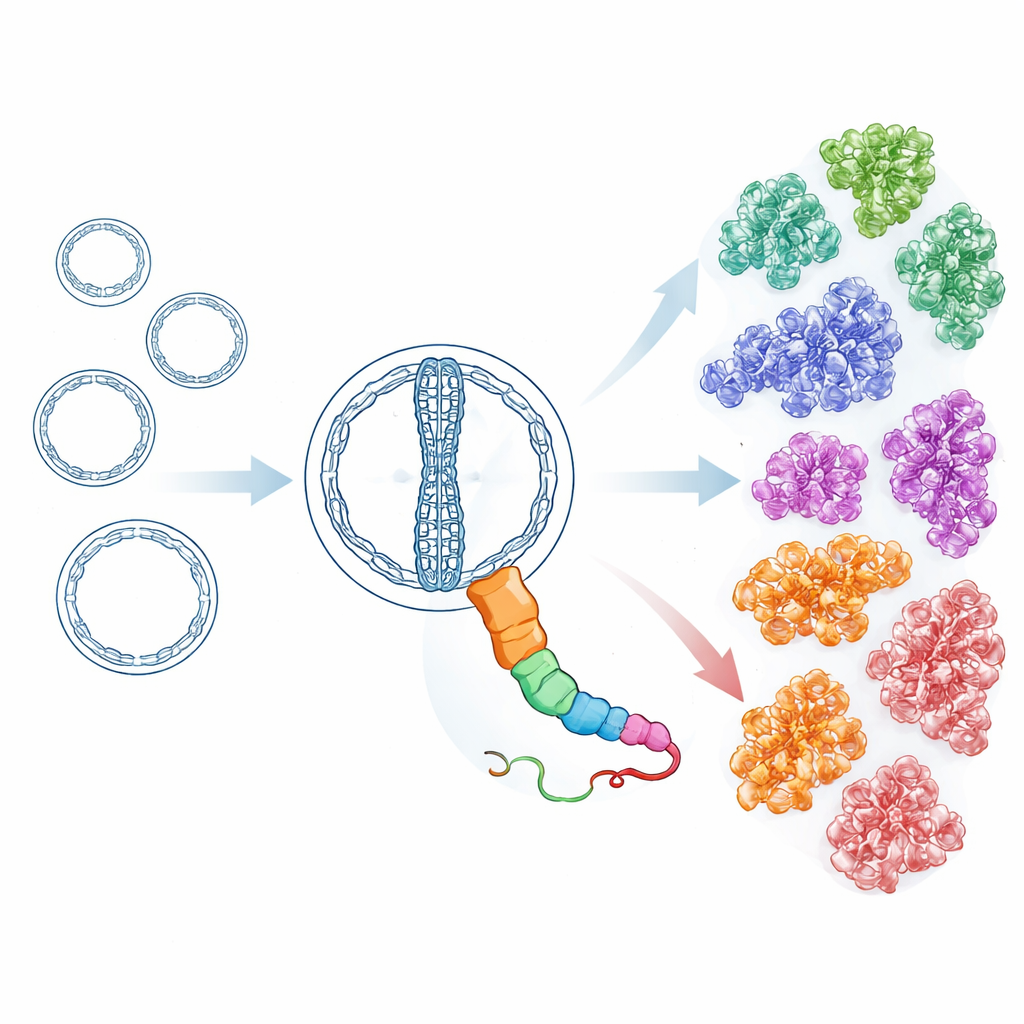
Ricostruire ospiti e stili di vita attraverso l’albero della vita
Per capire con chi convivono questi cerchi di RNA, il team ha cercato corrispondenze tra sequenze Obelisk e spacer CRISPR: brevi registri genetici che batteri e archaea conservano di infezioni passate. Hanno trovato dozzine di corrispondenze convincenti, soprattutto in batteri che abitano l’intestino umano e dei ruminanti, rafforzando l’idea che gli Obelisk comunemente infettino o coesistano con i batteri. Unito a lavori precedenti che avevano trovato Obelisk nella bocca umana e nelle acque marine, questi risultati suggeriscono che gli Obelisk non sono curiosità rare, ma membri diffusi delle comunità microbiche dagli oceani alle sorgenti termali fino ai microbiomi animali. Restano però molti enigmi: non è chiaro se gli Obelisk si comportino più come plasmidi (elementi genetici extra che si mantengono in una linea cellulare) o come agenti infettivi che si diffondono tra ospiti, e i dettagli di come si copiano rimangono ignoti.
Cosa significa questo per la nostra visione della diversità della vita
Per un non specialista, questi risultati mostrano che anche in luoghi tanto inospitali quanto pozze acide quasi bollenti, l’evoluzione ha popolato il mondo microscopico con entità genetiche non convenzionali. Gli Obelisk delle sorgenti termali dimostrano che repliconi di RNA circolari con un nucleo proteico condiviso possono prosperare ad alte temperature e in habitat molto diversi. Casi quasi raddoppiando la diversità nota di Obelisk e mappando i loro probabili partner batterici, questo studio rivela uno strato vasto e prima invisibile di vita genetica. Suggerisce che repliconi semplici a base di RNA non sono soltanto relitti storici, ma attori attivi e adattabili nella biosfera odierna, che modellano silenziosamente gli ecosistemi microbici su scala planetaria.
Citazione: Urayama, Si., Fukudome, A., Mutz, P. et al. Identification of hot spring Obelisk-like RNA replicons and expanded diversity of the Obelisk superfamily. Nat Commun 17, 3041 (2026). https://doi.org/10.1038/s41467-026-71096-6
Parole chiave: RNA circolare, sorgenti termali, ecosistemi microbici, repliconi di RNA, elementi Obelisk