Clear Sky Science · pt
Resistência antimicrobiana, plasmídeos conjugativos e patogenicidade em Escherichia spp. de águas residuais e águas doces em Estocolmo, Suécia
Por que a água e os micróbios importam no cotidiano
A maioria das pessoas associa resistência a antibióticos a hospitais, mas este estudo mostra como ela também pode ser moldada pela água que corre sob nossas cidades e banha nossas praias. Pesquisadores em Estocolmo, Suécia, acompanharam bactérias de estações de tratamento de esgoto e de lagos e águas costeiras próximas para responder a uma pergunta simples, porém urgente: nossos sistemas de esgoto estão ajudando a espalhar micróbios difíceis de tratar de volta ao ambiente onde as pessoas nadam, se divertem e captam água potável?
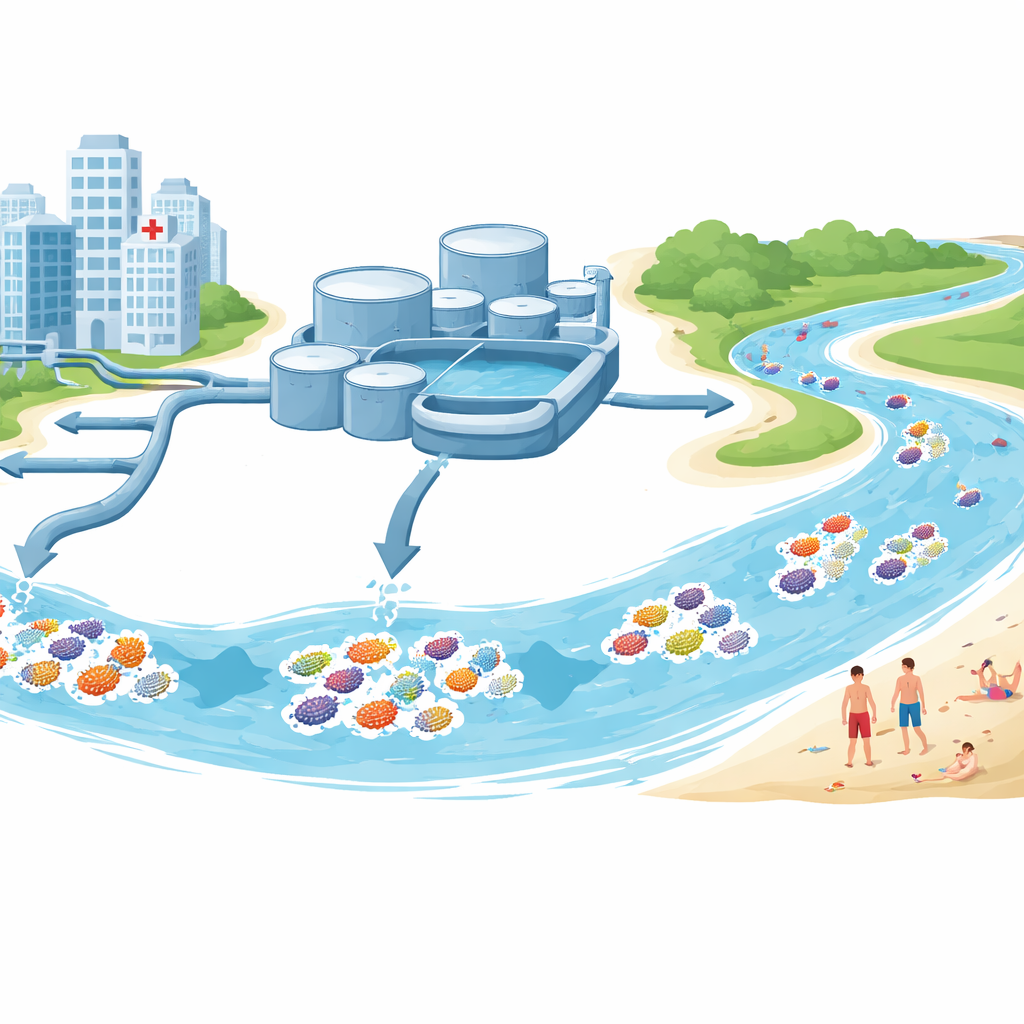
De onde vieram as amostras
A equipe coletou água e sedimento na região de Estocolmo durante o verão de 2022. Algumas amostras foram obtidas nas entradas e saídas de grandes estações de tratamento de águas residuais que recebem esgoto de residências e hospitais. Outras foram tiradas de lagos de água doce e praias de água salobra do Mar Báltico usadas para recreação. Dessas localidades isolaram 68 linhagens de espécies do gênero Escherichia, em sua maioria E. coli, uma bactéria intestinal comum que também é marcador padrão de contaminação fecal. Cada linhagem foi testada em laboratório para verificar a que antibióticos resistia e posteriormente teve seu DNA decodificado para revelar genes de resistência, genes relacionados à doença e os pequenos círculos de DNA chamados plasmídeos que podem pular entre bactérias.
Resistência mais forte em esgoto do que em águas naturais
O contraste entre esgoto e água natural foi marcante. Mais da metade das linhagens de E. coli provenientes de águas residuais eram resistentes a pelo menos três classes de antibióticos, e muitas carregavam grupos de genes de resistência, incluindo aqueles que inativam drogas amplamente usadas da terceira geração de cefalosporinas. Em particular, genes da família CTX‑M, e especialmente a variante CTX‑M‑15, eram comuns nas linhagens de esgoto, mas totalmente ausentes nas linhagens coletadas em lagos e praias. Várias bactérias de esgoto pertenciam a linhagens conhecidas por causar infecções do trato urinário e da corrente sanguínea em humanos, incluindo o problemático grupo global ST131, e essas apresentavam alguns dos maiores acúmulos de genes de resistência.
Resíduos de antibióticos e DNA móvel
Testes químicos na água mostraram que resíduos de antibióticos eram consistentemente mais altos nas entradas e saídas de estações de tratamento do que em locais naturais. Níveis do antibiótico ciprofloxacino em uma entrada e em uma saída ultrapassaram limites publicados acima dos quais se espera que a resistência seja favorecida. Esse pano de fundo químico importa porque muitos genes de resistência estavam localizados em plasmídeos conjugativos — círculos de DNA móveis que podem se mover de uma bactéria para outra. Em experimentos de conjugação em laboratório, plasmídeos de 16 linhagens transferiram-se com sucesso para uma linhagem receptora padrão, frequentemente levando resistência a múltiplos fármacos de uma só vez. Plasmídeos de certas famílias, especialmente IncN e IncI, moveram‑se com eficiência particularmente alta, o que sugere que são veículos potentes para espalhar resistência no ambiente lotado e rico em nutrientes dos sistemas de esgoto.
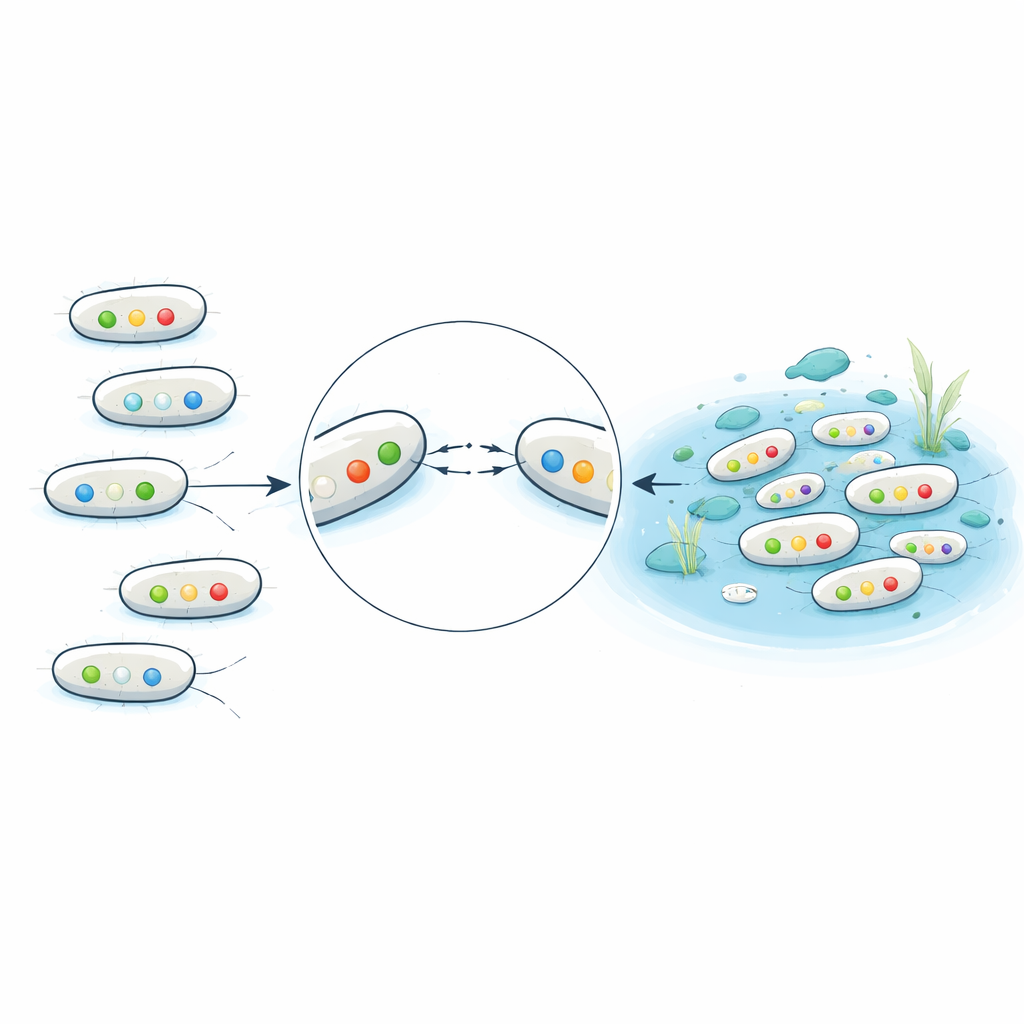
Traços ligados à doença em águas do dia a dia
Além da resistência a medicamentos, os cientistas buscaram nos genomas genes que ajudam a E. coli a causar doença, como aqueles para toxinas, adesinas que permitem às bactérias aderir ao intestino ou ao trato urinário, e fatores que as protegem na corrente sanguínea. Muitos isolados de esgoto carregavam combinações de genes típicas de patógenos extra‑intestinais e de trato urinário, ecoando padrões observados em infecções clínicas. Surpreendentemente, uma grande fração de E. coli de lagos e praias aparentemente limpos também apresentava alguns desses genes de virulência, embora em geral tivessem menos genes de resistência e nenhum gene de beta‑lactamase de amplo espectro. O estudo também encontrou parentes ambientais, como Escherichia marmotae, que carregavam genes associados a doenças, sugerindo que a vida selvagem e as águas naturais podem abrigar patógenos em potencial.
O que isso significa para pessoas e políticas públicas
Em conjunto, os achados colocam as estações de tratamento de águas residuais como cruzamentos importantes onde bactérias humanas, animais e ambientais se misturam, são expostas a antibióticos remanescentes e trocam DNA móvel que pode torná‑las tanto mais resistentes a fármacos quanto mais capazes de causar doença. Embora as estações removam muitos contaminantes, elas não eliminam totalmente E. coli resistentes ou patogênicos, e algumas dessas linhagens e seus plasmídeos são lançados em rios e águas costeiras usadas pelo público. Para leitores não especialistas, a mensagem central é que a resistência a antibióticos não se limita aos hospitais: ela é influenciada pela forma como tratamos águas residuais e protegemos as águas naturais. Monitorar esgotos e águas recreativas próximas, reduzir o uso de antibióticos e melhorar as tecnologias de tratamento pode ajudar a retardar a “reciclagem” ambiental de micróbios perigosos de volta para as pessoas.
Citação: Justh de Neczpal, A., Thorell, K., Tuts, L. et al. Antimicrobial resistance, conjugative plasmids and pathogenicity in wastewater and freshwater Escherichia spp. in Stockholm, Sweden. npj Antimicrob Resist 4, 32 (2026). https://doi.org/10.1038/s44259-026-00208-5
Palavras-chave: resistência a antibióticos, estação de tratamento de águas residuais, E. coli, microbiologia ambiental, transferência de plasmídeos