Clear Sky Science · es
Resistencia antimicrobiana, plásmidos conjugativos y patogenicidad en Escherichia spp. de aguas residuales y de agua dulce en Estocolmo, Suecia
Por qué el agua y los gérmenes importan en la vida cotidiana
La mayoría de la gente asocia la resistencia a los antibióticos con los hospitales, pero este estudio muestra cómo también puede formarse y propagarse en las aguas que fluyen bajo nuestras ciudades y bañan nuestras playas. Investigadores en Estocolmo, Suecia, siguieron bacterias procedentes de plantas de tratamiento de aguas residuales y de lagos y aguas costeras cercanas para plantear una pregunta simple pero urgente: ¿están nuestras tuberías de desagüe ayudando a difundir gérmenes difíciles de tratar de nuevo en el entorno donde la gente nada, se recrea y obtiene agua potable?
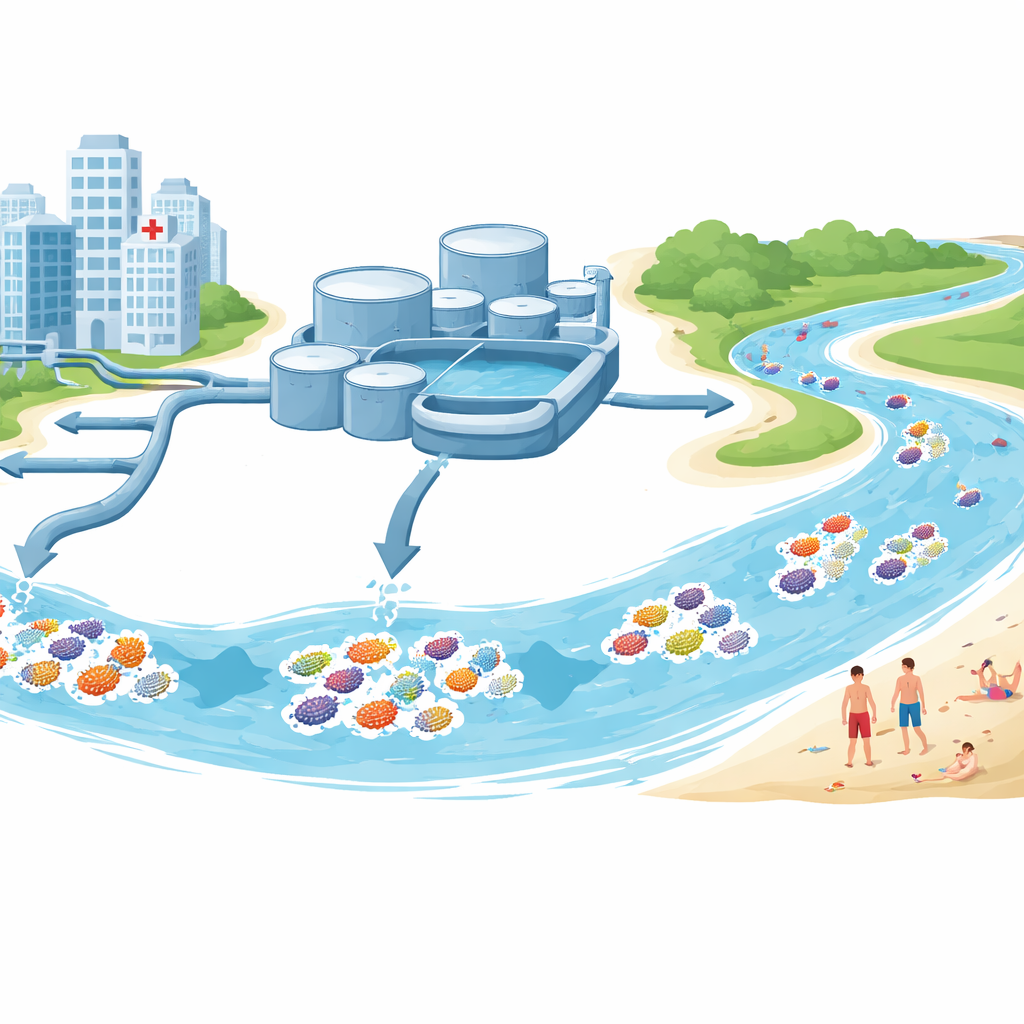
De dónde procedían las muestras
El equipo recogió agua y sedimentos en y alrededor de Estocolmo durante el verano de 2022. Algunas muestras provinieron de las entradas y salidas de grandes plantas de tratamiento de aguas residuales que reciben aguas domésticas y hospitalarias. Otras se tomaron de lagos de agua dulce y playas del Báltico de agua salobre utilizadas para recreo. De estos lugares aislaron 68 cepas de especies de Escherichia, mayoritariamente E. coli, una bacteria intestinal común que también se utiliza como marcador estándar de contaminación fecal. Cada cepa se sometió a pruebas en el laboratorio para determinar a qué antibióticos resistía y luego se secuenció su ADN para revelar sus genes de resistencia, genes relacionados con la enfermedad y los pequeños círculos de ADN llamados plásmidos que pueden saltar entre bacterias.
Resistencia más fuerte en aguas residuales que en aguas naturales
El contraste entre las aguas residuales y las aguas naturales fue llamativo. Más de la mitad de las cepas de E. coli procedentes de aguas residuales eran resistentes al menos a tres clases de antibióticos, y muchas portaban racimos de genes de resistencia, incluidos aquellos que neutralizan cefalosporinas de tercera generación ampliamente utilizadas. En particular, los genes de la familia CTX‑M, y especialmente la variante CTX‑M‑15, eran comunes en las cepas de aguas residuales pero estaban totalmente ausentes en las cepas tomadas de lagos y playas. Varias bacterias de aguas residuales pertenecían a linajes bien conocidos que causan infecciones del tracto urinario y bacteriemias en humanos, incluido el problemático grupo ST131 a nivel mundial, y estas portaban algunas de las mayores cargas de genes de resistencia.
Residuos de antibióticos y ADN móvil
Los análisis químicos del agua mostraron que los residuos de antibióticos eran sistemáticamente más altos en las entradas y salidas de las plantas de aguas residuales que en los sitios naturales. Los niveles del fármaco ciprofloxacino en una entrada y en una salida superaron umbrales publicados por encima de los cuales se espera que se favorezca la resistencia. Este telón químico importa porque muchos genes de resistencia se localizaron en plásmidos conjugativos: círculos de ADN móviles que pueden moverse de una bacteria a otra. En experimentos de apareamiento en laboratorio, los plásmidos de 16 cepas se transfirieron con éxito a una cepa receptora estándar, a menudo llevando consigo resistencia a múltiples fármacos a la vez. Plásmidos de ciertas familias, especialmente IncN e IncI, se movieron con particular alta eficiencia, lo que sugiere que son vehículos potentes para la difusión de la resistencia en el ambiente concurrido y rico en nutrientes de los sistemas de alcantarillado.
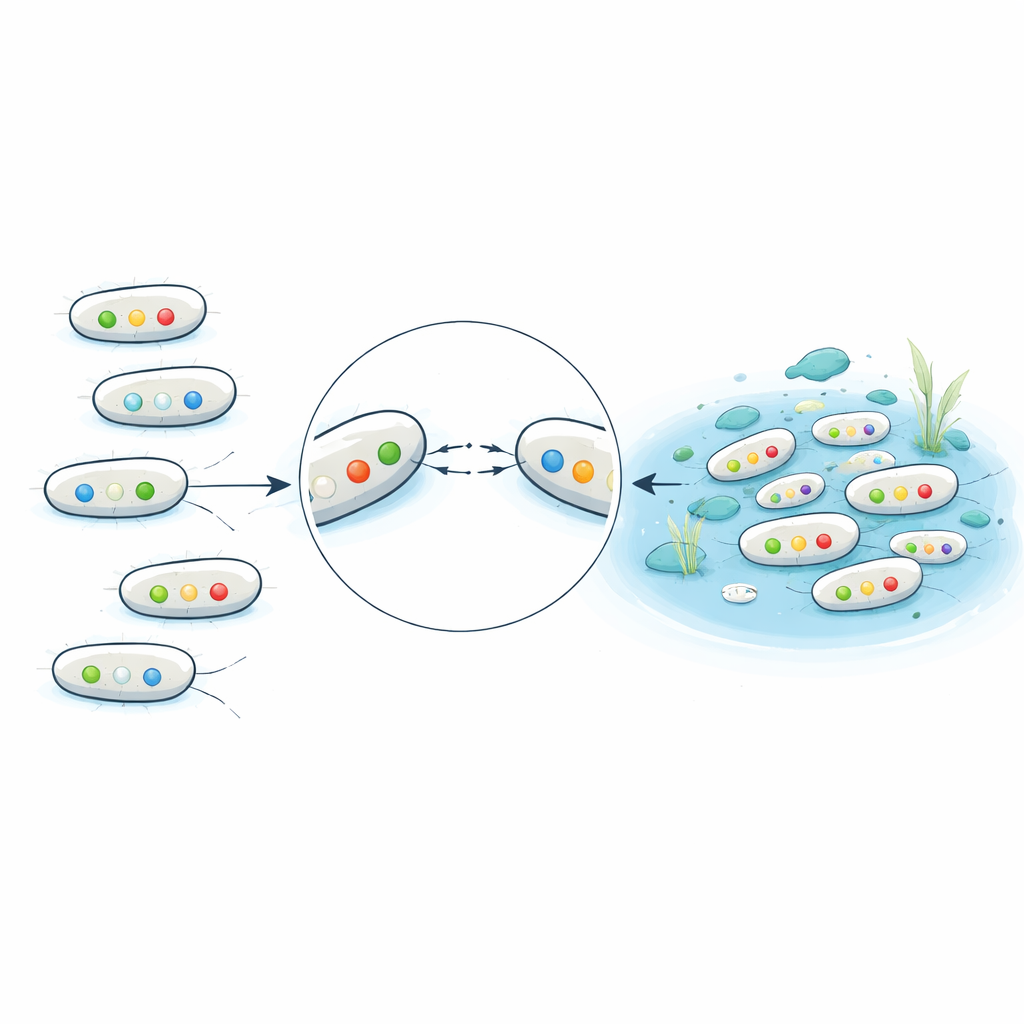
Rasgos vinculados a la enfermedad en aguas de uso cotidiano
Más allá de la resistencia a los fármacos, los científicos buscaron en los genomas genes que ayudan a E. coli a causar enfermedad, como los de toxinas, adhesinas que permiten a las bacterias adherirse al intestino o al tracto urinario, y factores que las protegen en la sangre. Muchos aislamientos de aguas residuales llevaban combinaciones de genes típicas de patógenos extraintestinales y del tracto urinario, reflejando patrones observados en infecciones clínicas. Sorprendentemente, una gran fracción de E. coli de lagos y playas aparentemente limpios también portaba algunos de estos genes de virulencia, aunque generalmente tenían menos genes de resistencia y carecían de genes de beta‑lactamasas de espectro extendido. El estudio también halló parientes ambientales como Escherichia marmotae que llevaban genes asociados a enfermedad, lo que sugiere que la fauna silvestre y las aguas naturales pueden albergar patógenos latentes.
Qué significa esto para la población y las políticas
En conjunto, los hallazgos presentan a las plantas de tratamiento de aguas residuales como cruces importantes donde bacterias humanas, animales y ambientales se mezclan, se exponen a antibióticos residuales e intercambian ADN móvil que puede volverlas tanto más resistentes a los fármacos como más capaces de causar enfermedad. Aunque las plantas eliminan muchos contaminantes, no erradican por completo las E. coli resistentes o potencialmente patógenas, y algunas de estas cepas y sus plásmidos se descargan en ríos y aguas costeras utilizadas por el público. Para el lector general, el mensaje central es que la resistencia a los antibióticos no se limita a los hospitales: está influida por cómo gestionamos las aguas residuales y protegemos las aguas naturales. Monitorizar las aguas residuales y las aguas recreativas cercanas, reducir el uso de antibióticos y mejorar las tecnologías de tratamiento pueden ayudar a frenar el “reciclaje” ambiental de gérmenes peligrosos de vuelta a las personas.
Cita: Justh de Neczpal, A., Thorell, K., Tuts, L. et al. Antimicrobial resistance, conjugative plasmids and pathogenicity in wastewater and freshwater Escherichia spp. in Stockholm, Sweden. npj Antimicrob Resist 4, 32 (2026). https://doi.org/10.1038/s44259-026-00208-5
Palabras clave: resistencia a antibióticos, tratamiento de aguas residuales, E. coli, microbiología ambiental, transferencia de plásmidos