Clear Sky Science · it
Resistenza antimicrobica, plasmidi coniugativi e patogenicità in Escherichia spp. delle acque reflue e dolci a Stoccolma, Svezia
Perché l’acqua e i germi contano nella vita quotidiana
La maggior parte delle persone associa la resistenza agli antibiotici agli ospedali, ma questo studio mostra come essa possa essere plasmata anche dall’acqua che scorre sotto le nostre città e lambisce le nostre spiagge. I ricercatori a Stoccolma, Svezia, hanno seguito batteri provenienti da impianti di trattamento delle acque reflue e da laghi e acque costiere vicine per porre una domanda semplice ma urgente: le nostre condotte fognarie stanno contribuendo a diffondere germi difficili da trattare nell’ambiente dove le persone nuotano, giocano e prendono l’acqua potabile?
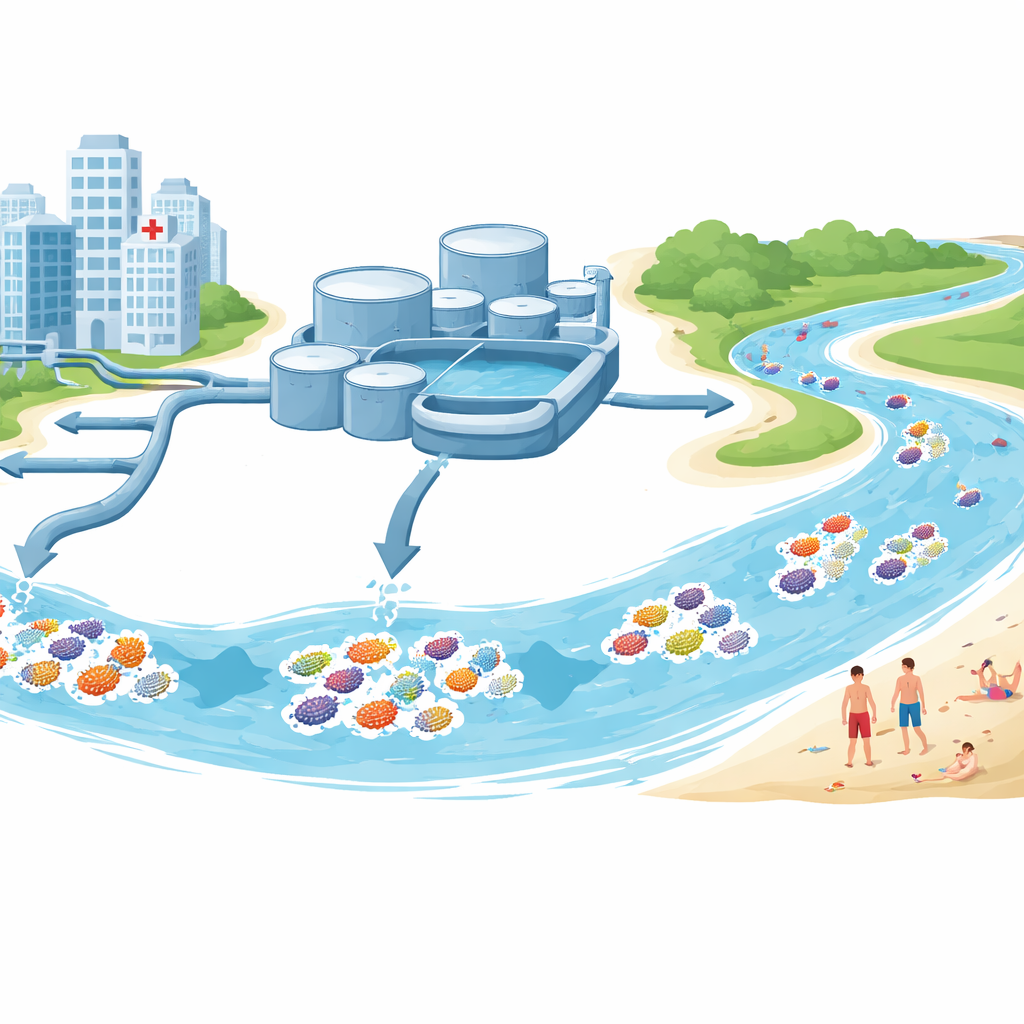
Da dove provenivano i campioni
Il team ha raccolto acqua e sedimenti in e intorno a Stoccolma durante l’estate del 2022. Alcuni campioni provenivano dalle entrate e dalle uscite di grandi impianti di trattamento delle acque reflue che ricevono scarichi domestici e ospedalieri. Altri sono stati prelevati da laghi d’acqua dolce e spiagge salmastre del Mar Baltico usate per svago. Da questi siti sono stati isolati 68 ceppi di specie del genere Escherichia, per lo più E. coli, un comune batterio intestinale che è anche un indicatore standard di contaminazione fecale. Ogni ceppo è stato testato in laboratorio per valutare a quali antibiotici fosse resistente e quindi sottoposto a sequenziamento del DNA per rivelare i suoi geni di resistenza, i geni legati alla patogenicità e i piccoli cerchi di DNA detti plasmidi che possono saltare da un batterio all’altro.
Resistenza più forte nelle acque reflue rispetto alle acque naturali
Il contrasto tra acque reflue e acque naturali è stato marcato. Più della metà dei ceppi di E. coli provenienti dalle acque reflue era resistente ad almeno tre classi di antibiotici, e molti portavano gruppi di geni di resistenza, inclusi quelli che disattivano i comuni cefalosporinici di terza generazione. In particolare, i geni della famiglia CTX‑M, e in special modo la variante CTX‑M‑15, erano comuni nei ceppi delle acque reflue ma del tutto assenti nei ceppi prelevati da laghi e spiagge. Diversi batteri delle acque reflue appartenevano a lignaggi noti per causare infezioni delle vie urinarie e batteriemie nell’uomo, inclusi il problematico gruppo globale ST131, e questi portavano alcuni dei maggiori carichi di geni di resistenza.
Residui di antibiotici e DNA mobile
I test chimici sull’acqua hanno mostrato che i residui di antibiotici erano costantemente più alti nelle entrate e nelle uscite degli impianti di trattamento rispetto ai siti naturali. I livelli del farmaco ciprofloxacina in una entrata e in una uscita superavano le soglie riportate in letteratura oltre le quali ci si aspetta che la resistenza sia favorita. Questo sfondo chimico è importante perché molti geni di resistenza erano localizzati su plasmidi coniugativi—cerchi di DNA mobili che possono spostarsi da un batterio all’altro. In esperimenti di coniugazione in laboratorio, plasmidi provenienti da 16 ceppi si sono trasferiti con successo in un ceppo ricettore standard, spesso portando con sé la resistenza a più farmaci contemporaneamente. Plasmidi di certe famiglie, in particolare IncN e IncI, si sono mossi con efficienza particolarmente alta, suggerendo che sono veicoli potenti per la diffusione della resistenza nell’ambiente affollato e ricco di nutrienti dei sistemi fognari.
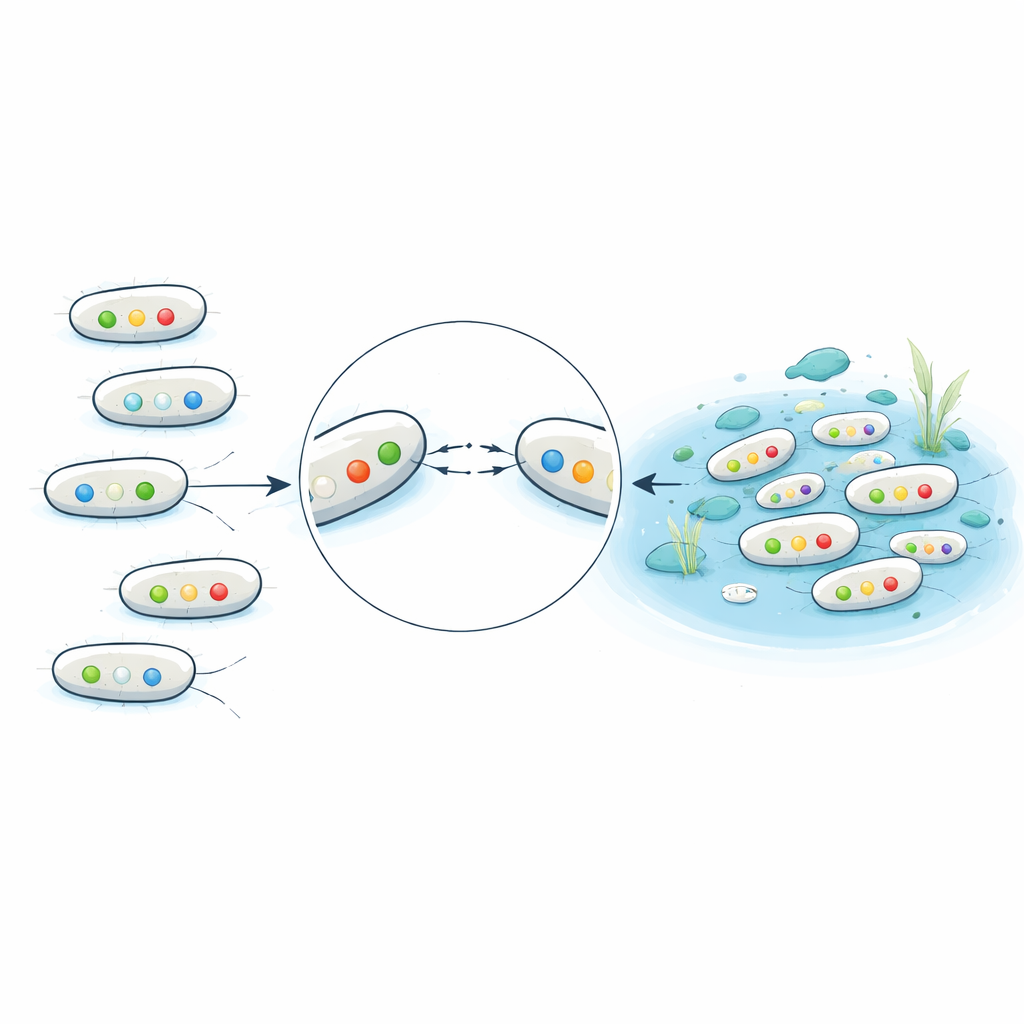
Caratteristiche legate alla malattia nelle acque di tutti i giorni
Oltre alla resistenza ai farmaci, gli scienziati hanno cercato nei genomi geni che aiutano E. coli a causare malattia, come quelli per tossine, adesine che permettono ai batteri di aderire all’intestino o alle vie urinarie, e fattori che li proteggono nel flusso sanguigno. Molti isolati provenienti dalle acque reflue portavano combinazioni di geni tipiche di patogeni extra‑intestinali e delle vie urinarie, rispecchiando i modelli osservati nelle infezioni cliniche. Sorprendentemente, una larga frazione di E. coli proveniente da laghi e spiagge apparentemente puliti portava comunque alcuni di questi geni di virulenza, sebbene in genere avesse meno geni di resistenza e nessun gene per beta‑lattamasi a spettro esteso. Lo studio ha inoltre trovato parenti ambientali come Escherichia marmotae che portavano geni associati alla malattia, suggerendo che fauna selvatica e acque naturali possono ospitare patogeni in potenza.
Cosa significa per le persone e per le politiche
Nel complesso, i risultati dipingono gli impianti di trattamento delle acque reflue come importanti snodi dove batteri umani, animali e ambientali si mescolano, sono esposti a residui di antibiotici e scambiano DNA mobile che può renderli sia più resistenti ai farmaci sia più capaci di causare malattia. Sebbene gli impianti rimuovano molti inquinanti, non eliminano completamente E. coli resistenti o patogeni, e alcuni di questi ceppi e i loro plasmidi vengono scaricati in fiumi e acque costiere usate dal pubblico. Per il lettore non specialistico, il messaggio principale è che la resistenza agli antibiotici non è confinata agli ospedali: è influenzata da come gestiamo le acque reflue e proteggiamo le acque naturali. Monitorare le acque fognarie e le acque ricreative vicine, ridurre l’uso di antibiotici e migliorare le tecnologie di trattamento possono tutti contribuire a rallentare il “riciclo” ambientale di germi pericolosi verso le persone.
Citazione: Justh de Neczpal, A., Thorell, K., Tuts, L. et al. Antimicrobial resistance, conjugative plasmids and pathogenicity in wastewater and freshwater Escherichia spp. in Stockholm, Sweden. npj Antimicrob Resist 4, 32 (2026). https://doi.org/10.1038/s44259-026-00208-5
Parole chiave: resistenza agli antibiotici, trattamento delle acque reflue, E. coli, microbiologia ambientale, trasferimento di plasmidi