Clear Sky Science · fr
Résistance aux antimicrobiens, plasmides conjugatifs et pathogénicité chez des Escherichia spp. des eaux usées et des eaux douces à Stockholm, Suède
Pourquoi l’eau et les microbes comptent au quotidien
La plupart des gens associent la résistance aux antibiotiques aux hôpitaux, mais cette étude montre qu’elle peut aussi être influencée par l’eau qui circule sous nos villes et borde nos plages. Des chercheurs de Stockholm, en Suède, ont suivi des bactéries issues d’usines de traitement des eaux usées ainsi que de lacs et de zones côtières proches pour poser une question simple mais urgente : nos canalisations contribuent‑elles à répandre des germes difficiles à traiter dans l’environnement où l’on se baigne, joue et puise de l’eau potable ?
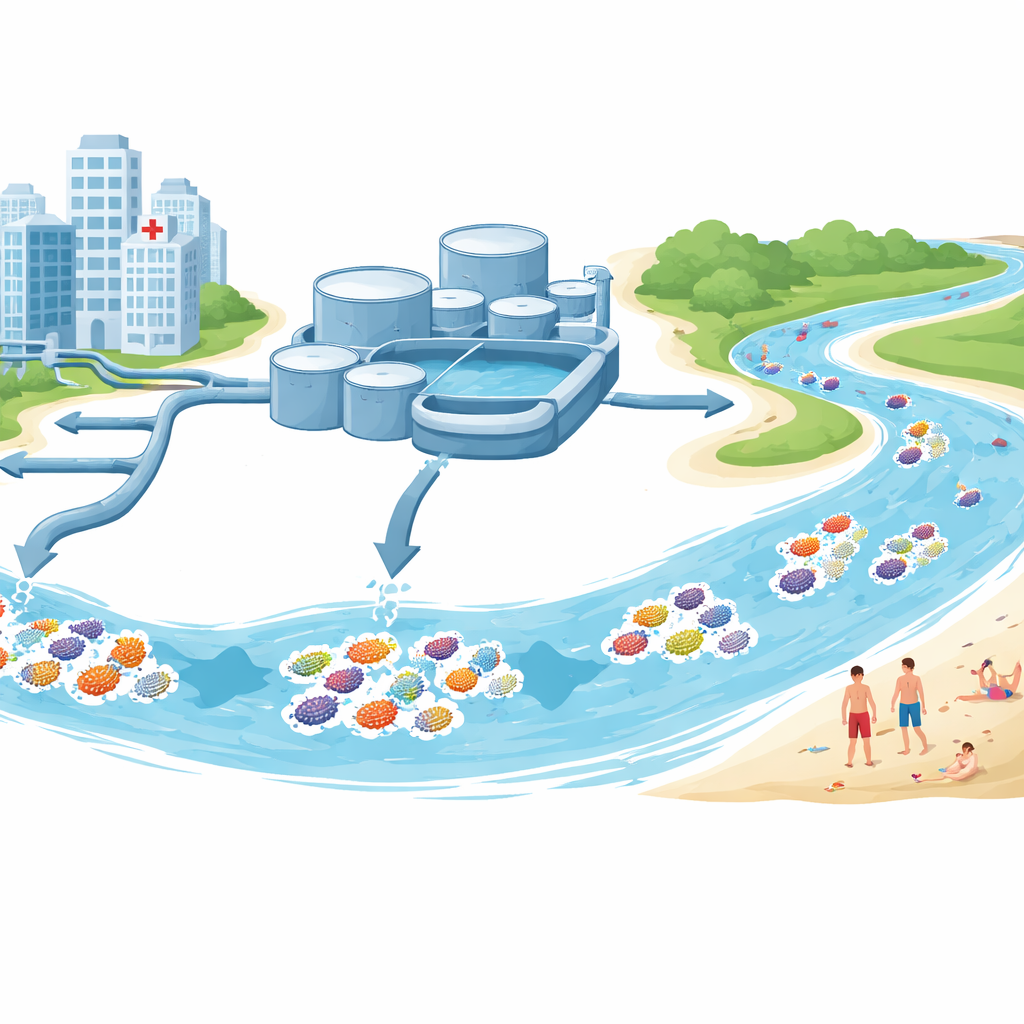
D’où provenaient les échantillons
L’équipe a prélevé de l’eau et des sédiments dans et autour de Stockholm durant l’été 2022. Certains échantillons provenaient des entrées et sorties des principales stations d’épuration recevant les eaux domestiques et hospitalières. D’autres ont été prélevés dans des lacs d’eau douce et sur des plages saumâtres de la mer Baltique fréquentées pour les loisirs. À partir de ces sites, ils ont isolé 68 souches d’espèces d’Escherichia, principalement E. coli, une bactérie intestinale courante et un indicateur standard de contamination fécale. Chaque souche a été testée en laboratoire pour déterminer les antibiotiques qu’elle résistait, puis son ADN a été séquencé pour révéler ses gènes de résistance, ses gènes liés à la virulence et les petites boucles d’ADN appelées plasmides qui peuvent sauter d’une bactérie à l’autre.
Une résistance plus forte dans les eaux usées que dans les eaux naturelles
Le contraste entre eaux usées et eaux naturelles était frappant. Plus de la moitié des souches d’E. coli issues des eaux usées résistaient à au moins trois classes d’antibiotiques, et beaucoup portaient des grappes de gènes de résistance, y compris ceux qui neutralisent des céphalosporines de troisième génération largement utilisées. En particulier, des gènes de la famille CTX‑M, et plus spécialement la variante CTX‑M‑15, étaient fréquents dans les souches d’eaux usées mais totalement absents des souches prélevées dans les lacs et sur les plages. Plusieurs bactéries issues des eaux usées appartenaient à des lignées bien connues responsables d’infections urinaires et de bactériémies chez l’humain, y compris le groupe mondialement problématique ST131 ; ces souches portaient certaines des charges les plus lourdes en gènes de résistance.
Résidus d’antibiotiques et ADN mobile
Les analyses chimiques de l’eau ont montré que les résidus d’antibiotiques étaient systématiquement plus élevés aux points d’entrée et de sortie des stations d’épuration qu’à ceux des sites naturels. Les concentrations de ciprofloxacine à un point d’entrée et un point de sortie dépassaient des seuils publiés au‑delà desquels on s’attend à une sélection de la résistance. Ce contexte chimique est important car de nombreux gènes de résistance étaient localisés sur des plasmides conjugatifs — des cercles d’ADN mobiles capables de passer d’une bactérie à une autre. Dans des expériences d’accouplement en laboratoire, des plasmides provenant de 16 souches se sont transférés avec succès dans une souche réceptrice standard, entraînant souvent une résistance simultanée à plusieurs antibiotiques. Les plasmides de certaines familles, notamment IncN et IncI, se sont déplacés avec une efficacité particulièrement élevée, ce qui suggère qu’ils sont des vecteurs puissants pour la propagation de la résistance dans l’environnement confiné et riche en nutriments des systèmes d’assainissement.
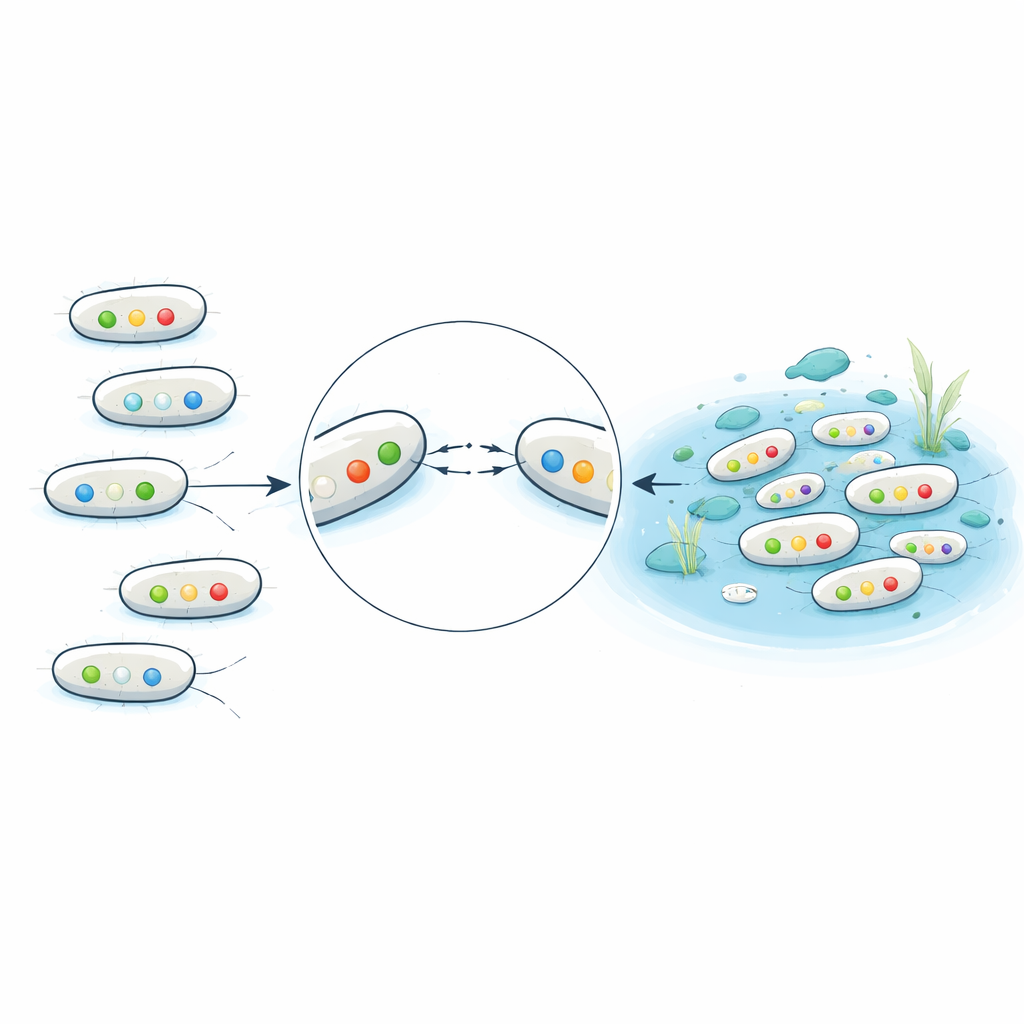
Traits liés à la maladie dans des eaux du quotidien
Au‑delà de la résistance aux médicaments, les scientifiques ont cherché dans les génomes des gènes qui aident E. coli à provoquer des maladies, tels que ceux codant pour des toxines, des adhésines permettant aux bactéries de s’accrocher à l’intestin ou aux voies urinaires, et des facteurs les protégeant dans le sang. De nombreux isolats d’eaux usées portaient des combinaisons de gènes typiques de pathogènes extra‑intestinaux et responsables d’infections urinaires, en écho aux profils observés dans les infections cliniques. De façon surprenante, une grande fraction d’E. coli provenant de lacs et de plages apparemment propres portait aussi certains de ces gènes de virulence, bien qu’elles présentassent généralement moins de gènes de résistance et aucune bêta‑lactamase à spectre étendu. L’étude a aussi identifié des proches environnementaux comme Escherichia marmotae portant des gènes associés à la maladie, suggérant que la faune sauvage et les eaux naturelles peuvent abriter des pathogènes potentiels.
Ce que cela signifie pour les personnes et les politiques
Pris dans leur ensemble, ces résultats présentent les stations d’épuration comme des carrefours importants où bactéries humaines, animales et environnementales se mélangent, sont exposées aux résidus d’antibiotiques et échangent de l’ADN mobile qui peut les rendre à la fois plus résistantes aux médicaments et plus aptes à déclencher des maladies. Bien que les stations éliminent de nombreux contaminants, elles n’éliminent pas complètement les E. coli résistantes ou pathogènes, et certaines de ces souches et leurs plasmides sont rejetées dans les rivières et les eaux côtières fréquentées par le public. Pour le grand public, le message essentiel est que la résistance aux antibiotiques ne se limite pas aux hôpitaux : elle dépend de notre gestion des eaux usées et de la protection des eaux naturelles. Surveiller les eaux usées et les eaux de baignade voisines, réduire l’usage des antibiotiques et améliorer les technologies de traitement peuvent tous contribuer à ralentir le « recyclage » environnemental des germes dangereux vers les humains.
Citation: Justh de Neczpal, A., Thorell, K., Tuts, L. et al. Antimicrobial resistance, conjugative plasmids and pathogenicity in wastewater and freshwater Escherichia spp. in Stockholm, Sweden. npj Antimicrob Resist 4, 32 (2026). https://doi.org/10.1038/s44259-026-00208-5
Mots-clés: résistance aux antibiotiques, traitement des eaux usées, E. coli, microbiologie environnementale, transfert de plasmides