Clear Sky Science · pt
Disseminação ambiental de Escherichia coli multirresistente através das interfaces One Health em Mymensingh, Bangladesh
Por que germes na água importam para todos
Os “superbactérias” resistentes a antibióticos costumam ser discutidas em hospitais, mas não permanecem apenas ali. Este estudo mostra como linhagens perigosas de Escherichia coli, uma bactéria intestinal comum, estão se espalhando pela água usada por pessoas, animais e fazendas em um distrito de Bangladesh. Ao rastrear esses microrganismos por hospitais, criações de animais, viveiros de peixes e um rio, os pesquisadores revelam como atividades cotidianas podem, silenciosamente, ajudar germes resistentes a se mover pelo ambiente e voltar a afetar humanos.
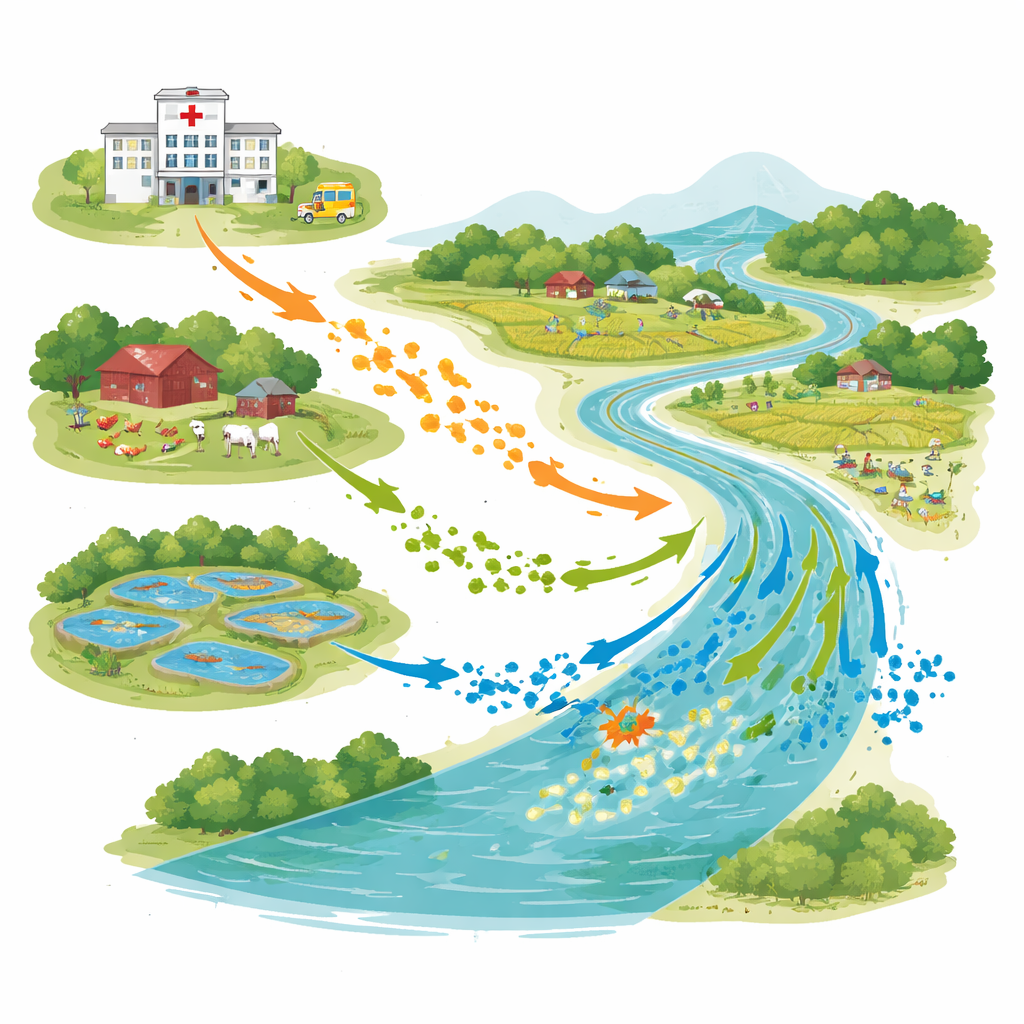
Uma paisagem conectada de pessoas, animais e água
A pesquisa foi realizada em Bhaluka Upazila, uma área semiurbana onde hospitais, granjas avícolas e de gado, viveiros de aquicultura e o rio Khiro coexistem na mesma paisagem. Em maio de 2022, os cientistas coletaram 28 amostras de água em saídas de esgoto hospitalar, efluentes de fazendas, viveiros de peixes e em dois pontos ao longo do rio, rio acima e rio abaixo dos pontos de descarga hospitalar. Usando um protocolo padrão da Organização Mundial da Saúde, contaram E. coli em cada amostra e focaram em linhagens que podem derrotar antibióticos potentes usados para infecções graves.
Altos níveis de bactérias resistentes em resíduos e na água do rio
A equipe encontrou E. coli em todas as amostras e descobriu que 86% continham linhagens resistentes a antibióticos “de terceira geração” amplamente usados. Os níveis foram mais altos em águas residuais hospitalares e efluentes de granjas avícolas e de gado, onde tanto o total de E. coli quanto os tipos resistentes eram extremamente abundantes. Linhagens resistentes a carbapenêmicos — capazes de suportar drogas de último recurso — foram menos comuns, mas mais preocupantes. Apareceram apenas em esgoto hospitalar e na água do rio abaixo dos pontos de descarga hospitalar, e estavam completamente ausentes nos viveiros de gado e aquicultura. No geral, os viveiros de peixes mostraram contaminação muito menor, sugerindo menos entrada de antibióticos ali.
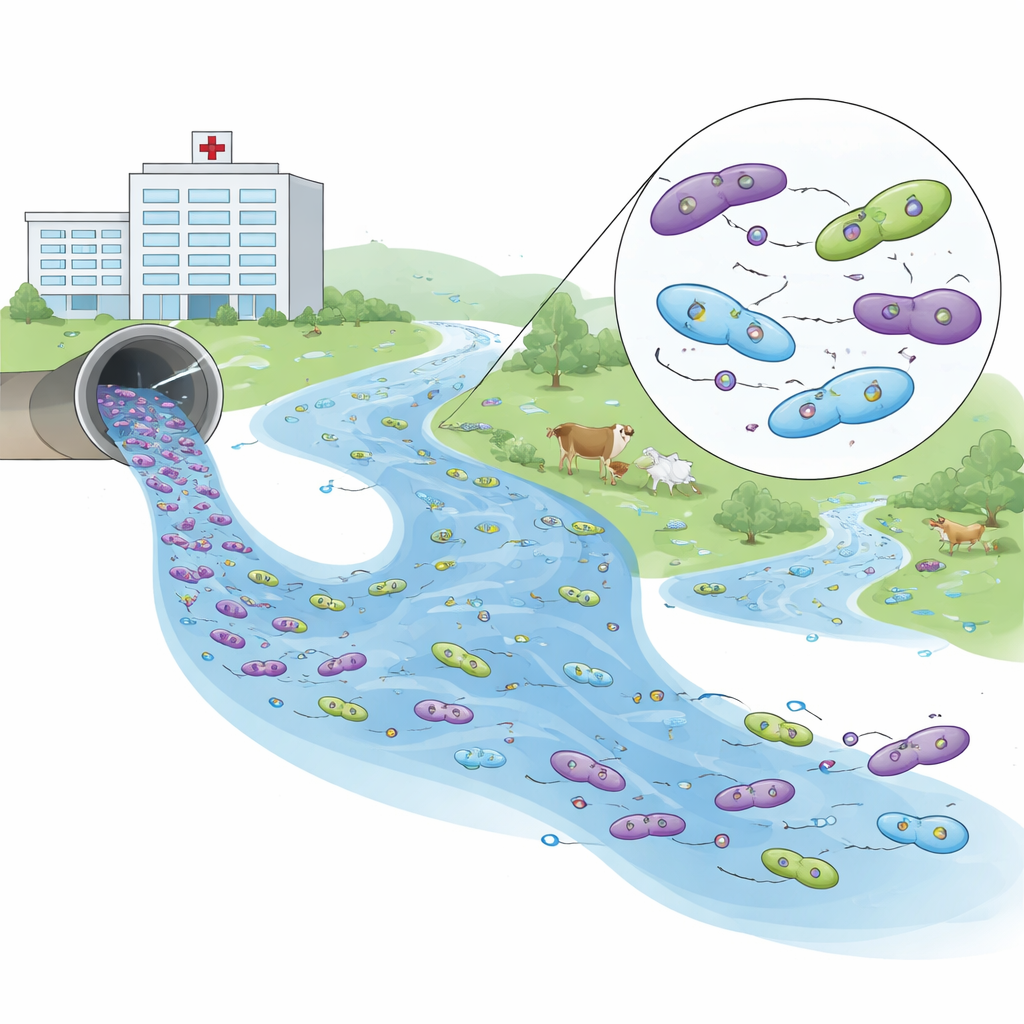
Lendo as impressões digitais do DNA da resistência
Para entender como essas bactérias estão relacionadas, os pesquisadores sequenciaram os genomas de 26 isolados representativos. Detectaram 93 genes diferentes de resistência, com um pequeno número ocorrendo repetidamente entre os locais. Uma família de genes, conhecida como blaCTX-M-15, que bloqueia muitos antibióticos beta-lactâmicos importantes, predominou em todos os ambientes. Outro gene, blaNDM-5, confere resistência a carbapenêmicos, alguns dos fármacos mais potentes da medicina moderna. Esse gene surgiu em amostras hospitalares e em um isolado do rio a jusante, associado a pequenos anéis de DNA móveis chamados plasmídeos, que podem ser transferidos entre bactérias.
Vínculos genéticos entre ralos hospitalares e o rio
Ao comparar pequenas diferenças no DNA — mudanças de uma única letra no genoma — os cientistas construíram uma árvore genealógica das E. coli coletadas. A maioria das bactérias se agrupou por fonte: isolados de aves formaram um grupo, isolados de gado constituíram seu próprio ramo, e cepas de aquicultura ficaram separadas com menos traços de resistência. Os isolados hospitalares foram mais diversos, mas, crucialmente, uma cepa hospitalar e uma cepa do rio a jusante compartilharam um arcabouço genético quase idêntico, sem diferenças no núcleo de seus genomas. Embora classificadas como tipos de sequência ligeiramente diferentes, essa correspondência quase perfeita, combinada com a presença do mesmo gene de resistência a carbapenêmicos em plasmídeos, indica fortemente um espalhamento recente do efluente hospitalar para o rio.
O que isso significa para a saúde e a política
Este trabalho oferece um retrato detalhado de como bactérias resistentes se movem através da interface “One Health” que liga pessoas, animais e meio ambiente. Mostra que o esgoto hospitalar é um ponto quente importante, liberando E. coli altamente resistentes em um rio do qual as comunidades locais dependem. Sistemas de criação de animais também contribuem com grande número de linhagens resistentes, embora ainda não com aquelas resistentes a drogas de último recurso. Mesmo com um número modesto de amostras coletadas em um único mês, os achados apoiam ações urgentes: melhor tratamento do esgoto hospitalar, uso mais cuidadoso de antibióticos em fazendas e clínicas, e monitoramento rotineiro de rios e outras fontes de água compartilhadas. Para leitores leigos, a mensagem-chave é que escolhas sobre o uso de antibióticos e o gerenciamento de resíduos não afetam apenas pacientes hospitalares — elas moldam o fluxo invisível de superbactérias pelo ambiente que todos compartilhamos.
Citação: Rahman, A., Roy, S., Afreen, N. et al. Environmental dissemination of multidrug-resistant Escherichia coli across one health interfaces in Mymensingh, Bangladesh. npj Antimicrob Resist 4, 27 (2026). https://doi.org/10.1038/s44259-026-00202-x
Palavras-chave: resistência antimicrobiana, contaminação ambiental, águas residuais, Escherichia coli, One Health