Clear Sky Science · it
Diffusione ambientale di Escherichia coli multiresistente attraverso le interfacce One Health a Mymensingh, Bangladesh
Perché i germi nell’acqua riguardano tutti
I “superbatteri” resistenti agli antibiotici sono spesso discussi negli ospedali, ma non restano lì. Questo studio mostra come ceppi pericolosi di Escherichia coli, un comune batterio intestinale, si stiano diffondendo attraverso le acque utilizzate da persone, animali e aziende agricole in un distretto del Bangladesh. Tracciando questi microrganismi attraverso ospedali, allevamenti, stagni di acquacoltura e un fiume, i ricercatori rivelano come le attività quotidiane possano favorire silenziosamente lo spostamento dei germi resistenti nell’ambiente e il loro ritorno agli esseri umani.
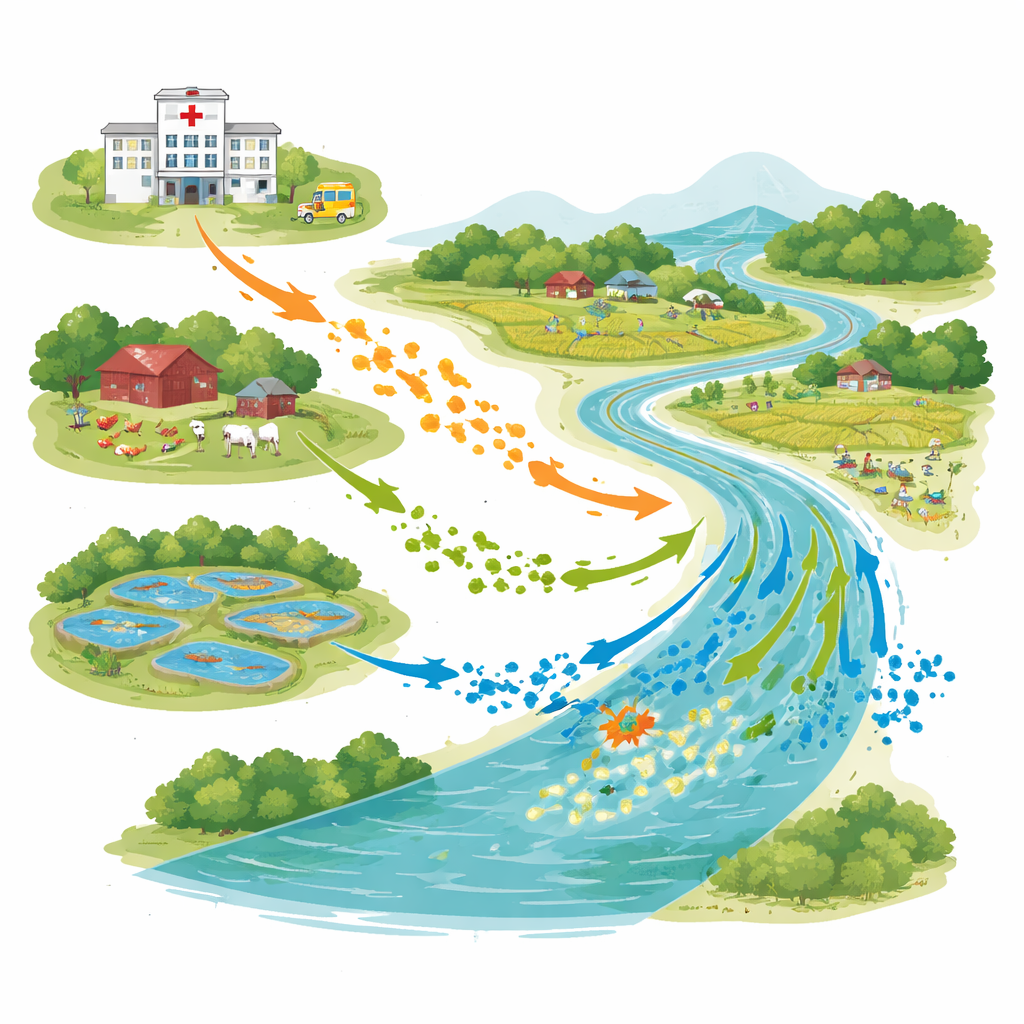
Un paesaggio connesso di persone, animali e acqua
La ricerca è stata condotta a Bhaluka Upazila, un’area semi‑urbana dove ospedali, allevamenti avicoli e bovini, stagni di acquacoltura e il fiume Khiro convivono nello stesso territorio. A maggio 2022, gli scienziati hanno prelevato 28 campioni d’acqua da scarichi ospedalieri, effluenti agricoli, stagni ittici e due punti lungo il fiume, a monte e a valle degli scarichi ospedalieri. Utilizzando un protocollo standard dell’Organizzazione Mondiale della Sanità, hanno contato gli E. coli in ciascun campione e si sono concentrati sui ceppi capaci di resistere agli antibiotici potenti usati per infezioni gravi.
Alti livelli di batteri resistenti in acque reflue e nel fiume
Il gruppo ha rilevato E. coli in tutti i campioni e ha scoperto che l’86% conteneva ceppi resistenti agli antibiotici di «terza generazione» ampiamente usati. I livelli più elevati si sono registrati nelle acque reflue ospedaliere e negli effluenti di allevamenti avicoli e bovini, dove sia gli E. coli totali sia i ceppi resistenti erano estremamente abbondanti. I ceppi resistenti ai carbapenemi—in grado di resistere ai farmaci di ultima istanza—erano meno comuni ma più preoccupanti. Sono comparsi solo nelle acque di scarico ospedaliere e nel tratto del fiume a valle degli scarichi ospedalieri, ed erano completamente assenti negli stagni e negli impianti di acquacoltura. Gli stagni ittici nel complesso hanno mostrato una contaminazione molto più bassa, suggerendo minori input antibiotici in quei siti.
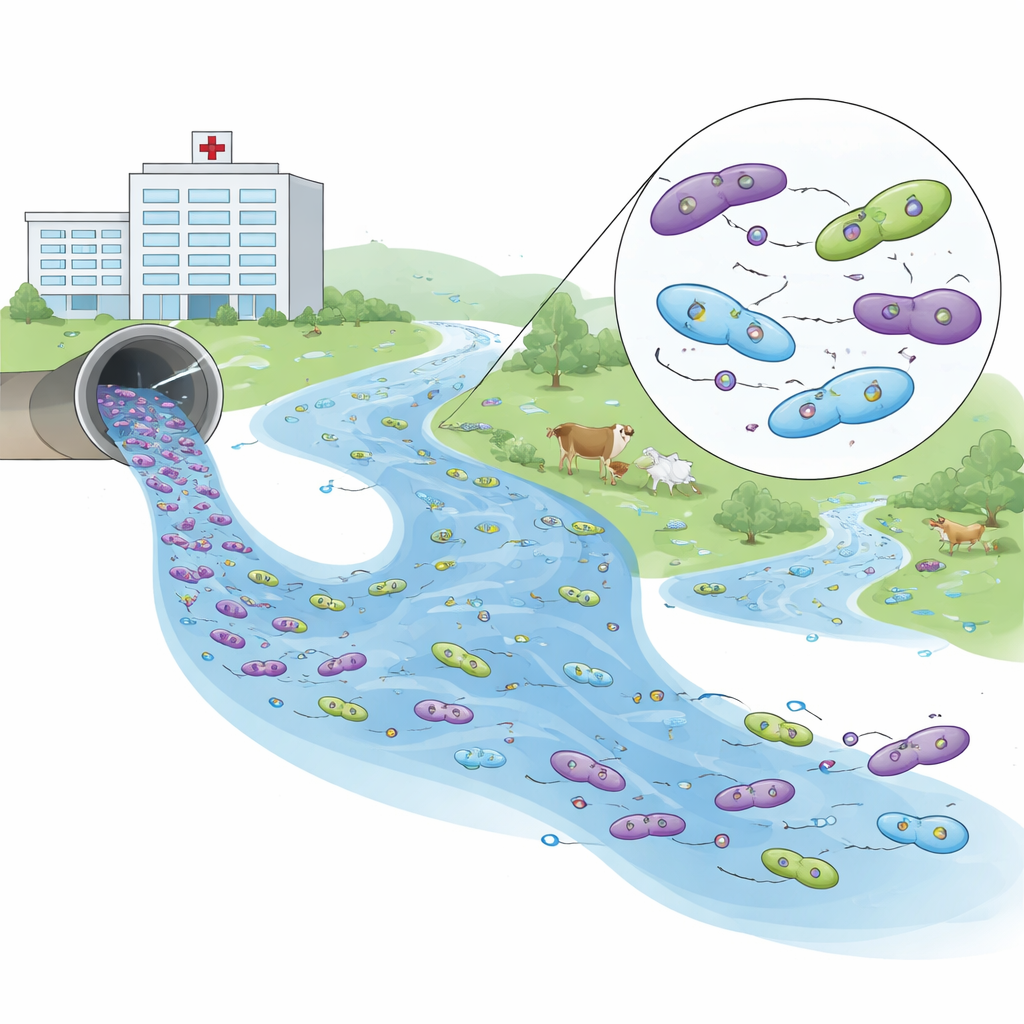
Leggere le impronte del DNA della resistenza
Per capire come questi batteri fossero correlati, i ricercatori hanno sequenziato i genomi di 26 isolati rappresentativi. Hanno rilevato 93 diversi geni di resistenza, con una manciata che ricompariva tra i siti. Una famiglia di geni, nota come blaCTX‑M‑15, che neutralizza molti importanti antibiotici beta‑lattamici, dominava in tutti gli ambienti. Un altro gene, blaNDM‑5, conferisce resistenza ai carbapenemi, alcuni dei farmaci più potenti in medicina moderna. Questo gene è emerso nei campioni ospedalieri e in un isolato del fiume a valle, ed è legato a piccoli elementi di DNA mobili chiamati plasmidi che possono spostarsi tra batteri.
Legami genetici tra scarichi ospedalieri e il fiume
Confrontando minuscole differenze nel DNA—cambiamenti di una sola lettera nel genoma—gli scienziati hanno costruito un albero genealogico degli E. coli raccolti. La maggior parte dei batteri si raggruppava per fonte: gli isolati avicoli formavano un gruppo, quelli bovini un altro ramo, e i ceppi di acquacoltura stavano separati con meno tratti di resistenza. Gli isolati ospedalieri erano più diversi ma, cosa cruciale, uno ceppo ospedaliero e un ceppo del fiume a valle condividevano una struttura genetica quasi identica, senza differenze nel nucleo dei loro genomi. Pur essendo classificati come tipi di sequenza leggermente diversi, questa corrispondenza quasi perfetta, unita alla presenza dello stesso gene di resistenza ai carbapenemi su plasmidi, indica fortemente una diffusione recente dall’effluente ospedaliero nel fiume.
Cosa significa per la salute e le politiche
Questo lavoro offre un’istantanea ravvicinata di come i batteri resistenti si muovano attraverso l’interfaccia «One Health» che collega persone, animali e ambiente. Mostra che le acque reflue ospedaliere sono un punto caldo principale, rilasciando E. coli altamente resistenti in un fiume da cui dipendono le comunità locali. Anche i sistemi zootecnici contribuiscono con grandi numeri di ceppi resistenti, sebbene non ancora con quelli resistenti ai farmaci di ultima istanza. Anche con un numero modesto di campioni raccolti in un solo mese, i risultati sostengono azioni urgenti: un miglior trattamento delle acque reflue ospedaliere, un uso più prudente degli antibiotici in allevamenti e cliniche e un monitoraggio di routine dei fiumi e di altre risorse idriche condivise. Per il lettore non specialista, il messaggio chiave è che le scelte sull’uso di antibiotici e sulla gestione dei rifiuti non riguardano solo i pazienti ospedalieri: modellano il flusso invisibile di superbatteri nell’ambiente che appartiene a tutti noi.
Citazione: Rahman, A., Roy, S., Afreen, N. et al. Environmental dissemination of multidrug-resistant Escherichia coli across one health interfaces in Mymensingh, Bangladesh. npj Antimicrob Resist 4, 27 (2026). https://doi.org/10.1038/s44259-026-00202-x
Parole chiave: resistenza antimicrobica, contaminazione ambientale, acque reflue, Escherichia coli, One Health