Clear Sky Science · pl
Środowiskowe rozprzestrzenianie się wielolekoopornego Escherichia coli w interfejsach One Health w Mymensingh, Bangladesz
Dlaczego zarazki w wodzie dotyczą nas wszystkich
„Superbakterie” odporne na antybiotyki zwykle pojawiają się w dyskusjach o szpitalach, ale nie pozostają tam na zawsze. Badanie pokazuje, jak niebezpieczne szczepy Escherichia coli, powszechnie występującej bakterii jelitowej, rozprzestrzeniają się w wodzie używanej przez ludzi, zwierzęta i gospodarstwa w jednym dystrykcie Bangladeszu. Śledząc te mikroby w szpitalach, gospodarstwach hodowlanych, stawach rybnych i rzece, badacze ujawnili, jak codzienne aktywności mogą po cichu ułatwiać przemieszczanie się odpornych drobnoustrojów w środowisku i ich powrót do ludzi.
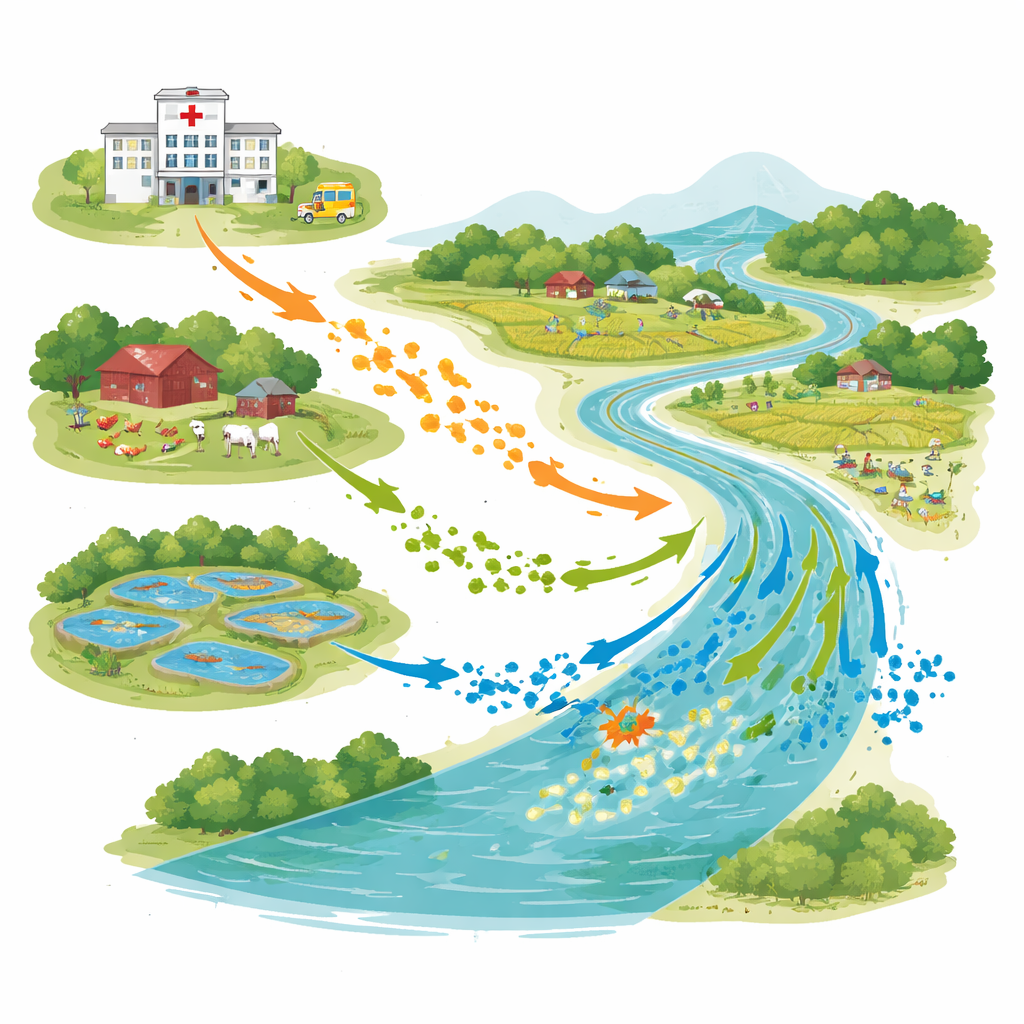
Powiązany krajobraz ludzi, zwierząt i wody
Badania przeprowadzono w Bhaluka Upazila, półmiejskim obszarze, gdzie szpitale, fermy drobiu i bydła, stawy akwakulturowe oraz rzeka Khiro znajdują się blisko siebie. W maju 2022 roku naukowcy pobrali 28 próbek wody z wylotów ścieków szpitalnych, cieków odpływowych z gospodarstw, stawów rybnych oraz z dwóch punktów rzeki — powyżej i poniżej miejsc, gdzie odprowadzane są ścieki ze szpitali. Zgodnie ze standardowym protokołem Światowej Organizacji Zdrowia policzyli E. coli w każdej próbce i skupili się na szczepach zdolnych do pokonania silnych antybiotyków stosowanych w ciężkich zakażeniach.
Wysoki poziom odpornych bakterii w odpadach i wodzie rzecznej
Zespół wykrył E. coli w każdej próbce i stwierdził, że w 86% występowały szczepy oporne na powszechnie stosowane antybiotyki „trzeciej generacji”. Najwyższe poziomy zanotowano w ściekach szpitalnych oraz w ciekach odpływowych z ferm drobiu i bydła, gdzie zarówno całkowite liczby E. coli, jak i szczepy oporne były wyjątkowo liczne. Szczepy oporne na karbapenemy — zdolne przeciwstawić się lekom ostatniej szansy — były rzadsze, ale bardziej niepokojące. Pojawiały się wyłącznie w ściekach szpitalnych i w wodzie rzeki poniżej punktów zrzutu ze szpitali, i nie stwierdzono ich w stawach hodowlanych i akwakulturach. Ogólnie stawy rybne wykazały znacznie niższe zanieczyszczenie, co sugeruje mniejszy dopływ antybiotyków w tych miejscach.
Odczytywanie odcisków palców DNA odporności
Aby zrozumieć, jak te bakterie są ze sobą powiązane, badacze zsekwencjonowali genom 26 reprezentatywnych izolowanych szczepów. Wykryli 93 różne geny odpowiedzialne za oporność, przy czym kilka pojawiało się wielokrotnie w różnych miejscach. Dominowała jedna rodzina genów, znana jako blaCTX-M-15, która blokuje wiele ważnych antybiotyków beta-laktamowych, występując we wszystkich środowiskach. Inny gen, blaNDM-5, nadaje oporność na karbapenemy, jedne z najsilniejszych leków we współczesnej medycynie. Gen ten pojawił się w próbkach szpitalnych oraz w izolacie z rzeki poniżej zrzutów, powiązany z małymi, ruchomymi pętlami DNA zwanymi plazmidami, które mogą przemieszczać się między bakteriami.
Powiązania genetyczne między odpływami szpitalnymi a rzeką
Porównując drobne różnice w DNA — pojedyncze zmiany liter w genomie — naukowcy zbudowali drzewo rodowe dla zebranych szczepów E. coli. Większość bakterii tworzyła skupiska według źródła: izolaty z drobiu grupowały się razem, izolaty bydła tworzyły oddzielną gałąź, a szczepy z akwakultury były odrębne i miały mniej cech oporności. Izolaty szpitalne były bardziej zróżnicowane, ale co istotne, jeden szczep ze szpitala i szczep z rzeki poniżej wykazały niemal identyczny szkielet genetyczny, bez różnic w rdzeniu ich genomów. Chociaż sklasyfikowano je jako nieco różne typy sekwencyjne, to niemal doskonałe dopasowanie, połączone z obecnością tego samego genu nadającego oporność na karbapenemy na plazmidach, silnie wskazuje na niedawne przedostanie się zanieczyszczeń ze ścieków szpitalnych do rzeki.
Co to oznacza dla zdrowia i polityki
To badanie dostarcza szczegółowego obrazu tego, jak bakterie odporne przemieszczają się przez interfejs „One Health”, łączący ludzi, zwierzęta i środowisko. Pokazuje, że ścieki szpitalne są głównym miejscem uwalniania silnie opornych E. coli do rzeki, od której zależą lokalne społeczności. Systemy hodowlane również wnoszą dużą liczbę szczepów opornych, choć jeszcze nie tych odpornych na leki ostatniej szansy. Nawet przy umiarkowanej liczbie próbek pobranych w ciągu jednego miesiąca, wyniki uzasadniają pilne działania: lepsze oczyszczanie ścieków szpitalnych, ostrożniejsze stosowanie antybiotyków w gospodarstwach i klinikach oraz rutynowe monitorowanie rzek i innych wspólnych źródeł wody. Dla laików kluczowe przesłanie jest takie, że decyzje dotyczące stosowania antybiotyków i zarządzania odpadami nie dotyczą tylko pacjentów szpitalnych — kształtują one niewidoczny przepływ superbakterii przez środowisko, którym wszyscy się dzielimy.
Cytowanie: Rahman, A., Roy, S., Afreen, N. et al. Environmental dissemination of multidrug-resistant Escherichia coli across one health interfaces in Mymensingh, Bangladesh. npj Antimicrob Resist 4, 27 (2026). https://doi.org/10.1038/s44259-026-00202-x
Słowa kluczowe: oporność na antybiotyki, zanieczyszczenie środowiska, ścieki, Escherichia coli, One Health