Clear Sky Science · es
Diseminación ambiental de Escherichia coli multirresistente a través de interfaces One Health en Mymensingh, Bangladés
Por qué los gérmenes en el agua importan a todos
Los “superbacterias” resistentes a los antibióticos suelen mencionarse en hospitales, pero no se quedan ahí. Este estudio muestra cómo cepas peligrosas de Escherichia coli, una bacteria intestinal común, se están propagando a través del agua que usan personas, animales y explotaciones agrícolas en un distrito de Bangladés. Al rastrear estos microbios en hospitales, granjas, estanques de piscicultura y un río, los investigadores revelan cómo las actividades cotidianas pueden facilitar silenciosamente que los gérmenes resistentes se muevan por el medio ambiente y regresen a los humanos.
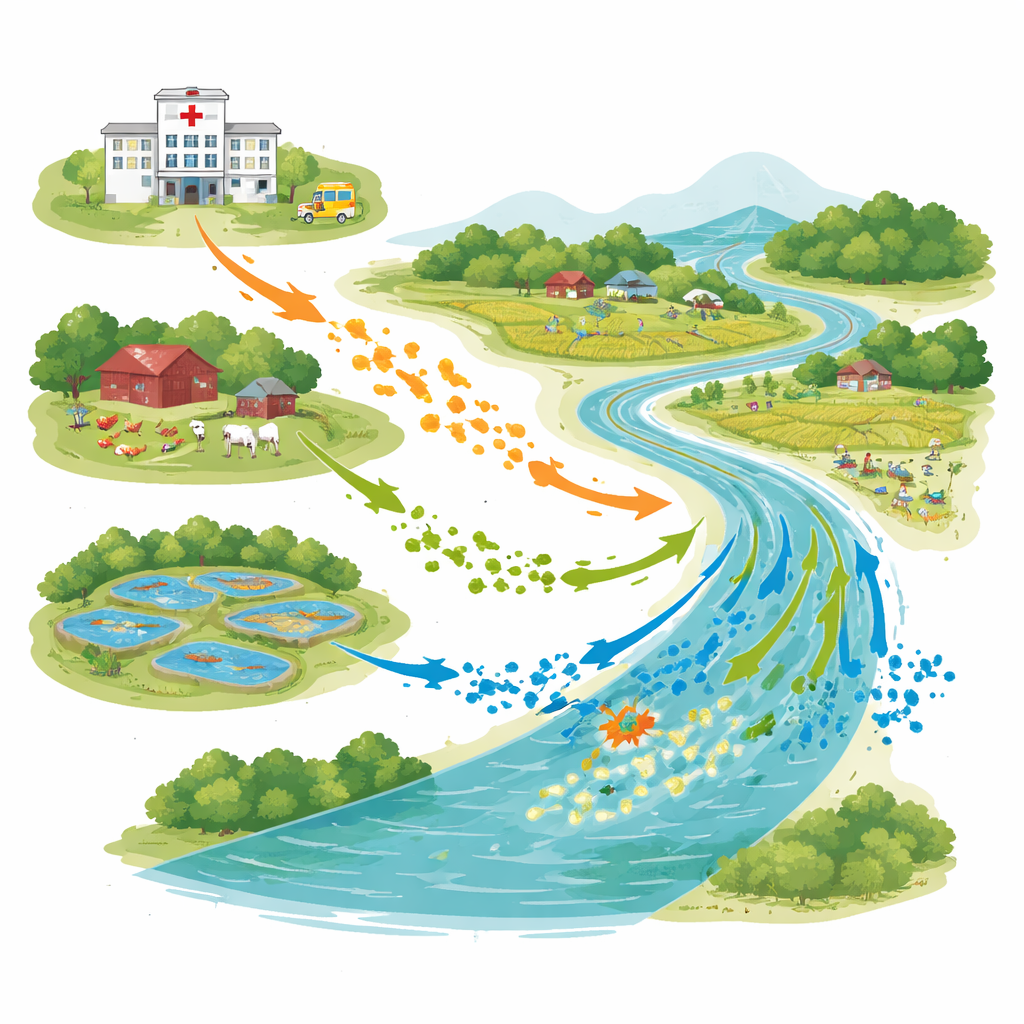
Un paisaje conectado de personas, animales y agua
La investigación se llevó a cabo en Bhaluka Upazila, una zona semiurbana donde hospitales, granjas avícolas y bovinas, estanques de acuicultura y el río Khiro conviven en el mismo territorio. En mayo de 2022, los científicos recogieron 28 muestras de agua de desagües hospitalarios, efluentes de granjas, estanques de peces y dos puntos del río, río arriba y río abajo de las descargas hospitalarias. Usando un protocolo estándar de la Organización Mundial de la Salud, contaron E. coli en cada muestra y se centraron en cepas capaces de vencer antibióticos potentes empleados para infecciones graves.
Altos niveles de bacterias resistentes en aguas residuales y del río
El equipo detectó E. coli en todas las muestras y descubrió que el 86% contenía cepas resistentes a antibióticos de uso común de la “tercera generación”. Los niveles fueron más altos en las aguas residuales hospitalarias y en los efluentes de granjas avícolas y bovinas, donde tanto el total de E. coli como las variantes resistentes eran extremadamente abundantes. Las cepas resistentes a carbapenémicos —capaces de soportar fármacos de último recurso— fueron menos frecuentes pero más preocupantes. Aparecieron únicamente en aguas residuales hospitalarias y en el agua del río río abajo de los puntos de descarga hospitalaria, y estuvieron completamente ausentes en estanques de ganado y de acuicultura. En general, los estanques de peces mostraron una contaminación mucho menor, lo que sugiere menos aportes de antibióticos allí.
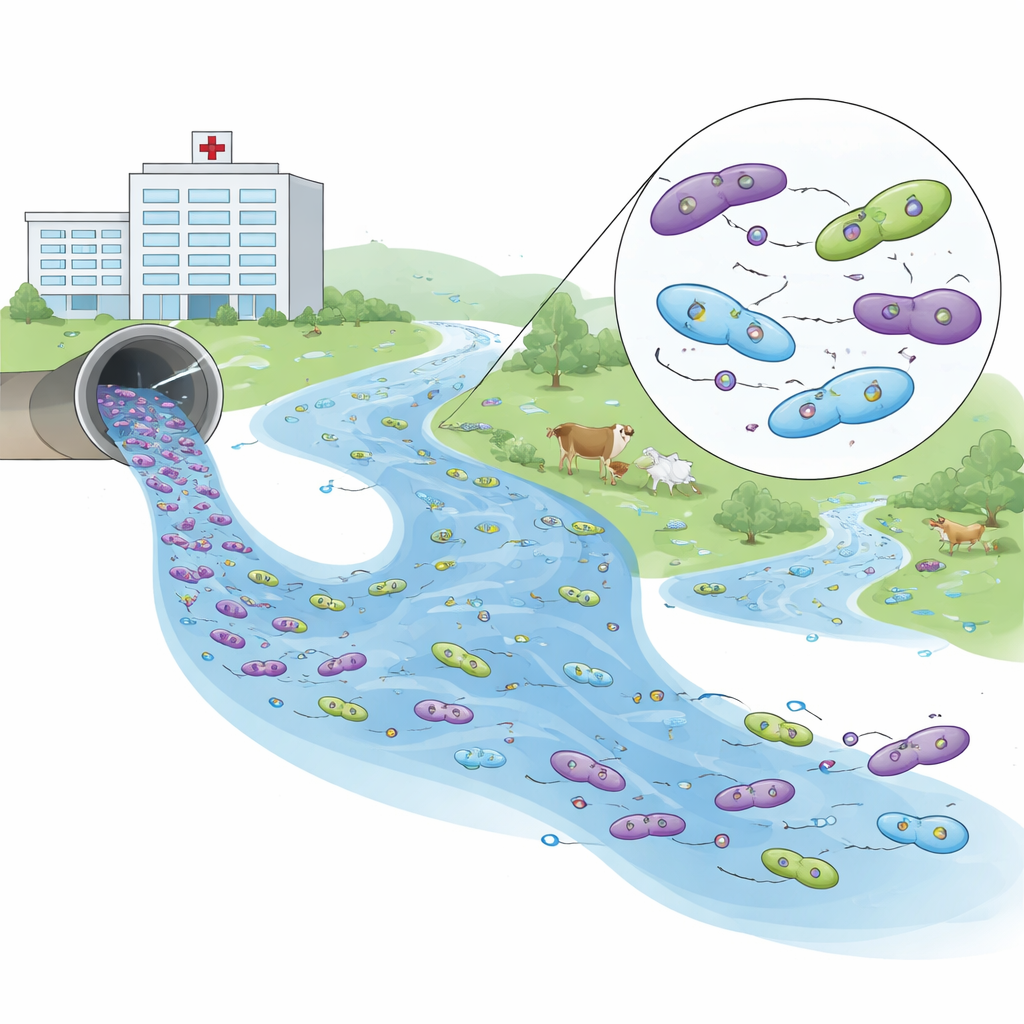
Leyendo las huellas genéticas de la resistencia
Para entender la relación entre estas bacterias, los investigadores secuenciaron los genomas de 26 aislados representativos. Detectaron 93 genes de resistencia diferentes, con un puñado que reaparecía en varios sitios. Una familia de genes, conocida como blaCTX-M-15, que inactiva muchos antibióticos beta-lactámicos importantes, dominó en todos los ambientes. Otro gen, blaNDM-5, confiere resistencia a los carbapenémicos, algunos de los fármacos más potentes de la medicina moderna. Este gen apareció en muestras hospitalarias y en un aislado del río río abajo, vinculado a pequeños elementos de ADN móviles llamados plásmidos que pueden trasladarse entre bacterias.
Vínculos genéticos entre desagües hospitalarios y el río
Comparando pequeñas diferencias en el ADN —cambios de una sola letra en el genoma—, los científicos construyeron un árbol genealógico de las E. coli recogidas. La mayoría de las bacterias se agruparon según su origen: los aislados avícolas formaron un grupo, los bovinos su propia rama y las cepas de acuicultura quedaron aparte con menos rasgos de resistencia. Los aislados hospitalarios fueron más diversos pero, crucialmente, una cepa hospitalaria y una cepa del río río abajo compartieron una columna vertebral genética casi idéntica, sin diferencias en el núcleo de sus genomas. Aunque se clasificaron como tipos de secuencia ligeramente distintos, esta coincidencia casi perfecta, combinada con la presencia del mismo gen de resistencia a carbapenémicos en plásmidos, apunta con fuerza a una propagación reciente desde el efluente hospitalario hacia el río.
Qué significa esto para la salud y las políticas
Este trabajo ofrece una imagen cercana de cómo las bacterias resistentes se desplazan a través de la interfaz “One Health” que conecta personas, animales y el medio ambiente. Muestra que las aguas residuales hospitalarias son un punto caliente importante, liberando E. coli altamente resistentes en un río del que depende la comunidad local. Los sistemas ganaderos también aportan grandes cantidades de cepas resistentes, aunque todavía no a las que resisten a fármacos de último recurso. Incluso con un número modesto de muestras tomadas en un solo mes, los hallazgos respaldan acciones urgentes: un mejor tratamiento de las aguas residuales hospitalarias, un uso más prudente de antibióticos en granjas y clínicas, y vigilancia rutinaria de ríos y otras fuentes de agua compartidas. Para el público general, el mensaje clave es que las decisiones sobre el uso de antibióticos y la gestión de residuos no solo afectan a los pacientes hospitalarios: modelan el flujo invisible de superbacterias por el medio ambiente que compartimos todos.
Cita: Rahman, A., Roy, S., Afreen, N. et al. Environmental dissemination of multidrug-resistant Escherichia coli across one health interfaces in Mymensingh, Bangladesh. npj Antimicrob Resist 4, 27 (2026). https://doi.org/10.1038/s44259-026-00202-x
Palabras clave: resistencia a los antimicrobianos, contaminación ambiental, aguas residuales, Escherichia coli, One Health