Clear Sky Science · pt
Mapeando interações genéticas positivas específicas por tipo celular em resolução de célula única para adenocarcinoma de pulmão
Por que pequenas diferenças entre células importam
Médicos sabem que duas pessoas com o “mesmo” câncer de pulmão podem responder de maneiras muito diferentes ao tratamento. Uma razão é que um tumor não é um bloco uniforme, mas um mosaico de muitos tipos celulares — células cancerosas em estados distintos, células imunes que podem combater ou ajudar o tumor, e outros. Este estudo faz uma pergunta simples, mas potente: será que conseguimos ler os padrões de como genes atuam em conjunto dentro de células individuais para identificar quais tumores são mais perigosos e quais pacientes têm maior probabilidade de se beneficiar da imunoterapia?
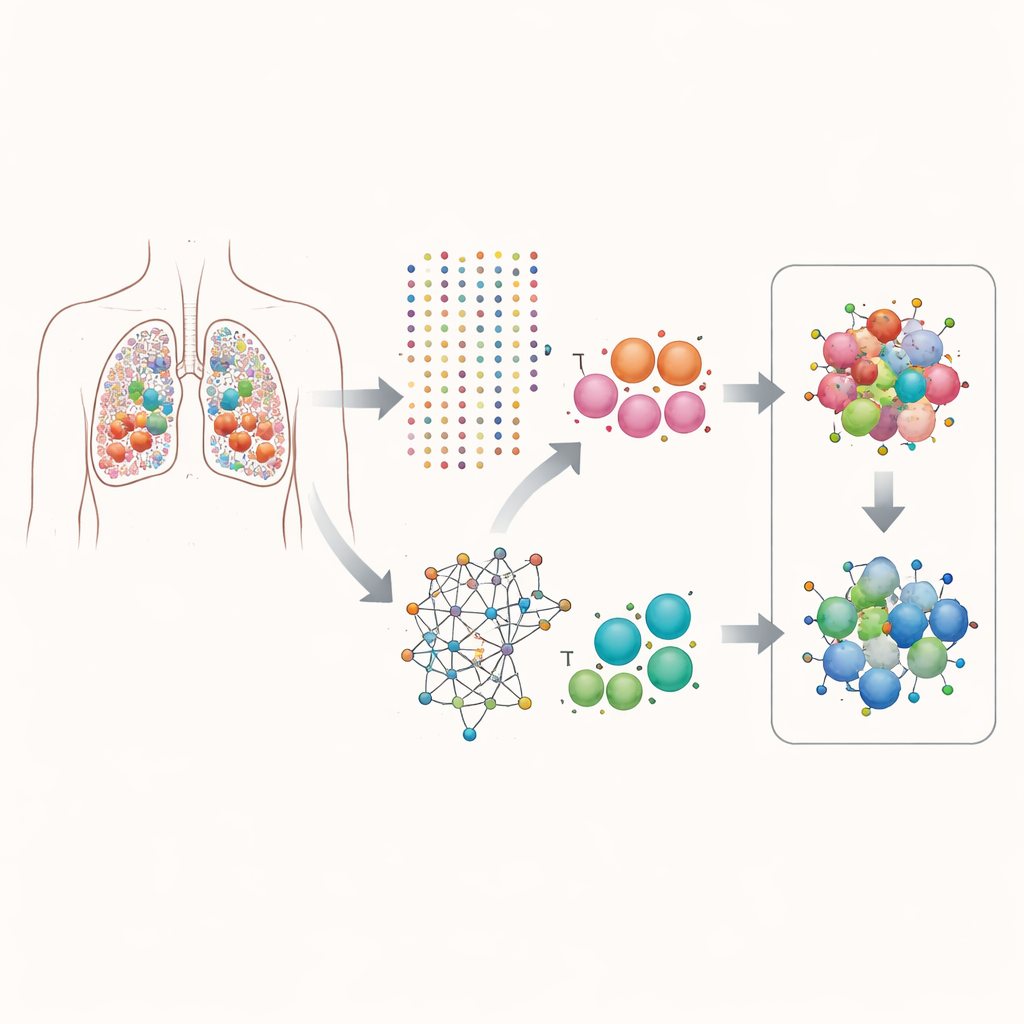
Olhando para dentro dos tumores uma célula por vez
Os pesquisadores focaram no adenocarcinoma de pulmão, uma forma comum de câncer de pulmão. Usando sequenciamento de RNA de célula única, mediram quais genes estavam ativos em mais de 160.000 células individuais extraídas de tumores de pacientes. Em vez de observar a atividade média dos genes em todo o tumor, separaram os dados por tipo celular, dando atenção especial às células epiteliais (as que se tornam cancerosas) e às células T (células imunes que podem atacar tumores). Essa visão célula a célula permitiu perguntar quais genes tendem a ser ativados juntos dentro da mesma célula e como essas combinações se relacionam com a velocidade aparente de divisão celular.
Encontrando parcerias genéticas úteis
A equipe construiu um pipeline computacional que chama de scPGI-finder para caçar “interações genéticas positivas” em resolução de célula única. Em termos simples, procuraram pares de genes que frequentemente estão ativos em conjunto na mesma célula e cuja atividade conjunta está ligada a maior aptidão celular, medida por assinaturas de divisão e crescimento celular. Após várias etapas de filtragem — verificando com que frequência cada par é coativo, se essas células parecem mais proliferativas, se os genes são fortemente coexpressos e se compartilham papéis biológicos semelhantes — reuniram dois grandes mapas de parcerias gene–gene: cerca de 50.000 pares em células epiteliais e 16.000 em células T. Essas redes de interação estavam fortemente conectadas em mapas conhecidos de proteínas e vias, sugerindo que capturam programas cooperativos reais em vez de coincidências aleatórias.
Lendo a malignidade a partir do circuito das células cancerosas
Entre as interações epiteliais, os autores destacaram um subconjunto que era muito mais coativo em células cancerosas malignas do que em células epiteliais não malignas vizinhas. Eles combinaram esses pares em um escore que reflete quantos desses pares genéticos “epiteliais malignos” estão ativos em conjunto em uma dada célula ou amostra de tecido. Células cancerosas com escores mais altos apresentavam características mais semelhantes a células-tronco, menos diferenciadas e mais associadas a marcas clássicas do câncer, como crescimento descontrolado. Quando aplicado a amostras tumorais globais de várias coortes de pacientes, esse escore foi consistentemente mais alto em tumores do que em pulmão normal adjacente e separou tumor de tecido normal com altíssima precisão. Pacientes cujos tumores tinham escores elevados tenderam a ter sobrevida pior, e algumas linhas celulares de alto escore foram mais sensíveis a diversos medicamentos que miram sinais de estímulo ao crescimento, particularmente fármacos direcionados à via EGFR.
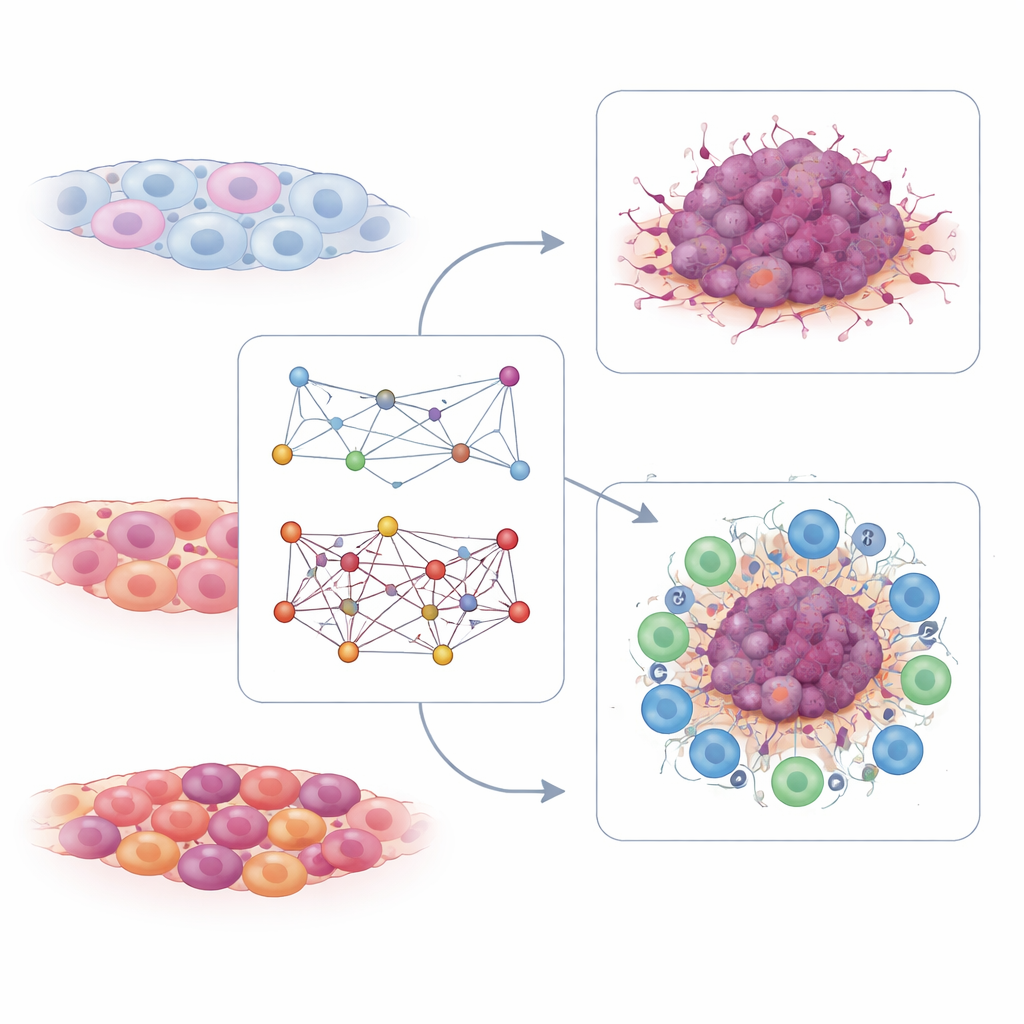
Avaliando a força imune a partir das células T
O mapa de interações de células T contou uma história complementar. Aqui, os pesquisadores buscaram pares de genes cuja atividade conjunta em células T estava ligada a boas ou más respostas à terapia com inibidores de checkpoint imunológico, uma forma de imunoterapia que libera as células T contra o câncer. Encontraram centenas de pares conectados tanto à responsividade quanto à resistência. A partir desses, destilaram uma assinatura pequena composta por apenas seis pares de interação ligados ao sinal do receptor de células T. Em múltiplos conjuntos independentes de pacientes, valores mais altos desse escore de interação de células T foram observados em pessoas que responderam à imunoterapia baseada em PD-1 e se associaram a maior sobrevida. Tumores com escores elevados de células T tendiam a ter um microambiente imune “quente”, rico em células imunes ativas, enquanto escores baixos marcavam tumores “frios”, menos propensos a se beneficiar desses medicamentos.
O que isso significa para o futuro do cuidado do câncer
Este trabalho mostra que olhar não apenas quais genes estão ativados, mas como pares de genes são coativados dentro de tipos celulares específicos, pode revelar estruturas ocultas nos tumores. No adenocarcinoma de pulmão, padrões de atividade cooperativa de genes em células cancerosas ajudam a sinalizar doenças mais agressivas, enquanto padrões semelhantes em células T ajudam a prever quem se beneficiará da imunoterapia. Embora esses mapas de interação sejam baseados em correlações em vez de experimentos diretos, eles oferecem uma nova maneira de ler o circuito interno de um tumor a partir de dados de célula única e podem guiar diagnósticos, prognósticos e escolhas de tratamento mais precisos à medida que a abordagem for refinada e estendida a outros cânceres.
Citação: Chen, B., Liu, M., Dong, Q. et al. Charting cell-type-specific positive genetic interaction at single-cell resolution for lung adenocarcinoma. npj Precis. Onc. 10, 137 (2026). https://doi.org/10.1038/s41698-026-01328-x
Palavras-chave: adenocarcinoma de pulmão, genômica de célula única, interações genéticas, microambiente tumoral, resposta à imunoterapia