Clear Sky Science · fr
Cartographier les interactions génétiques positives spécifiques aux types cellulaires à résolution monocellulaire pour l’adénocarcinome pulmonaire
Pourquoi de minuscules différences entre cellules comptent
Les médecins savent que deux personnes atteintes du « même » cancer du poumon peuvent répondre très différemment au traitement. Une raison est qu’une tumeur n’est pas une masse uniforme, mais un patchwork de nombreux types cellulaires : cellules cancéreuses dans des états différents, cellules immunitaires qui peuvent combattre ou aider la tumeur, et plus encore. Cette étude pose une question simple mais puissante : peut-on lire, à partir des modèles de coopération des gènes à l’intérieur de cellules individuelles, quelles tumeurs sont les plus dangereuses et quels patients ont le plus de chances de bénéficier de l’immunothérapie ?
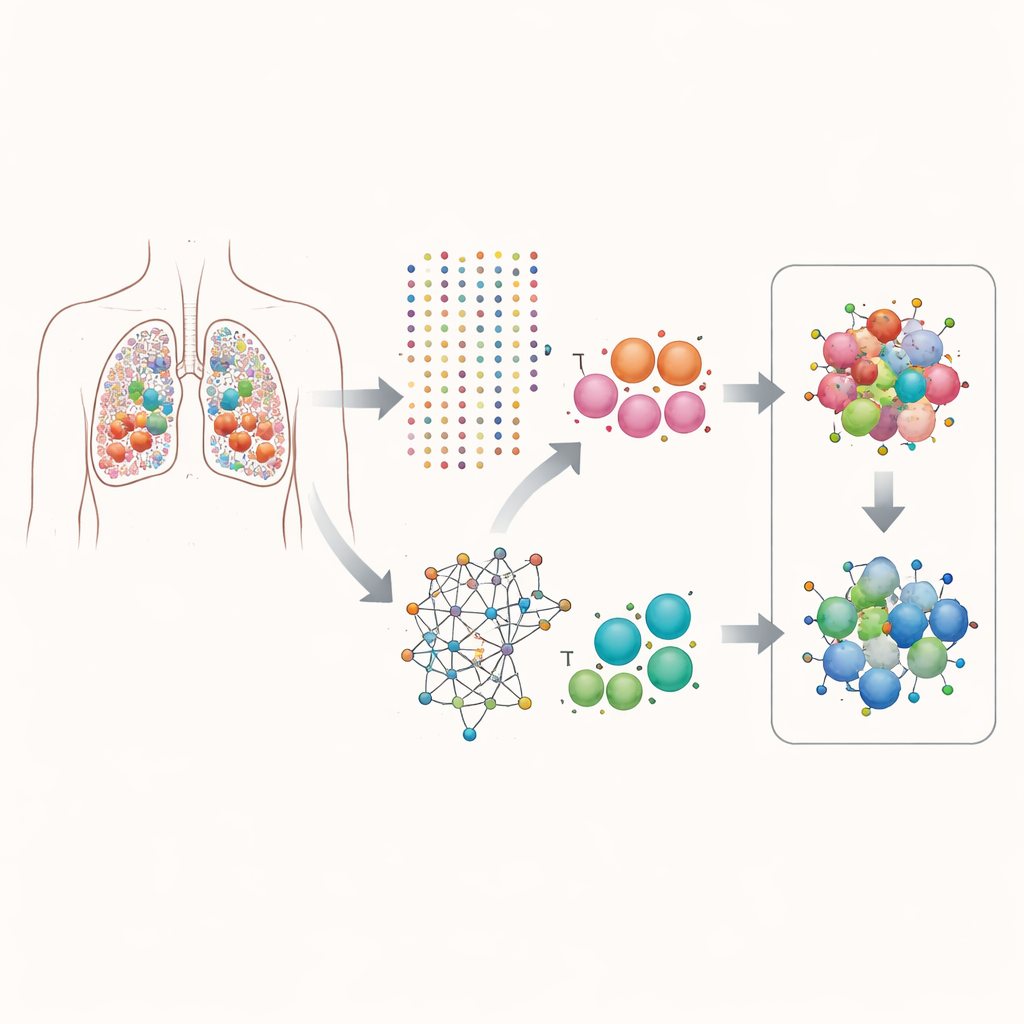
Regarder les tumeurs cellule par cellule
Les chercheurs se sont concentrés sur l’adénocarcinome pulmonaire, une forme courante de cancer du poumon. En utilisant le séquençage de l’ARN à l’échelle unicellulaire, ils ont mesuré quels gènes étaient activés dans plus de 160 000 cellules individuelles prélevées sur des tumeurs de patients. Plutôt que d’examiner l’activité génique moyenne sur l’ensemble de la tumeur, ils ont séparé les données par type cellulaire, en prêtant une attention particulière aux cellules épithéliales (les cellules qui deviennent cancéreuses) et aux cellules T (cellules immunitaires capables d’attaquer les tumeurs). Cette vue cellule par cellule leur a permis de déterminer quels gènes tendent à être activés ensemble dans la même cellule et comment ces couplages se rapportent à la vitesse apparente de division des cellules.
Identifier des partenariats génétiques utiles
L’équipe a développé un pipeline computationnel qu’ils appellent scPGI-finder pour rechercher des « interactions génétiques positives » à résolution monocellulaire. En termes simples, ils ont cherché des paires de gènes qui sont souvent actives conjointement dans la même cellule et dont l’activité conjointe est liée à une meilleure fitness cellulaire, mesurée par des signatures de division et de croissance. Après plusieurs étapes de filtrage — vérification de la fréquence de co-activation de chaque paire, examen de l’état prolifératif des cellules concernées, force de co-expression des gènes et similitude de leurs rôles biologiques — ils ont assemblé deux grandes cartes de partenariats gène–gène : environ 50 000 paires dans les cellules épithéliales et 16 000 dans les cellules T. Ces réseaux d’interaction étaient étroitement connectés aux cartes protéiques et aux voies connues, suggérant qu’ils captent de véritables programmes coopératifs plutôt que des coïncidences aléatoires.
Lire la malignité à partir du câblage des cellules cancéreuses
Parmi les interactions épithéliales, les auteurs ont mis en évidence un sous-ensemble beaucoup plus fortement co-actif dans les cellules cancéreuses malignes que dans les cellules épithéliales non malignes environnantes. Ils ont combiné ces paires en un score reflétant le nombre de ces paires « épithéliales malignes » actives conjointement dans une cellule ou un échantillon tissulaire donné. Les cellules tumorales avec des scores plus élevés semblaient plus à l’état de cellules souches, moins différenciées et davantage associées aux caractéristiques classiques du cancer telles que la croissance incontrôlée. Appliqué à des échantillons tumoraux en vrac issus de nombreuses cohortes de patients, ce score était systématiquement plus élevé dans les tumeurs que dans le poumon normal adjacent et séparait le tissu tumoral du tissu normal avec une très grande précision. Les patients dont les tumeurs affichaient des scores élevés avaient tendance à présenter une survie plus faible, et certaines lignées cellulaires à score élevé étaient plus sensibles à plusieurs médicaments ciblant les signaux promoteurs de croissance, en particulier des médicaments visant la voie EGFR.
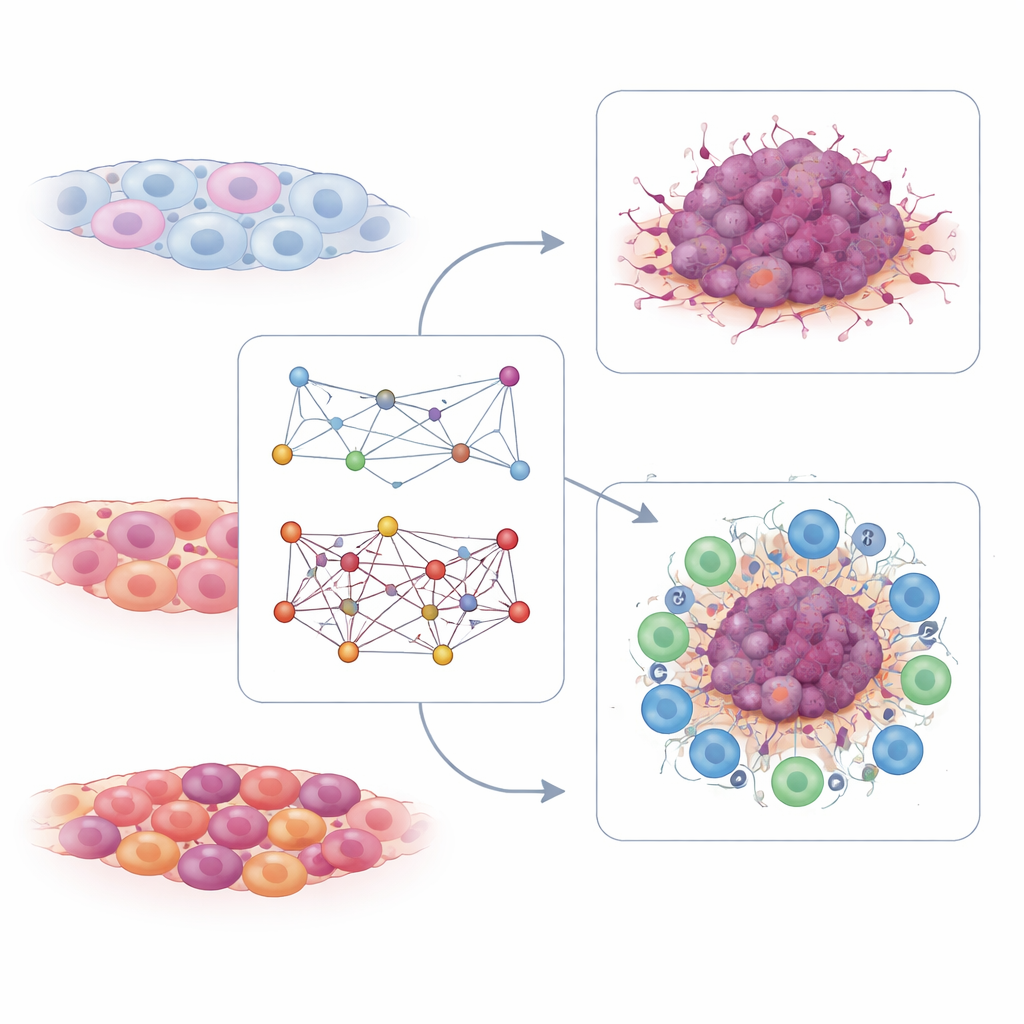
Évaluer la vigueur immunitaire à partir des cellules T
La carte d’interaction des cellules T raconte une histoire complémentaire. Les chercheurs y ont recherché des paires de gènes dont l’activité conjointe dans les cellules T était liée à une bonne ou une mauvaise réponse à la thérapie par inhibiteurs de points de contrôle immunitaires, une forme d’immunothérapie qui libère l’action des cellules T contre le cancer. Ils ont identifié des centaines de paires associées soit à la sensibilité soit à la résistance. À partir de celles-ci, ils ont extrait une petite signature constituée de seulement six paires d’interactions liées au signalement du récepteur des cellules T. Dans plusieurs ensembles de données de patients indépendants, des valeurs plus élevées de ce score d’interaction des cellules T ont été observées chez les personnes répondant à l’immunothérapie basée sur le PD-1 et étaient associées à une survie plus longue. Les tumeurs avec des scores élevés de cellules T avaient tendance à présenter un microenvironnement immunitaire « chaud », riche en cellules immunitaires actives, tandis que les scores faibles caractérisaient des tumeurs « froides » moins susceptibles de bénéficier de ces médicaments.
Ce que cela implique pour les soins futurs contre le cancer
Ce travail montre que regarder non seulement quels gènes sont activés, mais aussi comment des paires de gènes sont co-activées au sein de types cellulaires spécifiques, peut révéler une structure cachée dans les tumeurs. Dans l’adénocarcinome pulmonaire, les modèles d’activité génique coopérative dans les cellules cancéreuses aident à signaler une maladie plus agressive, tandis que des schémas similaires dans les cellules T aident à prédire qui bénéficiera de l’immunothérapie. Bien que ces cartes d’interaction reposent sur des corrélations plutôt que sur des expériences directes, elles offrent un nouveau moyen d’interpréter le câblage interne d’une tumeur à partir de données monocellulaires et pourraient orienter des diagnostics, pronostics et choix thérapeutiques plus précis à mesure que l’approche sera affinée et étendue à d’autres cancers.
Citation: Chen, B., Liu, M., Dong, Q. et al. Charting cell-type-specific positive genetic interaction at single-cell resolution for lung adenocarcinoma. npj Precis. Onc. 10, 137 (2026). https://doi.org/10.1038/s41698-026-01328-x
Mots-clés: adénocarcinome pulmonaire, génomique unicellulaire, interactions génétiques, microenvironnement tumoral, réponse à l’immunothérapie