Clear Sky Science · pt
RNA intrônico móvel de um predador bacteriano acumula em células arqueanas mortas
Predadores minúsculos e mensagens ocultas
Em cantos escuros e sem oxigênio do nosso planeta, predadores microscópicos caçam outros microrganismos em batalhas em câmera lenta que moldam como o carbono é reciclado e como o metano é produzido. Este estudo examina um viajante inesperado que se move durante esses encontros: um fragmento de RNA genético de um predador bacteriano que acaba dentro de células mortas de um domínio diferente da vida, as arqueias. O trabalho oferece um raro vislumbre em tempo real de como elementos genéticos podem pular entre ramos distantes da árvore da vida, alimentando ideias de longa data sobre transferência horizontal de genes e o antigo mundo do RNA.
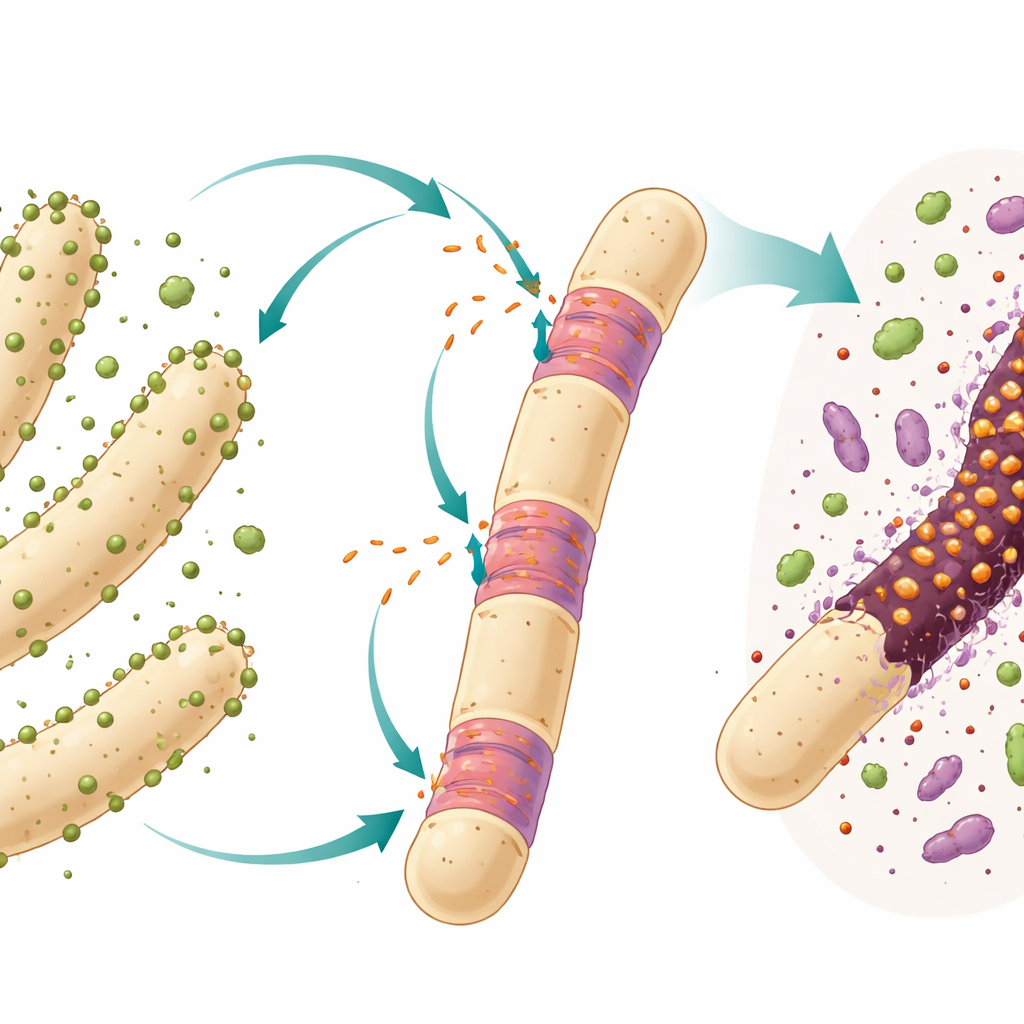
Genes saltadores em células simples
Muitas bactérias e arqueias carregam penetras genéticos chamados íntrons, trechos de DNA que são copiados em RNA e depois cortados antes que uma molécula funcional seja produzida. Em organismos complexos, íntrons são características rotineiras dos genes, mas em células simples eles são mais raros e frequentemente se comportam como aproveitadores móveis que podem se deslocar e invadir novos pontos no genoma. O foco aqui é um íntron particular do tipo “grupo I” localizado dentro do gene do RNA ribossomal 23S de um predador bacteriano ultraminiatura chamado Candidatus Velamenicoccus archaeovorus. Essa bactéria vive presa a longas células arqueanas em forma de filamentos em uma cultura laboratorial de longa duração que degrada o composto vegetal limoneno e produz metano lentamente.
Um mundo microbiano lento e fechado
Os pesquisadores trabalharam com uma cultura de enriquecimento anaeróbica mantida por mais de vinte anos em limoneno com apenas uma transferência por ano. Nesse sistema fechado, diferentes micróbios cooperam e competem. Um parceiro bacteriano decompõe o limoneno em compostos menores, e várias arqueias metanogênicas, incluindo a espécie formadora de filamentos Methanothrix soehngenii, convertem esses produtos em metano. A ultramicrobactéria Ca. Velamenicoccus archaeovorus vive como um epibionte, ligada à superfície desses filamentos. Trabalhos anteriores sugeriram que ela age como predadora: algumas células do filamento parecem mortas, mas ainda contêm DNA e lipídios, o que implica que o predador extrai materiais celulares-chave deixando uma concha parcial para trás.
Vendo RNA estrangeiro dentro de células mortas
Para testar se o predador envia seu RNA intrônico para suas vítimas arqueanas, a equipe usou uma técnica de imagem sensível chamada CARD‑FISH, que utiliza sondas de DNA curtas marcadas para iluminar moléculas de RNA correspondentes dentro de células preservadas. Eles desenharam três sondas que reconhecem o RNA do íntron e as combinaram com sondas para o RNA ribossomal do predador e para a coloração do DNA. Ao microscópio, o sinal do íntron apareceu tanto nas minúsculas células esféricas do predador quanto, crucialmente, em certos segmentos dos grandes filamentos de Methanothrix. Essas células do filamento que exibiam sinal do íntron haviam perdido seu próprio RNA ribossomal, um marco de morte, mas ainda continham DNA, confirmando que estavam mortas mas não totalmente decompostas. Sondas controle com sequências invertidas não acenderam, o que indica que o sinal era específico para o íntron.
Contando viajantes raros de RNA
Para complementar as imagens, os autores reexaminaram um grande conjunto de dados de sequenciamento de RNA previamente gerado a partir da mesma cultura. Como o RNA ribossomal não havia sido removido dessa amostra, eles puderam comparar diretamente com que frequência a sequência do íntron aparecia em relação ao RNA 23S maduro e processado. Eles descobriram que leituras correspondentes ao íntron eram cerca de 1 em 20.000 em comparação com o RNA 23S maduro, o que significa que a maioria das cópias do íntron é cortada com sucesso do transcriptos primários. Algumas poucas leituras atravessavam as fronteiras entre o íntron e sua sequência vizinha, indicando que uma fração muito pequena dos transcritos permanecia não emendado. Junto com a imagem, isso mostrou que moléculas de RNA do íntron excisadas existem na cultura e podem ser encontradas fora de sua célula hospedeira original.
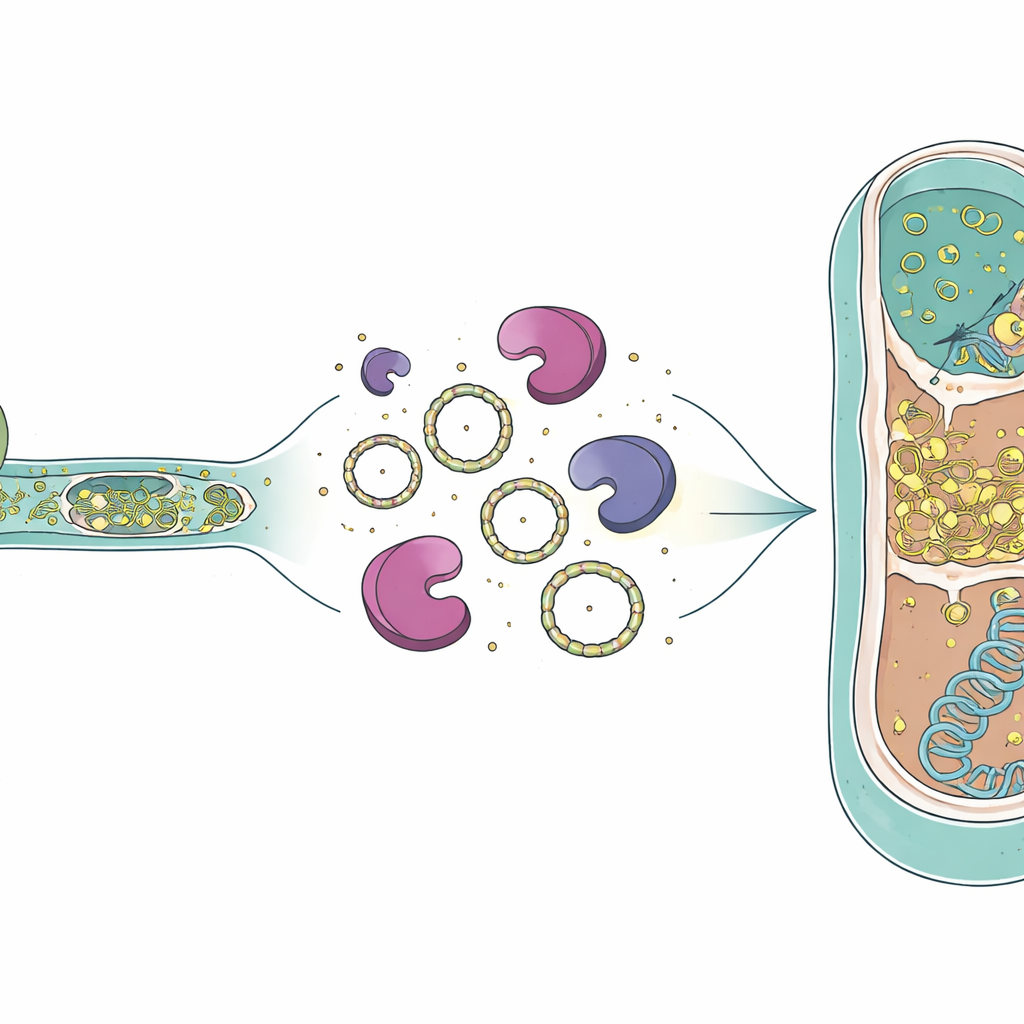
Como o RNA pode sobreviver e seguir adiante
A presença de RNA intrônico dentro de células arqueanas mortas levanta questões sobre como essas moléculas persistem tempo suficiente para ter efeito. Trabalhos anteriores mostraram que íntrons do grupo I podem formar anéis circulares de RNA após o splicing, e esses círculos são mais resistentes às enzimas que normalmente degradam RNA. O genoma do predador também codifica uma transcriptase reversa especial — uma enzima que pode copiar RNA de volta em DNA — que já havia sido detectada como proteína na mesma cultura. Imagens de microscopia eletrônica de estudos anteriores mostraram contatos citoplasmáticos abertos entre predador e vítima, sugerindo que não apenas RNA, mas possivelmente essa enzima, poderia passar para a célula arqueana. Se o RNA intrônico circular e uma transcriptase reversa entrarem juntos em uma célula vítima, eles poderiam, em princípio, ser copiados em DNA e inseridos no genoma arqueano, criando um novo íntron em um novo hospedeiro.
Por que isso importa para o tráfego genético da vida
Para não especialistas, a principal conclusão é que este estudo fornece evidência direta, microscópica, de que um fragmento móvel de RNA bacteriano pode deixar sua célula de origem e se acumular nos restos mortos de um microrganismo muito diferente. Esse movimento é um passo inicial chave na transferência horizontal de genes, o processo pelo qual genes e elementos genéticos se espalham entre espécies. O trabalho também amplia os papéis conhecidos do RNA extracelular, que já inclui sinalização e inibição de crescimento, ao adicionar RNA intrônico móvel à lista. Em um panorama mais amplo, tais RNAs móveis e suas enzimas associadas ajudam a explicar como inovações genéticas foram embaralhadas através de comunidades microbianas ao longo do tempo evolutivo, borrando as fronteiras entre ramos separados da vida.
Citação: Kizina, J., Lonsing, A. & Harder, J. Mobile intron RNA from a bacterial predator accumulates in dead archaeal cells. Sci Rep 16, 14654 (2026). https://doi.org/10.1038/s41598-026-51721-6
Palavras-chave: introns móveis, RNA extracelular, predação microbiana, transferência horizontal de genes, arqueias metanogênicas