Clear Sky Science · nl
Mobiel intron‑RNA van een bacterieel roofdier hoopt zich op in dode archaeale cellen
Kleine roofdieren en verborgen boodschappen
In de donkere, zuurstofloze hoeken van onze planeet jagen microscopische roofdieren op andere microben in traag verlopende gevechten die bepalen hoe koolstof wordt gerecycled en hoe methaan ontstaat. Deze studie richt zich op een onverwachte reiziger die tijdens zulke ontmoetingen beweegt: een stukje genetisch RNA van een bacterieel roofdier dat uiteindelijk in dode cellen van een andere levensdomein, de archaea, terechtkomt. Het werk biedt een zeldzame blik in real time op hoe genetische elementen mogelijk tussen verre takken van de levensboom springen en voedt lang bestaande ideeën over “horizontale” genoverdracht en de oude RNA‑wereld.
Springende genen in eenvoudige cellen
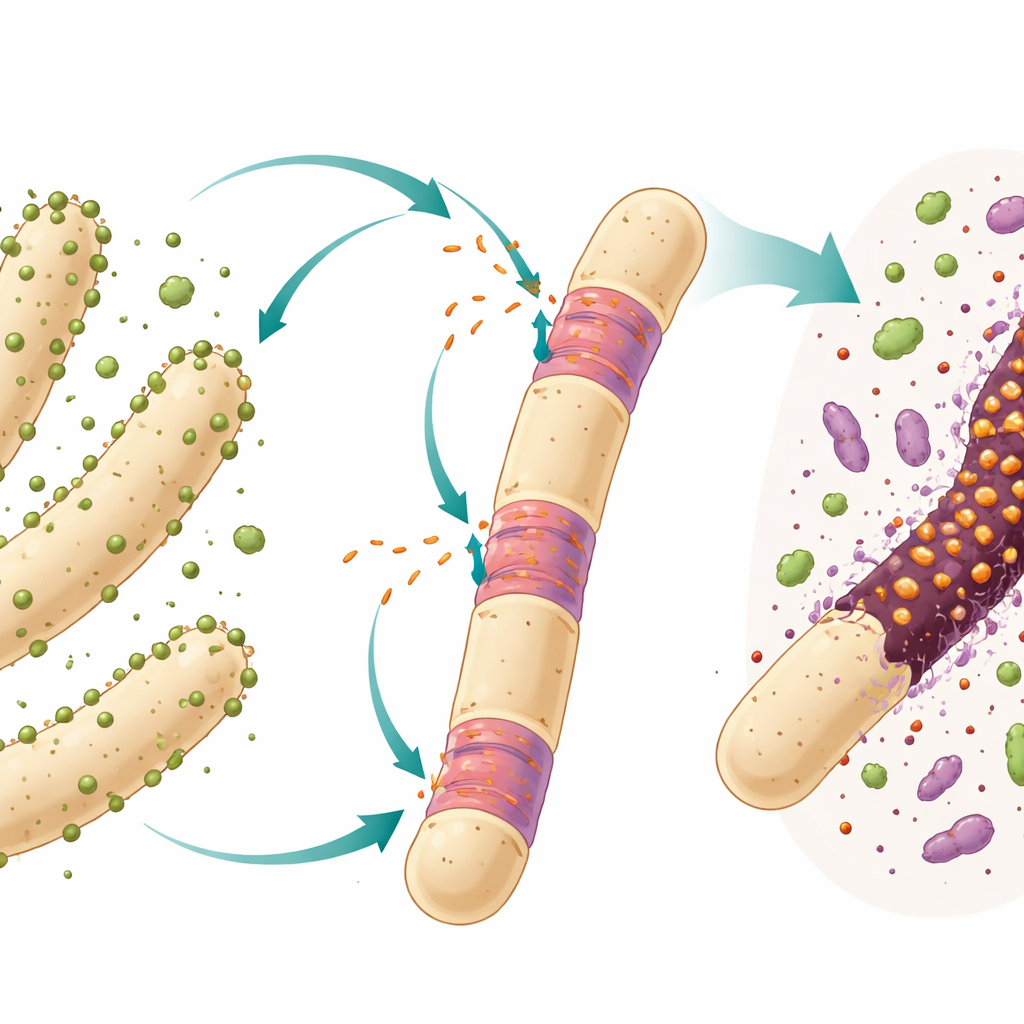
Veel bacteriën en archaea dragen genetische sluipgangers die introns worden genoemd: DNA‑stukken die in RNA worden gekopieerd en vervolgens weer uit dat RNA worden verwijderd voordat een werkend molecuul ontstaat. Bij complexe organismen zijn introns routineonderdelen van genen, maar in eenvoudige cellen zijn ze zeldzamer en gedragen ze zich vaak als mobiele profiteurs die kunnen verplaatsen en nieuwe plaatsen in het genoom kunnen binnendringen. De aandacht gaat hier uit naar een specifiek intron van het “groep I”‑type dat in het 23S ribosomaal RNA‑gen zit van een ultraklein bacterieel roofdier genaamd Candidatus Velamenicoccus archaeovorus. Deze bacterie leeft vastgehecht aan lang filamentvormige archaeale cellen in een langlopende laboratoriumcultuur die het plantbestanddeel limoneen afbreekt en langzaam methaan produceert.
Een trage, gesloten microbiele wereld
De onderzoekers werkten met een anaerobe verrijkingscultuur die al meer dan twintig jaar op limoneen wordt onderhouden met slechts één overdracht per jaar. In dit gesloten systeem werken verschillende microben samen en concurreren ze. Een bacterieel partner breekt limoneen af tot kleinere verbindingen, en meerdere methanogene archaea, waaronder de filamentvormende soort Methanothrix soehngenii, zetten die producten om in methaan. De ultramicrobacterie Ca. Velamenicoccus archaeovorus leeft als epibiont, vastgehecht aan het oppervlak van deze filamenten. Eerder onderzoek suggereerde dat het als een roofdier fungeert: sommige filamentcellen lijken dood maar bevatten toch DNA en lipiden, wat erop wijst dat het roofdier belangrijke cellulaire materialen onttrekt terwijl het een deels achtergebleven omhulsel nalaat.
Vreemd RNA zien in dode cellen
Om te testen of het roofdier zijn intron‑RNA in zijn archaeale slachtoffers stuurt, gebruikte het team een gevoelige beeldvormingstechniek genaamd CARD‑FISH, waarbij korte gelabelde DNA‑probes worden gebruikt om overeenkomende RNA‑moleculen in behouden cellen te markeren. Ze ontwierpen drie sondes die het intron‑RNA herkennen en combineerden die met sondes voor het ribosomaal RNA van het roofdier en voor DNA‑kleuring. Onder de microscoop verscheen het intron‑signaal zowel in de kleine bolvormige roofdiercellen als, cruciaal, in bepaalde segmenten van de grote Methanothrix‑filamenten. Deze filamentcellen met intron‑signaal hadden hun eigen ribosomaal RNA verloren, een kenmerk van de dood, maar bevatten nog wel DNA, wat bevestigt dat ze dood waren maar nog niet volledig ontbonden. Controleprobes met omgekeerde sequenties gaven geen signaal, wat erop wijst dat het gedetecteerde signaal specifiek voor het intron was.
Zeldzame RNA‑reizigers tellen
Ter aanvulling op de beelden heronderzoekten de auteurs een grote RNA‑sequencingdataset die eerder van dezelfde cultuur was gegenereerd. Omdat ribosomaal RNA niet uit dit monster was verwijderd, konden ze rechtstreeks vergelijken hoe vaak de intronsequentie voorkwam ten opzichte van het normale, volledig verwerkte 23S ribosomale RNA. Ze vonden dat reads die overeenkwamen met het intron ongeveer 1 op 20.000 waren vergeleken met het rijpe 23S‑RNA, wat betekent dat de meeste intronkopieën met succes uit het primaire transcriptaat worden verwijderd. Een handvol reads overspande de grenzen tussen intron en de aangrenzende sequentie, wat aangeeft dat een zeer klein deel van de transcripten ongespliced bleef. Samen met de beeldvorming toonde dit aan dat uitgeknipte intron‑RNA‑moleculen in de cultuur bestaan en buiten hun oorspronkelijke gastheercel kunnen worden aangetroffen.
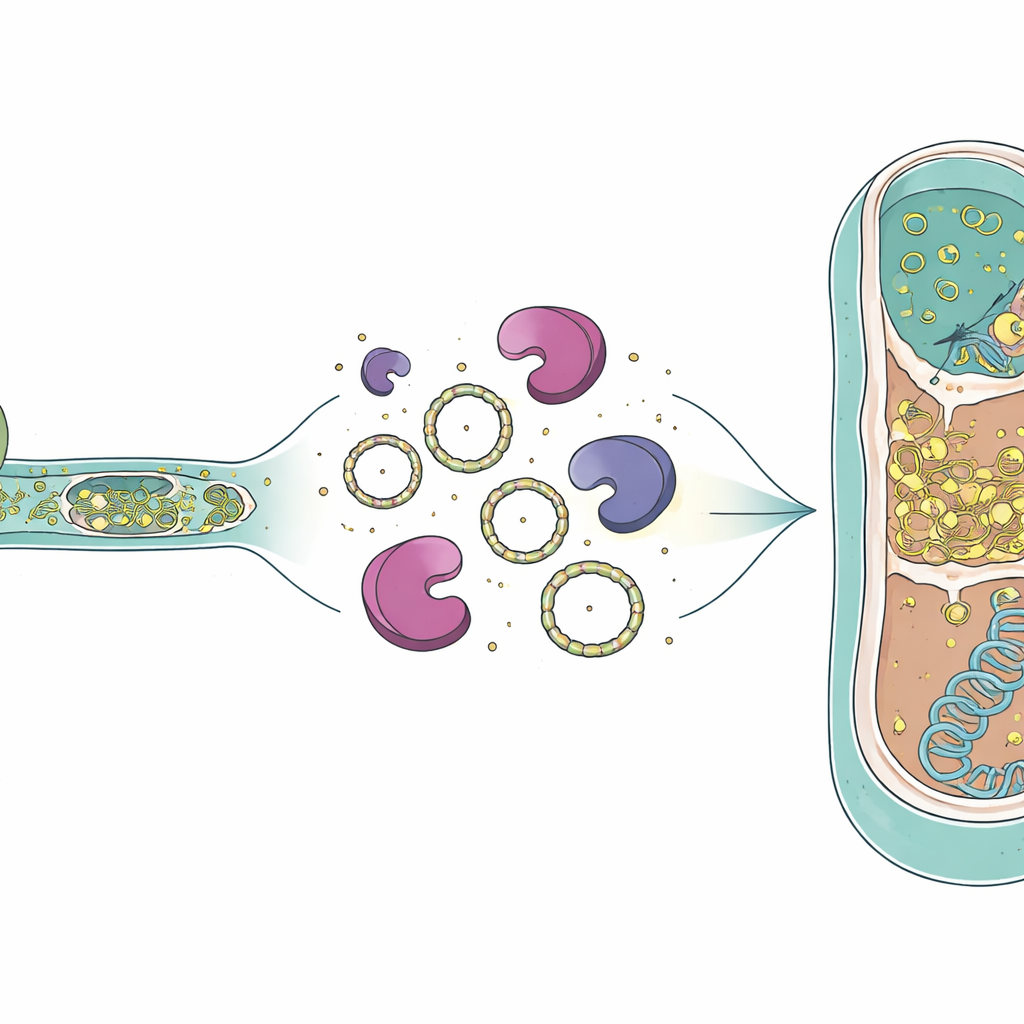
Hoe het RNA kan overleven en zich verplaatsen
De aanwezigheid van intron‑RNA in dode archaeale cellen roept de vraag op hoe deze moleculen lang genoeg standhouden om van belang te zijn. Eerder werk heeft aangetoond dat groep I‑introns na splicing cirkelvormige RNA‑ringen kunnen vormen, en zulke cirkels zijn beter bestand tegen enzymen die normaal RNA afbreken. Het genoom van het roofdier codeert ook voor een speciale reverse transcriptase—een enzym dat RNA terug naar DNA kan kopiëren—dat eerder als eiwit in dezelfde cultuur is gedetecteerd. Elektronenmicroscopiebeelden uit eerdere studies toonden open cytoplasmatische contacten tussen roofdier en slachtoffer, wat suggereert dat niet alleen RNA maar mogelijk ook dit enzym in de archaeale cel kan passeren. Als circulair intron‑RNA en een reverse transcriptase samen een slachtoffercel binnendringen, zouden ze in principe naar DNA gekopieerd en in het archaeale genoom ingevoegd kunnen worden, waardoor een nieuw intron in een nieuwe gastheer ontstaat.
Waarom dit ertoe doet voor het genetische verkeer van het leven
Voor niet‑specialisten is de belangrijkste conclusie dat deze studie direct microscopisch bewijs levert dat een mobiel stukje bacterieel RNA zijn thuissel kan verlaten en zich ophopen in de dode resten van een heel ander microbe. Die beweging is een cruciale vroege stap in horizontale genoverdracht, het proces waarmee genen en genetische elementen zich over soortgrenzen verspreiden. Het werk vergroot ook de bekende rollen van extracellulair RNA, die al signalering en groeiremming omvatten, door mobiel intron‑RNA aan dat palet toe te voegen. In het bredere perspectief helpen dergelijke mobiele RNA’s en hun bijbehorende enzymen verklaren hoe genetische innovaties door microbiele gemeenschappen zijn geschoven in de loop van evolutionaire tijd, waarmee de grenzen tussen afzonderlijke takken van het leven vervagen.
Bronvermelding: Kizina, J., Lonsing, A. & Harder, J. Mobile intron RNA from a bacterial predator accumulates in dead archaeal cells. Sci Rep 16, 14654 (2026). https://doi.org/10.1038/s41598-026-51721-6
Trefwoorden: mobiele introns, extracellulair RNA, microbiële predatie, horizontale genoverdracht, methanogene archaea