Clear Sky Science · it
RNA intronica mobile di un predatore batterico si accumula nelle cellule archeali morte
Predatori minuscoli e messaggi nascosti
Negli angoli oscuri e privi di ossigeno del nostro pianeta, predatori microscopici cacciano altri microrganismi in battaglie al rallentatore che determinano come il carbonio viene riciclato e come si produce il metano. Questo studio esamina un viaggiatore inatteso che si sposta durante quegli incontri: un frammento di RNA genetico proveniente da un predatore batterico che finisce all’interno di cellule morte di un altro dominio della vita, le archee. Il lavoro offre uno sguardo raro e in tempo reale su come elementi genetici possano saltare tra rami lontani dell’albero della vita, sostenendo idee di lunga data sul trasferimento genico “orizzontale” e sul primordiale mondo dell’RNA.
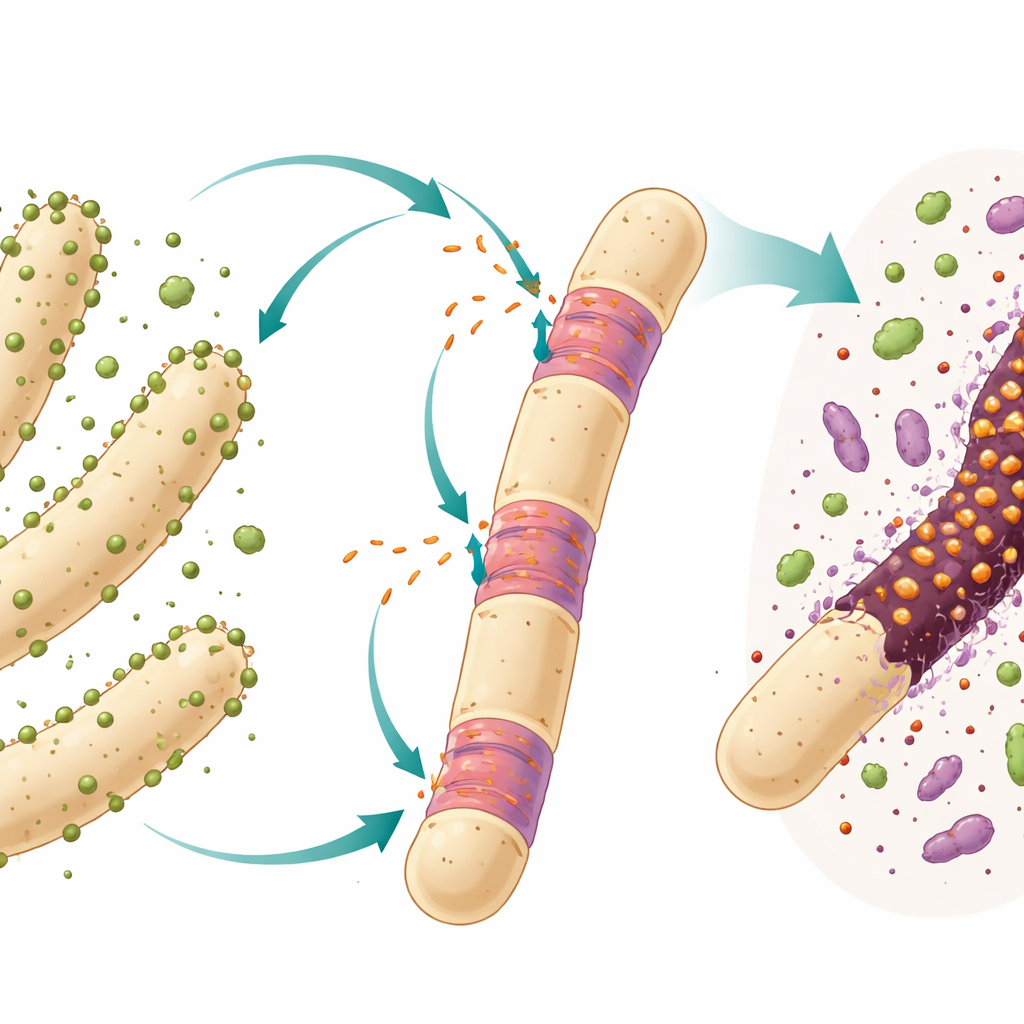
Geni saltellanti in cellule semplici
Molti batteri e archee ospitano passeggeri genetici chiamati introni, tratti di DNA che vengono trascritti in RNA e poi rimossi prima che si produca una molecola funzionante. Negli organismi complessi gli introni sono caratteristiche comuni dei geni, ma nelle cellule semplici sono più rari e spesso si comportano come parassiti mobili che possono spostarsi e invadere nuove posizioni nel genoma. Il soggetto qui è un introne di tipo “gruppo I” inserito nel gene dell’RNA ribosomale 23S di un predatore batterico ultrominuto denominato Candidatus Velamenicoccus archaeovorus. Questo batterio vive aderendo a lunghe cellule filamentose di archee in una coltura di laboratorio mantenuta da lungo tempo che degrada il limonene, un composto vegetale, producendo lentamente metano.
Un mondo microbico chiuso e lento
I ricercatori hanno lavorato con una coltura di arricchimento anaerobica mantenuta da oltre vent’anni con limonene e trasferita solo una volta all’anno. In questo sistema chiuso, differenti microrganismi cooperano e competono. Un partner batterico decompone il limonene in composti più piccoli e diverse archee metanogeniche, inclusa la specie filamentosa Methanothrix soehngenii, trasformano quei prodotti in metano. L’ultramicrobacterio Ca. Velamenicoccus archaeovorus vive come epibionte, attaccato alla superficie di questi filamenti. Lavori precedenti hanno suggerito che si comporti da predatore: alcune cellule filamentose appaiono morte ma contengono ancora DNA e lipidi, il che fa pensare che il predatore estragga materiali cellulari chiave lasciando dietro una sorta di guscio parziale.
Osservare RNA estraneo dentro cellule morte
Per verificare se il predatore invia il suo RNA intronico nelle vittime archeali, il team ha usato una tecnica di imaging sensibile chiamata CARD‑FISH, che impiega brevi sonde di DNA marcate per illuminare molecole di RNA corrispondenti all’interno di cellule fissate. Hanno progettato tre sonde che riconoscono l’RNA dell’introne e le hanno combinate con sonde per l’RNA ribosomale del predatore e con una colorazione del DNA. Al microscopio, il segnale dell’introne è apparso sia nelle piccole cellule sferiche del predatore sia, in modo cruciale, all’interno di alcuni segmenti dei grandi filamenti di Methanothrix. Le cellule filamentose che mostravano il segnale dell’introne avevano perso il proprio RNA ribosomale, un marcatore di morte, ma contenevano ancora DNA, confermando che erano morte ma non ancora completamente decomposte. Sonde di controllo con sequenze invertite non hanno prodotto segnale, a supporto del fatto che il rilevamento fosse specifico per l’introne.
Contare i rari viaggiatori RNA
Per completare le immagini, gli autori hanno riesaminato un ampio set di dati di sequenziamento RNA precedentemente generato dalla stessa coltura. Poiché l’RNA ribosomale non era stato rimosso da quel campione, hanno potuto confrontare direttamente quanto frequentemente la sequenza dell’introne compariva rispetto all’RNA 23S maturo e correttamente processato. Hanno riscontrato che le letture corrispondenti all’introne erano circa 1 su 20.000 rispetto all’RNA 23S maturo, il che significa che la maggior parte delle copie dell’introne viene correttamente rimossa dal trascritto primario. Una manciata di letture attraversava i confini tra introne e sequenza vicina, indicando che una piccolissima frazione di trascritti rimaneva non splicata. Insieme all’imaging, ciò dimostra che molecole di RNA intronico eccise esistono nella coltura e possono essere trovate al di fuori della loro cellula originaria.
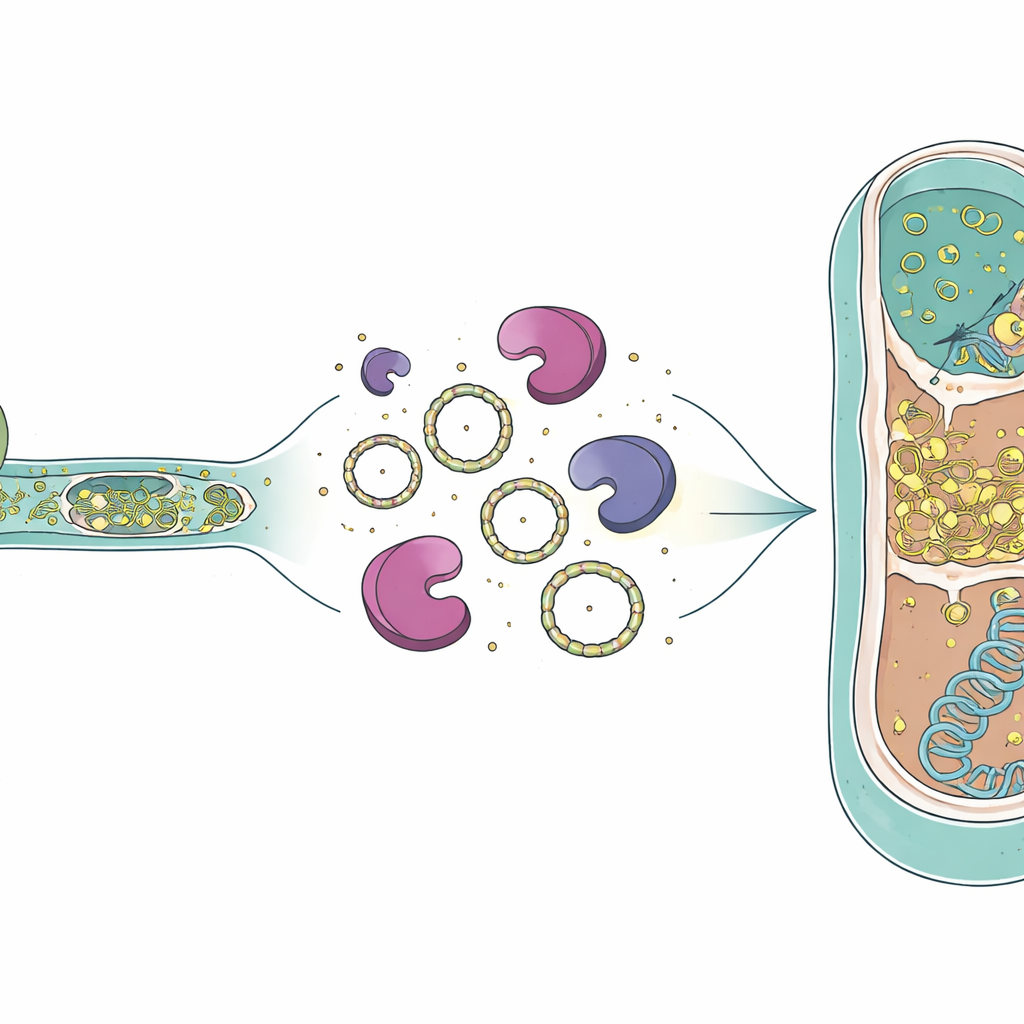
Come l’RNA potrebbe sopravvivere e spostarsi
La presenza di RNA intronico dentro cellule archeali morte solleva interrogativi su come queste molecole possano persistere a sufficienza per avere effetto. Studi precedenti hanno mostrato che gli introni di gruppo I possono formare anelli circolari di RNA dopo lo splicing, e tali circoli sono più resistenti agli enzimi che normalmente degradano l’RNA. Il genoma del predatore codifica anche una speciale trascrittasi inversa—un enzima che può copiare RNA in DNA—la quale era stata rilevata in precedenza come proteina nella stessa coltura. Immagini al microscopio elettronico da studi precedenti mostravano contatti citoplasmatici aperti fra predatore e vittima, suggerendo che non solo RNA ma forse anche questo enzima potrebbero passare nella cellula archeale. Se l’introne circolare e una trascrittasi inversa entrassero insieme in una cellula vittima, in linea di principio potrebbero essere copiati in DNA e inseriti nel genoma archeale, creando un nuovo introne in un nuovo ospite.
Perché questo importa per il traffico genetico della vita
Per chi non è specialista, il punto principale è che questo studio fornisce evidenza diretta e microscopica che un frammento mobile di RNA batterico può lasciare la sua cellula d’origine e accumularsi nei resti morti di un microrganismo molto diverso. Quel movimento è un passaggio iniziale cruciale nel trasferimento genico orizzontale, il processo mediante il quale geni ed elementi genetici si diffondono tra le specie. Il lavoro amplia anche i ruoli noti dell’RNA extracellulare, che già includeva segnali e inibizione della crescita, aggiungendo alla lista gli introni mobili. In prospettiva più ampia, tali RNA mobili e gli enzimi associati aiutano a spiegare come innovazioni genetiche siano state mescolate nelle comunità microbiche nel corso dell’evoluzione, sfumando i confini tra rami separati della vita.
Citazione: Kizina, J., Lonsing, A. & Harder, J. Mobile intron RNA from a bacterial predator accumulates in dead archaeal cells. Sci Rep 16, 14654 (2026). https://doi.org/10.1038/s41598-026-51721-6
Parole chiave: introni mobili, RNA extracellulare, predazione microbica, trasferimento genico orizzontale, archee metanogeniche