Clear Sky Science · es
ARN intrónico móvil de un depredador bacteriano se acumula en células arqueales muertas
Pequeños depredadores y mensajes ocultos
En los rincones oscuros y sin oxígeno de nuestro planeta, depredadores microscópicos cazan a otros microbios en batallas a cámara lenta que configuran cómo se recicla el carbono y se produce el metano. Este estudio examina a un viajero inesperado que se desplaza durante esos encuentros: un fragmento de ARN genético de un depredador bacteriano que acaba dentro de células muertas de un dominio distinto de la vida, las arqueas. El trabajo ofrece una rara visión en tiempo real de cómo elementos genéticos pueden saltar entre ramas distantes del árbol de la vida, apoyando ideas de larga data sobre la transferencia horizontal de genes y el antiguo mundo del ARN.
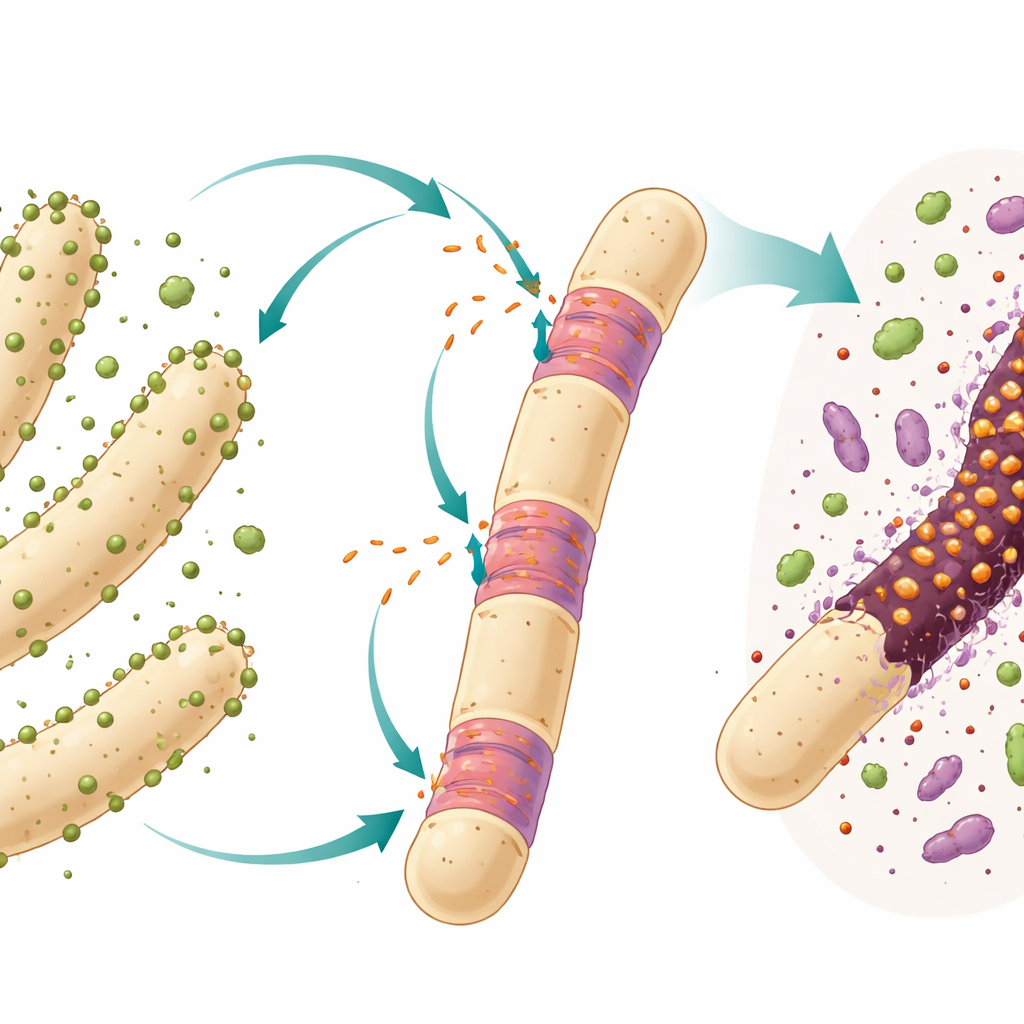
Genes saltarines en células simples
Muchas bacterias y arqueas albergan polizones genéticos llamados intrones, tramos de ADN que se copian a ARN y luego se recortan antes de que se produzca una molécula funcional. En organismos complejos, los intrones son rasgos habituales de los genes, pero en células simples son más raros y con frecuencia se comportan como aprovechados móviles que pueden desplazarse e invadir nuevos lugares del genoma. Aquí la atención se centra en un intrón particular del tipo “grupo I” situado dentro del gen del ARN ribosómico 23S de un ultraminúsculo depredador bacteriano llamado Candidatus Velamenicoccus archaeovorus. Esta bacteria vive adherida a largas células arqueales con forma de filamento en una cultura de laboratorio mantenida durante mucho tiempo que descompone el compuesto vegetal limoneno y produce metano lentamente.
Un mundo microbiano cerrado y lento
Los investigadores trabajaron con una cultura de enriquecimiento anaerobia que se ha mantenido durante más de veinte años con limoneno y con solo una transferencia al año. En este sistema cerrado, distintos microbios cooperan y compiten. Un socio bacteriano descompone el limoneno en compuestos más pequeños, y varias arqueas metanogénicas, incluida la especie formadora de filamentos Methanothrix soehngenii, convierten esos productos en metano. El ultramicrobacterio Ca. Velamenicoccus archaeovorus vive como epibionte, adherido a la superficie de estos filamentos. Trabajos previos sugerían que actúa como depredador: algunas células del filamento parecen muertas pero aún contienen ADN y lípidos, lo que implica que el depredador extrae materiales celulares clave dejando atrás una cáscara parcial.
Ver ARN ajeno dentro de células muertas
Para probar si el depredador envía su ARN intrónico a sus víctimas arqueales, el equipo utilizó una técnica de imagen sensible llamada CARD‑FISH, que emplea sondas de ADN cortas marcadas para iluminar moléculas de ARN coincidentes dentro de células preservadas. Diseñaron tres sondas que reconocen el ARN del intrón y las combinaron con sondas para el ARN ribosómico del depredador y para la tinción del ADN. Bajo el microscopio, la señal del intrón apareció tanto en las diminutas células esféricas del depredador como, crucialmente, dentro de ciertos segmentos de los grandes filamentos de Methanothrix. Esas células filamentosas que mostraban señal del intrón habían perdido su propio ARN ribosómico, una señal distintiva de muerte, pero aún contenían ADN, confirmando que estaban muertas pero no completamente descompuestas. Sondas de control con secuencias invertidas no se iluminaron, lo que sugiere que la señal era específica del intrón.
Contando a los raros viajeros de ARN
Para complementar las imágenes, los autores reexaminaron un gran conjunto de datos de secuenciación de ARN generado previamente a partir de la misma cultura. Dado que en esa muestra no se había eliminado el ARN ribosómico, pudieron comparar directamente con qué frecuencia aparecía la secuencia del intrón en relación con el ARN ribosómico 23S normal y totalmente procesado. Hallaron que las lecturas que coincidían con el intrón eran aproximadamente 1 de cada 20.000 en comparación con el ARN 23S maduro, lo que significa que la mayoría de las copias del intrón se recortan con éxito del transcrito primario. Un puñado de lecturas atravesaba los límites entre el intrón y la secuencia vecina, indicando que una fracción muy pequeña de transcritos permanecía no empalmada. Junto con la microscopía, esto mostró que moléculas de ARN intrónico excisado existen en la cultura y pueden hallarse fuera de su célula hospedadora original.
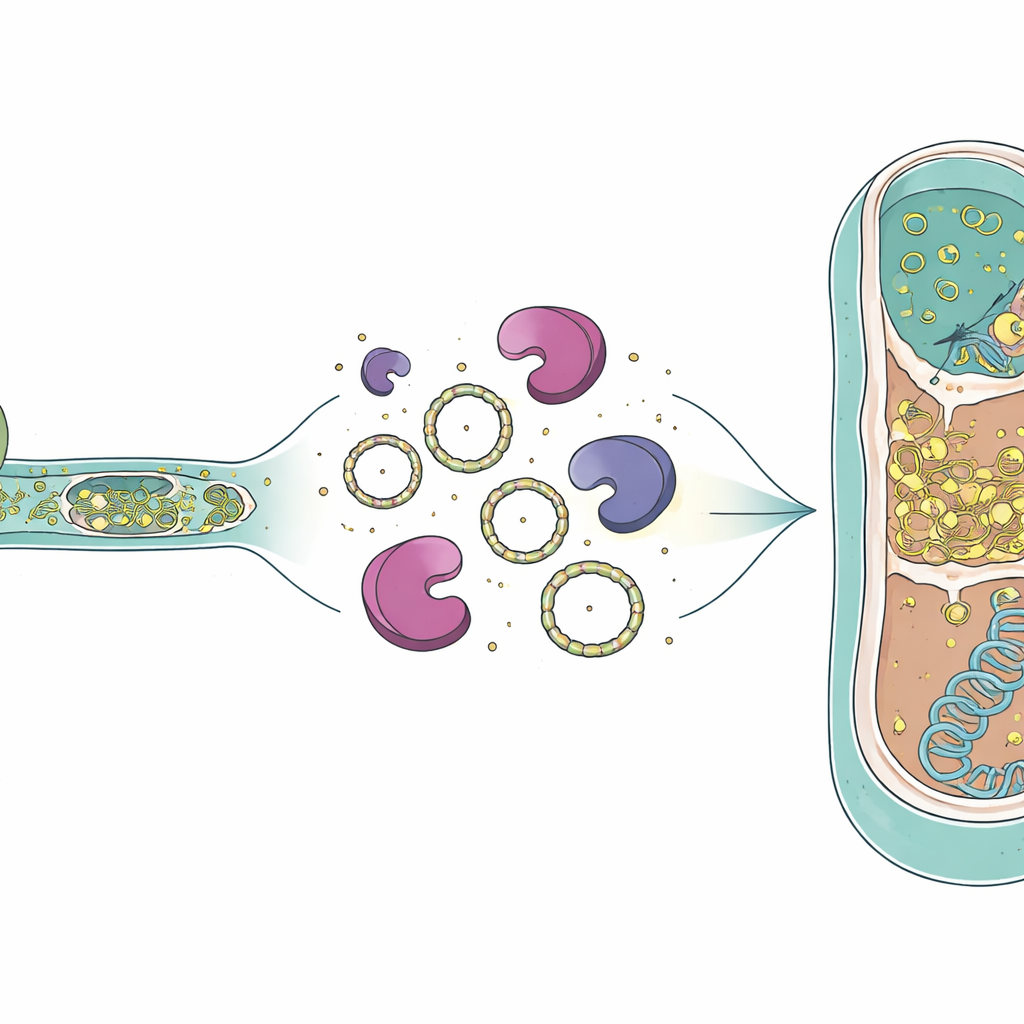
Cómo puede sobrevivir el ARN y seguir su camino
La presencia de ARN intrónico dentro de células arqueales muertas plantea preguntas sobre cómo estas moléculas persisten el tiempo suficiente para tener efecto. Trabajos previos han mostrado que los intrones de grupo I pueden formar anillos de ARN circulares tras el empalme, y tales círculos son más resistentes a las enzimas que normalmente degradan el ARN. El genoma del depredador también codifica una transcriptasa reversa especial—una enzima que puede copiar ARN de vuelta a ADN—que ya se detectó como proteína en la misma cultura. Imágenes de microscopia electrónica de estudios anteriores mostraron contactos citoplasmáticos abiertos entre depredador y víctima, lo que sugiere que no solo el ARN sino posiblemente esa enzima podrían pasar al interior de la célula arqueal. Si el ARN intrónico circular y una transcriptasa reversa entraran juntos en una célula víctima, en principio podrían copiarse a ADN e insertarse en el genoma arqueal, creando un nuevo intrón en un nuevo hospedador.
Por qué esto importa para el tráfico genético de la vida
Para no especialistas, la conclusión principal es que este estudio aporta evidencia directa y microscópica de que un fragmento móvil de ARN bacteriano puede abandonar su célula de origen y acumularse dentro de los restos muertos de un microbio muy distinto. Ese movimiento es un paso inicial clave en la transferencia horizontal de genes, el proceso por el cual genes y elementos genéticos se diseminan a través de las líneas de las especies. El trabajo también amplía los roles conocidos del ARN extracelular, que ya incluyen señalización e inhibición del crecimiento, al añadir el ARN intrónico móvil a la lista. En un panorama más amplio, estos ARNs móviles y sus enzimas asociadas ayudan a explicar cómo las innovaciones genéticas se han barajado a través de las comunidades microbianas a lo largo del tiempo evolutivo, difuminando las fronteras entre ramas separadas de la vida.
Cita: Kizina, J., Lonsing, A. & Harder, J. Mobile intron RNA from a bacterial predator accumulates in dead archaeal cells. Sci Rep 16, 14654 (2026). https://doi.org/10.1038/s41598-026-51721-6
Palabras clave: intrones móviles, ARN extracelular, depredación microbiana, transferencia horizontal de genes, arqueas metanogénicas