Clear Sky Science · de
Mobile Intron‑RNA eines bakteriellen Räubers reichert sich in toten archaealen Zellen an
Kleine Räuber und verborgene Botschaften
In den dunklen, sauerstofffreien Nischen unseres Planeten jagen mikroskopische Räuber andere Mikroben in langsamen Kämpfen, die beeinflussen, wie Kohlenstoff recycelt und Methan produziert wird. Diese Studie untersucht einen unerwarteten Reisenden, der während solcher Begegnungen wandert: ein Stück genetischer RNA aus einem bakteriellen Räuber, das in toten Zellen einer anderen Lebensdomäne, den Archaea, landet. Die Arbeit bietet einen seltenen Echtzeit‑Einblick, wie genetische Elemente zwischen weit entfernten Zweigen des Lebensbaums springen können, und stützt langjährige Vorstellungen über ‚horizontalen‘ Gentransfer und die frühe RNA‑Welt.
Springende Gene in einfachen Zellen
Viele Bakterien und Archaea tragen genetische Blutsauger, sogenannte Introns, Abschnitte der DNA, die in RNA kopiert und dann wieder herausgeschnitten werden, bevor ein funktionsfähiges Molekül entsteht. Bei komplexen Organismen sind Introns gewöhnliche Bestandteile von Genen, in einfachen Zellen sind sie seltener und verhalten sich oft wie mobile Trittbrettfahrer, die sich im Genom bewegen und neue Stellen besetzen können. Hier steht ein bestimmtes „Gruppe‑I“‑Intron im 23S‑ribosomalen‑RNA‑Gen eines ultrakleinen bakteriellen Räubers mit dem vorläufigen Namen Candidatus Velamenicoccus archaeovorus im Mittelpunkt. Dieses Bakterium lebt angeheftet an langen fadenförmigen Archaeazellen in einer langjährig geführten Laborkultur, die den Pflanzenbaustein Limonen abbaut und langsam Methan erzeugt.
Eine langsame, geschlossene mikrobielle Welt
Die Forscher arbeiteten mit einer anaeroben Angereicherungs‑Kultur, die seit über zwanzig Jahren auf Limonen gehalten wird und nur einmal pro Jahr weitergegeben wird. In diesem geschlossenen System kooperieren und konkurrieren verschiedene Mikroben. Ein bakterieller Partner baut Limonen in kleinere Verbindungen ab, und mehrere methanogene Archaea, darunter die fadenbildende Art Methanothrix soehngenii, wandeln diese Produkte in Methan um. Das Ultramikrobakterium Ca. Velamenicoccus archaeovorus lebt als Epibiont, angeheftet an der Oberfläche dieser Filamente. Frühere Arbeiten deuteten darauf hin, dass es als Räuber wirkt: Einige Filamentzellen erscheinen tot, enthalten aber noch DNA und Lipide, was darauf hindeutet, dass der Räuber wesentliche zelluläre Materialien entzieht und nur eine teilweise Hülle zurücklässt.
Fremde RNA in toten Zellen nachweisen
Um zu prüfen, ob der Räuber seine Intron‑RNA in seine archaealen Opfer schickt, nutzte das Team eine empfindliche Bildgebungstechnik namens CARD‑FISH, die kurze markierte DNA‑Sonden verwendet, um passende RNA‑Moleküle in erhaltenen Zellen sichtbar zu machen. Sie entwarfen drei Sonden, die die Intron‑RNA erkennen, und kombinierten sie mit Sonden für ribosomale RNA des Räubers sowie mit DNA‑Färbung. Unter dem Mikroskop erschien das Intron‑Signal sowohl in den winzigen kugeligen Räuberzellen als auch, entscheidend, in bestimmten Segmenten der großen Methanothrix‑Filamente. Diese Filamentzellen mit Intron‑Signal hatten ihre eigene ribosomale RNA verloren – ein Kennzeichen des Todes – enthielten aber noch DNA, was bestätigt, dass sie tot, aber noch nicht vollständig zersetzt waren. Kontrollsonden mit umgekehrten Sequenzen leuchteten nicht auf, was dafür spricht, dass das Signal spezifisch für das Intron war.
Seltene RNA‑Reisende zählen
Zur Ergänzung der Bilder werteten die Autoren einen großen RNA‑Sequenzierungsdatensatz aus, der zuvor aus derselben Kultur erzeugt worden war. Da die ribosomale RNA in dieser Probe nicht entfernt worden war, konnten sie direkt vergleichen, wie oft die Intronsequenz im Verhältnis zur normalen, vollständig prozessierten 23S‑rRNA auftauchte. Sie fanden heraus, dass Leseeindrücke, die dem Intron entsprachen, etwa 1 zu 20.000 im Vergleich zur reifen 23S‑rRNA waren, was bedeutet, dass die meisten Intron‑Kopien erfolgreich aus dem Primärtranskript herausgeschnitten werden. Eine Handvoll Reads überspannte die Grenzen zwischen Intron und angrenzender Sequenz, was darauf hinweist, dass ein sehr kleiner Bruchteil der Transkripte unverarbeitet blieb. Zusammen mit der Bildgebung zeigte dies, dass excidierte Intron‑RNA‑Moleküle in der Kultur existieren und außerhalb ihrer ursprünglichen Wirtszelle gefunden werden können.
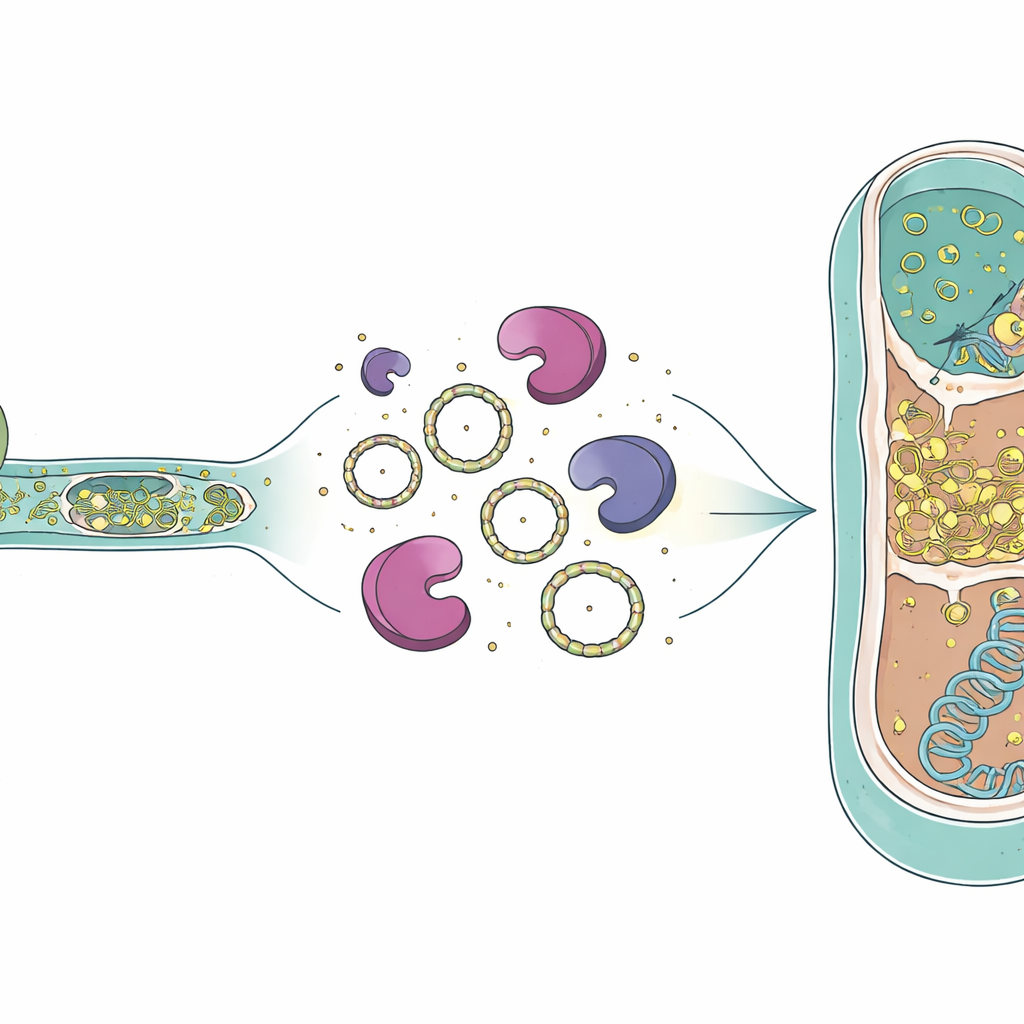
Wie die RNA überdauern und weiterziehen könnte
Das Vorkommen der Intron‑RNA in toten archaealen Zellen wirft Fragen auf, wie diese Moleküle lange genug bestehen bleiben, um relevant zu sein. Frühere Arbeiten haben gezeigt, dass Gruppe‑I‑Introns nach dem Spleißen zirkuläre RNA‑Ringe bilden können, und solche Kreise sind gegenüber den Enzymen, die RNA normalerweise abbauen, resistenter. Das Genom des Räubers kodiert außerdem eine spezielle Reverse Transkriptase – ein Enzym, das RNA wieder in DNA kopieren kann – die zuvor als Protein in derselben Kultur nachgewiesen wurde. Elektronenmikroskopische Bilder aus früheren Studien zeigten offene zytoplasmatische Kontakte zwischen Räuber und Opfer, was nahelegt, dass nicht nur RNA, sondern möglicherweise auch dieses Enzym in die archaeale Zelle gelangen könnte. Wenn zirkuläre Intron‑RNA und eine Reverse Transkriptase gemeinsam in eine Wirtszelle eindringen, könnten sie prinzipiell in DNA umgeschrieben und in das archaeale Genom eingefügt werden und so ein neues Intron in einem neuen Wirt erzeugen.
Warum das für den genetischen Verkehr des Lebens wichtig ist
Für Nicht‑Spezialisten ist die wichtigste Erkenntnis, dass diese Studie direkte mikroskopische Belege liefert, dass ein mobiles Stück bakterieller RNA seine Wirtszelle verlassen und sich in den toten Überresten eines sehr unterschiedlichen Mikrobengattens anreichern kann. Diese Bewegung ist ein entscheidender früher Schritt beim horizontalen Gentransfer, dem Prozess, durch den Gene und genetische Elemente über Artgrenzen hinweg verbreitet werden. Die Arbeit erweitert auch die bekannten Rollen extrazellulärer RNA, zu denen bereits Signalübertragung und Wachstumshemmung gehören, indem sie mobile Intron‑RNA hinzufügt. Im größeren Zusammenhang helfen solche mobilen RNAs und ihre assoziierten Enzyme zu erklären, wie genetische Innovationen im Laufe der Evolution durch mikrobielle Gemeinschaften hervorgebracht und verteilt wurden und dabei die Grenzen zwischen getrennten Zweigen des Lebens verwischten.
Zitation: Kizina, J., Lonsing, A. & Harder, J. Mobile intron RNA from a bacterial predator accumulates in dead archaeal cells. Sci Rep 16, 14654 (2026). https://doi.org/10.1038/s41598-026-51721-6
Schlüsselwörter: mobile Introns, extrazelluläre RNA, mikrobielle Prädation, horizontaler Gentransfer, methanogene Archaea