Clear Sky Science · pt
Investigação integrada DFT, docking molecular e dinâmica molecular de alguns novos análogos de 2-tiohidantoína como inibidores potentes de CDK2 para terapia anticâncer
Por que esta pesquisa importa para o futuro do tratamento do câncer
Medicamentos contra o câncer frequentemente atuam como ferramentas grosseiras, danificando células saudáveis ao atacar tumores. Este artigo explora uma estratégia mais precisa: projetar pequenas moléculas que desliguem seletivamente um motor chave da divisão celular, uma proteína chamada CDK2. Ao usar simulações computacionais avançadas em vez de química por tentativa e erro, os pesquisadores identificam vários candidatos promissores que um dia poderiam se tornar medicamentos anticâncer mais seguros e direcionados.
Interrompendo a divisão celular descontrolada na sua origem
Muitos cânceres crescem porque o ciclo celular — o relógio interno que controla quando as células se dividem — saiu do controle. A CDK2 é um dos principais interruptores que impulsionam as células através desse ciclo. Drogas anteriores que tentaram bloquear a CDK2 mostraram potencial, mas frequentemente também atingiam proteínas estreitamente relacionadas essenciais para células normais, levando a efeitos colaterais. Os autores focam em uma família química pouco explorada chamada 2‑tiohidantoínas, moléculas em forma de anel que podem ser afinadas eletronicamente e estruturalmente. O objetivo é verificar se membros selecionados dessa família poderiam se ligar à CDK2 com mais força e seletividade do que a própria molécula de combustível da célula, o ATP, evitando outras quinases.
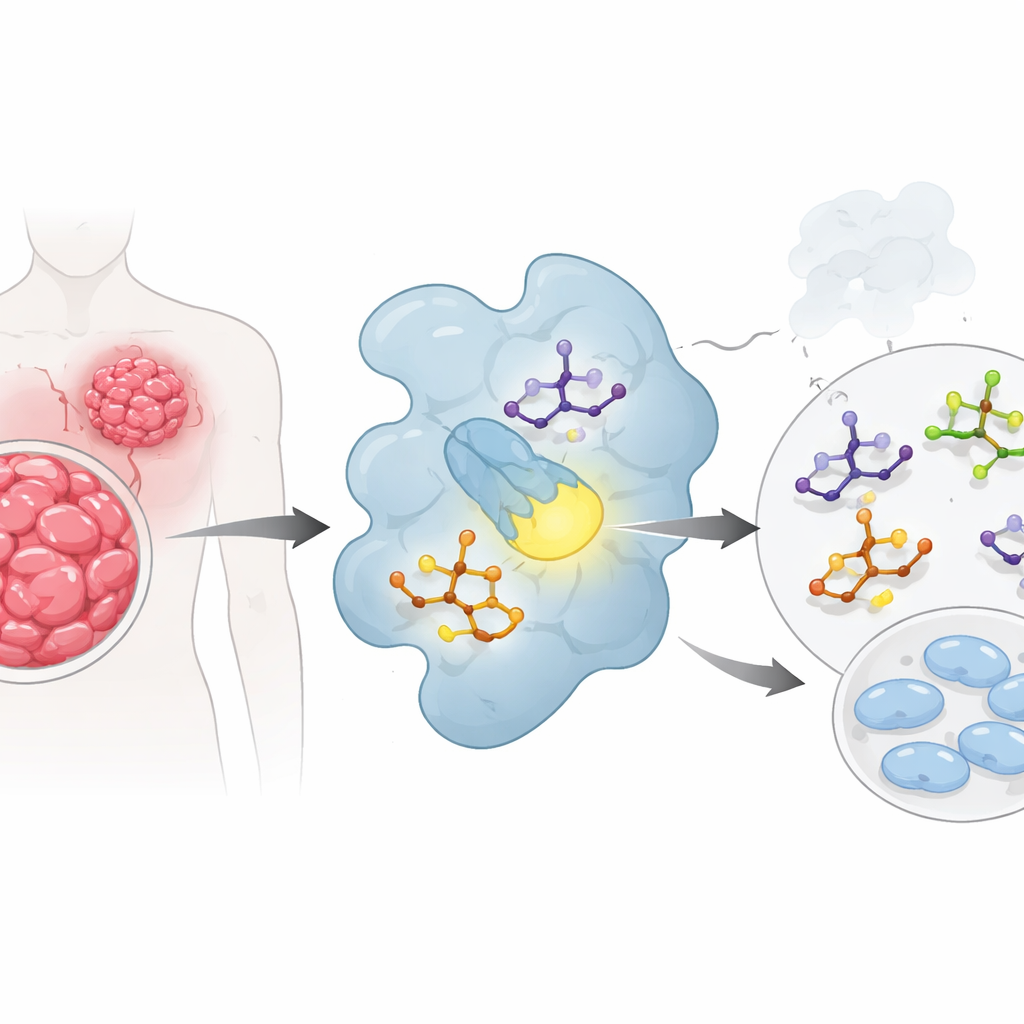
Usando computadores para “pré-testar” candidatos a fármacos
Em vez de ir direto ao bancada de laboratório, a equipe primeiro utilizou várias camadas de química quântica e modelagem molecular para entender como suas moléculas se comportam. Calcularam com que facilidade cada composto pode mover elétrons em sua estrutura, quão polar é e quais partes da molécula são mais propensas a formar contatos atrativos com uma proteína. Compostos rotulados 2b a 2e se destacaram: apresentavam pequenas lacunas de energia entre seus estados eletrônicos chave e alta “eletrofilicidade”, o que sugere que deveriam interagir prontamente com parceiros biológicos. Mapas da superfície elétrica de cada molécula destacaram regiões fortemente negativas ao redor de átomos de oxigênio e enxofre e regiões positivas ao redor de certos hidrogênios — pontos naturais de formação de ligações de hidrogênio quando um fármaco se acomoda em um bolso protéico.
Testando o encaixe dentro do bolso da CDK2
O próximo passo foi o docking virtual: posicionar cada candidato na estrutura tridimensional da CDK2 e deixar o computador procurar o melhor encaixe, de modo semelhante a testar chaves em uma fechadura. Várias moléculas, particularmente 2b, 2c e 2d, se ligaram à CDK2 com mais afinco que o próprio ATP nessas simulações. Formaram ligações de hidrogênio cruciais com duas cadeias laterais, Lys33 e Thr14, que ficam no centro do bolso de ligação ao ATP, e também se acomodaram contra aminoácidos hidrofóbicos que revestem a cavidade. Em contraste, o esqueleto parental sem substituições direcionadas ligou-se de forma fraca, destacando como mudanças sutis na decoração química do anel podem alterar dramaticamente o desempenho.
Observando o complexo proteína–fármaco em movimento
Como proteínas e fármacos não são rígidos, os autores realizaram simulações de dinâmica molecular, essencialmente filmes em câmera lenta na escala atômica, ao longo de dez bilionésimos de segundo. Essas simulações mostraram que a forma geral da CDK2 permaneceu estável enquanto alguns pares droga–proteína oscilaram ou até se afastaram. Uma molécula, 2f, mostrou-se excepcionalmente estável, mal mudando de posição dentro do bolso e mantendo em média quase três ligações de hidrogênio com a proteína. Outras, como 2c e 2d, equilibraram forte ligação com flexibilidade moderada. Para traduzir esses movimentos em uma “aderência” global, a equipe usou uma técnica chamada MM‑PBSA para estimar energias livres de ligação. Nesse cenário, o composto 2d emergiu como o melhor desempenho geral, com um equilíbrio especialmente favorável entre forças atrativas dentro do bolso e o custo energético de deixar o solvente circundante.
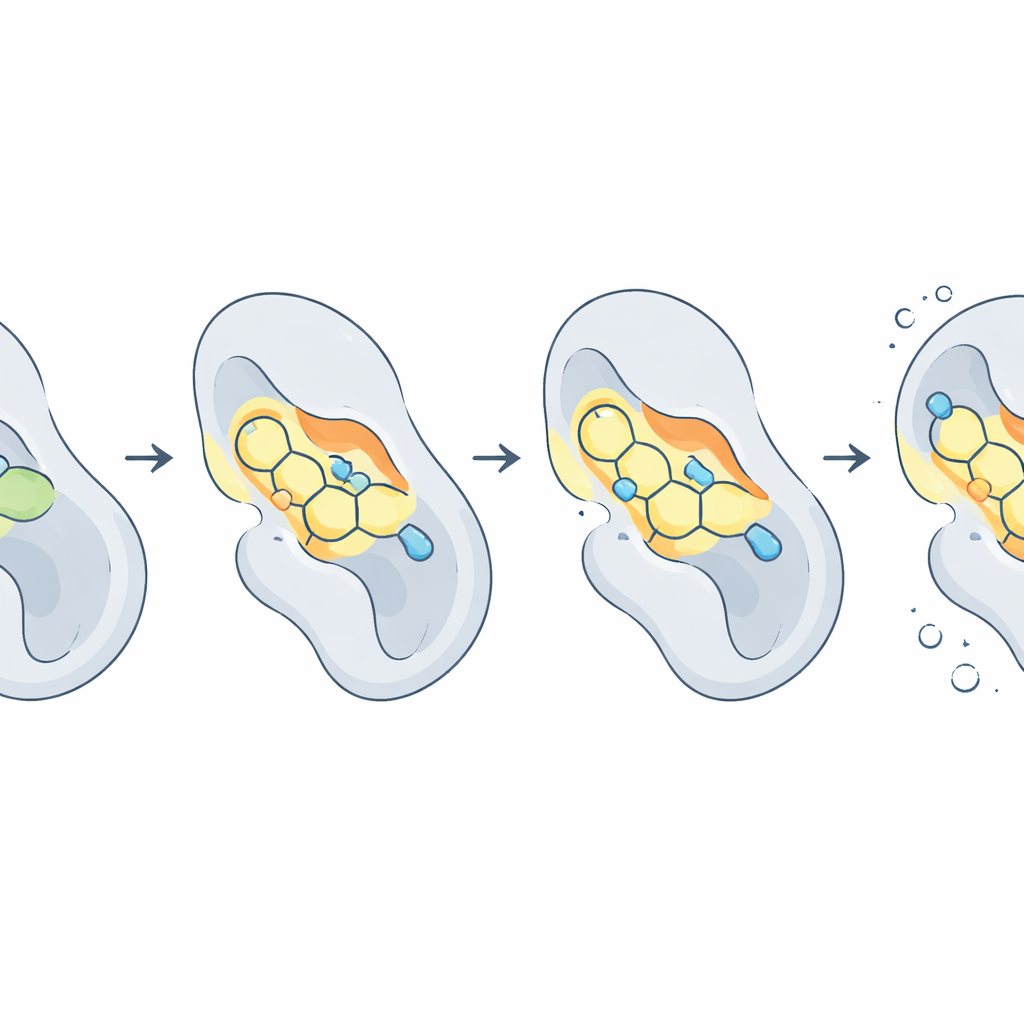
O que isso pode significar para pacientes
Tomadas em conjunto, as simulações destacam quatro compostos de 2‑tiohidantoína — 2b, 2c, 2d e 2f — como pontos de partida especialmente promissores para o desenvolvimento de fármacos anticâncer. Eles combinam propriedades eletrônicas favoráveis, uma ligação forte e bem orientada à CDK2 e, no caso de 2d, uma energia de ligação global particularmente vantajosa. Embora esses achados sejam puramente computacionais e ainda precisem ser confirmados experimentalmente, fornecem um roteiro detalhado para químicos: onde colocar grupos halogênio, ácido ou éster no anel central para fortalecer a ligação e a seletividade. Se testes laboratoriais futuros confirmarem essas previsões, o trabalho poderá acelerar a criação de terapias direcionadas à CDK2 mais precisas, que retardem o crescimento tumoral poupando células saudáveis.
Citação: Khaled, N.A., Ahmed, S.A., Ibrahim, M.A. et al. Integrated DFT, molecular docking, and molecular dynamics investigation of some novel 2-thiohydantoin analogues as potent CDK2 inhibitors for anticancer therapy. Sci Rep 16, 10985 (2026). https://doi.org/10.1038/s41598-026-42330-4
Palavras-chave: inibidores de CDK2, terapia contra o câncer direcionada, docking molecular, 2-tiohidantoína, desenho de fármacos computacional