Clear Sky Science · pt
Aprendizado profundo orientado por dados sintéticos para microscopia de força atômica autônoma sem rótulos
Vendo o mundo minúsculo sem olhos humanos
Nossa capacidade de projetar novos materiais, estudar dispositivos de energia limpos ou investigar células vivas frequentemente depende de enxergar estruturas mil vezes menores que um fio de cabelo. Microscópios de força atômica (AFMs) podem mapear essas paisagens minúsculas em 3D, mas hoje ainda dependem fortemente de operadores especialistas que precisam escolher onde olhar e como interpretar as imagens. Este artigo apresenta o SimuScan, uma maneira de ensinar computadores a operar AFMs e reconhecer feições em escala nanométrica treinando-os com imagens simuladas realistas em vez de dados experimentais rotulados com esforço.
Por que o imageamento em nanoescala emperra hoje
Os AFMs tornaram-se ferramentas centrais em ciência dos materiais, pesquisa em energia e biologia porque conseguem “sentir” superfícies com precisão de nanômetros. Ainda assim são lentos, cobrem apenas pequenas áreas por vez e exigem muitas decisões de um usuário habilidoso: onde escanear, quais configurações usar e quais formas minúsculas importam. Ao contrário de microscópios ópticos ou eletrônicos que podem capturar imagens de varredura amplas, os AFMs constroem superfícies linha a linha. Além disso, métodos modernos de inteligência artificial prosperam com enormes coleções de imagens rotuladas, como as disponíveis para fotos comuns, mas tais conjuntos de dados simplesmente não existem para AFM. Cada imagem de AFM é influenciada por sutilezas do instrumento — ruído, distorções e forma da ponta — de modo que ferramentas genéricas de visão computacional treinadas em fotos ordinárias frequentemente falham quando aplicadas diretamente.
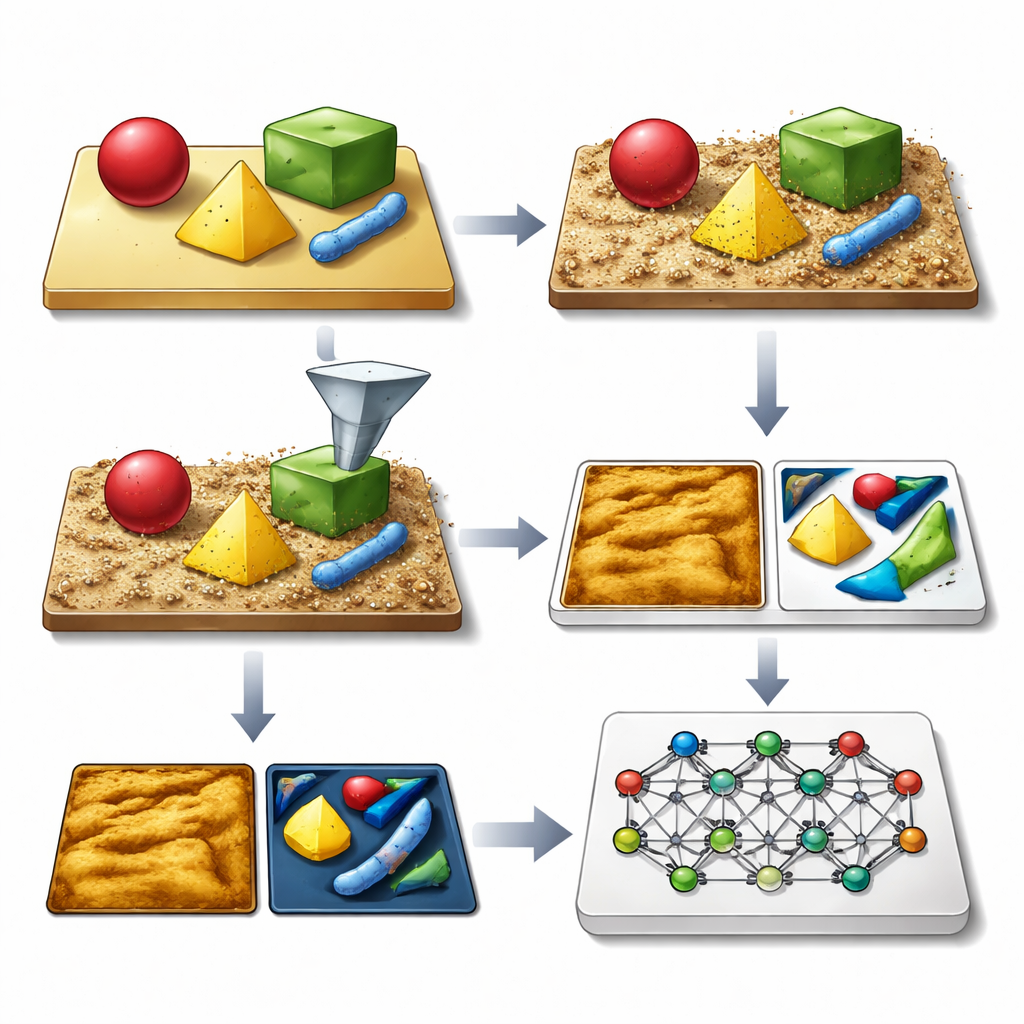
Ensinando um microscópio com imagens fictícias
A ideia central dos autores é gerar vastas bibliotecas de imagens sintéticas de AFM que se parecem e se comportam como as reais, incluindo todas as imperfeições usuais. A estrutura SimuScan começa definindo as formas que podem aparecer em uma amostra: blocos e hastes simples, montagens delicadas de DNA ou células bacterianas inteiras. Essas formas podem vir de descrições matemáticas, arquivos CAD ou até superfícies 3D extraídas de algumas imagens reais de AFM. O SimuScan então posiciona esses objetos sobre substratos simulados que podem incluir degraus, rugosidade, padrões periódicos e detritos aleatórios, criando paisagens pré-distorcidas realistas. Por fim, passa essas superfícies por um modelo direto detalhado do microscópio que adiciona os efeitos de uma ponta de sonda finita, falhas de feedback, correções linha a linha e ruído eletrônico. O resultado é uma imagem que imita de perto o que um AFM mediria, emparelhada com um “ground truth” exato do contorno de cada objeto.
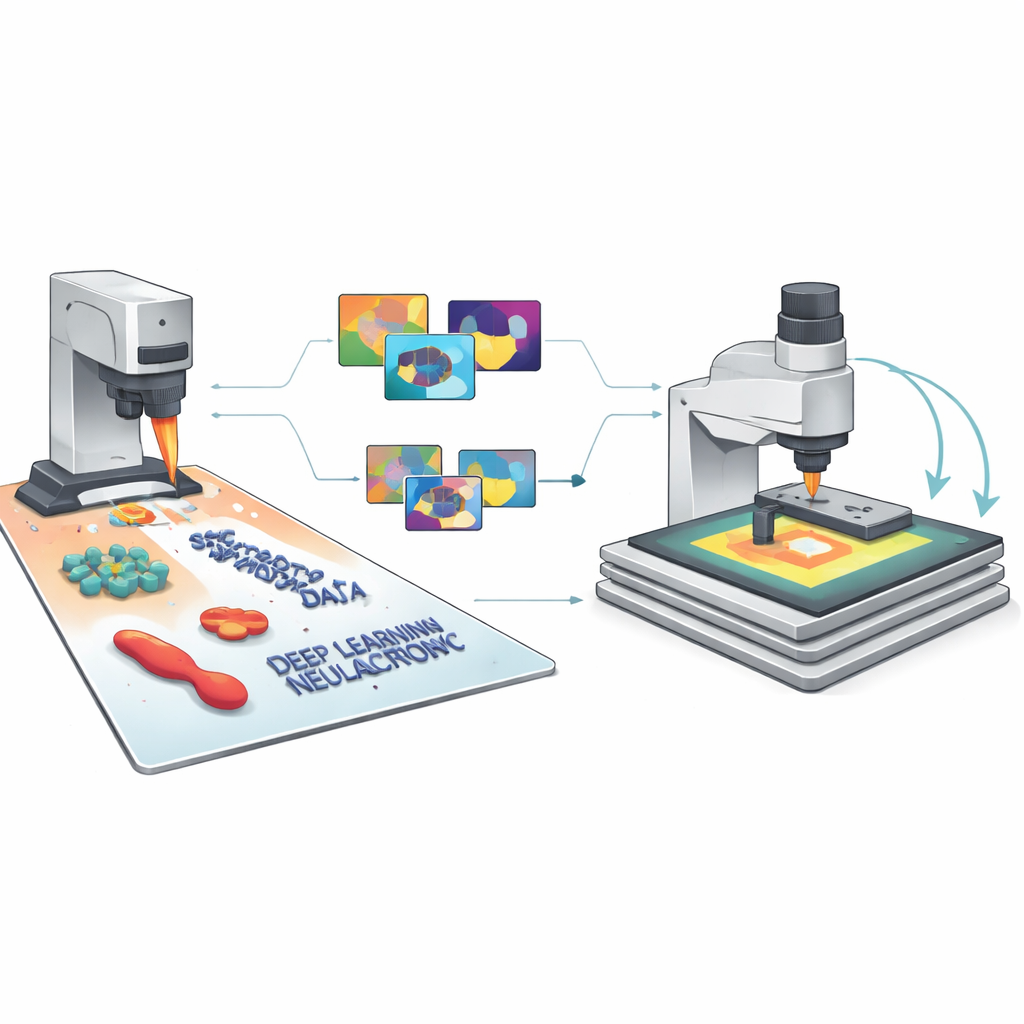
Dos pixels simulados à IA confiável
Como cada imagem sintética vem com rótulos perfeitos para toda feição e pixel, o SimuScan pode alimentar modelos modernos de aprendizado profundo com o tipo de material de treinamento rico que normalmente falta no imageamento em nanoescala. A equipe testou várias arquiteturas populares — YOLOv8 para detecção rápida de objetos, U-Net para contornos detalhados e Mask R-CNN para máscaras a nível de instância — usando mais de 5.000 imagens sintéticas por tarefa. Notavelmente, modelos treinados apenas nesses conjuntos artificiais tiveram desempenho forte quando avaliados em imagens reais de AFM de nanostruturas fabricadas e bactérias que haviam sido cuidadosamente anotadas por especialistas. As pontuações de detecção e a precisão de segmentação foram altas para diferentes formas e tipos de células, mostrando que as imagens simuladas capturaram a aparência essencial dessas estruturas minúsculas e seus artefatos de imageamento comuns.
Deixando o microscópio decidir onde olhar
Os pesquisadores então fecharam o ciclo entre simulação, IA e o instrumento físico. Em seu fluxo de trabalho semi-autônomo, o AFM primeiro faz uma varredura panorâmica de baixa resolução sobre uma área relativamente grande. Um modelo treinado com dados SimuScan analisa essa imagem em tempo real, encontra estruturas de interesse — como certas formas bacterianas ou padrões nanofabricados específicos — e seleciona regiões promissoras para varreduras ampliadas de alta resolução. O microscópio move-se automaticamente, refaz a varredura e repete esse ciclo pela amostra, guiado por regras simples definidas pelo usuário, como o número desejado de objetos ou a área total a cobrir. Com essa abordagem, o sistema pôde encontrar e imagear autonomamente centenas de bactérias individuais, então medir variações em seu tamanho e forma em uma população, algo que seria proibitivamente demorado de fazer manualmente.
Um novo caminho para microscópios mais inteligentes
Para um não especialista, a principal conclusão é que o SimuScan mostra como dados “imaginários, mas realistas” podem ajudar microscópios a se tornarem mais como instrumentos autônomos. Ao simular tanto os pequenos objetos em uma superfície quanto as idiossincrasias de como o AFM os vê, os autores eliminam a necessidade de grandes conjuntos de treinamento rotulados manualmente e permitem que modelos de IA de uso geral funcionem bem em experimentos reais. Isso desbloqueia estudos por AFM que podem explorar áreas maiores, analisar muito mais objetos e adaptar seu comportamento em tempo real, tornando a caracterização em nanoescala mais rápida, mais reprodutível e acessível a não especialistas. A longo prazo, estratégias similares baseadas em dados sintéticos poderiam ajudar a levar operação autônoma orientada por descobertas a muitos outros tipos de instrumentos científicos.
Citação: Millan-Solsona, R., Checa, M., Brown, S.R. et al. Synthetic data-driven deep learning for label-free autonomous atomic force microscopy. Nat Commun 17, 3886 (2026). https://doi.org/10.1038/s41467-026-70421-3
Palavras-chave: microscopia de força atômica, dados sintéticos, aprendizado profundo, microscopia autônoma, imageamento de nanostruturas