Clear Sky Science · it
Dati sintetici e deep learning per microscopia a forza atomica autonoma senza etichette
Vedere il mondo minuscolo senza occhi umani
La nostra capacità di progettare nuovi materiali, studiare dispositivi per energie pulite o indagare cellule vive dipende spesso dall’osservare strutture migliaia di volte più piccole di un capello umano. I microscopi a forza atomica (AFM) possono mappare questi minuscoli paesaggi in 3D, ma oggi dipendono ancora in larga misura da operatori esperti che devono decidere dove guardare e come interpretare le immagini. Questo articolo presenta SimuScan, un metodo per insegnare ai computer a gestire gli AFM e riconoscere caratteristiche su scala nano addestrandoli su immagini simulate realistiche invece che su dati sperimentali faticosamente etichettati.
Perché l’imaging su scala nanometrica si blocca oggi
Gli AFM sono strumenti fondamentali in scienza dei materiali, ricerca sull’energia e biologia perché riescono a percepire superfici con precisione nanometrica. Tuttavia sono lenti, coprono solo piccole aree per volta e richiedono molte decisioni da parte di un utente qualificato: dove scansire, quali impostazioni usare e quali piccole forme sono rilevanti. A differenza di microscopi ottici o elettronici che possono acquisire grandi immagini di panoramica, gli AFM costruiscono le superfici riga per riga. Inoltre, i moderni metodi di intelligenza artificiale prosperano su enormi collezioni di immagini etichettate come quelle disponibili per le foto di uso quotidiano, ma tali dataset semplicemente non esistono per l’AFM. Ogni immagine AFM è influenzata da sottili proprietà dello strumento — rumore, distorsioni e forma della punta — perciò strumenti generici di visione artificiale addestrati su immagini ordinarie spesso falliscono se applicati direttamente.
Insegnare a un microscopio con immagini di fantasia
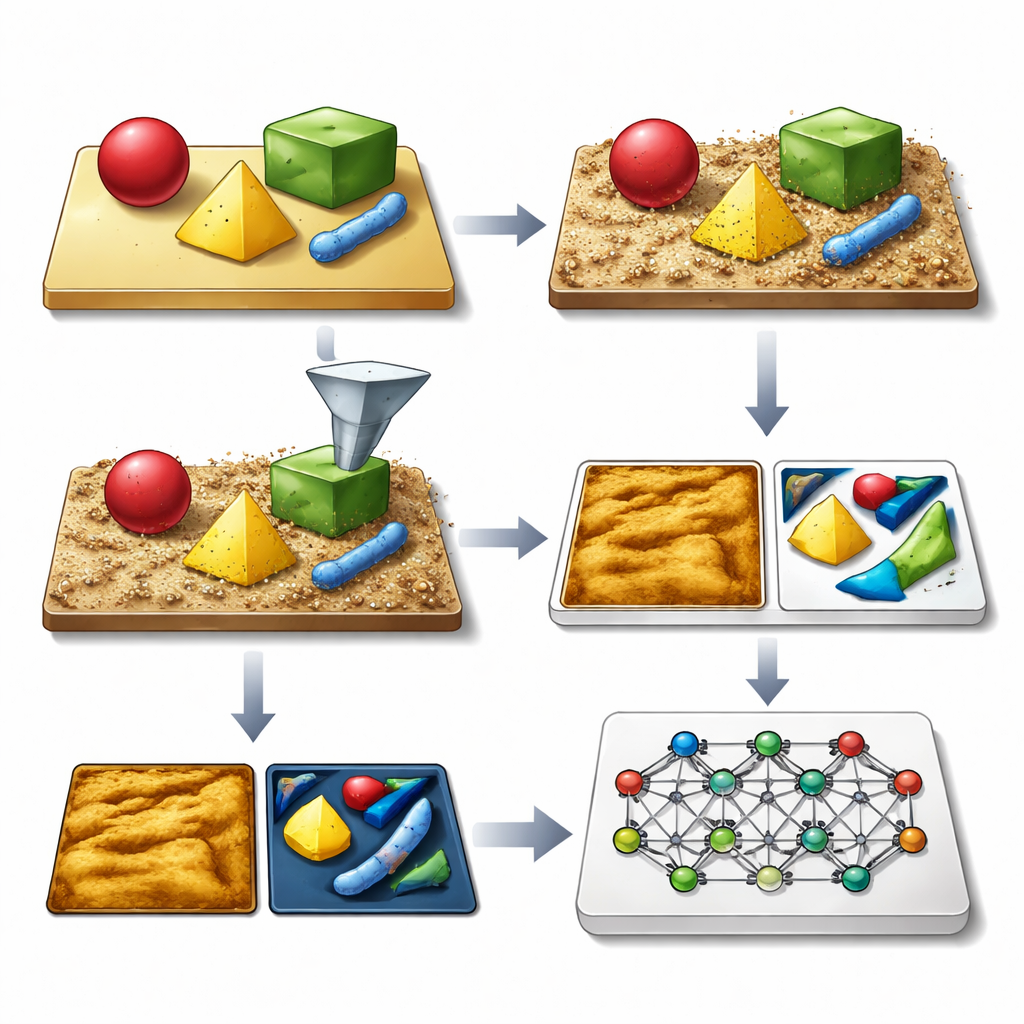
L’idea chiave degli autori è generare vaste librerie di immagini AFM sintetiche che assomiglino e si comportino come quelle reali, comprensive di tutte le imperfezioni abituali. Il framework SimuScan parte definendo le forme che potrebbero comparire su un campione: semplici blocchi e sbarre, delicate strutture di DNA o intere cellule batteriche. Queste forme possono derivare da descrizioni matematiche, file CAD o anche superfici 3D estratte da alcune immagini AFM reali. SimuScan quindi colloca questi oggetti su substrati simulati che possono includere gradini, rugosità, pattern periodici e detriti casuali, creando paesaggi pre-distorti realistici. Infine, passa queste superfici attraverso un modello diretto dettagliato del microscopio che aggiunge gli effetti di una punta finita, glitch del feedback, correzioni riga per riga e rumore elettronico. Il risultato è un’immagine che imita strettamente ciò che un AFM misurerebbe, accompagnata da una «verità di base» esatta con il contorno di ogni oggetto.
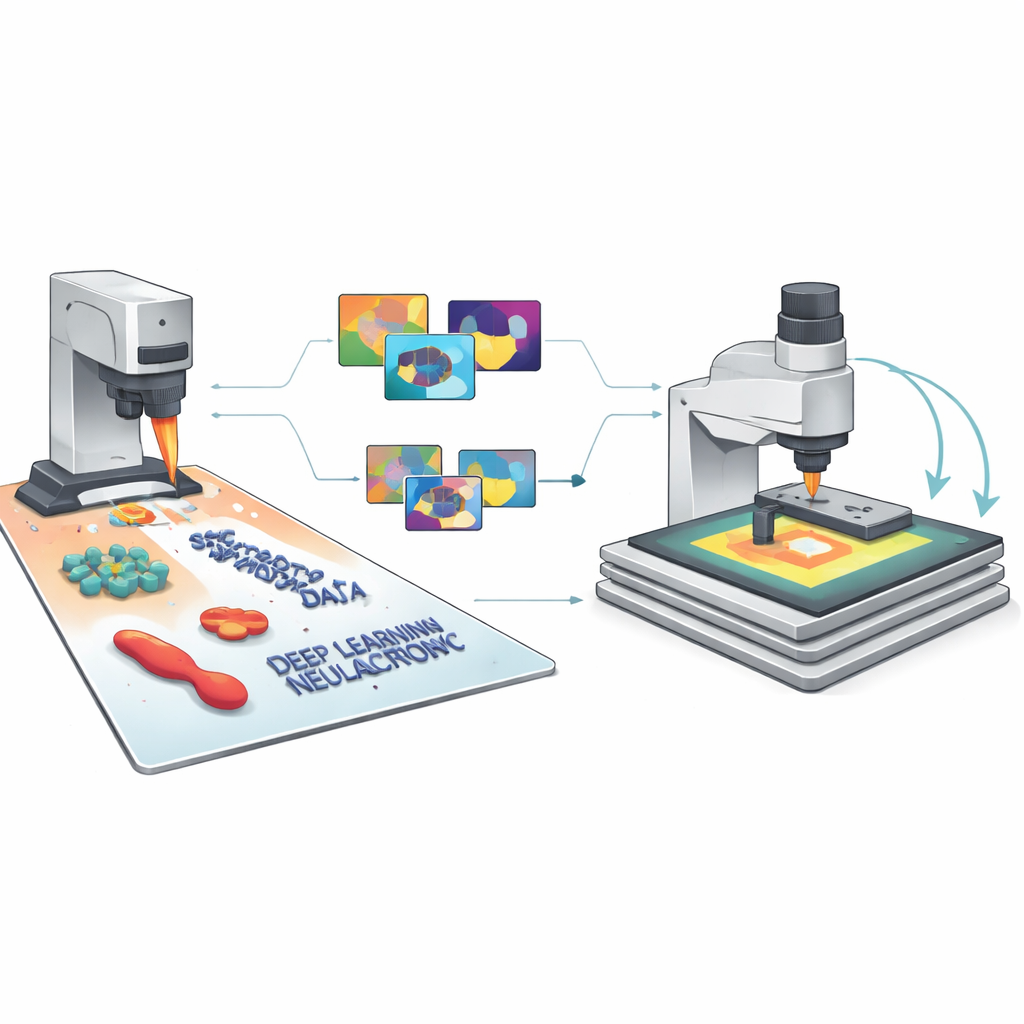
Dai pixel simulati a un’IA affidabile
Poiché ogni immagine sintetica è fornita con etichette perfette per ogni caratteristica e pixel, SimuScan può alimentare i moderni modelli di deep learning con il tipo di materiale di addestramento ricco che normalmente manca nell’imaging su scala nanometrica. Il team ha testato diverse architetture popolari — YOLOv8 per il rilevamento rapido di oggetti, U-Net per contorni dettagliati e Mask R-CNN per maschere a livello di istanza — usando più di 5.000 immagini sintetiche per attività. Sorprendentemente, i modelli addestrati solo su questi dataset artificiali hanno mostrato buone prestazioni quando valutati su immagini AFM reali di nanostrutture fabbricate e batteri accuratamente annotate da esperti. I punteggi di rilevamento e l’accuratezza delle segmentazioni sono stati elevati per diverse forme e tipi cellulari, dimostrando che le immagini simulate avevano catturato l’aspetto essenziale di queste minuscole strutture e i loro comuni artefatti di imaging.
Lascare al microscopio la decisione di dove guardare
I ricercatori hanno poi chiuso il ciclo tra simulazione, IA e strumento fisico. Nel loro flusso di lavoro semi-autonomo, l’AFM esegue prima una scansione panoramica a bassa risoluzione su un’area relativamente ampia. Un modello addestrato sui dati SimuScan analizza questa immagine in tempo reale, individua strutture d’interesse — come certe forme batteriche o pattern nanofabbricati specifici — e seleziona regioni promettenti per scansioni ravvicinate ad alta risoluzione. Il microscopio si muove automaticamente, effettua nuove scansioni e ripete questo ciclo attraverso il campione, guidato da regole semplici definite dall’utente come il numero desiderato di oggetti o l’area totale da coprire. Con questo approccio il sistema è stato in grado di trovare e acquisire autonomamente centinaia di batteri individuali, quindi misurare variazioni nelle loro dimensioni e forme attraverso una popolazione, operazione che richiederebbe tempi proibitivi se fatta manualmente.
Una nuova strada verso microscopi più intelligenti
Per un non specialista, la conclusione principale è che SimuScan dimostra come dati «immaginari ma realistici» possano aiutare i microscopi a funzionare più come strumenti a guida autonoma. Simulando sia i minuscoli oggetti su una superficie sia le particolarità di come l’AFM li osserva, gli autori eliminano la necessità di grandi set di addestramento etichettati manualmente e permettono ai modelli di IA generalisti di funzionare bene su esperimenti reali. Questo apre la strada a studi AFM che possono esplorare aree più ampie, analizzare molti più oggetti e adattare il proprio comportamento al volo, rendendo la caratterizzazione su scala nanometrica più veloce, più riproducibile e accessibile ai non esperti. A lungo termine, strategie simili basate su dati sintetici potrebbero favorire l’operazione autonoma e orientata alla scoperta di molti altri tipi di strumenti scientifici.
Citazione: Millan-Solsona, R., Checa, M., Brown, S.R. et al. Synthetic data-driven deep learning for label-free autonomous atomic force microscopy. Nat Commun 17, 3886 (2026). https://doi.org/10.1038/s41467-026-70421-3
Parole chiave: microscopia a forza atomica, dati sintetici, deep learning, microscopia autonoma, imaging di nanostrutture