Clear Sky Science · nl
Door synthetische data aangedreven deep learning voor labelvrije autonome atomaire-krachtmicroscopie
De kleine wereld zien zonder menselijke ogen
Ons vermogen om nieuwe materialen te ontwerpen, apparaten voor schone energie te bestuderen of levende cellen te onderzoeken hangt vaak af van het zien van structuren die duizend keer kleiner zijn dan een mensenhaar. Atomaire-krachtmicroscopen (AFM's) kunnen deze miniatuurlandschappen in 3D in kaart brengen, maar ze zijn vandaag de dag nog sterk afhankelijk van deskundige operators die moeten beslissen waar te kijken en hoe de beelden te interpreteren. Dit artikel introduceert SimuScan, een manier om computers AFM's te leren bedienen en nanoschaalkenmerken te herkennen door ze te trainen op levensechte gesimuleerde beelden in plaats van op tijdrovend gelabelde experimentele data.
Waarom hedendaagse nanoschaalbeeldvorming vastloopt
AFM's zijn centrale instrumenten geworden in materiaalkunde, energiewetenschappen en biologie omdat ze oppervlakken met nanometerprecisie kunnen 'voelen'. Toch zijn ze traag, bestrijken ze telkens maar kleine gebieden en vragen ze veel beslissingen van een bekwame gebruiker: waar te scannen, welke instellingen te gebruiken en welke kleine vormen relevant zijn. In tegenstelling tot optische of elektronenmicroscopen die grote overzichten kunnen vastleggen, bouwen AFM's oppervlakken lijn voor lijn op. Bovendien floreren moderne methoden uit de kunstmatige intelligentie op enorme gelabelde beeldverzamelingen zoals bij alledaagse foto’s, maar zulke datasets bestaan simpelweg niet voor AFM. Elk AFM-beeld wordt beïnvloed door subtiele instrumenteigenaardigheden—ruis, vervormingen en de vorm van de probe—zodat generieke computer-visiontools die op gewone plaatjes zijn getraind vaak falen wanneer ze direct worden toegepast.
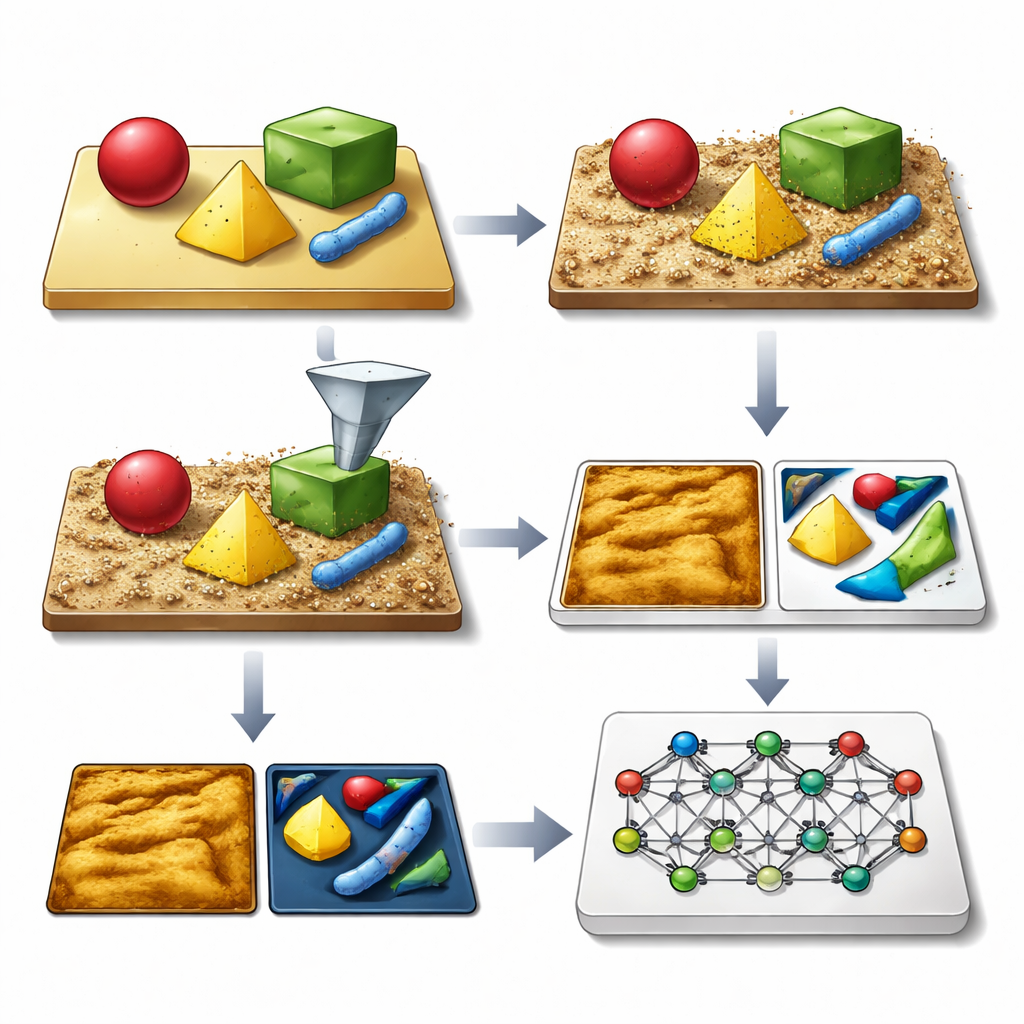
Een microscoop leren met bedachtbeelden
Het kernidee van de auteurs is het genereren van omvangrijke bibliotheken van synthetische AFM-beelden die eruitzien en zich gedragen als het echte werk, inclusief alle gebruikelijke imperfecties. Hun SimuScan-framework begint met het definiëren van de vormen die op een monster kunnen voorkomen: eenvoudige blokken en staven, delicate DNA-assemblages of hele bacteriële cellen. Deze vormen kunnen afkomstig zijn uit wiskundige beschrijvingen, CAD-bestanden of zelfs 3D-oppervlakken geëxtraheerd uit een paar echte AFM-beelden. SimuScan plaatst deze objecten vervolgens op gesimuleerde substraten die stappen, ruwheid, periodieke patronen en willekeurig puin kunnen bevatten, wat realistische, vooraf-vervormde landschappen oplevert. Ten slotte voert het deze oppervlakken door een gedetailleerd voorwaarts model van de microscoop dat de effecten toevoegt van een eindige probe-tip, feedbackstoringen, lijn-voor-lijn correcties en elektronische ruis. Het resultaat is een beeld dat nauwkeurig nabootst wat een AFM zou meten, gekoppeld aan een exacte “ground-truth” kaart van de omtrek van elk object.
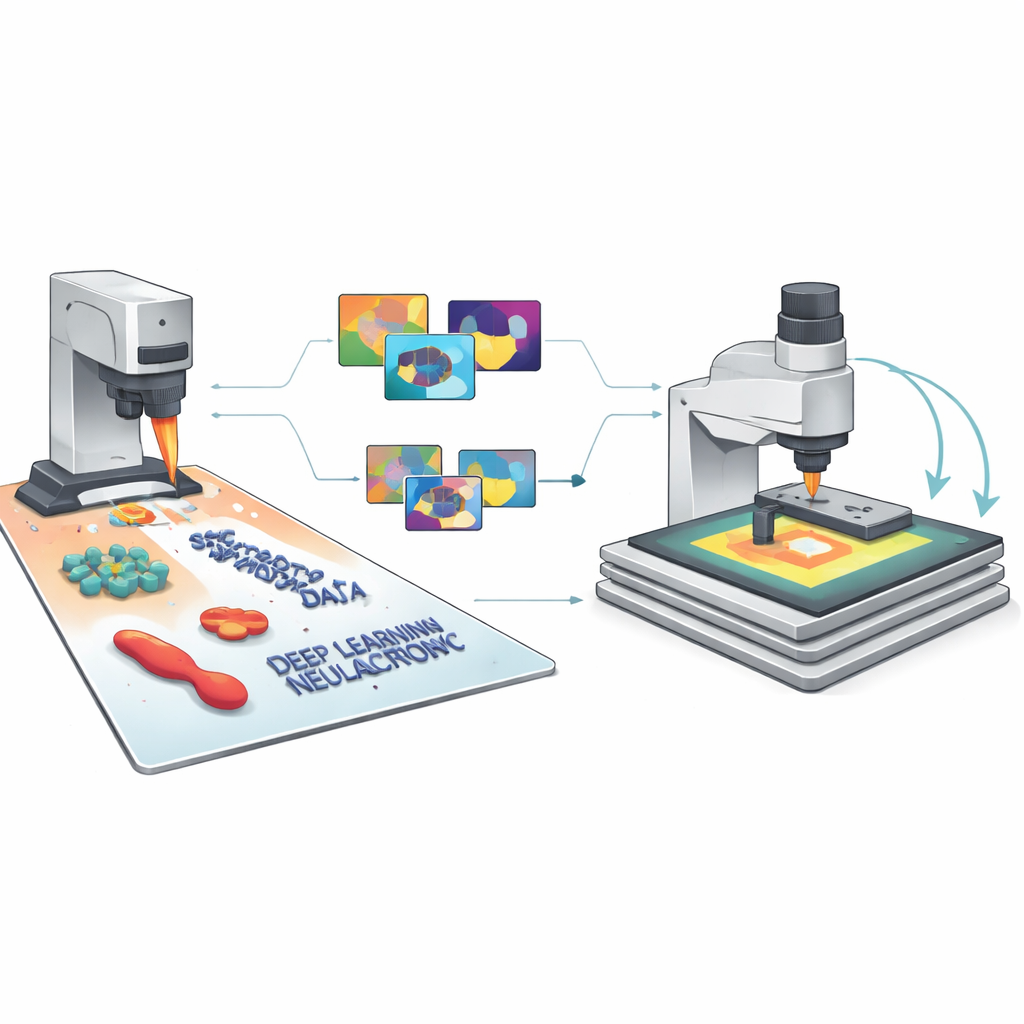
Van gesimuleerde pixels naar betrouwbare AI
Omdat elk synthetisch beeld perfecte labels bevat voor elk kenmerk en elke pixel, kan SimuScan moderne deep-learningmodellen voeden met de soort rijke trainingsdata die ze normaal gesproken missen in nanoschaalbeeldvorming. Het team testte verschillende populaire architecturen—YOLOv8 voor snelle objectdetectie, U-Net voor gedetailleerde omtrekken en Mask R-CNN voor instantieniveaumaskers—met meer dan 5.000 synthetische beelden per taak. Opmerkelijk genoeg presteerden modellen die alleen op deze kunstmatige datasets waren getraind goed bij evaluatie op echte AFM-beelden van gefabriceerde nanostructuren en bacteriën die door experts nauwgezet waren geannoteerd. Detectiescores en segmentatienauwkeurigheid waren hoog voor verschillende vormen en celtypen, wat laat zien dat de gesimuleerde beelden het wezenlijke uiterlijk van deze kleine structuren en hun veelvoorkomende beeldartefacten hadden vastgelegd.
De microscoop zelf laten beslissen waar te kijken
De onderzoekers sloten vervolgens de lus tussen simulatie, AI en het fysieke instrument. In hun semi-autonome workflow maakt de AFM eerst een lage-resolutie overzichtsscan over een relatief groot gebied. Een model dat op SimuScan-data is getraind analyseert dit beeld in realtime, vindt structuren van belang—zoals bepaalde bacterievormen of specifieke nanogefabriceerde patronen—en selecteert veelbelovende regio’s voor ingezoomde, hoge-resolutiescans. De microscoop beweegt automatisch, scant opnieuw en herhaalt deze cyclus over het monster, geleid door eenvoudige door de gebruiker gedefinieerde regels zoals het gewenste aantal objecten of de totale te bestrijken oppervlakte. Met deze aanpak kon het systeem autonoom honderden individuele bacteriën vinden en in beeld brengen, en vervolgens variaties in grootte en vorm binnen een populatie meten, iets wat handmatig te tijdrovend zou zijn.
Een nieuwe weg naar slimere microscopen
Voor een niet-specialist is de belangrijkste conclusie dat SimuScan aantoont hoe “verzonnen maar realistische” data microscopen meer als zelfrijdende instrumenten kunnen maken. Door zowel de kleine objecten op een oppervlak als de eigenaardigheden van hoe de AFM ze waarneemt te simuleren, elimineren de auteurs de noodzaak van grote, handmatig gelabelde trainingssets en maken ze het mogelijk dat algemene AI-modellen goed presteren op echte experimenten. Dit opent AFM-studies die grotere gebieden kunnen verkennen, veel meer objecten kunnen analyseren en hun gedrag direct kunnen aanpassen, waardoor nanoschaalkarakterisering sneller, beter reproduceerbaar en toegankelijker voor niet-experts wordt. Op lange termijn zouden vergelijkbare synthetische-data strategieën autonome, ontdekkingsgestuurde werking naar veel andere typen wetenschappelijke instrumenten kunnen brengen.
Bronvermelding: Millan-Solsona, R., Checa, M., Brown, S.R. et al. Synthetic data-driven deep learning for label-free autonomous atomic force microscopy. Nat Commun 17, 3886 (2026). https://doi.org/10.1038/s41467-026-70421-3
Trefwoorden: atomaire-krachtmicroscopie, synthetische data, deep learning, autonome microscopie, beeldvorming van nanostructuren