Clear Sky Science · es
Aprendizaje profundo impulsado por datos sintéticos para microscopía de fuerza atómica autónoma sin etiquetas
Ver el mundo minúsculo sin ojos humanos
Nuestra capacidad para diseñar nuevos materiales, estudiar dispositivos de energía limpia o sondear células vivas depende a menudo de ver estructuras mil veces más pequeñas que un cabello humano. Los microscopios de fuerza atómica (AFM) pueden cartografiar estos paisajes diminutos en 3D, pero hoy siguen dependiendo en gran medida de operadores expertos que deben elegir dónde mirar y cómo interpretar las imágenes. Este artículo presenta SimuScan, una forma de enseñar a los ordenadores a manejar AFM y reconocer características a escala nanométrica entrenándolos con imágenes simuladas verosímiles en lugar de con datos experimentales etiquetados con mucho esfuerzo.
Por qué la imagen a nanoescala se atasca hoy
Los AFM se han convertido en herramientas centrales en ciencia de materiales, investigación energética y biología porque pueden «tocar» superficies con precisión nanométrica. Sin embargo, son lentos, cubren sólo pequeñas áreas a la vez y exigen muchas decisiones por parte de un usuario cualificado: dónde escanear, qué ajustes usar y qué formas diminutas importan. A diferencia de los microscopios ópticos o electrónicos que pueden capturar imágenes de sondeo amplias, los AFM construyen superficies línea a línea. Además, los métodos modernos de inteligencia artificial prosperan con colecciones enormes de imágenes etiquetadas, como las disponibles para fotos cotidianas, pero tales conjuntos de datos simplemente no existen para AFM. Cada imagen de AFM está influida por peculiaridades sutiles del instrumento —ruido, distorsiones y la forma de la sonda—, por lo que las herramientas genéricas de visión por ordenador entrenadas con fotografías habituales suelen fallar al aplicarse directamente.
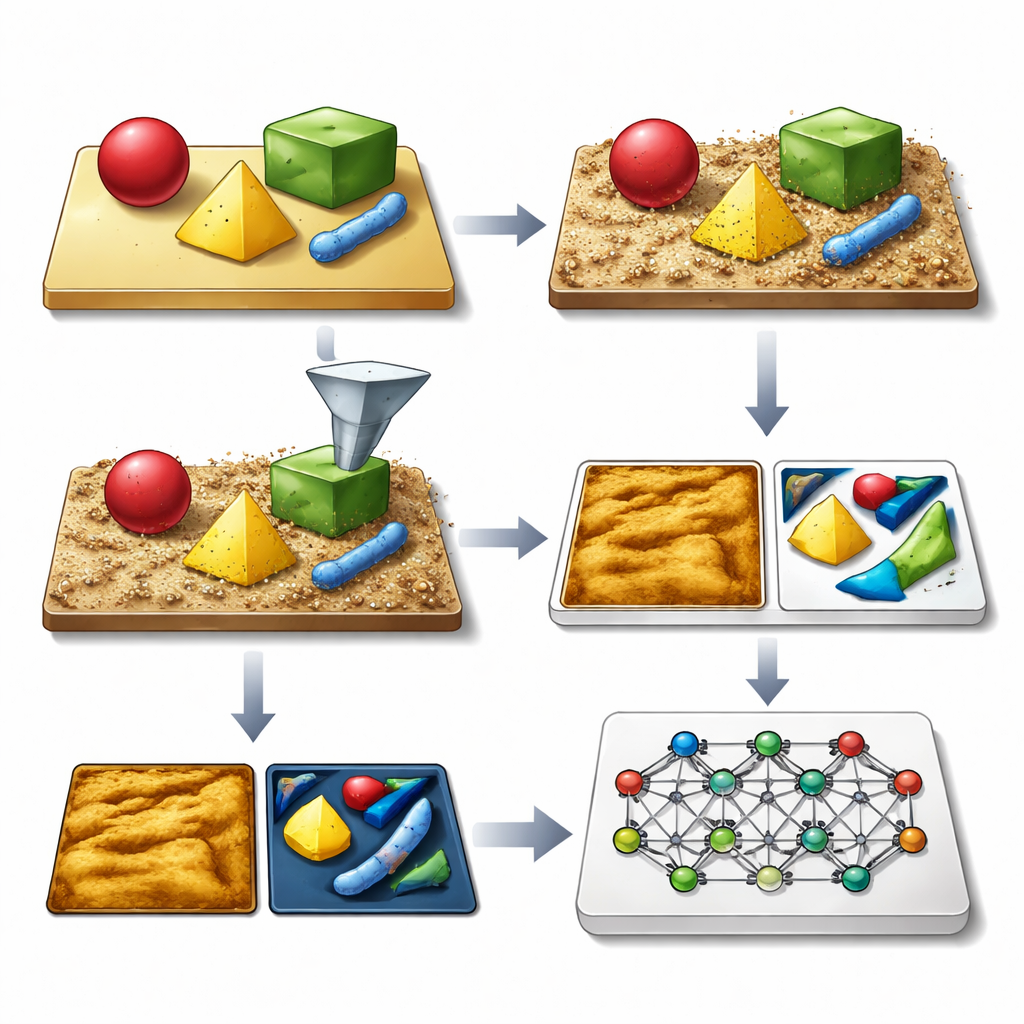
Enseñar a un microscopio con imágenes de mentira que parecen reales
La idea clave de los autores es generar vastas bibliotecas de imágenes sintéticas de AFM que parezcan y se comporten como las reales, incluidas todas las imperfecciones habituales. Su marco SimuScan comienza definiendo las formas que podrían aparecer en una muestra: bloques y varillas simples, delicadas ensambladuras de ADN o células bacterianas completas. Estas formas pueden provenir de descripciones matemáticas, archivos de diseño asistido por ordenador o incluso superficies 3D extraídas de unas pocas imágenes reales de AFM. SimuScan coloca luego estos objetos sobre sustratos simulados que pueden incluir escalones, rugosidad, patrones periódicos y escombros aleatorios, creando paisajes pre-distorsionados realistas. Finalmente, pasa estas superficies por un modelo directo detallado del microscopio que añade los efectos de una punta de sonda finita, fallos de retroalimentación, correcciones línea por línea y ruido electrónico. El resultado es una imagen que imita estrechamente lo que mediría un AFM, acompañada de un “ground truth” exacto del contorno de cada objeto.
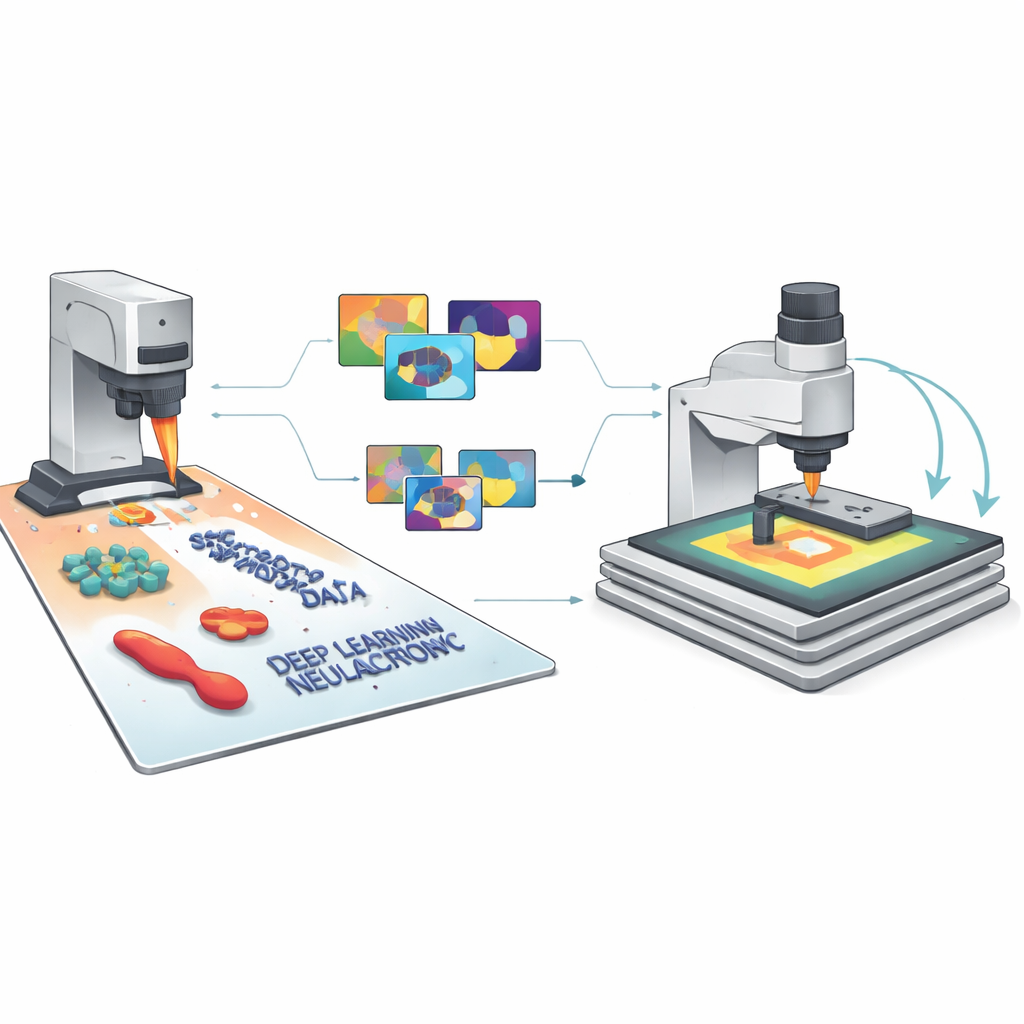
De píxeles simulados a IA confiable
Puesto que cada imagen sintética viene con etiquetas perfectas para cada característica y píxel, SimuScan puede alimentar modelos modernos de aprendizaje profundo con el tipo de material de entrenamiento rico que normalmente falta en la imagen a nanoescala. El equipo probó varias arquitecturas populares —YOLOv8 para detección rápida de objetos, U-Net para contornos detallados y Mask R-CNN para máscaras a nivel de instancia— usando más de 5.000 imágenes sintéticas por tarea. De forma notable, los modelos entrenados sólo con estos conjuntos de datos artificiales rindieron bien cuando se evaluaron con imágenes reales de AFM de nanoestructuras fabricadas y bacterias que habían sido anotadas minuciosamente por expertos. Las puntuaciones de detección y la precisión de segmentación fueron altas para distintas formas y tipos celulares, lo que demuestra que las imágenes simuladas capturaron la apariencia esencial de estas estructuras diminutas y sus artefactos comunes de imagen.
Permitir que el microscopio decida dónde mirar
Los investigadores cerraron entonces el ciclo entre simulación, IA e instrumento físico. En su flujo de trabajo semiautónomo, el AFM primero realiza un escaneo de vista general a baja resolución sobre un área relativamente grande. Un modelo entrenado con datos de SimuScan analiza esta imagen en tiempo real, encuentra estructuras de interés —como ciertas formas bacterianas o patrones nanofabricados específicos— y selecciona regiones prometedoras para escaneos ampliados de alta resolución. El microscopio se mueve automáticamente, vuelve a escanear y repite este ciclo a lo largo de la muestra, guiado por reglas sencillas definidas por el usuario, como el número deseado de objetos o el área total a cubrir. Con este enfoque, el sistema pudo encontrar e imagenar de forma autónoma cientos de bacterias individuales y luego medir variaciones en su tamaño y forma a lo largo de una población, algo que sería prohibitivamente lento de hacer a mano.
Un nuevo camino hacia microscopios más inteligentes
Para un no especialista, la conclusión principal es que SimuScan muestra cómo los datos “imaginarios pero realistas” pueden ayudar a que los microscopios se parezcan más a instrumentos autónomos. Al simular tanto los diminutos objetos sobre una superficie como las peculiaridades de cómo el AFM los percibe, los autores eliminan la necesidad de grandes conjuntos de entrenamiento etiquetados manualmente y permiten que modelos de IA de propósito general funcionen bien en experimentos reales. Esto desbloquea estudios con AFM que pueden explorar áreas más grandes, analizar muchos más objetos y adaptar su comportamiento sobre la marcha, haciendo la caracterización a nanoescala más rápida, más reproducible y accesible a no expertos. A largo plazo, estrategias similares basadas en datos sintéticos podrían ayudar a llevar la operación autónoma orientada al descubrimiento a muchos otros tipos de instrumentos científicos.
Cita: Millan-Solsona, R., Checa, M., Brown, S.R. et al. Synthetic data-driven deep learning for label-free autonomous atomic force microscopy. Nat Commun 17, 3886 (2026). https://doi.org/10.1038/s41467-026-70421-3
Palabras clave: microscopía de fuerza atómica, datos sintéticos, aprendizaje profundo, microscopía autónoma, imagen de nanoestructuras