Clear Sky Science · fr
Apprentissage profond basé sur des données synthétiques pour la microscopie à force atomique autonome sans marquage
Voir le monde minuscule sans yeux humains
Notre capacité à concevoir de nouveaux matériaux, étudier des dispositifs pour les énergies propres ou sonder des cellules vivantes dépend souvent de l’observation de structures mille fois plus fines qu’un cheveu humain. Les microscopes à force atomique (AFM) peuvent cartographier ces paysages minuscules en 3D, mais aujourd’hui ils reposent encore fortement sur des opérateurs experts qui doivent choisir où regarder et comment interpréter les images. Cet article présente SimuScan, une méthode pour apprendre aux ordinateurs à piloter des AFM et reconnaître des caractéristiques à l’échelle nanométrique en les entraînant sur des images simulées réalistes plutôt que sur des données expérimentales laborieusement annotées.
Pourquoi l’imagerie nanoscale actuelle bute
Les AFM sont devenus des outils centraux en science des matériaux, recherche énergétique et biologie car ils « sentent » les surfaces avec une précision nanométrique. Pourtant ils sont lents, ne couvrent que de petites zones à la fois et exigent de nombreuses décisions d’un utilisateur expérimenté : où balayer, quels paramètres utiliser et quelles minuscules formes comptent. Contrairement aux microscopes optiques ou électroniques qui peuvent capturer de larges images d’ensemble, les AFM reconstruisent les surfaces ligne par ligne. De plus, les méthodes modernes d’intelligence artificielle prospèrent avec d’énormes collections d’images annotées comme celles disponibles pour les photographies courantes, mais de tels jeux de données n’existent tout simplement pas pour les AFM. Chaque image AFM est influencée par des particularités instrumentales subtiles — bruit, distorsions et forme de la pointe — si bien que des outils génériques de vision par ordinateur entraînés sur des images ordinaires échouent souvent lorsqu’ils sont appliqués directement.
Apprendre à un microscope avec des images inventées
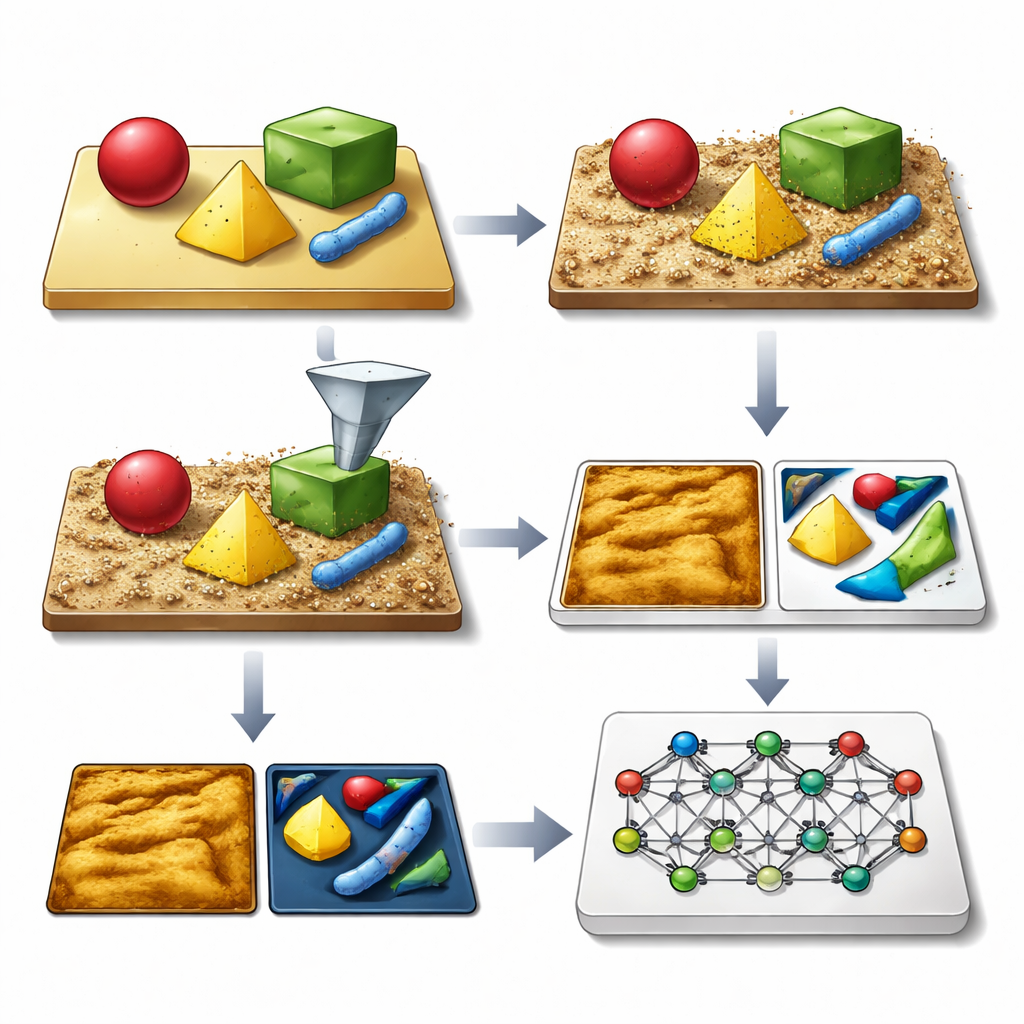
L’idée centrale des auteurs est de générer d’immenses bibliothèques d’images AFM synthétiques qui ressemblent et se comportent comme les vraies, en incluant toutes les imperfections usuelles. Leur cadre SimuScan commence par définir les formes susceptibles d’apparaître sur un échantillon : blocs et barres simples, assemblages délicats d’ADN, ou cellules bactériennes entières. Ces formes peuvent provenir de descriptions mathématiques, de fichiers de conception assistée par ordinateur ou même de surfaces 3D extraites de quelques images AFM réelles. SimuScan place ensuite ces objets sur des substrats simulés pouvant inclure marches, rugosité, motifs périodiques et débris aléatoires, créant des paysages pré‑distordus réalistes. Enfin, il fait passer ces surfaces dans un modèle direct détaillé du microscope qui ajoute les effets d’une pointe finie, des anomalies de rétroaction, des corrections ligne par ligne et du bruit électronique. Le résultat est une image qui imite de près ce qu’un AFM mesurerait, associée à une « vérité terrain » exacte de l’empreinte de chaque objet.
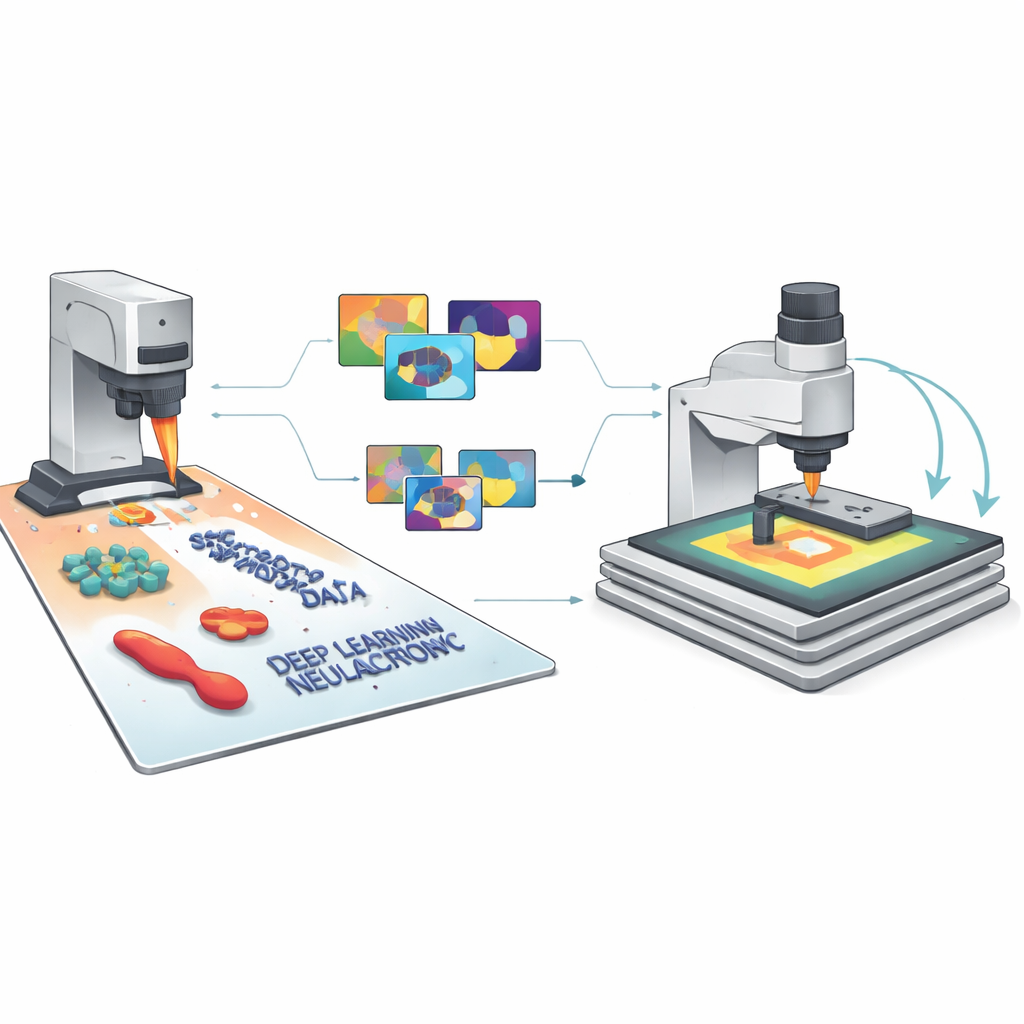
Des pixels simulés à une IA fiable
Parce que chaque image synthétique est fournie avec des étiquettes parfaites pour chaque caractéristique et chaque pixel, SimuScan peut alimenter les modèles d’apprentissage profond modernes avec le type de matériel d’entraînement riche qui fait défaut en imagerie nanoscopique. L’équipe a testé plusieurs architectures populaires — YOLOv8 pour la détection d’objets rapide, U‑Net pour les contours détaillés, et Mask R‑CNN pour les masques d’instance — en utilisant plus de 5 000 images synthétiques par tâche. De manière remarquable, des modèles entraînés uniquement sur ces jeux de données artificiels ont bien performé lorsqu’on les a évalués sur des images AFM réelles de nanostructures fabriquées et de bactéries annotées minutieusement par des experts. Les scores de détection et la précision de segmentation étaient élevés sur différentes formes et types cellulaires, montrant que les images simulées avaient capturé l’apparence essentielle de ces structures minuscules et leurs artefacts d’imagerie courants.
Laisser le microscope décider où regarder
Les chercheurs ont ensuite fermé la boucle entre simulation, IA et instrument physique. Dans leur flux de travail semi‑autonome, l’AFM réalise d’abord un balayage d’aperçu à faible résolution sur une zone relativement large. Un modèle entraîné sur des données SimuScan analyse cette image en temps réel, repère les structures d’intérêt — comme certaines formes bactériennes ou des motifs nanofabriqués spécifiques — et sélectionne des régions prometteuses pour des scans agrandis à haute résolution. Le microscope se déplace automatiquement, refait le scan et répète ce cycle sur l’échantillon, guidé par des règles simples définies par l’utilisateur comme le nombre désiré d’objets ou la surface totale à couvrir. Grâce à cette approche, le système pouvait trouver et imager de façon autonome des centaines de bactéries individuelles, puis mesurer les variations de taille et de forme au sein d’une population, ce qui serait prohibitif en temps si fait manuellement.
Une nouvelle voie vers des microscopes plus intelligents
Pour un non‑spécialiste, l’essentiel est que SimuScan montre comment des données « imaginaires mais réalistes » peuvent aider les microscopes à devenir davantage des instruments autonomes. En simulant à la fois les petits objets sur une surface et les particularités de la manière dont l’AFM les perçoit, les auteurs suppriment le besoin de gros ensembles d’entraînement annotés manuellement et permettent à des modèles d’IA polyvalents de bien fonctionner sur des expériences réelles. Cela ouvre la voie à des études AFM explorant des zones plus vastes, analysant bien plus d’objets et adaptant leur comportement à la volée, rendant la caractérisation à l’échelle nanométrique plus rapide, plus reproductible et accessible aux non‑experts. À long terme, des stratégies similaires basées sur des données synthétiques pourraient permettre l’exploitation autonome et guidée par la découverte de nombreux autres types d’instruments scientifiques.
Citation: Millan-Solsona, R., Checa, M., Brown, S.R. et al. Synthetic data-driven deep learning for label-free autonomous atomic force microscopy. Nat Commun 17, 3886 (2026). https://doi.org/10.1038/s41467-026-70421-3
Mots-clés: microscopie à force atomique, données synthétiques, apprentissage profond, microscopie autonome, imagerie de nanostructures