Clear Sky Science · pt
Design funcional de proteínas e aprimoramento com iteração de reforço ontológico
Ensinando Computadores a Construir Proteínas Melhores
As proteínas realizam quase todo o trabalho dentro das células vivas, desde a quebra de nutrientes até o combate a infecções. Cientistas gostariam de projetar novas proteínas sob demanda — como enzimas industriais mais resistentes ou ferramentas médicas melhores —, mas transformar ideias computacionais em moléculas reais e funcionais ainda é difícil. Este estudo apresenta um novo sistema chamado ORI que conecta diretamente inteligência artificial a experimentos de laboratório, com o objetivo de tornar o projeto de proteínas mais rápido, confiável e fácil de controlar.
Por Que Projetar Proteínas é Tão Difícil
Cada proteína é construída a partir de uma longa cadeia de aminoácidos, e mudanças minúsculas nessa sequência podem alterar dramaticamente como a molécula se dobra e se comporta. A IA moderna pode prever formas de proteínas e até gerar novas sequências, mas existe uma lacuna persistente entre o que parece promissor no computador e o que realmente funciona no tubo de ensaio. Muitos projetos falham porque são instáveis, não se dobram corretamente ou não têm a atividade desejada, forçando os pesquisadores a depender de tentativa e erro lenta.
Um Ciclo Fechado entre Computador e Laboratório
A estrutura ORI enfrenta esse problema criando um ciclo de feedback entre modelos de IA e experimentos reais 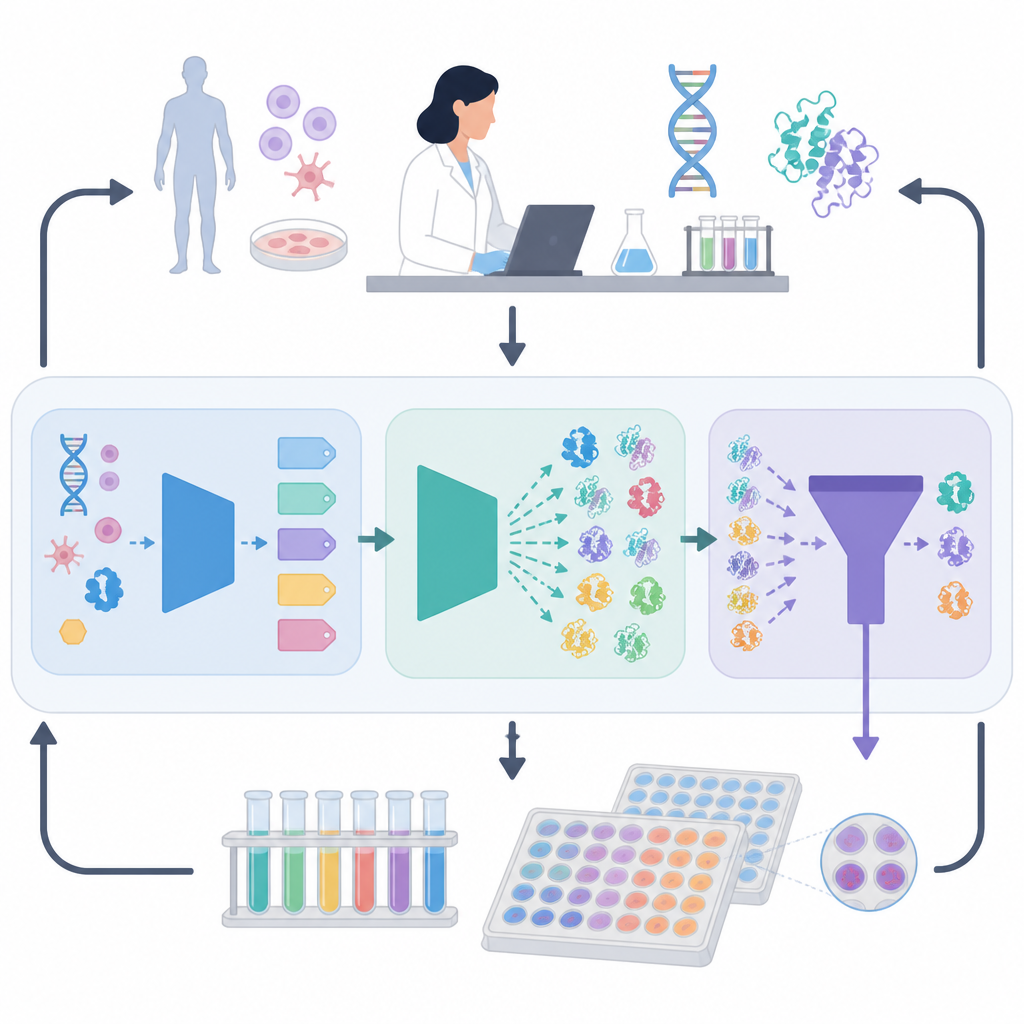
Aprendendo com o Feedback Experimental
O que diferencia o ORI é que ele não se limita à predição; ele aprende com os sucessos e fracassos do laboratório. Designs de proteínas selecionados são sintetizados e testados quanto à expressão, atividade e comportamento sob estresse. Esses resultados são então reintegrados à IA usando uma estratégia adaptada de aprendizado por reforço, permitindo que o sistema passe a favorecer gradualmente padrões de sequência que têm bom desempenho no mundo real, em vez de apenas no papel. Ao longo de várias rodadas, a IA melhora ao propor candidatos que sobrevivem a esse crivo experimental 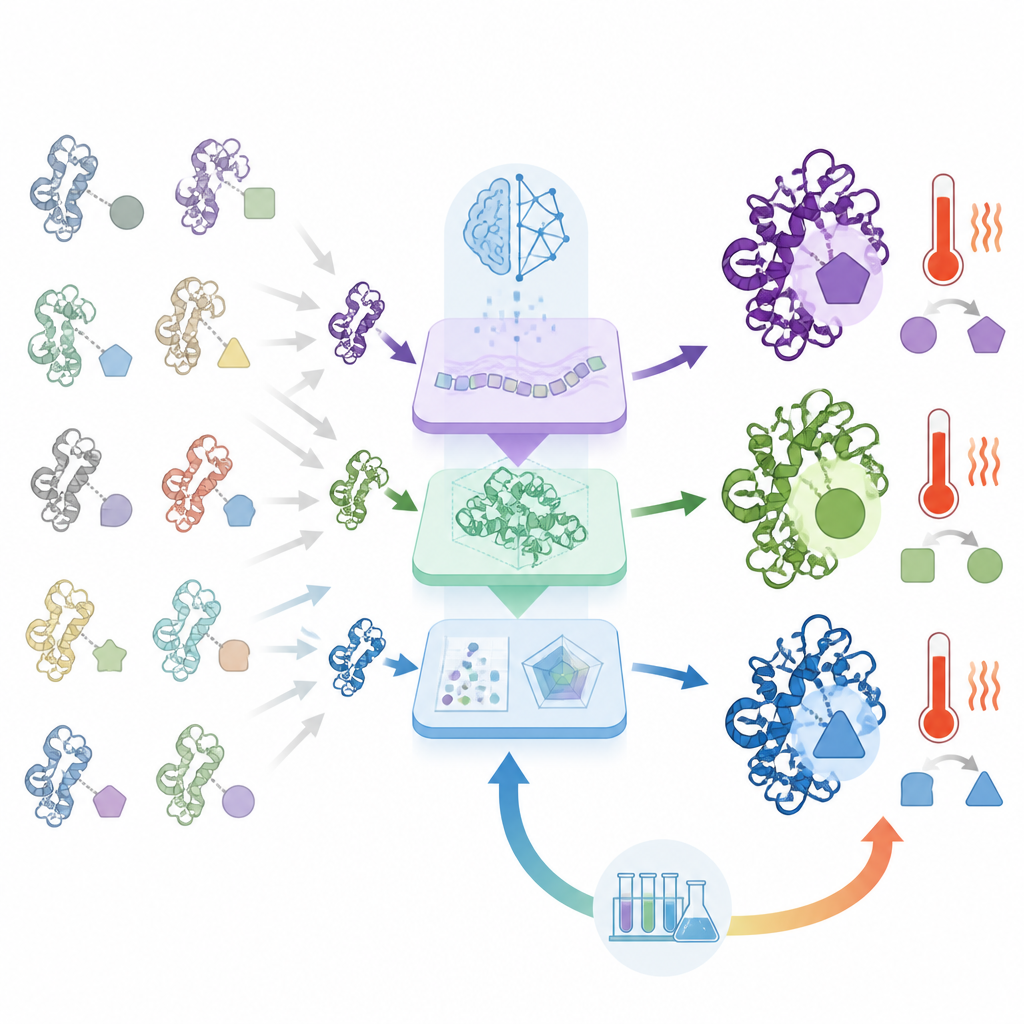
Construindo Enzimas Mais Fortes, mais Tolerantes ao Calor e com Dupla Função
Para demonstrar o que o ORI pode fazer, os autores o aplicaram a vários desafios de projeto de enzimas. Para lisozimas, que degradam paredes celulares bacterianas, o sistema gerou muitas variantes e, após aprender com o feedback experimental, produziu versões com atividade muito superior às lisozimas naturais, incluindo uma cerca de cem vezes mais ativa que uma referência padrão. O ORI também foi usado para projetar quitinases, enzimas que digerem a quitina encontrada em carapaças de insetos e fungos. Ao orientar o modelo para características resistentes ao calor, a equipe criou quitinases que mantiveram atividade em temperaturas em torno de 85 graus Celsius, muito além do que a maioria das versões naturais tolera. Finalmente, o sistema engenheirou proteínas únicas que combinam atividades de lisozima e quitinase, e algumas dessas enzimas de dupla função superaram seus equivalentes naturais especializados em ambas as tarefas.
Uma Nova Forma de Explorar Possibilidades de Proteínas
Para não especialistas, a ideia central é que o ORI transforma o projeto de proteínas em uma conversa contínua entre modelos computacionais e o laboratório experimental, em vez de uma predição única. O sistema usa conhecimento estruturado sobre tipos e propriedades de proteínas para orientar sua criatividade, e ouve atentamente o que os experimentos dizem sobre cada novo design. Ao percorrer esse processo repetidamente, o ORI pode não apenas igualar proteínas naturais, mas por vezes superá‑las em resistência, tolerância ao calor ou versatilidade. Isso aponta para um futuro em que proteínas sob medida para medicina, indústria e aplicações ambientais possam ser desenvolvidas de forma mais eficiente e com maior confiança.
Citação: He, B., Qin, C., Zhao, Y. et al. Functional protein design and enhancement with ontology reinforcement iteration. Nat Commun 17, 4158 (2026). https://doi.org/10.1038/s41467-026-69855-6
Palavras-chave: engenharia de proteínas, projeto de enzimas, inteligência artificial, enzimas termorresistentes, proteínas multifuncionais