Clear Sky Science · es
Diseño y mejora funcional de proteínas con iteración de refuerzo ontológico
Enseñar a las computadoras a construir mejores proteínas
Las proteínas realizan casi todo el trabajo dentro de las células vivas, desde descomponer los alimentos hasta combatir infecciones. A los científicos les encantaría diseñar nuevas proteínas a demanda, como enzimas industriales más resistentes o herramientas médicas mejores, pero convertir las ideas computacionales en moléculas reales y funcionales sigue siendo difícil. Este estudio presenta un nuevo sistema llamado ORI que conecta la inteligencia artificial directamente con experimentos de laboratorio, con el objetivo de hacer el diseño de proteínas más rápido, más fiable y más fácil de controlar.
Por qué es tan difícil diseñar proteínas
Cada proteína se construye a partir de una larga cadena de aminoácidos, y cambios minúsculos en esa cadena pueden alterar drásticamente cómo se pliega y cómo se comporta la molécula. La IA moderna puede predecir formas de proteínas e incluso generar nuevas secuencias, pero existe una brecha persistente entre lo que parece prometedor en un ordenador y lo que realmente funciona en un tubo de ensayo. Muchos diseños fracasan porque son inestables, no se pliegan correctamente o carecen de la actividad deseada, lo que obliga a los investigadores a recurrir a ensayo y error lento.
Un bucle cerrado entre ordenador y laboratorio
El marco ORI aborda este problema creando un bucle de retroalimentación entre modelos de IA y experimentos reales 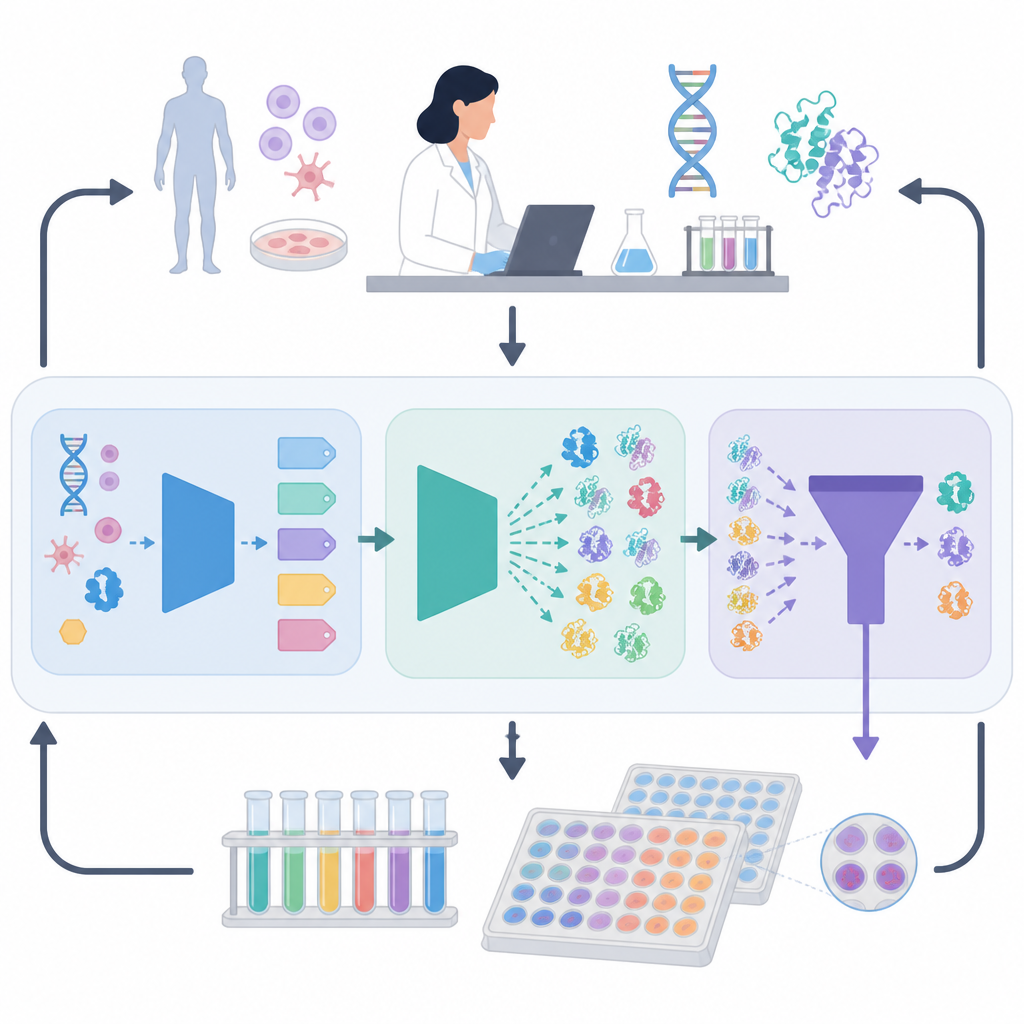
Aprender de la retroalimentación experimental
Lo que distingue a ORI es que no se queda en la predicción; aprende de los éxitos y fracasos del laboratorio. Diseños de proteínas seleccionados se sintetizan y se prueban para evaluar su expresión, su actividad y su comportamiento bajo estrés. Estos resultados se retroalimentan a la IA usando una estrategia adaptada del aprendizaje por refuerzo, lo que permite que el sistema gradualmente favorezca patrones de secuencia que funcionan bien en la práctica y no solo en teoría. Tras varias rondas, la IA mejora en proponer candidatos que superan este filtro del mundo real 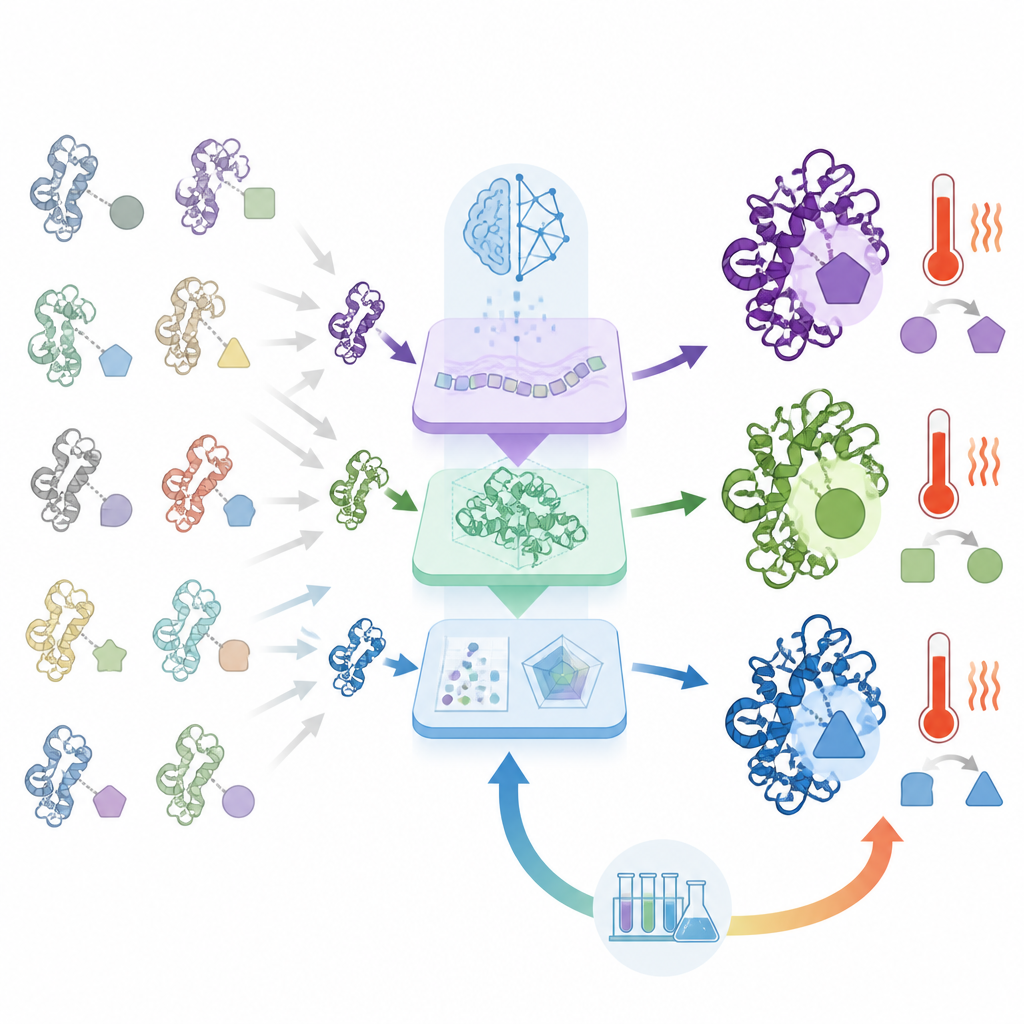
Construir enzimas más fuertes, resistentes al calor y con funciones duales
Para demostrar lo que ORI puede hacer, los autores lo aplicaron a varios retos de diseño de enzimas. Para las lisozimas, que degradan las paredes celulares bacterianas, el sistema generó muchas variantes y, tras aprender de la retroalimentación experimental, produjo versiones con actividad mucho mayor que las lisozimas naturales, incluyendo una aproximadamente cien veces más activa que una referencia estándar. ORI también se utilizó para diseñar quitinasas, enzimas que digieren la quitina presente en caparazones de insectos y hongos. Al orientar el modelo hacia características resistentes al calor, el equipo creó quitinasas que se mantuvieron activas a temperaturas cercanas a 85 grados Celsius, mucho más allá de lo que toleran la mayoría de las versiones naturales. Finalmente, el sistema diseñó proteínas únicas que combinan tanto actividad de lisozima como de quitinasa, y algunas de estas enzimas de función dual superaron a sus contrapartes naturales especializadas en ambas tareas.
Una nueva forma de explorar las posibilidades de las proteínas
Para quienes no son especialistas, la idea clave es que ORI convierte el diseño de proteínas en una conversación continua entre modelos computacionales y el laboratorio húmedo, en lugar de una predicción puntual. El sistema utiliza conocimiento estructurado sobre tipos y propiedades de proteínas para guiar su imaginación, y escucha atentamente lo que dicen los experimentos sobre cada nuevo diseño. Al repetir este proceso, ORI no solo puede igualar proteínas naturales, sino a veces superarlas en resistencia, tolerancia al calor o versatilidad. Esto sugiere un futuro en el que proteínas a medida para la medicina, la industria y aplicaciones medioambientales puedan desarrollarse con mayor eficiencia y mayor confianza.
Cita: He, B., Qin, C., Zhao, Y. et al. Functional protein design and enhancement with ontology reinforcement iteration. Nat Commun 17, 4158 (2026). https://doi.org/10.1038/s41467-026-69855-6
Palabras clave: ingeniería de proteínas, diseño de enzimas, inteligencia artificial, enzimas termostables, proteínas multifuncionales