Clear Sky Science · fr
Identification et analyse par regroupement des gènes répondant aux médicaments et variant dans le temps grâce au séquençage longitudinal à haute fréquence
Pourquoi observer les gènes au fil du temps est important
Quand nous prenons un médicament, notre organisme ne réagit pas en un instant unique. Les cellules s’ajustent, ripostent, réparent les dommages et se rétablissent pendant des heures et des jours. Pourtant, la plupart des tests en laboratoire ne mesurent que le « avant » et le « après » du traitement, manquant ce qui se passe entre les deux. Cette étude montre qu’en prélevant fréquemment de petites quantités de sang et en lisant l’activité génique jour après jour, les chercheurs peuvent révéler des vagues de réponse aux médicaments qui resteraient autrement invisibles. Le travail porte sur des médicaments qui stressent le foie chez le rat, mais l’approche ouvre la voie à une médecine plus précise et consciente du facteur temps chez l’humain.
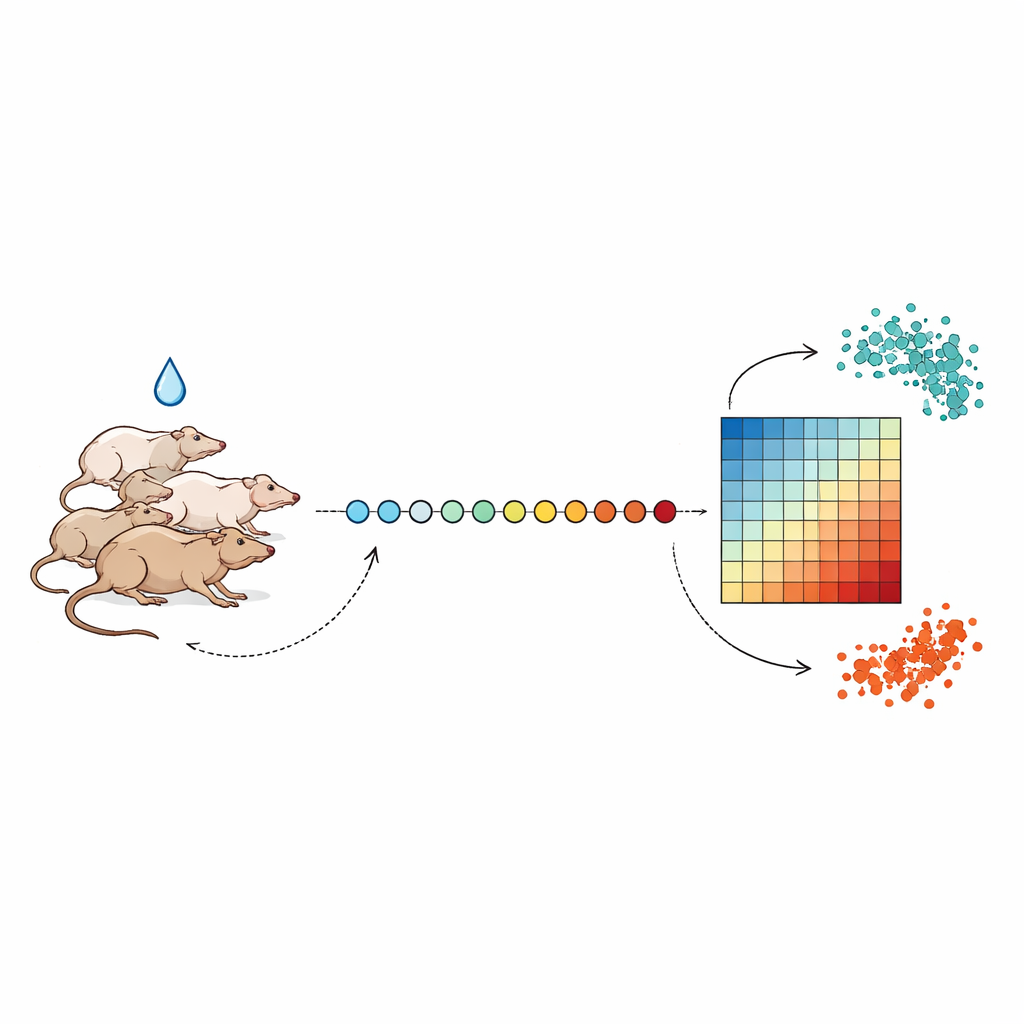
Prendre des instantanés quotidiens de la réaction de l’organisme
Les chercheurs ont suivi des groupes de rats pendant jusqu’à trois semaines, prélevant une très petite quantité de sang presque à la même heure chaque jour pour éviter les variations normales liées au rythme jour–nuit. Après quelques jours d’échantillonnage de référence, les animaux ont reçu une dose unique de l’un des plusieurs composés hépatotoxiques, notamment l’antibiotique tétracycline et le médicament antituberculeux isoniazide, à différentes intensités. À partir de chaque prélèvement sanguin, l’équipe a extrait l’ARN — les molécules messagères qui reflètent quels gènes sont activés ou désactivés — et a utilisé le séquençage à haut débit pour mesurer l’activité de milliers de gènes simultanément. En alignant ces mesures au fil des jours, ils ont pu observer comment l’activité génique s’éloignait d’un état sain puis, dans la plupart des cas, revenait progressivement.
Identifier les gènes qui varient avec le temps, pas seulement en moyenne
Les analyses classiques de ce type de données comparent en général un point temporel avant le traitement à un point après, signalant comme « différents » les gènes présentant de grands changements moyens. Mais cette vision en instantané peut rater des gènes qui connaissent des pics ou des creux brefs, ou qui répondent plus tard puis se normalisent. Pour y remédier, les auteurs ont utilisé un cadre méthodologique pour identifier les « gènes variant dans le temps » — des gènes dont l’activité fluctue de façon significative pendant la durée du traitement, même si leurs niveaux de départ et de fin semblent similaires. En notant la force des montées et descentes de chaque gène au fil des jours, et en filtrant le bruit de routine comme les effets modestes d’un saignement répété, ils ont mis au jour des milliers de gènes dont le comportement contient une information temporelle riche sur la réponse au médicament.
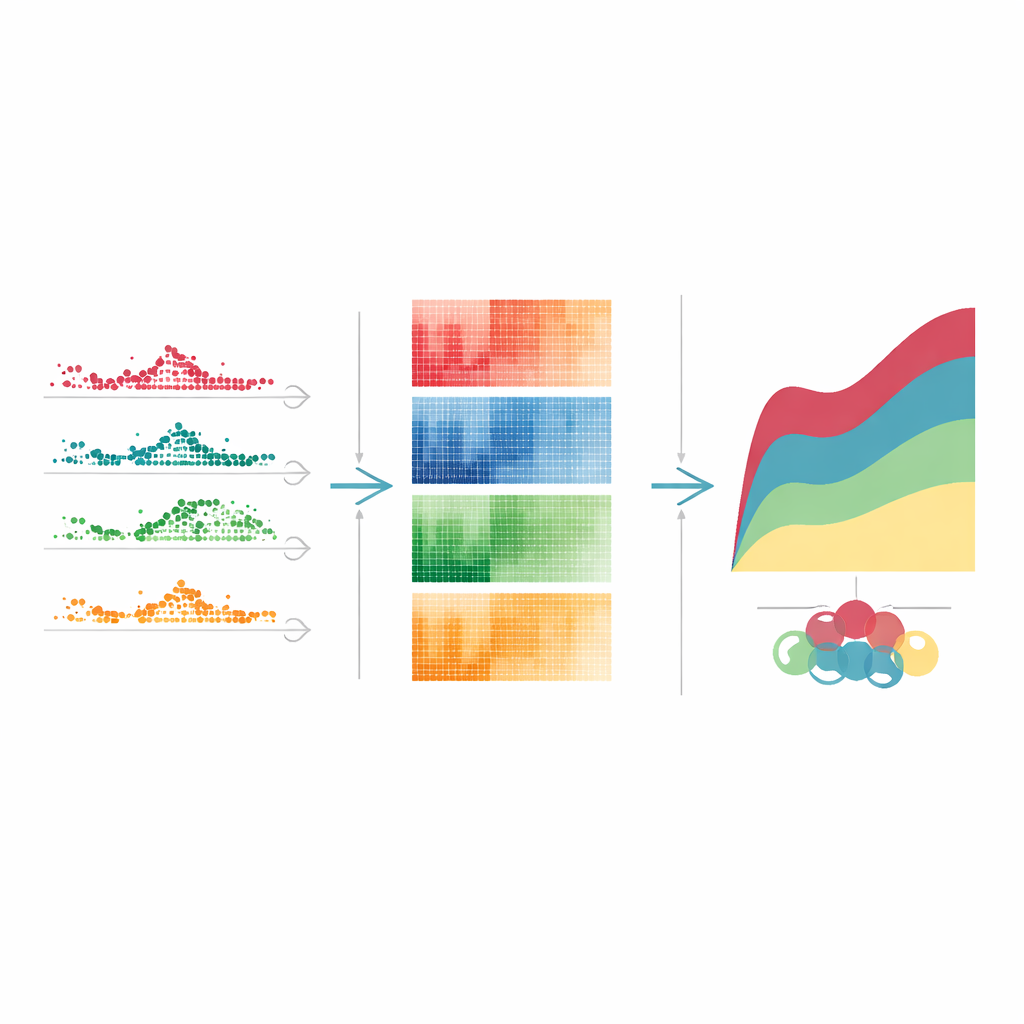
Schémas d’alerte précoce, stress soutenu et récupération tardive
En regroupant ces gènes variables dans le temps selon l’évolution de leur activité après une forte dose de tétracycline, des motifs clairs sont apparus. Certains gènes ont bondi rapidement puis se sont stabilisés en quelques jours, jouant le rôle de premières alarmes. D’autres sont montés et sont restés élevés pendant le pic d’impact du médicament, reflétant un stress soutenu sur la production de protéines et d’autres processus cellulaires essentiels. Un troisième groupe s’est activé ou désactivé plus tard, marquant des phases plus lentes de réparation et de nettoyage. Des schémas de timing similaires, quoique non identiques, sont apparus avec d’autres médicaments hépatotoxiques. En reliant chaque motif à des tâches cellulaires connues — comme la défense immunitaire, l’élimination des déchets ou la réparation de l’ADN — les auteurs ont pu esquisser une histoire en étapes : comment le foie perçoit d’abord la lésion, puis s’adapte, et enfin tente de se guérir.
Signes d’alerte partagés et empreintes spécifiques aux médicaments
En regardant au travers de quatre composés toxiques différents, les chercheurs ont catalogué plus de 4 000 gènes uniques variant dans le temps. Seuls 186 d’entre eux ont changé de manière coordonnée pour chaque médicament, formant une signature « cœur » partagée du stress hépatique, particulièrement riche en gènes impliqués dans la gestion du fer et dans une forme de mort cellulaire appelée ferroptose. Le reste était spécifique à chaque médicament, soulignant que différentes substances endommagent les cellules par des voies distinctes et déclenchent des programmes de récupération différents. L’équipe a aussi examiné comment les réponses géniques dépendaient de la dose. Certains gènes réagissaient même aux niveaux les plus faibles du médicament, ce qui en fait des marqueurs d’alerte précoce prometteurs, tandis que d’autres ne répondaient qu’aux doses les plus élevées, pointant vers des voies engagées lorsque les lésions deviennent sévères. Ces seuils de dose peuvent aider à expliquer pourquoi un même traitement provoque un inconfort léger chez une personne et des dommages sérieux chez une autre.
Ce que cela signifie pour les traitements futurs
Pris ensemble, les résultats montrent que suivre l’activité génique au fil du temps peut révéler des réponses subtiles, rapides ou retardées que des tests plats à un seul point temporel ignorent. Les auteurs soutiennent que ces gènes variables dans le temps offrent une façon plus sensible de distinguer les effets directs d’un médicament des tentatives d’adaptation et de réparation de l’organisme, et de séparer les niveaux d’exposition sûrs des niveaux dangereux. Bien que l’étude ait été réalisée chez le rat et se concentre sur des composés hépatotoxiques, l’idée sous-jacente — des prélèvements denses et répétés combinés à une analyse intelligente — pourrait s’appliquer largement. À mesure que le séquençage devient moins coûteux et que l’analyse des données gagne en puissance, un suivi moléculaire longitudinal de ce type pourrait aider à adapter les doses de médicaments, détecter plus tôt les effets secondaires et mieux assortir les traitements au profil de réponse propre à chaque personne.
Citation: Jiang, Q., Weng, X., Chai, Y. et al. Identification and clustering analysis of drug-responsive temporally varying genes through high-frequency longitudinal RNA sequencing. Sci Rep 16, 14143 (2026). https://doi.org/10.1038/s41598-026-44560-y
Mots-clés: séquençage longitudinal de l’ARN, lésions hépatiques induites par des médicaments, dynamique d’expression génique, biomarqueurs en toxicologie, pharmacologie de précision