Clear Sky Science · de
Identifikation und Clusteranalyse von arzneimittelreaktiven, zeitlich variierenden Genen mittels hochfrequenter longitudinaler RNA-Sequenzierung
Warum es wichtig ist, Gene über die Zeit zu beobachten
Wenn wir ein Medikament einnehmen, reagiert unser Körper nicht in einem einzigen Augenblick. Zellen passen sich an, wehren sich, reparieren Schäden und erholen sich über Stunden und Tage. Die meisten Labortests betrachten jedoch nur Zeitpunkte vor und nach der Behandlung und übersehen, was dazwischen geschieht. Diese Studie zeigt, dass Forscher durch häufige kleine Blutproben und tägliche Messungen der Genaktivität verborgene Reaktionswellen auf Medikamente aufdecken können, die andernfalls unsichtbar blieben. Die Arbeit konzentriert sich auf leberbelastende Wirkstoffe bei Ratten, doch der Ansatz weist auf eine präzisere, zeitbewusste Medizin für Menschen hin.
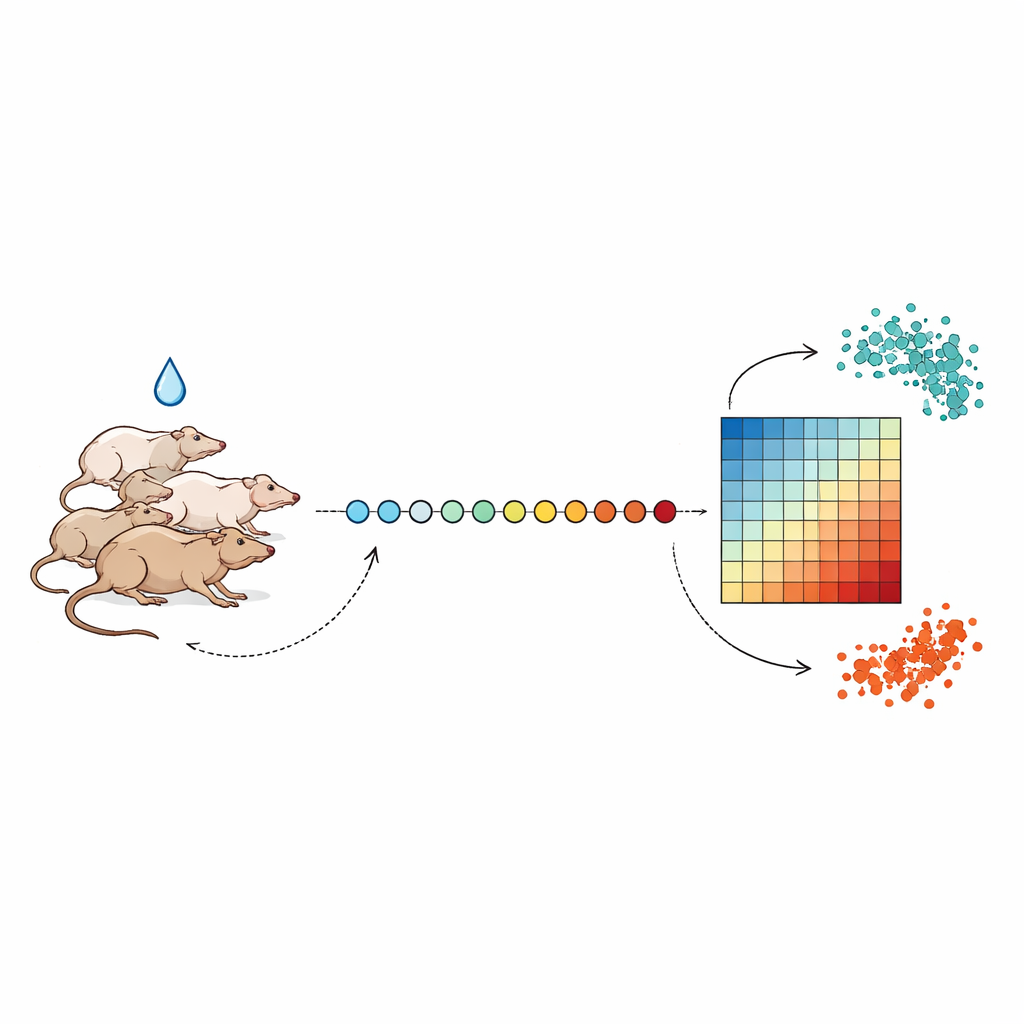
Tägliche Momentaufnahmen der Reaktion des Körpers
Die Forschenden begleiteten Rattengruppen bis zu drei Wochen und entnahmen jeden Tag zur nahezu gleichen Zeit sehr kleine Blutmengen, um normale Tag–Nacht-Schwankungen der Biologie zu vermeiden. Nach einigen Tagen mit Basisproben erhielten die Tiere einmalig eine Dosis eines von mehreren lebertoxischen Verbindungen, darunter das Antibiotikum Tetracyclin und das Tuberkulosemittel Isoniazid, in unterschiedlichen Stärken. Aus jeder Blutprobe isolierte das Team RNA — die Botenmoleküle, die anzeigen, welche Gene an- oder ausgeschaltet sind — und verwendete Hochdurchsatz-Sequenzierung, um die Aktivität von Tausenden Genen gleichzeitig zu messen. Indem sie diese Messungen über die Tage hinweg aneinanderreihen, konnten sie beobachten, wie die Genaktivität vom gesunden Ausgangsniveau abwich und sich in den meisten Fällen allmählich wieder normalisierte.
Gene finden, die sich über die Zeit ändern, nicht nur im Mittel
Übliche Analysen solcher Daten vergleichen meist einen Zeitpunkt vor der Behandlung mit einem Zeitpunkt danach und markieren Gene mit großen durchschnittlichen Veränderungen als „different“. Diese Momentaufnahme kann jedoch Gene übersehen, die kurzzeitig hochschnellen oder abfallen oder erst später reagieren und dann wieder normal werden. Um dem zu begegnen, nutzten die Autoren ein Framework zur Identifikation „zeitlich variierender Gene“ – Gene, deren Aktivität sich im Verlauf der Behandlung auf bedeutsame Weise verändert, selbst wenn Anfangs- und Endwerte ähnlich erscheinen. Indem sie bewerteten, wie stark die Pegel jedes Gens über die Tage stiegen und fielen, und Routinegeräusche wie milde Effekte wiederholter Blutentnahmen herausfilterten, enthüllten sie Tausende Gene, deren Verhalten reiche zeitliche Informationen über die Arzneimittelreaktion barg.
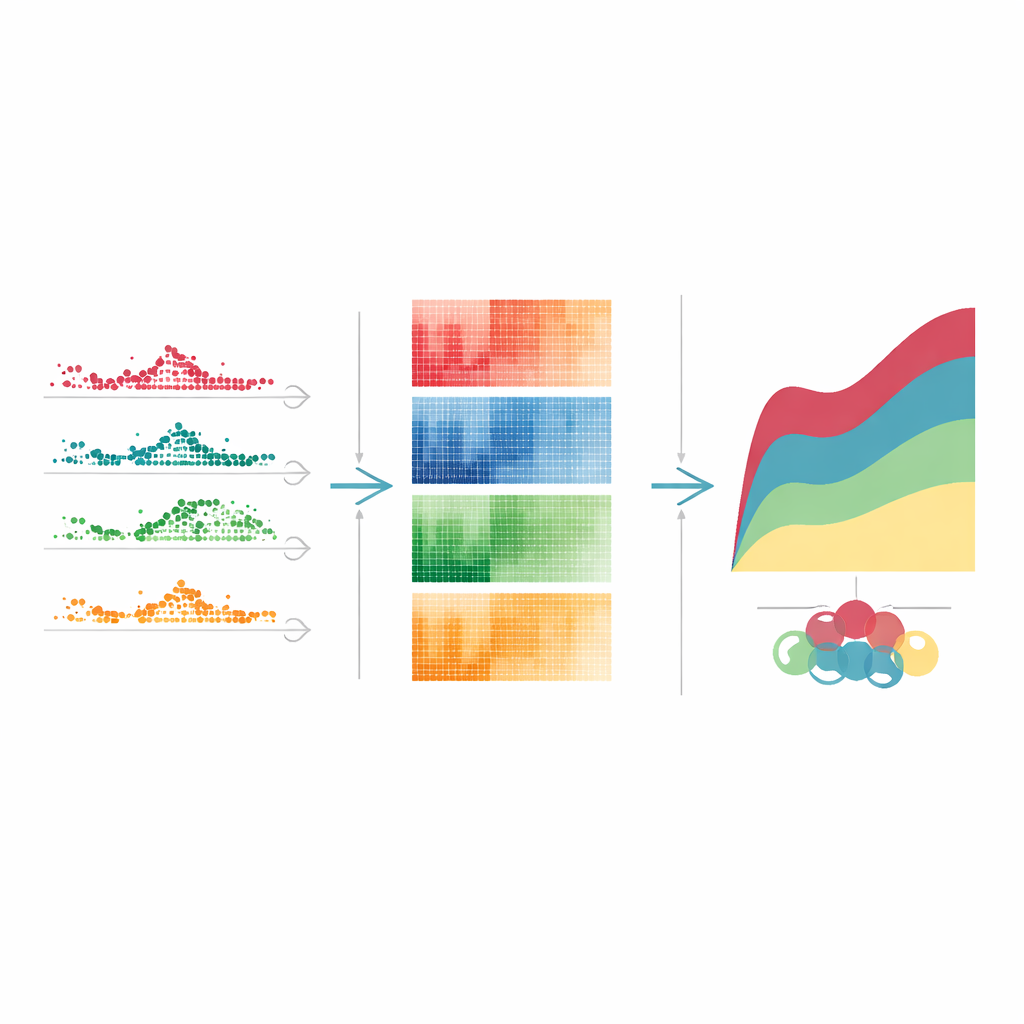
Muster früher Alarmierung, anhaltender Belastung und später Erholung
Als das Team diese zeitlich variierenden Gene nach ihrem Verhalten nach einer hohen Tetracyclin-Dosis gruppierte, traten klare Muster hervor. Einige Gene schossen schnell hoch und normalisierten sich innerhalb weniger Tage wieder, sie funktionierten wie frühe Alarmglocken. Andere stiegen an und blieben während der Spitzenwirkung des Medikaments erhöht, was anhaltenden Stress bei der Proteinproduktion und anderen zentralen Zellprozessen widerspiegelt. Eine dritte Gruppe schaltete sich später ein oder aus und markierte langsamere Reparatur- und Aufräumphasen. Ähnliche, wenn auch nicht identische zeitliche Muster zeigten sich bei anderen lebertoxischen Substanzen. Indem die Autoren jedes Muster bekannten zellulären Aufgaben — etwa Immunabwehr, Müllentsorgung oder DNA-Reparatur — zuordneten, konnten sie eine schrittweise Erzählung skizzieren, wie die Leber zunächst Verletzungen wahrnimmt, sich anpasst und schließlich zu heilen versucht.
Geteilte Warnsignale und wirkstoffspezifische Fingerabdrücke
Im Vergleich von vier verschiedenen toxischen Verbindungen katalogisierten die Forschenden mehr als 4.000 einzigartige zeitlich variierende Gene. Nur 186 davon änderten sich bei jedem Wirkstoff koordiniert und bildeten eine gemeinsame „Kern“-Signatur von Leberstress, die besonders reich an Genen war, die mit Eisen und einer Form des Zelltods namens Ferroptose umgehen. Der Rest war wirkstoffspezifisch und zeigte, dass unterschiedliche Chemikalien Zellen auf verschiedenen Wegen schädigen und unterschiedliche Erholungsprogramme auslösen. Das Team untersuchte auch, wie Genantworten von der Dosis abhängen. Einige Gene reagierten bereits bei den niedrigsten Wirkstoffkonzentrationen und sind damit vielversprechende Frühwarnmarker, während andere nur bei den stärksten Dosen ansprangen und auf Pfade hinweisen, die bei schwerer Schädigung aktiviert werden. Diese Dosis-Schwellen können erklären, warum dieselbe Behandlung bei einer Person nur zu leichten Beschwerden führt, bei einer anderen aber ernsthaften Schaden verursacht.
Was das für künftige Behandlungen bedeutet
In der Summe zeigt die Studie, dass die Beobachtung der Genaktivität über die Zeit subtile, schnelle oder verzögerte Reaktionen offenbaren kann, die flache Einzelzeitpunkt-Tests übersehen. Die Autoren argumentieren, dass diese zeitlich variierenden Gene eine sensiblere Methode bieten, direkte Arzneimitteleffekte von den eigenen Anpassungs- und Reparaturversuchen des Körpers zu trennen und sichere Expositionsniveaus von gefährlichen zu unterscheiden. Obwohl die Arbeit an Ratten und mit lebertoxischen Verbindungen durchgeführt wurde, ist die zugrundeliegende Idee — dichte, wiederholte Probenahme kombiniert mit intelligenter Analyse — breit anwendbar. Mit sinkenden Kosten für Sequenzierung und stärkerer Datenanalyse könnten solche longitudinalen molekularen Verfolgungen helfen, Medikamentendosierungen individuell anzupassen, Nebenwirkungen früher zu erkennen und Behandlungen besser an das jeweils eigene Reaktionsmuster anzupassen.
Zitation: Jiang, Q., Weng, X., Chai, Y. et al. Identification and clustering analysis of drug-responsive temporally varying genes through high-frequency longitudinal RNA sequencing. Sci Rep 16, 14143 (2026). https://doi.org/10.1038/s41598-026-44560-y
Schlüsselwörter: longitudinale RNA-Sequenzierung, arzneimittelinduzierte Leberschädigung, Dynamik der Genexpression, Toxikologie-Biomarker, präzisionspharmakologie