Clear Sky Science · es
Identificación y análisis de agrupamiento de genes con variación temporal sensibles a fármacos mediante secuenciación longitudinal de ARN de alta frecuencia
Por qué importa observar los genes a lo largo del tiempo
Cuando tomamos un medicamento, nuestro cuerpo no responde en un solo instante. Las células se ajustan, contraatacan, reparan daños y se recuperan durante horas y días. Sin embargo, la mayoría de las pruebas de laboratorio solo comparan antes y después del tratamiento, perdiendo lo que ocurre en medio. Este estudio muestra que, tomando pequeñas muestras de sangre con frecuencia y leyendo la actividad génica día a día, los investigadores pueden descubrir oleadas ocultas de respuesta a fármacos que de otro modo serían invisibles. El trabajo se centra en fármacos que estresan el hígado en ratas, pero el enfoque apunta hacia una medicina más precisa y consciente del tiempo en humanos.
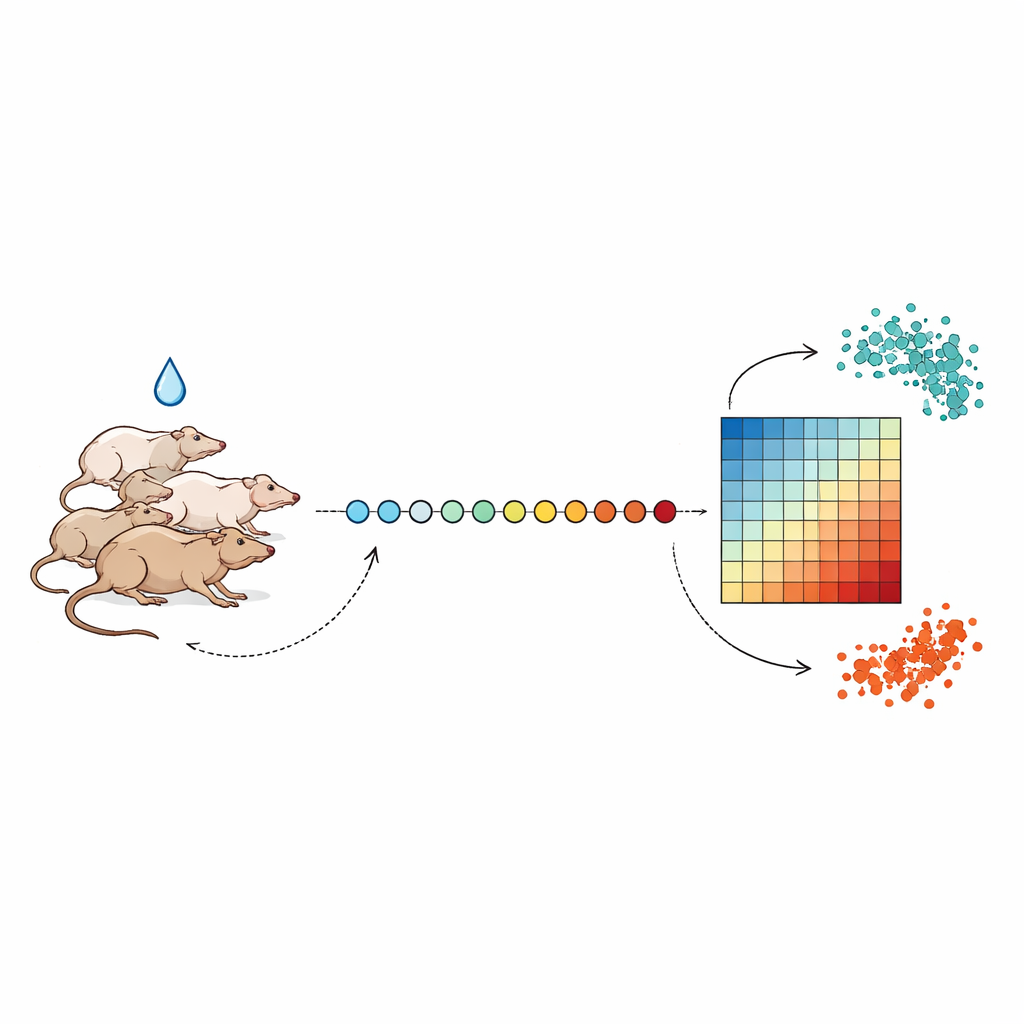
Tomando instantáneas diarias de la reacción del organismo
Los investigadores siguieron a grupos de ratas durante hasta tres semanas, extrayendo una cantidad muy pequeña de sangre casi a la misma hora cada día para evitar las variaciones biológicas normales entre día y noche. Tras unos días de muestreo basal, los animales recibieron una dosis única de uno de varios compuestos tóxicos para el hígado, incluidos el antibiótico tetraciclina y el fármaco contra la tuberculosis isoniazida, en distintas intensidades. Del cada muestra de sangre, el equipo extrajo ARN —las moléculas mensajeras que reflejan qué genes están encendidos o apagados— y usó secuenciación de alto rendimiento para medir la actividad de miles de genes a la vez. Alineando estas mediciones a lo largo de los días, pudieron observar cómo la actividad génica se desviaba de una línea de base saludable y luego, en la mayoría de los casos, regresaba gradualmente.
Encontrar genes que cambian con el tiempo, no solo en promedio
Los análisis estándar de este tipo de datos suelen comparar un punto temporal antes del tratamiento con otro después, marcando como “diferentes” los genes con grandes cambios promedio. Pero esa visión por instantánea puede pasar por alto genes que se disparan o bajan brevemente, o que responden más tarde y luego se normalizan. Para abordar esto, los autores usaron un marco para identificar “genes con variación temporal”: genes cuya actividad fluctúa de manera significativa durante el curso del tratamiento, incluso si sus niveles iniciales y finales parecen similares. Al puntuar cuánto subían y bajaban los niveles de cada gen a lo largo de los días, y filtrando el ruido rutinario como los efectos leves de sangrados repetidos, descubrieron miles de genes cuyo comportamiento contenía información temporal rica sobre la respuesta al fármaco.
Patrones de alarma temprana, estrés sostenido y recuperación tardía
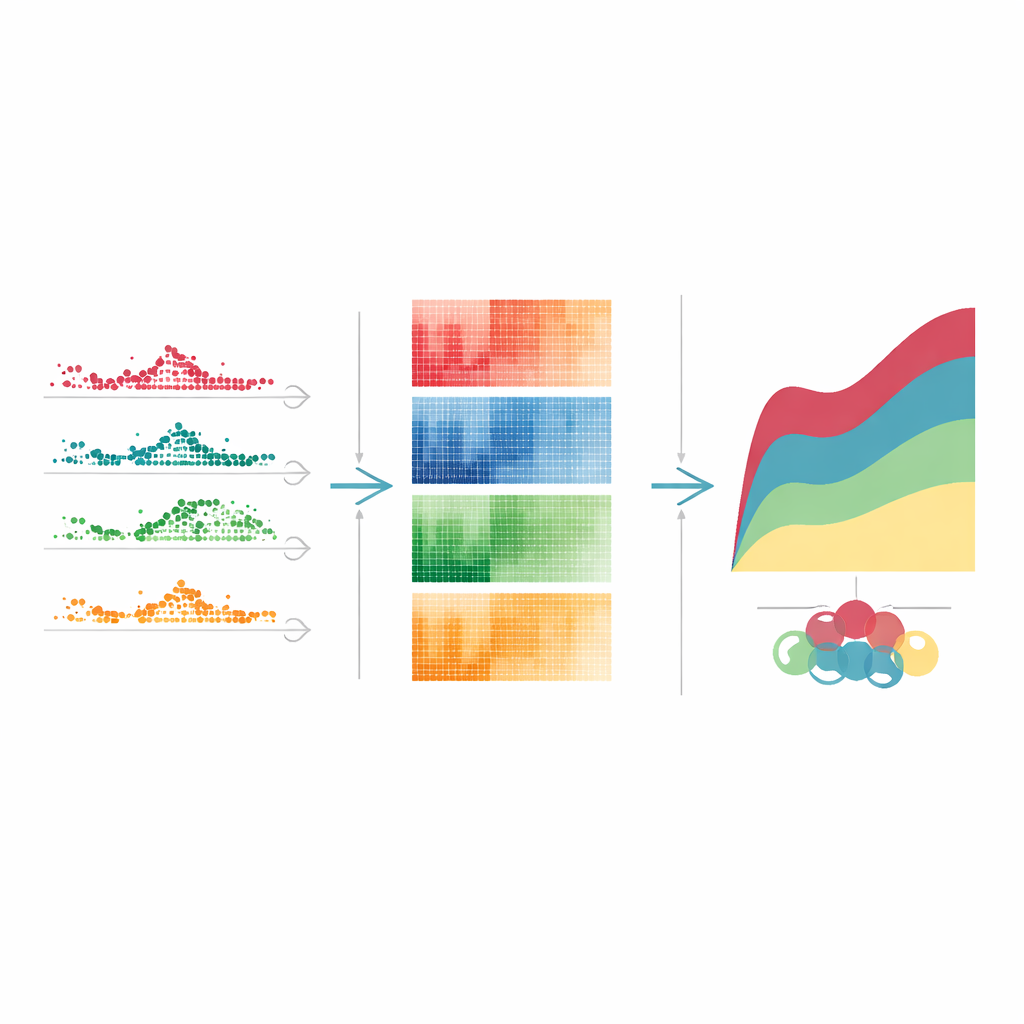
Cuando el equipo agrupó estos genes con variación temporal según cómo cambió su actividad tras una dosis alta de tetraciclina, surgieron patrones claros. Algunos genes se dispararon rápidamente y luego volvieron a la normalidad en pocos días, actuando como alarmas tempranas. Otros aumentaron y se mantuvieron altos durante el pico del impacto del fármaco, reflejando estrés sostenido en la síntesis de proteínas y otros procesos celulares centrales. Un tercer grupo se activó o desactivó más tarde, marcando fases más lentas de reparación y limpieza. Patrones de sincronización similares, aunque no idénticos, aparecieron con otros medicamentos tóxicos para el hígado. Al vincular cada patrón con tareas celulares conocidas —como defensa inmune, eliminación de residuos o reparación del ADN— los autores pudieron esbozar una historia por etapas de cómo el hígado primero detecta la lesión, luego se adapta y finalmente intenta curarse.
Señales de advertencia compartidas y huellas dactilares específicas de cada fármaco
Al comparar cuatro compuestos tóxicos diferentes, los investigadores catalogaron más de 4.000 genes únicos con variación temporal. Solo 186 de ellos cambiaron de forma coordinada para cada fármaco, formando una firma “central” compartida de estrés hepático especialmente rica en genes implicados en el manejo del hierro y en una forma de muerte celular llamada ferroptosis. El resto fue específico de cada fármaco, lo que subraya que diferentes químicos dañan las células por rutas distintas y desencadenan programas de recuperación diferentes. El equipo también examinó cómo las respuestas génicas dependían de la dosis. Algunos genes reaccionaron incluso con los niveles más bajos de fármaco, lo que los hace prometedores marcadores de aviso temprano, mientras que otros respondieron solo a las dosis más altas, señalando vías que se activan cuando el daño se vuelve severo. Estos umbrales de dosis pueden ayudar a explicar por qué el mismo tratamiento provoca molestias leves en una persona y daños graves en otra.
Qué significa esto para tratamientos futuros
En conjunto, el estudio demuestra que observar la actividad génica a lo largo del tiempo puede revelar respuestas sutiles, rápidas o retardadas que las pruebas planas de un solo punto temporal pasan por alto. Los autores sostienen que estos genes con variación temporal ofrecen una forma más sensible de distinguir los efectos directos del fármaco de los intentos del organismo por adaptarse y reparar, y de separar niveles de exposición seguros de los peligrosos. Aunque el trabajo se realizó en ratas y se centró en compuestos tóxicos para el hígado, la idea subyacente —muestreo denso y repetido combinado con análisis inteligentes— podría aplicarse de forma amplia. A medida que la secuenciación sea más barata y el análisis de datos más potente, este seguimiento molecular longitudinal podría ayudar a ajustar las dosis de los fármacos, detectar efectos secundarios antes y adaptar mejor los tratamientos al patrón único de respuesta de cada persona.
Cita: Jiang, Q., Weng, X., Chai, Y. et al. Identification and clustering analysis of drug-responsive temporally varying genes through high-frequency longitudinal RNA sequencing. Sci Rep 16, 14143 (2026). https://doi.org/10.1038/s41598-026-44560-y
Palabras clave: secuenciación longitudinal de ARN, lesión hepática inducida por fármacos, dinámica de la expresión génica, biomarcadores en toxicología, farmacología de precisión